peptides
spectra
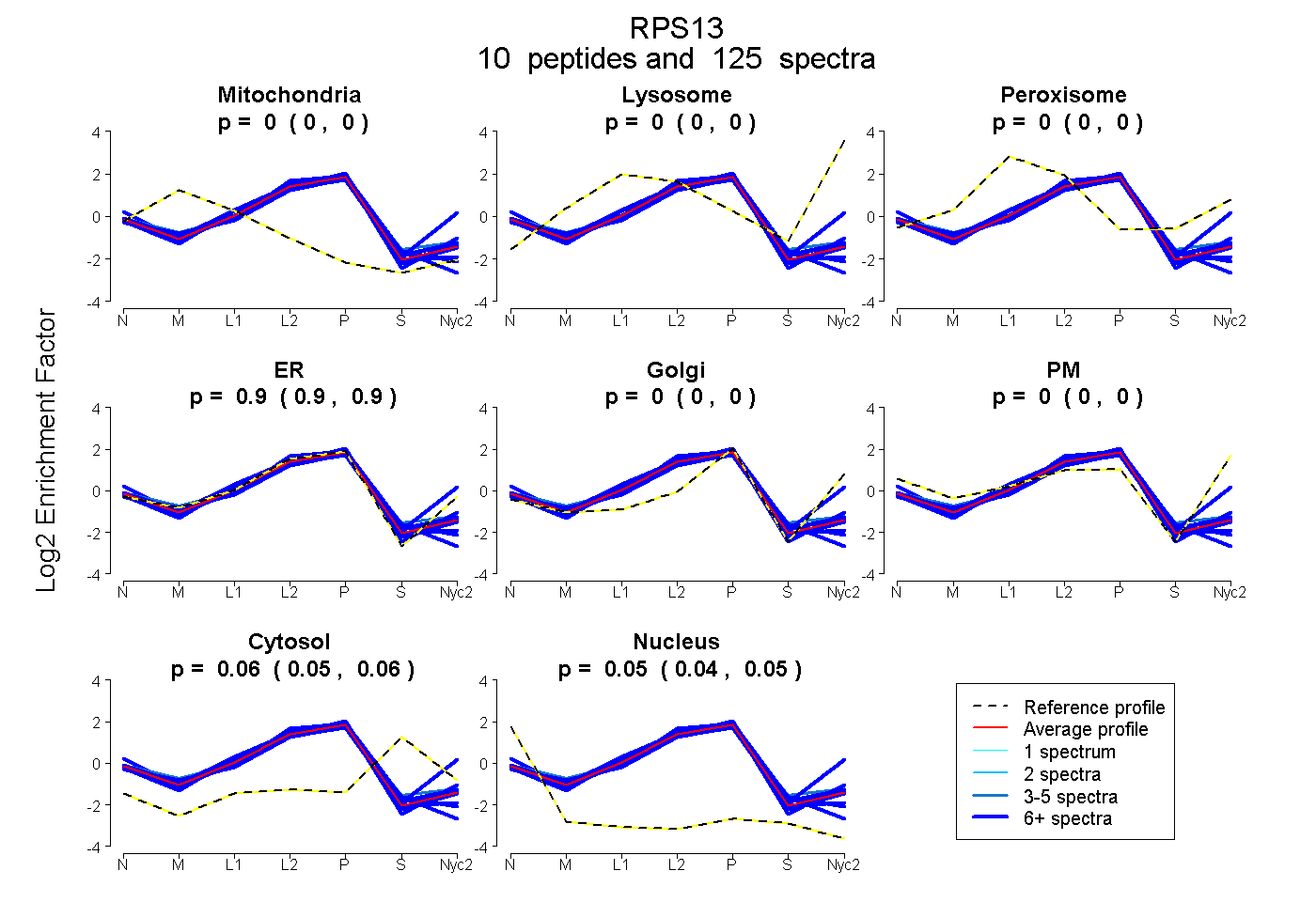
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.896 | 0.899
0.000 | 0.000
0.000 | 0.000
0.054 | 0.060
0.042 | 0.048
peptides
spectra

0.000 | 0.000
0.197 | 0.227
0.728 | 0.753
0.000 | 0.000
0.000 | 0.000
0.035 | 0.053
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
125 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.898 0.896 | 0.899 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.057 0.054 | 0.060 |
0.045 0.042 | 0.048 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
24 spectra |
 |
0.000 0.000 | 0.000 |
0.214 0.197 | 0.227 |
0.742 0.728 | 0.753 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.044 0.035 | 0.053 |
0.000 0.000 | 0.000 |
| 3 spectra, GLAPDLPEDFYHLIK | 0.000 | 0.179 | 0.763 | 0.000 | 0.000 | 0.058 | 0.000 | |||
| 1 spectrum, MHAPGK | 0.000 | 0.434 | 0.537 | 0.000 | 0.000 | 0.029 | 0.000 | |||
| 9 spectra, GLSQSALPYR | 0.000 | 0.019 | 0.916 | 0.000 | 0.000 | 0.064 | 0.000 | |||
| 3 spectra, VLPPNWK | 0.000 | 0.320 | 0.636 | 0.044 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, SVPTWLK | 0.000 | 0.156 | 0.697 | 0.000 | 0.122 | 0.025 | 0.000 | |||
| 3 spectra, GLTPSQIGVILR | 0.000 | 0.179 | 0.678 | 0.081 | 0.000 | 0.063 | 0.000 | |||
| 2 spectra, DSHGVAQVR | 0.000 | 0.400 | 0.338 | 0.236 | 0.026 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
208 spectra |
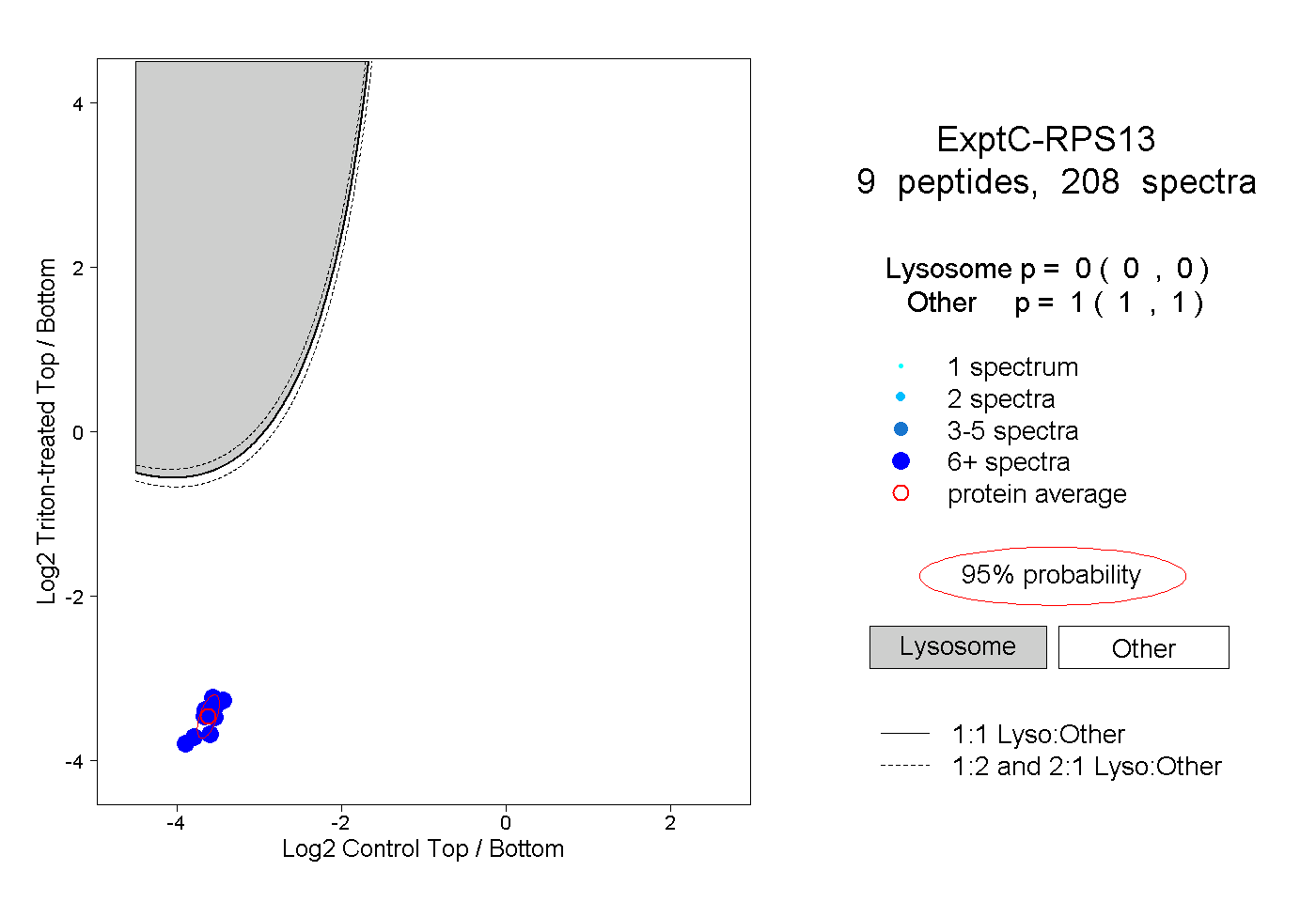 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
11 spectra |
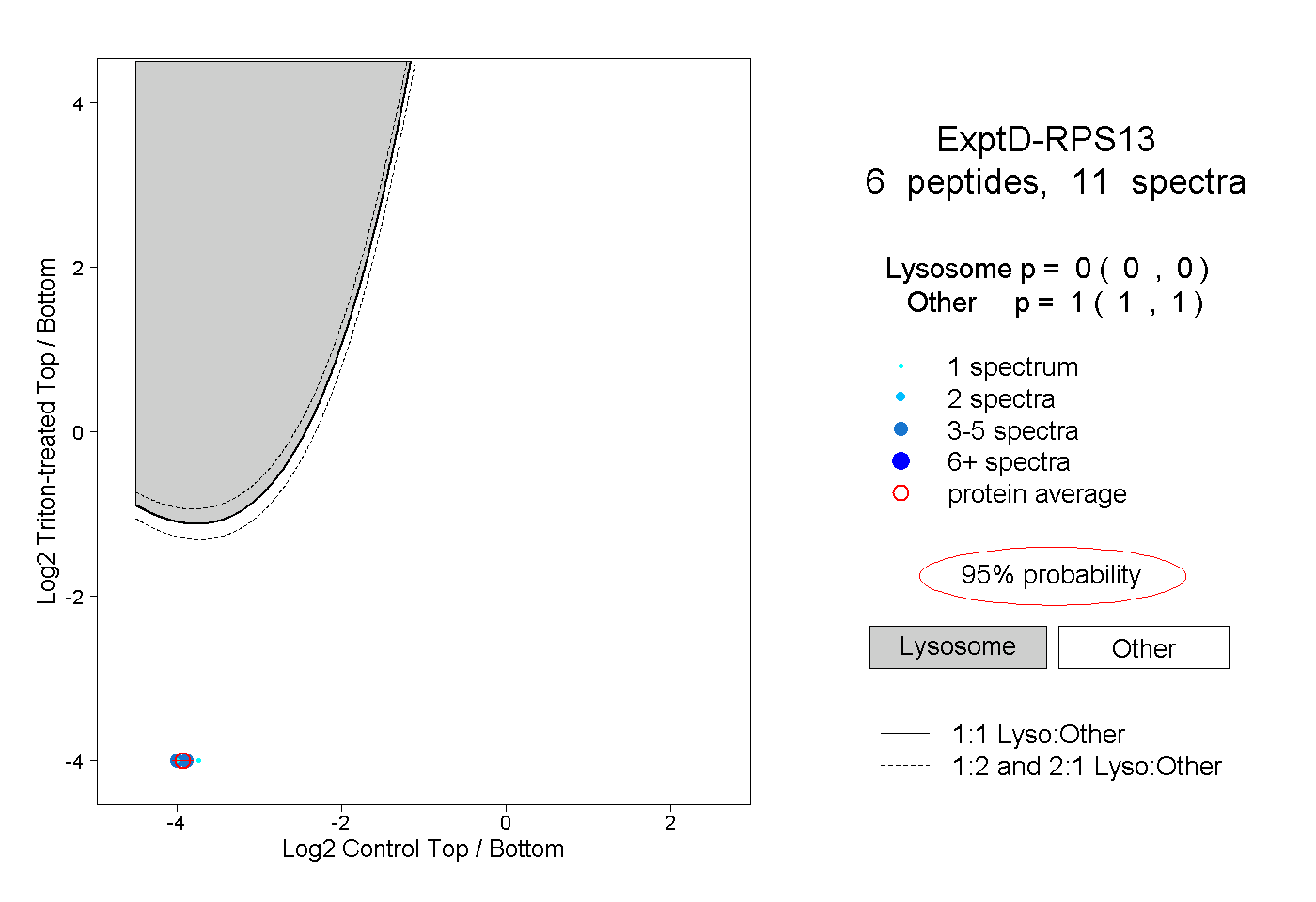 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |