peptides
spectra
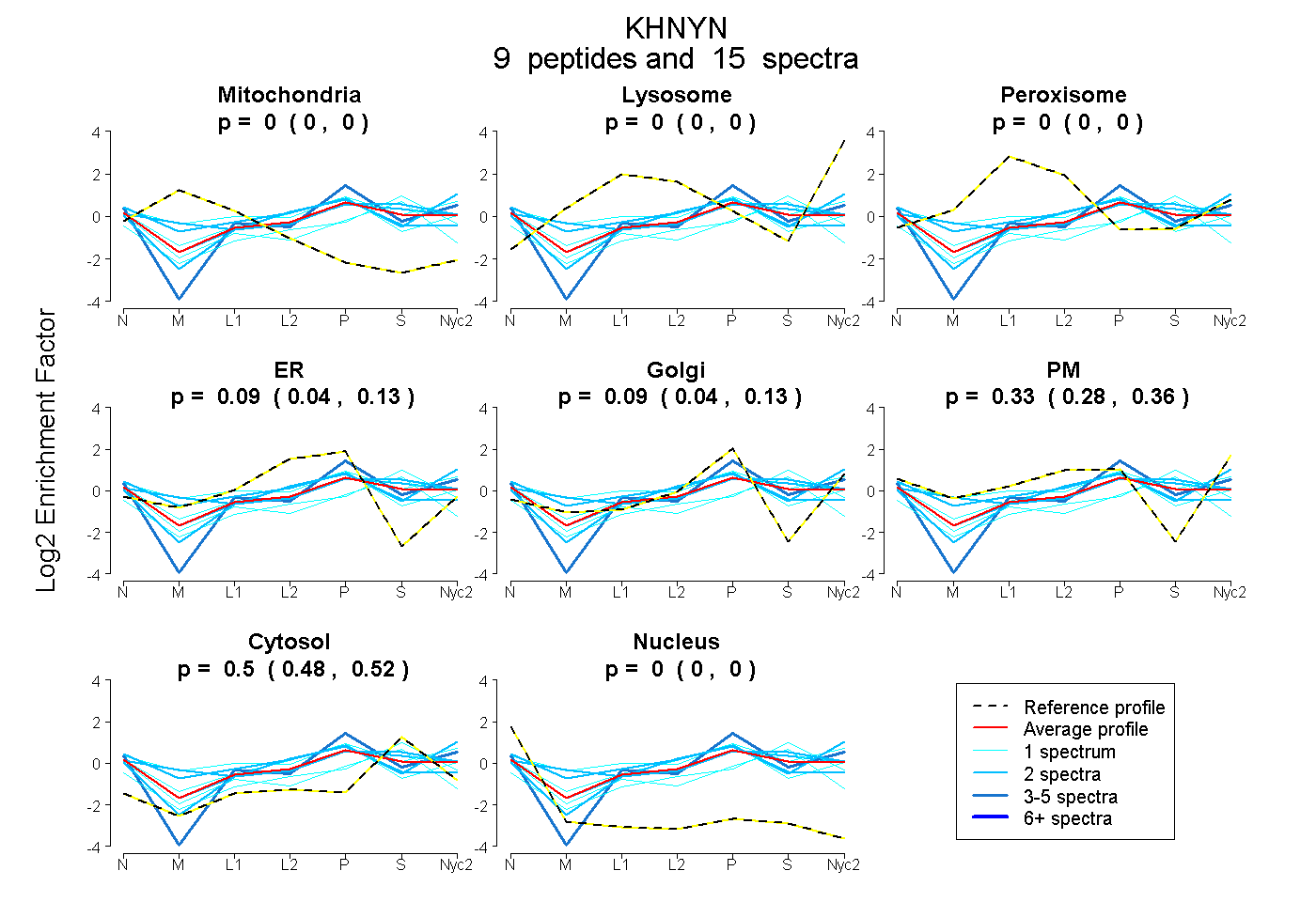
0.000 | 0.000
0.000 | 0.000
0.000 | 0.001
0.036 | 0.128
0.041 | 0.128
0.277 | 0.365
0.482 | 0.516
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
15 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.001 |
0.087 0.036 | 0.128 |
0.087 0.041 | 0.128 |
0.325 0.277 | 0.365 |
0.500 0.482 | 0.516 |
0.000 0.000 | 0.000 |
| 2 spectra, QEVPQQR | 0.000 | 0.000 | 0.000 | 0.039 | 0.141 | 0.226 | 0.594 | 0.000 | ||
| 1 spectrum, GLCSPELQSEIR | 0.000 | 0.000 | 0.073 | 0.150 | 0.033 | 0.000 | 0.630 | 0.114 | ||
| 1 spectrum, NGPTLDEFLK | 0.000 | 0.000 | 0.000 | 0.029 | 0.025 | 0.176 | 0.771 | 0.000 | ||
| 2 spectra, LAEETDGIIVSNDQFR | 0.000 | 0.000 | 0.005 | 0.000 | 0.000 | 0.689 | 0.306 | 0.000 | ||
| 3 spectra, GGNLVTGTQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.523 | 0.039 | 0.438 | 0.000 | ||
| 1 spectrum, DLAEESDK | 0.000 | 0.000 | 0.016 | 0.000 | 0.108 | 0.470 | 0.406 | 0.000 | ||
| 2 spectra, GPTEHGHQQQGK | 0.082 | 0.000 | 0.017 | 0.345 | 0.014 | 0.204 | 0.338 | 0.000 | ||
| 1 spectrum, ESHFLQK | 0.040 | 0.000 | 0.237 | 0.000 | 0.402 | 0.121 | 0.164 | 0.037 | ||
| 2 spectra, DFSALLQTR | 0.000 | 0.000 | 0.000 | 0.060 | 0.066 | 0.337 | 0.537 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
14 spectra |
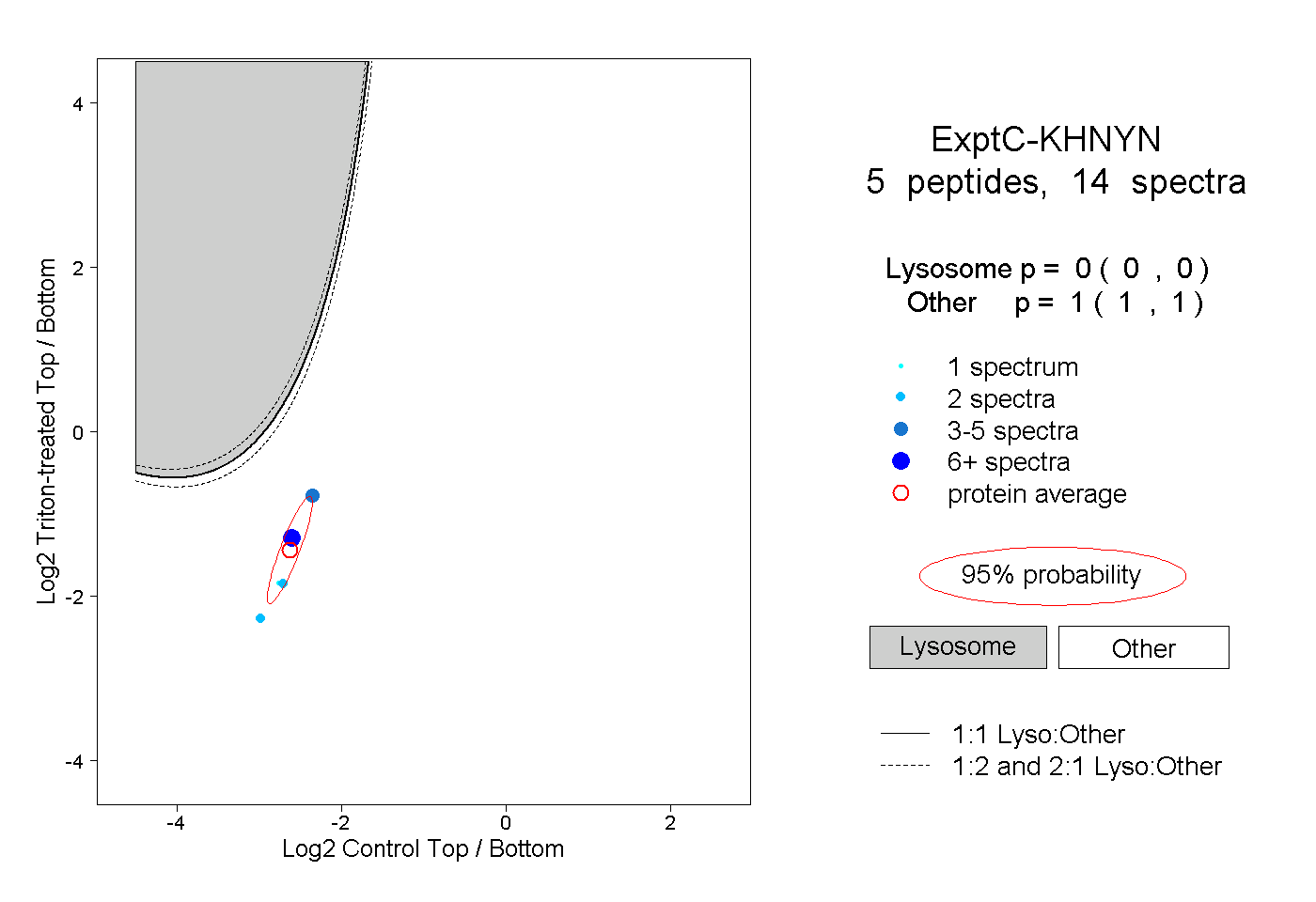 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
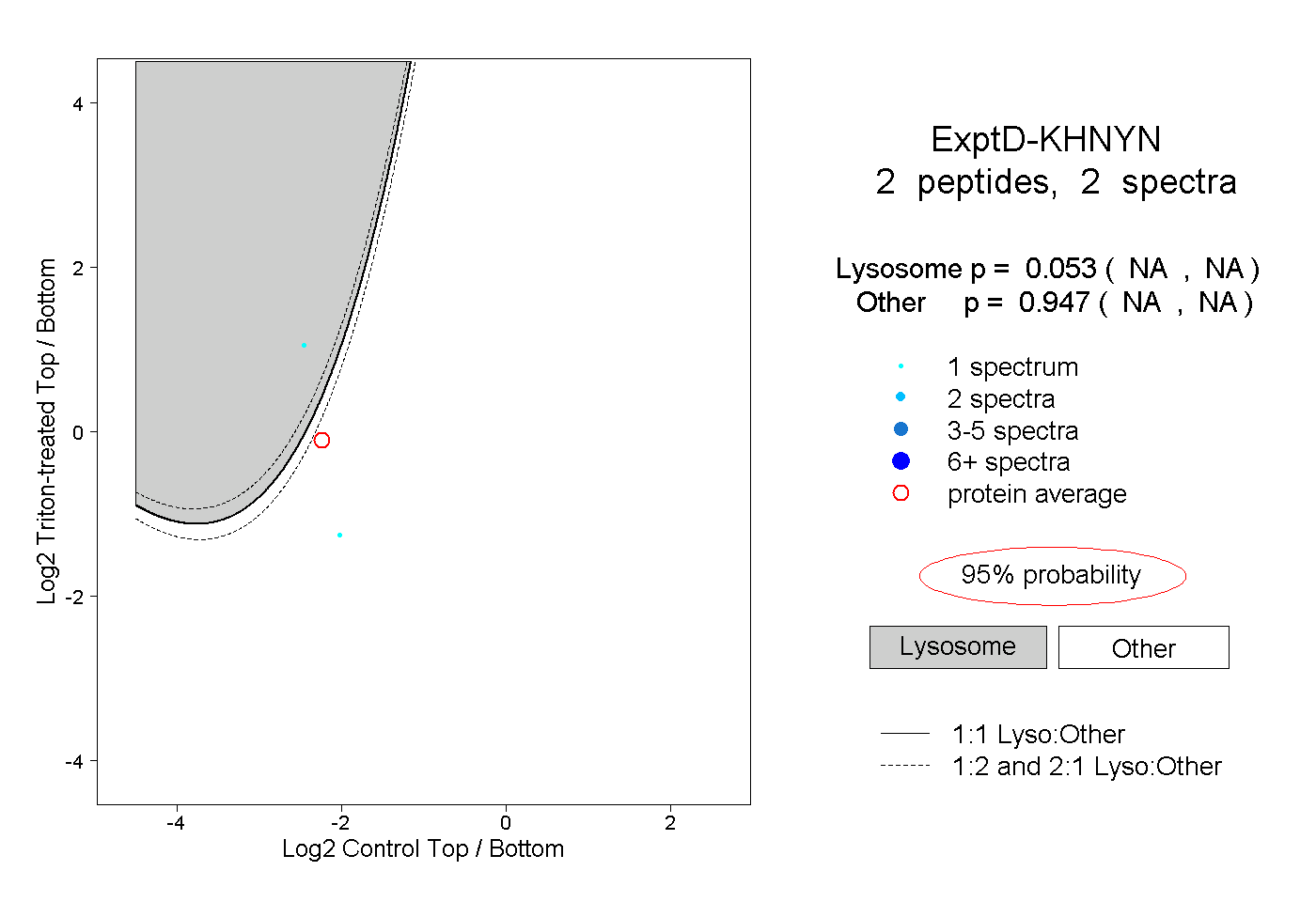 |
0.053 NA | NA |
0.947 NA | NA |