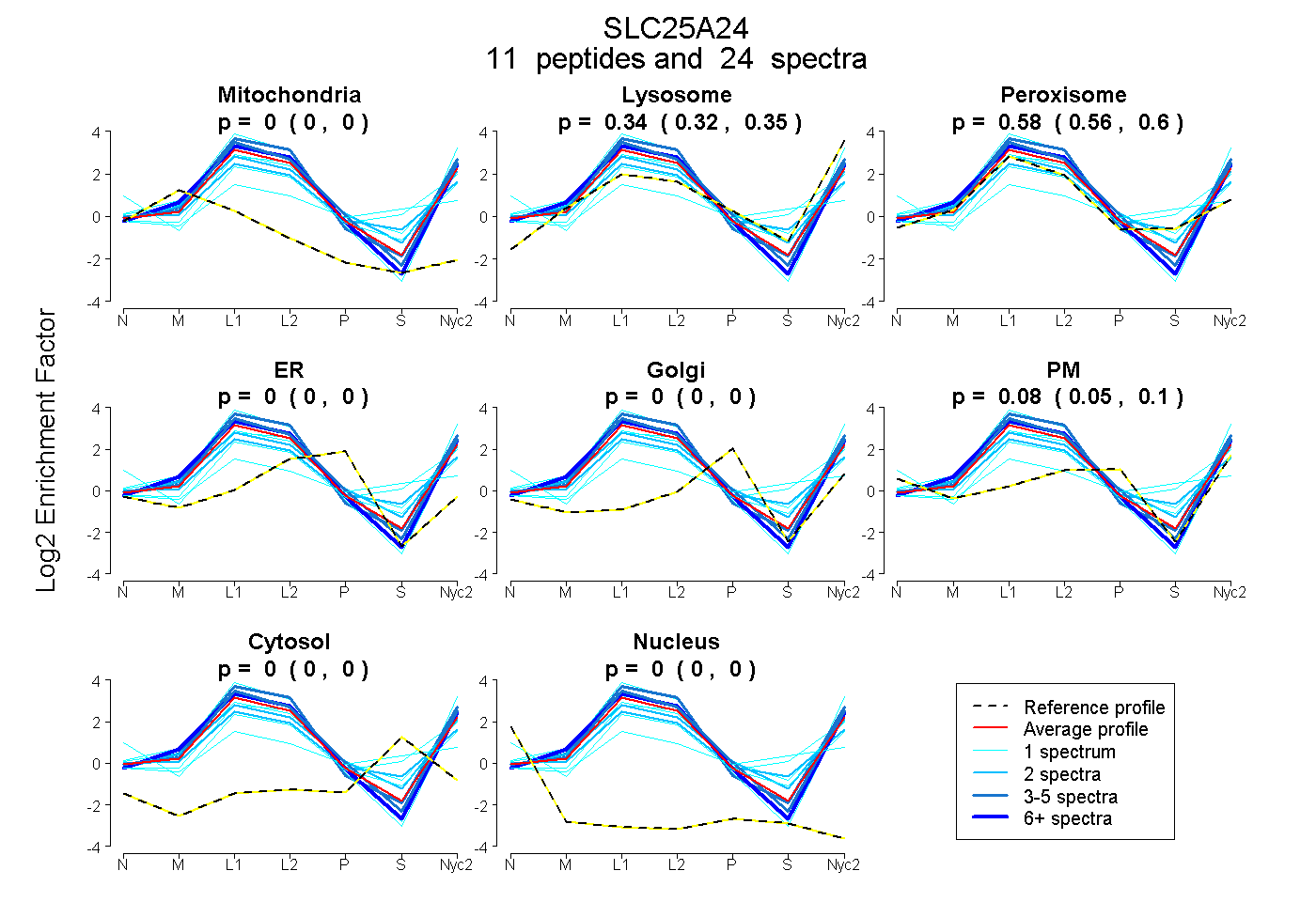
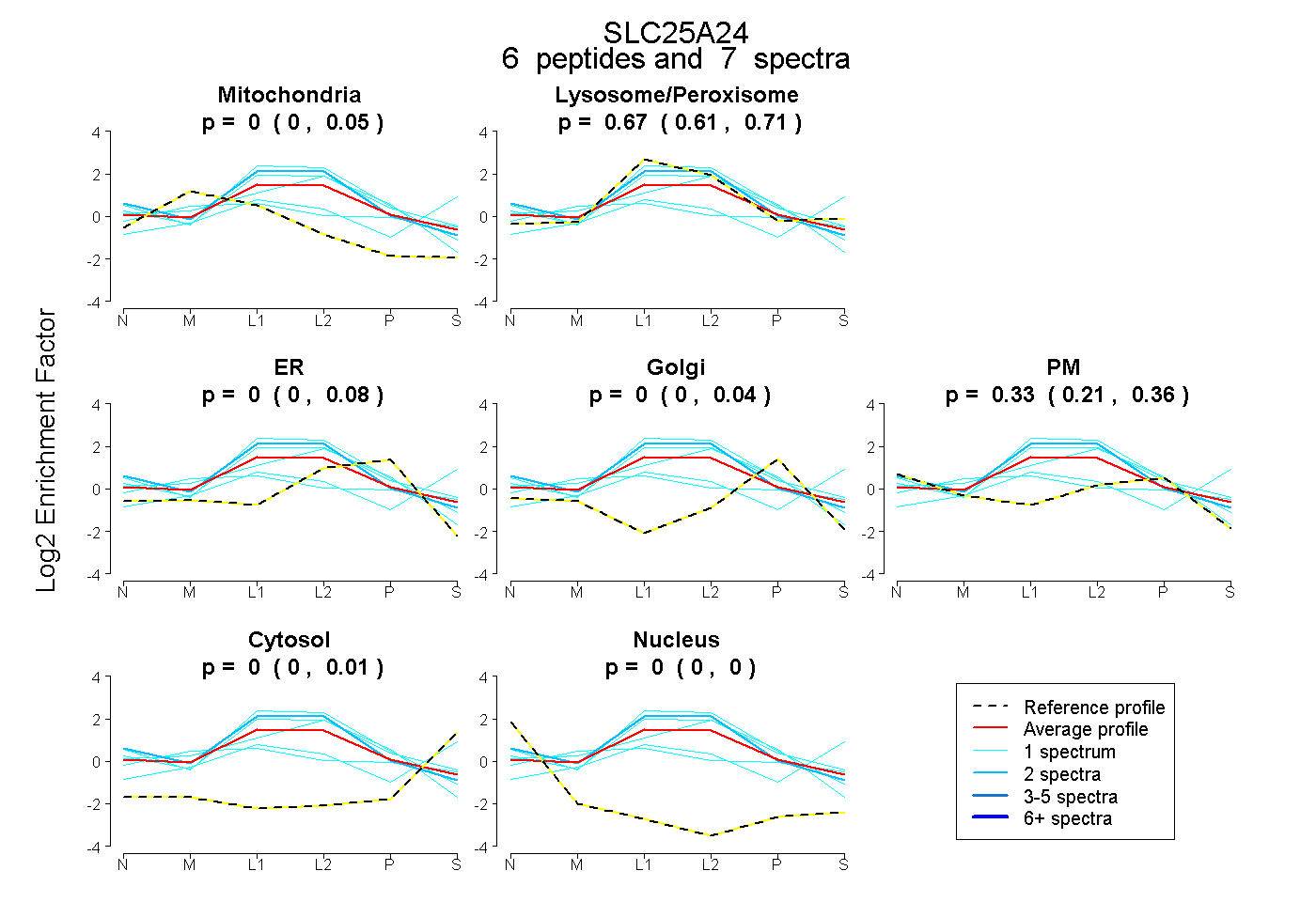
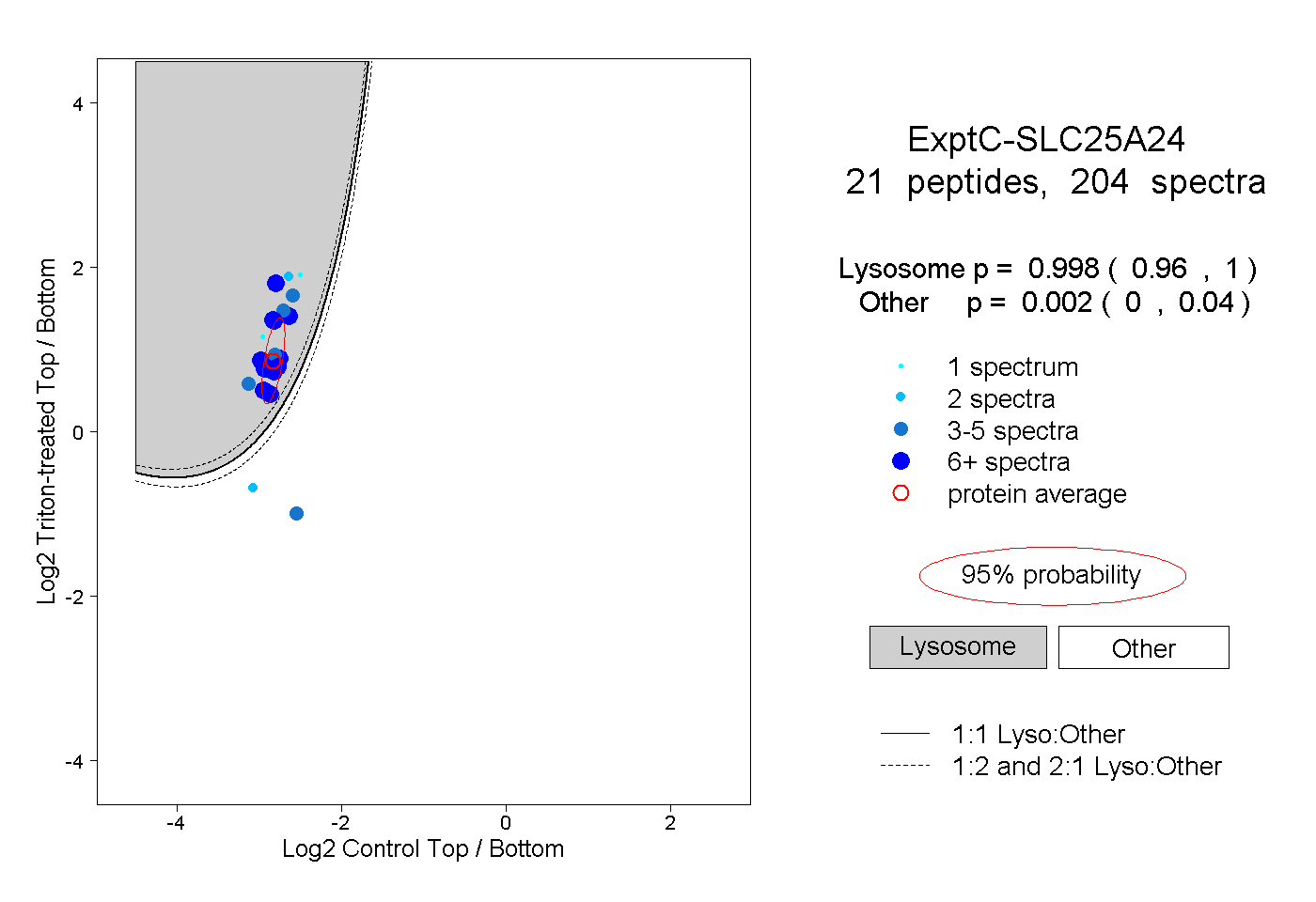
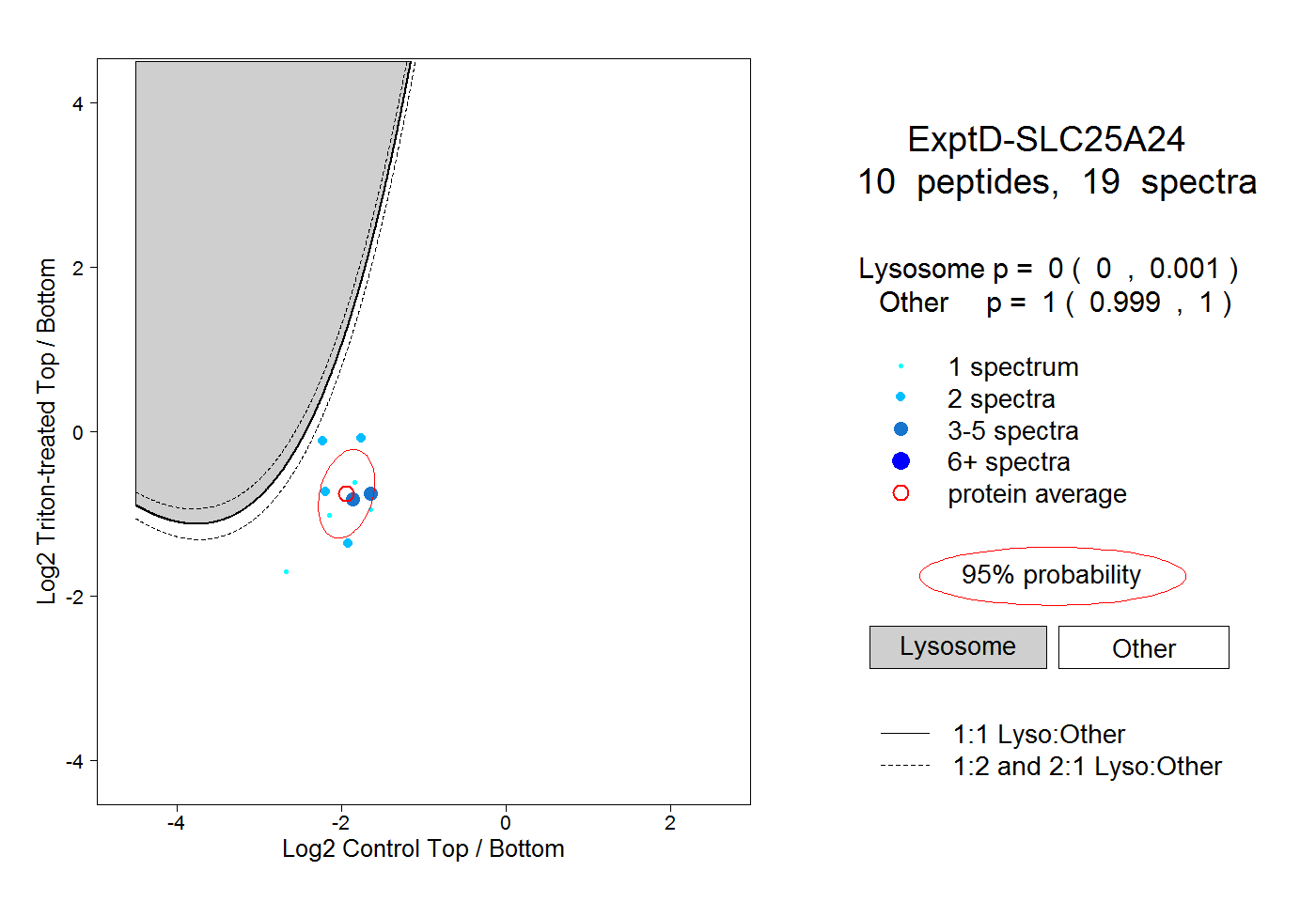
| 1 spectrum, MQAQATTEGAPQLSMVGLFQR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, VLPAVGISYVVYENMK |
|
0.005 |
|
|
|
|
|
|
|
0.995 |
| 26 spectra, SMNIFGGFR |
|
0.999 |
|
|
|
|
|
|
|
0.001 |
| 4 spectra, YETLFR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 6 spectra, GNGINVLK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 4 spectra, IFTTGDVNK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, FWAYEQYK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 6 spectra, QLLAGGVAGAVSR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 4 spectra, LGTSER |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 3 spectra, VMMQVHGSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, LLTEEGQK |
|
0.994 |
|
|
|
|
|
|
|
0.006 |
| 6 spectra, SGQWWR |
|
0.967 |
|
|
|
|
|
|
|
0.033 |
| 4 spectra, TGQYSGIYGCAK |
|
0.999 |
|
|
|
|
|
|
|
0.001 |
| 1 spectrum, DYFLFNPVTDIEEIIR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 33 spectra, IAPETAVK |
|
0.996 |
|
|
|
|
|
|
|
0.004 |
| 15 spectra, GITPNFMK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 6 spectra, LDFEEFMK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 12 spectra, QTLGVAQK |
|
0.997 |
|
|
|
|
|
|
|
0.003 |
| 6 spectra, SYWLDNFAK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 15 spectra, EGVSGLYR |
|
0.992 |
|
|
|
|
|
|
|
0.008 |
| 26 spectra, TSTAPLDR |
|
0.993 |
|
|
|
|
|
|
|
0.007 |