peptides
spectra
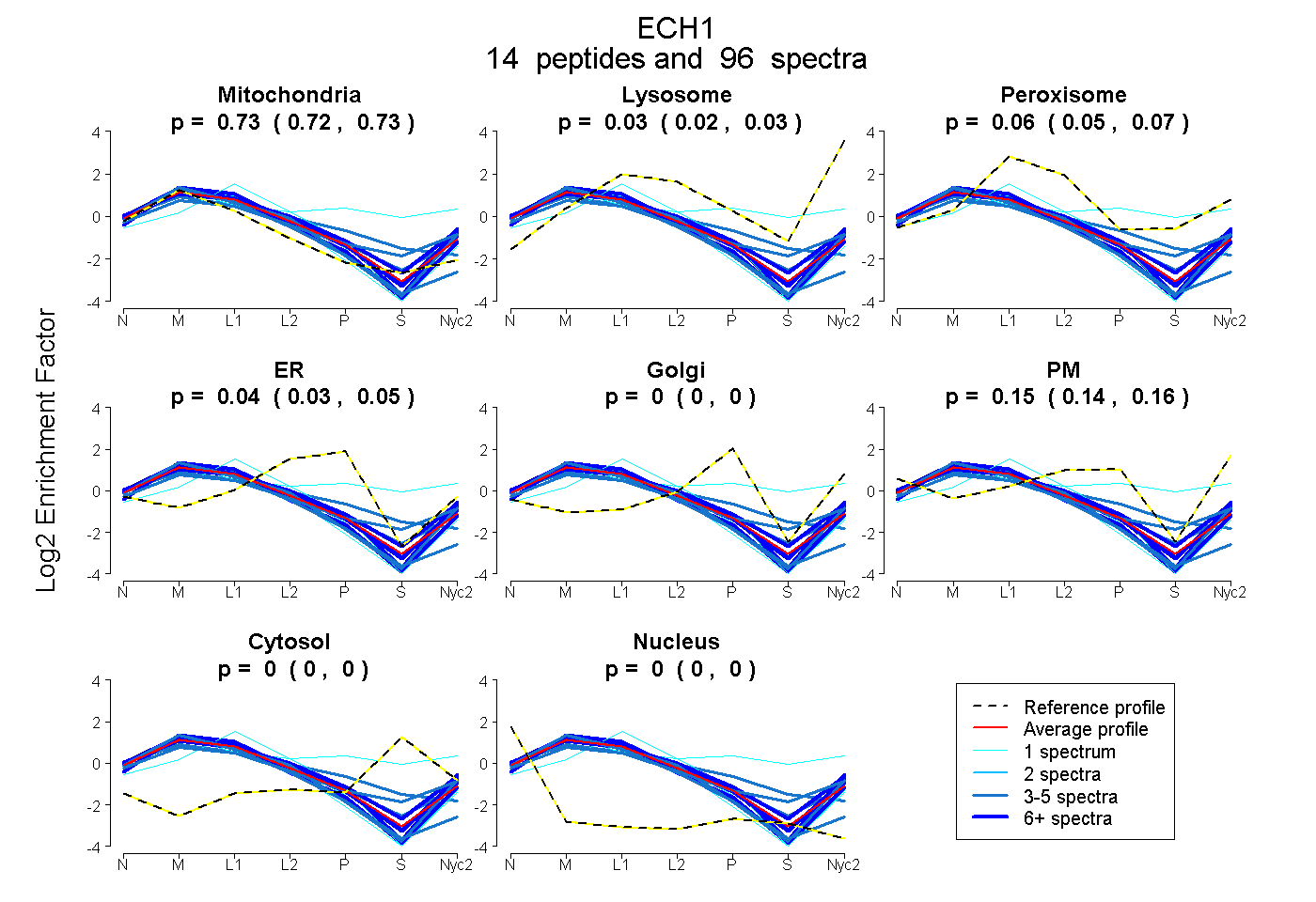
0.722 | 0.730
0.020 | 0.034
0.048 | 0.068
0.028 | 0.045
0.000 | 0.000
0.141 | 0.159
0.000 | 0.000
0.000 | 0.000
peptides
spectra
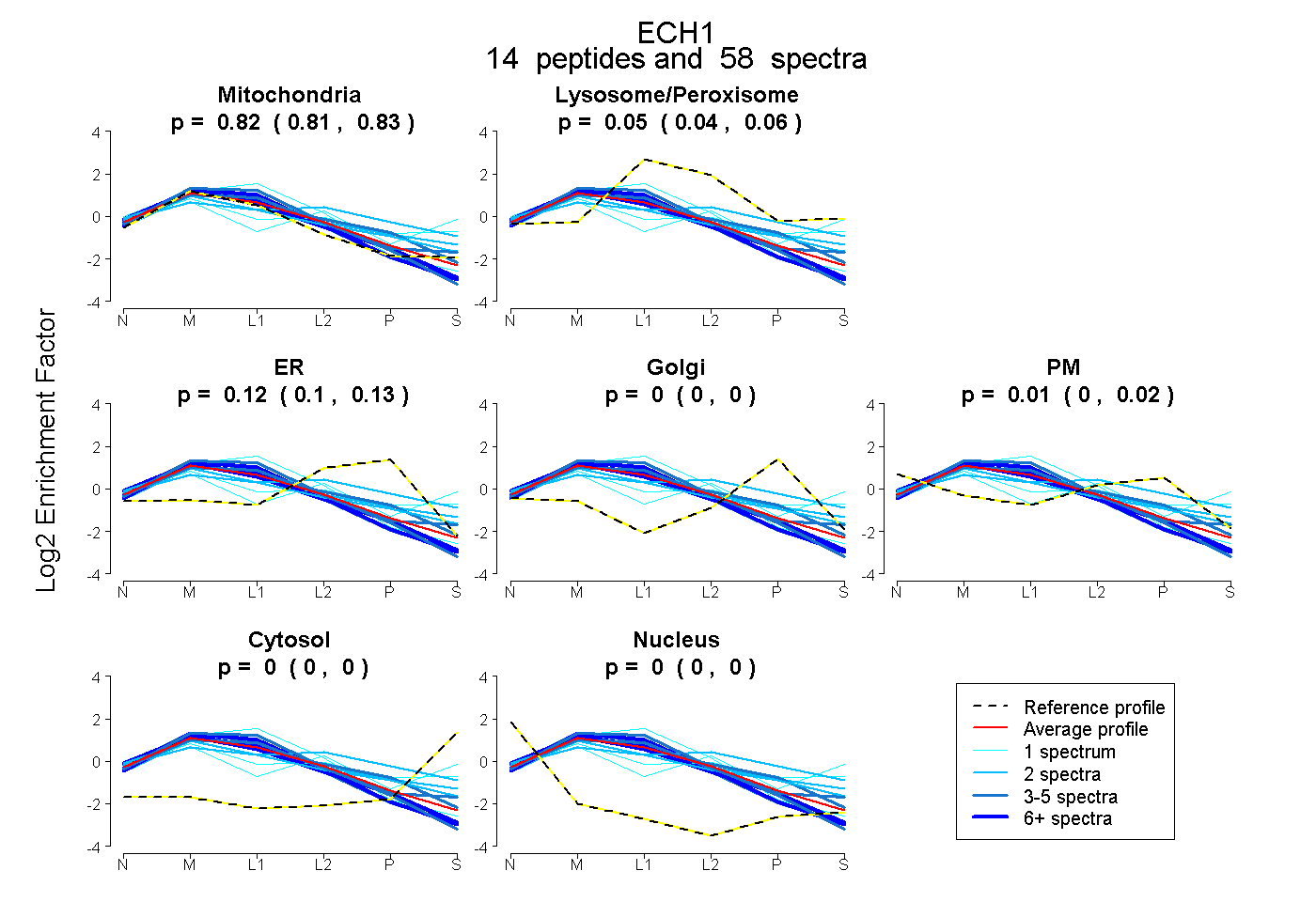
0.815 | 0.831
0.039 | 0.059
0.101 | 0.128
0.000 | 0.000
0.000 | 0.023
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
96 spectra |
 |
0.726 0.722 | 0.730 |
0.027 0.020 | 0.034 |
0.059 0.048 | 0.068 |
0.037 0.028 | 0.045 |
0.000 0.000 | 0.000 |
0.151 0.141 | 0.159 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
58 spectra |
 |
0.824 0.815 | 0.831 |
0.050 0.039 | 0.059 |
0.115 0.101 | 0.128 |
0.000 0.000 | 0.000 |
0.011 0.000 | 0.023 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, SVQAAMEK | 0.646 | 0.064 | 0.000 | 0.000 | 0.291 | 0.000 | 0.000 | |||
| 2 spectra, SPVAVQGSK | 0.304 | 0.328 | 0.000 | 0.145 | 0.206 | 0.016 | 0.000 | |||
| 3 spectra, SITFSK | 0.705 | 0.058 | 0.237 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, CPKPVIAAIHGGCIGGGVDLISACDIR | 0.813 | 0.187 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, EVDVGLAADVGTLQR | 0.338 | 0.180 | 0.000 | 0.000 | 0.219 | 0.263 | 0.000 | |||
| 6 spectra, SLVNELTFTAR | 0.897 | 0.000 | 0.103 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, MMADEALDSGLVSR | 0.419 | 0.170 | 0.000 | 0.000 | 0.276 | 0.135 | 0.000 | |||
| 16 spectra, IAWYLR | 0.993 | 0.004 | 0.003 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, HVLHVQLNRPEK | 0.640 | 0.256 | 0.000 | 0.104 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, ELVECFQK | 0.856 | 0.129 | 0.000 | 0.000 | 0.015 | 0.000 | 0.000 | |||
| 3 spectra, AVVVSGAGK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, YCTQDAFFQVK | 0.804 | 0.159 | 0.000 | 0.000 | 0.037 | 0.000 | 0.000 | |||
| 11 spectra, INLIYSR | 0.894 | 0.000 | 0.069 | 0.000 | 0.037 | 0.000 | 0.000 | |||
| 4 spectra, TFTVIEK | 0.925 | 0.028 | 0.047 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
516 spectra |
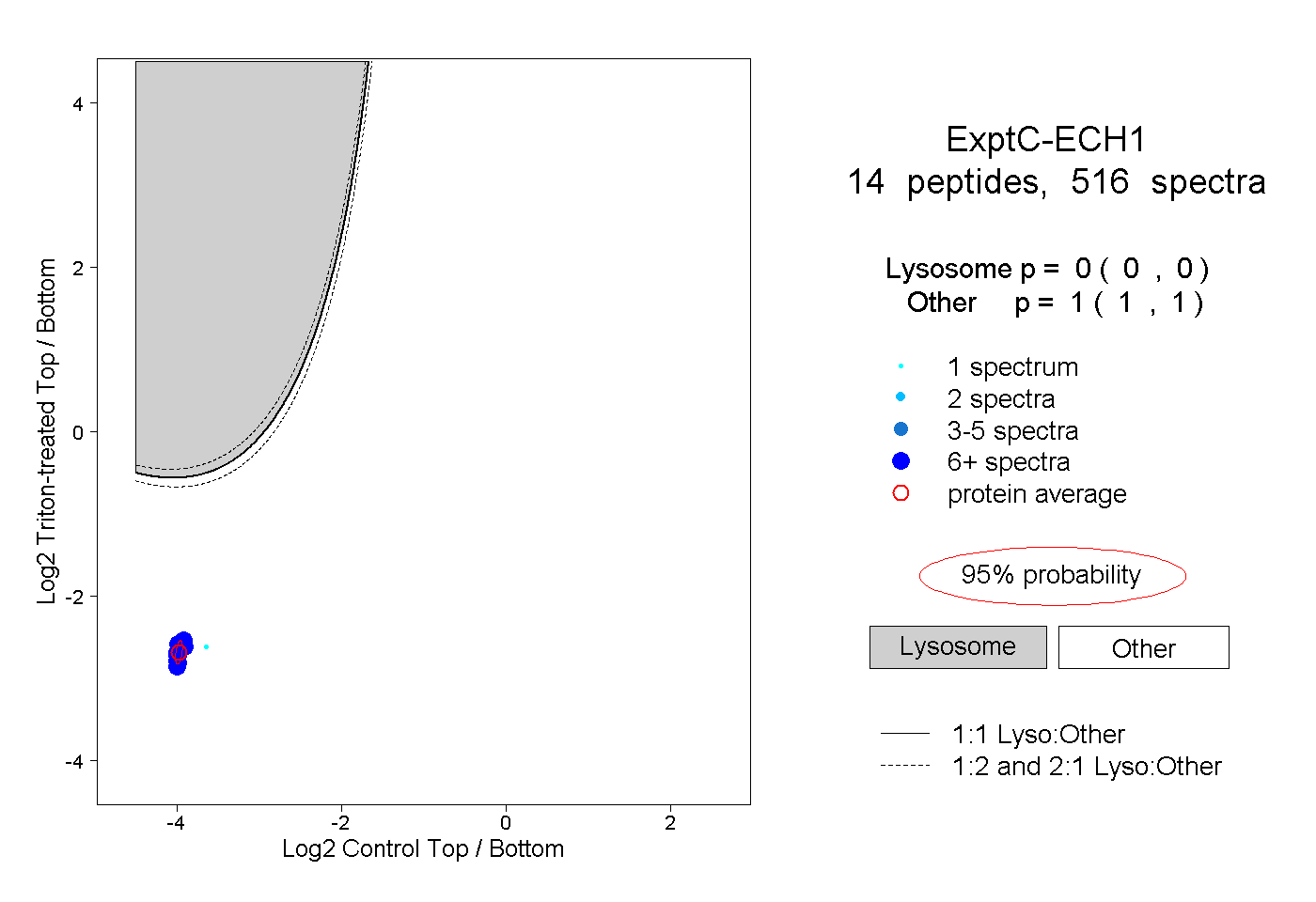 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
54 spectra |
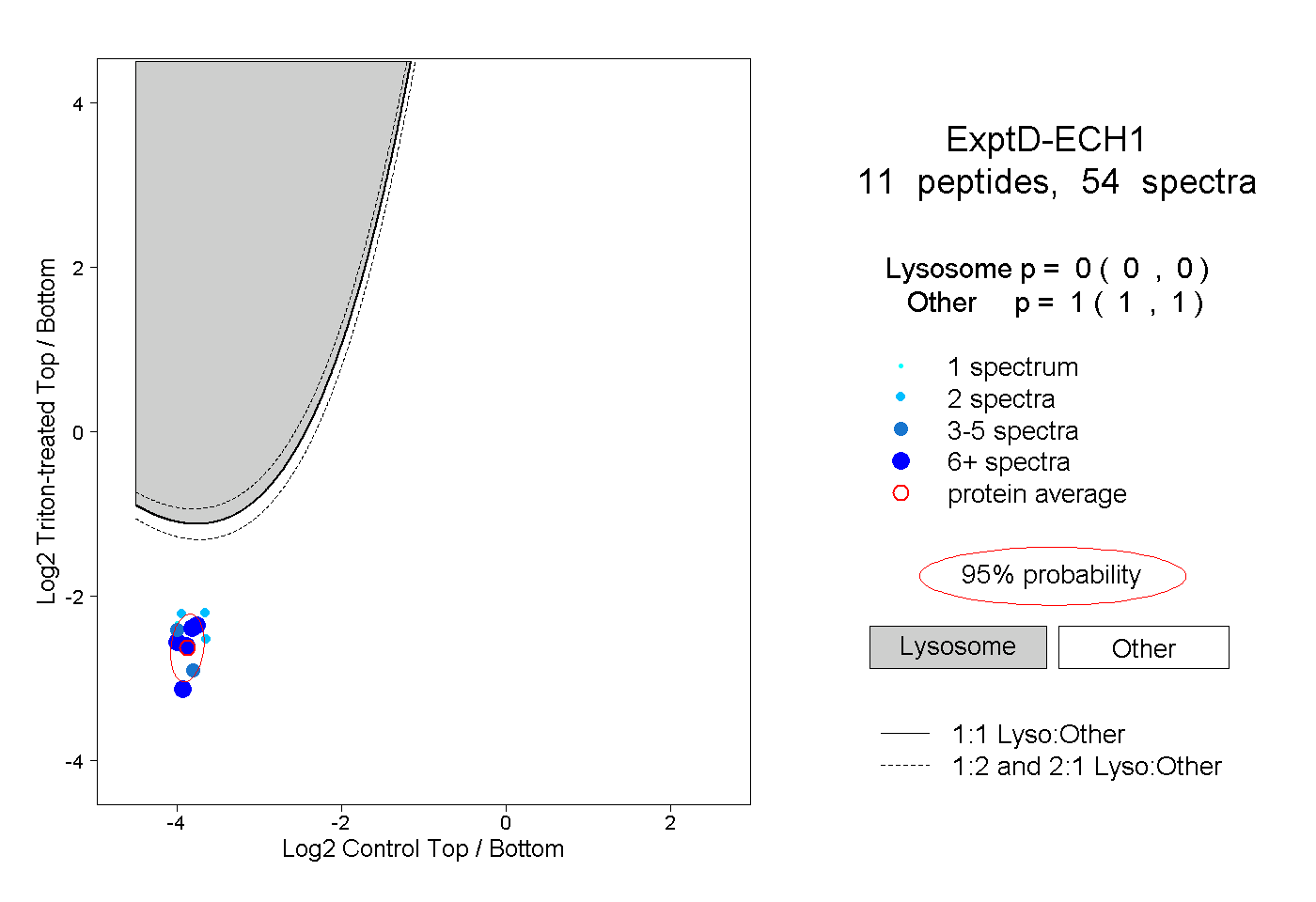 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |