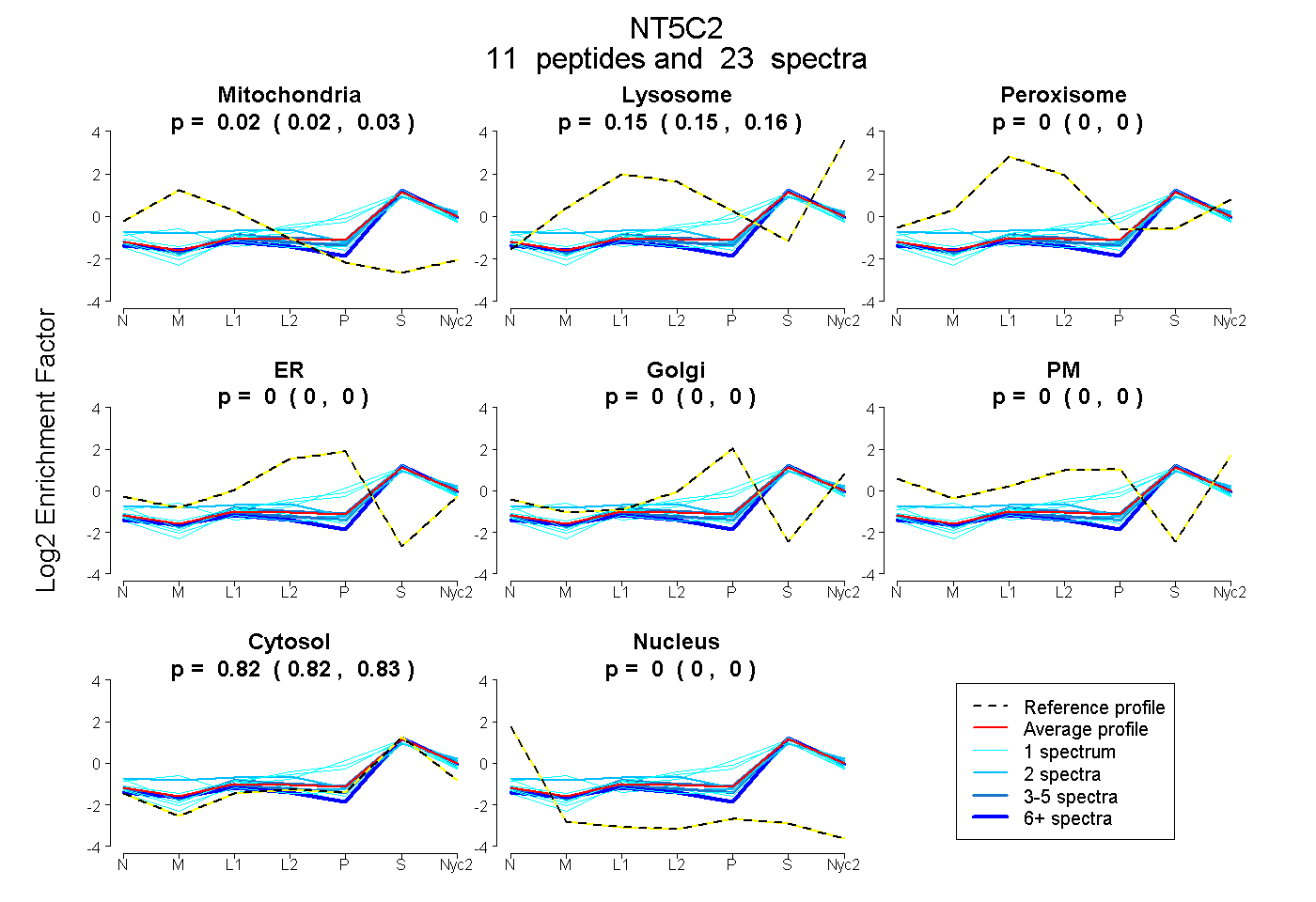
peptides
spectra
0.016 | 0.028
0.148 | 0.157
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.818 | 0.829
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
23 spectra |
 |
0.023 0.016 | 0.028 |
0.153 0.148 | 0.157 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.824 0.818 | 0.829 |
0.000 0.000 | 0.000 |
| 1 spectrum, DILYIGDHIFGDILK | 0.206 | 0.074 | 0.000 | 0.000 | 0.000 | 0.000 | 0.720 | 0.000 | ||
| 2 spectra, QTLFASQVMR | 0.100 | 0.188 | 0.055 | 0.000 | 0.000 | 0.000 | 0.657 | 0.000 | ||
| 2 spectra, DGDLFMSYR | 0.004 | 0.151 | 0.000 | 0.000 | 0.000 | 0.000 | 0.845 | 0.000 | ||
| 1 spectrum, SMFQDVR | 0.000 | 0.083 | 0.000 | 0.000 | 0.000 | 0.000 | 0.917 | 0.000 | ||
| 4 spectra, DAVDWVHYK | 0.003 | 0.159 | 0.012 | 0.000 | 0.000 | 0.000 | 0.826 | 0.000 | ||
| 1 spectrum, EQYPNK | 0.000 | 0.064 | 0.000 | 0.000 | 0.175 | 0.000 | 0.761 | 0.000 | ||
| 1 spectrum, GLVFDTLYGNLLK | 0.048 | 0.156 | 0.000 | 0.000 | 0.000 | 0.000 | 0.796 | 0.000 | ||
| 1 spectrum, TVENLEK | 0.000 | 0.000 | 0.094 | 0.021 | 0.151 | 0.047 | 0.686 | 0.000 | ||
| 6 spectra, LPLLLSR | 0.047 | 0.090 | 0.000 | 0.000 | 0.000 | 0.000 | 0.863 | 0.000 | ||
| 3 spectra, KPLFFGEGTVLR | 0.025 | 0.121 | 0.000 | 0.000 | 0.000 | 0.000 | 0.854 | 0.000 | ||
| 1 spectrum, VFLATNSDYK | 0.000 | 0.145 | 0.002 | 0.056 | 0.042 | 0.000 | 0.755 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
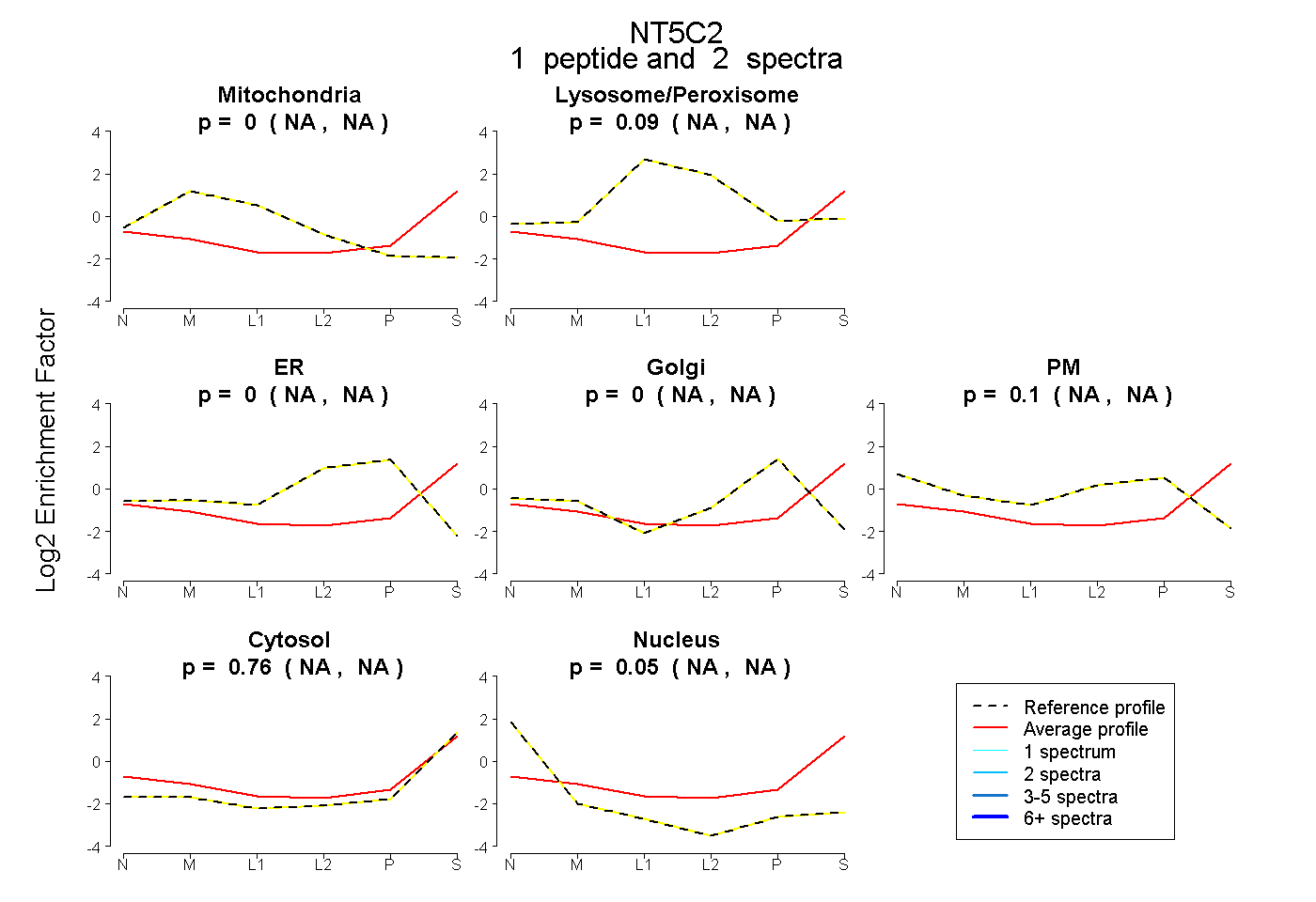 |
0.000 NA | NA |
0.088 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.098 NA | NA |
0.765 NA | NA |
0.049 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
35 spectra |
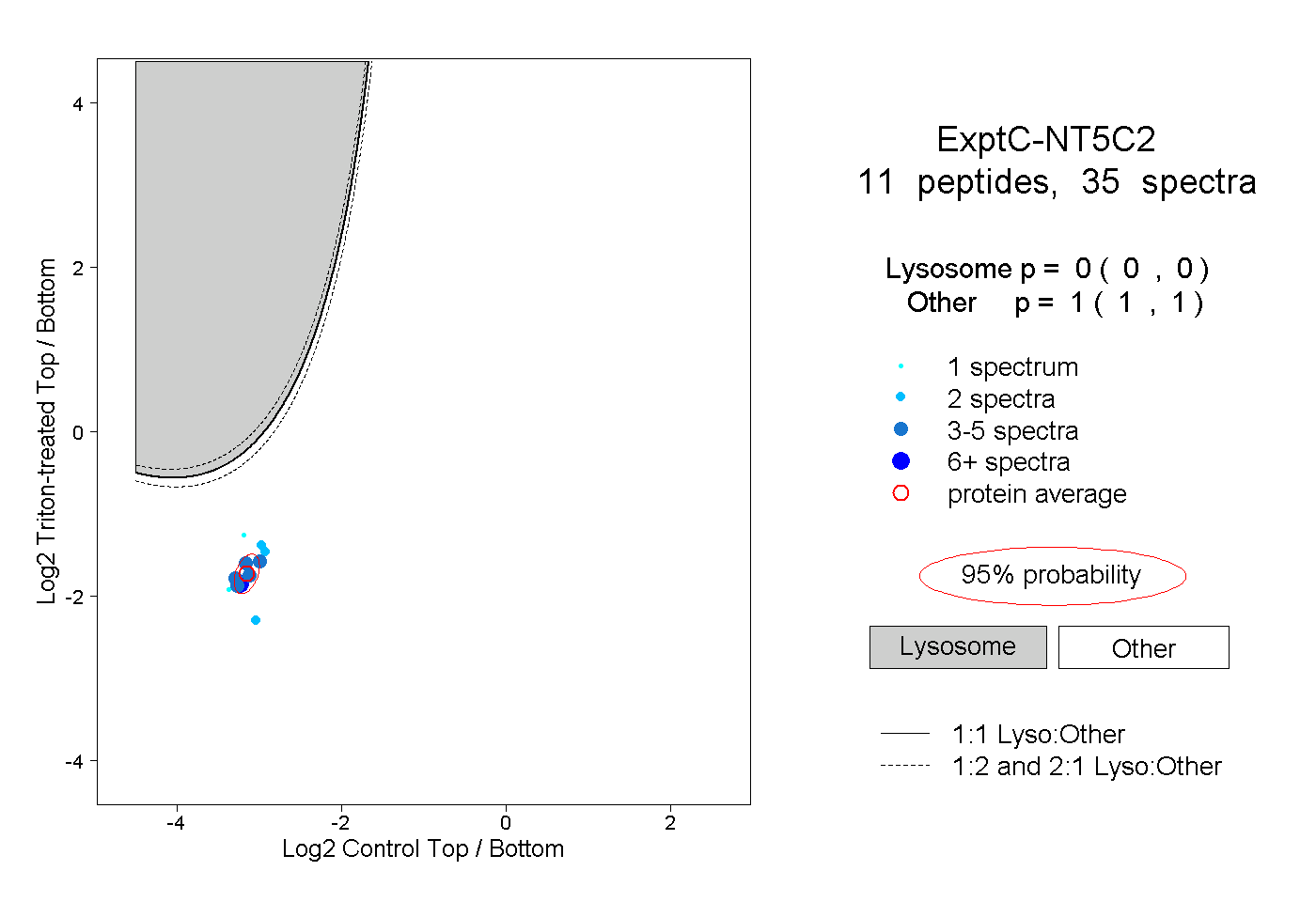 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |