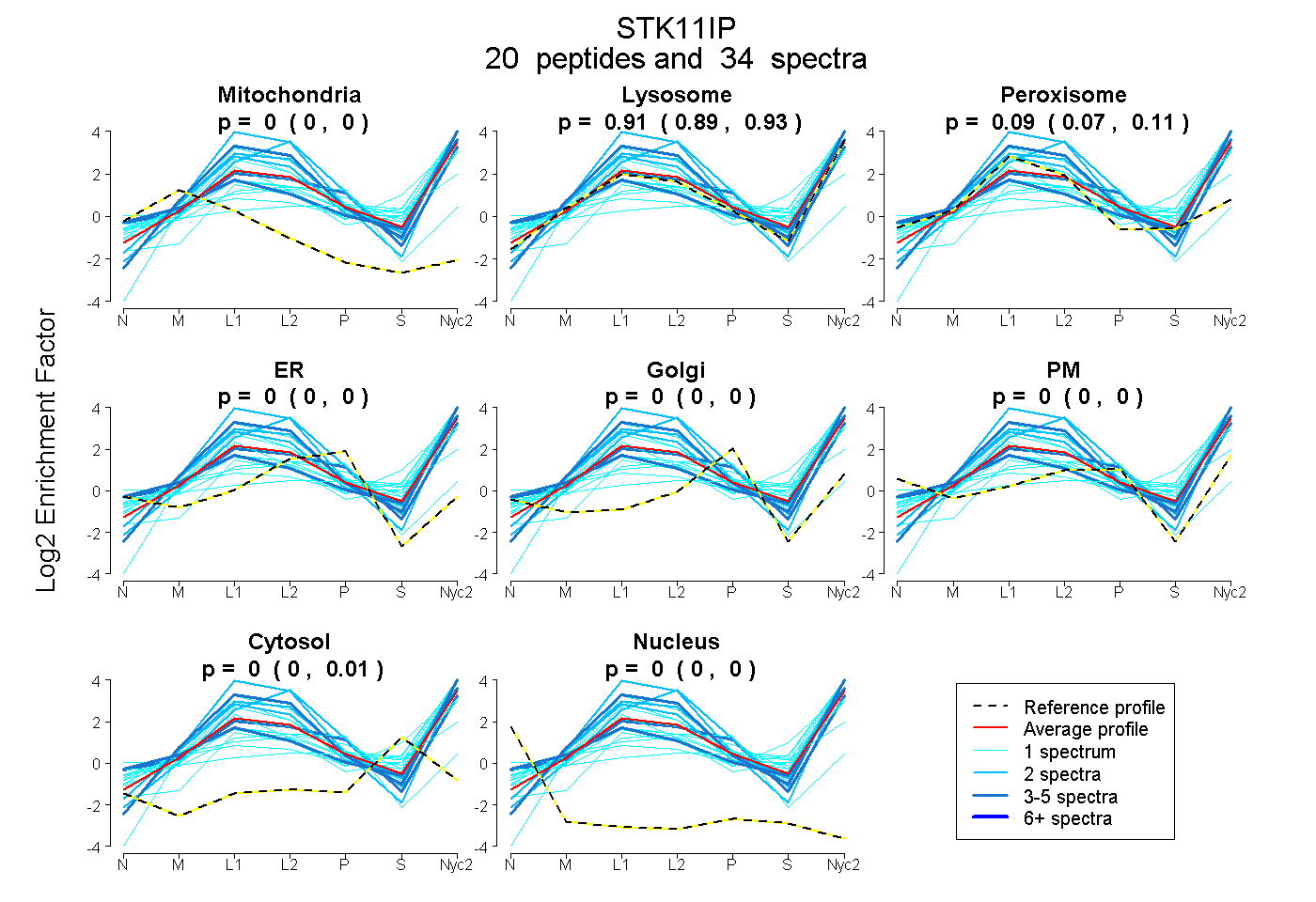
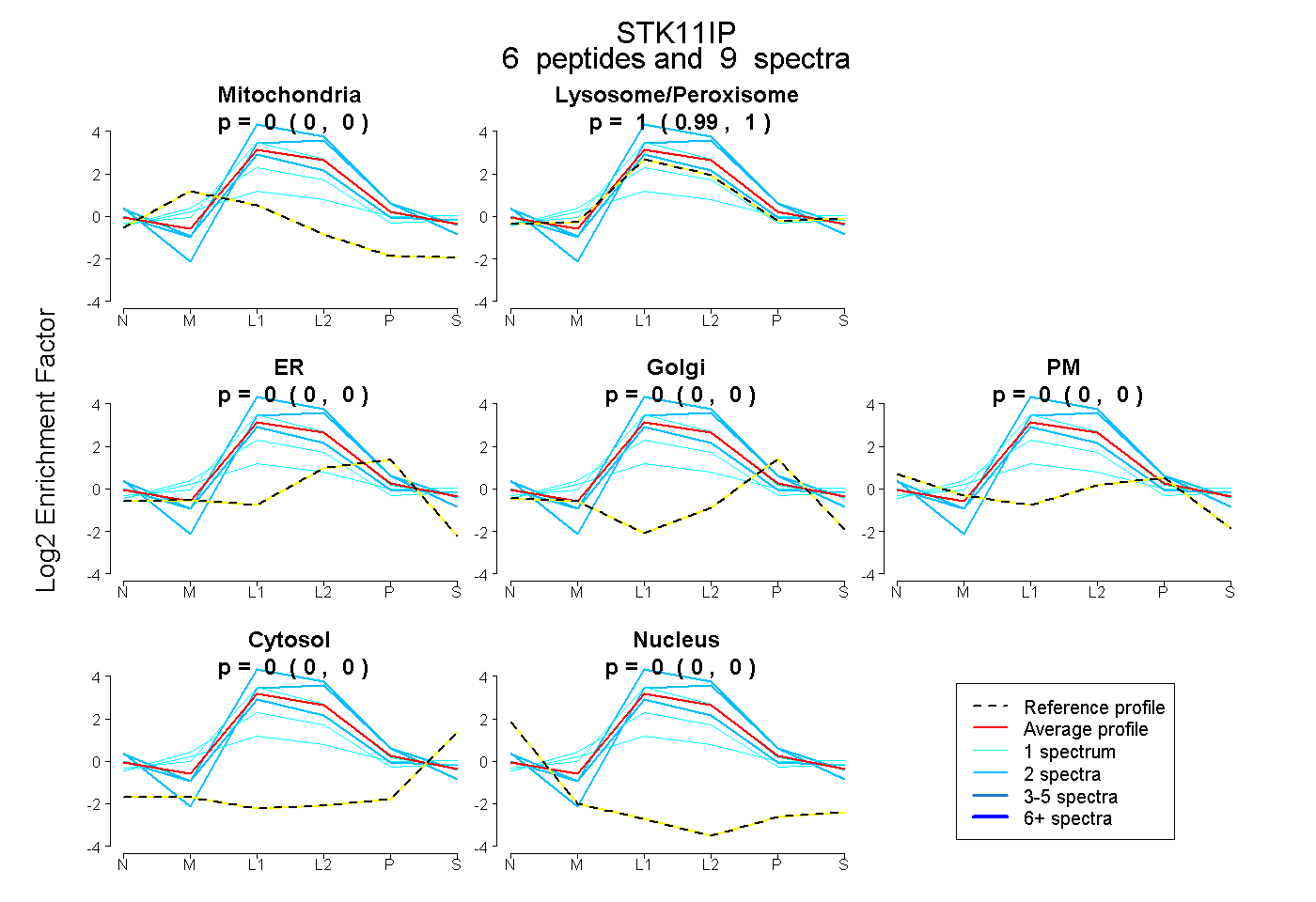
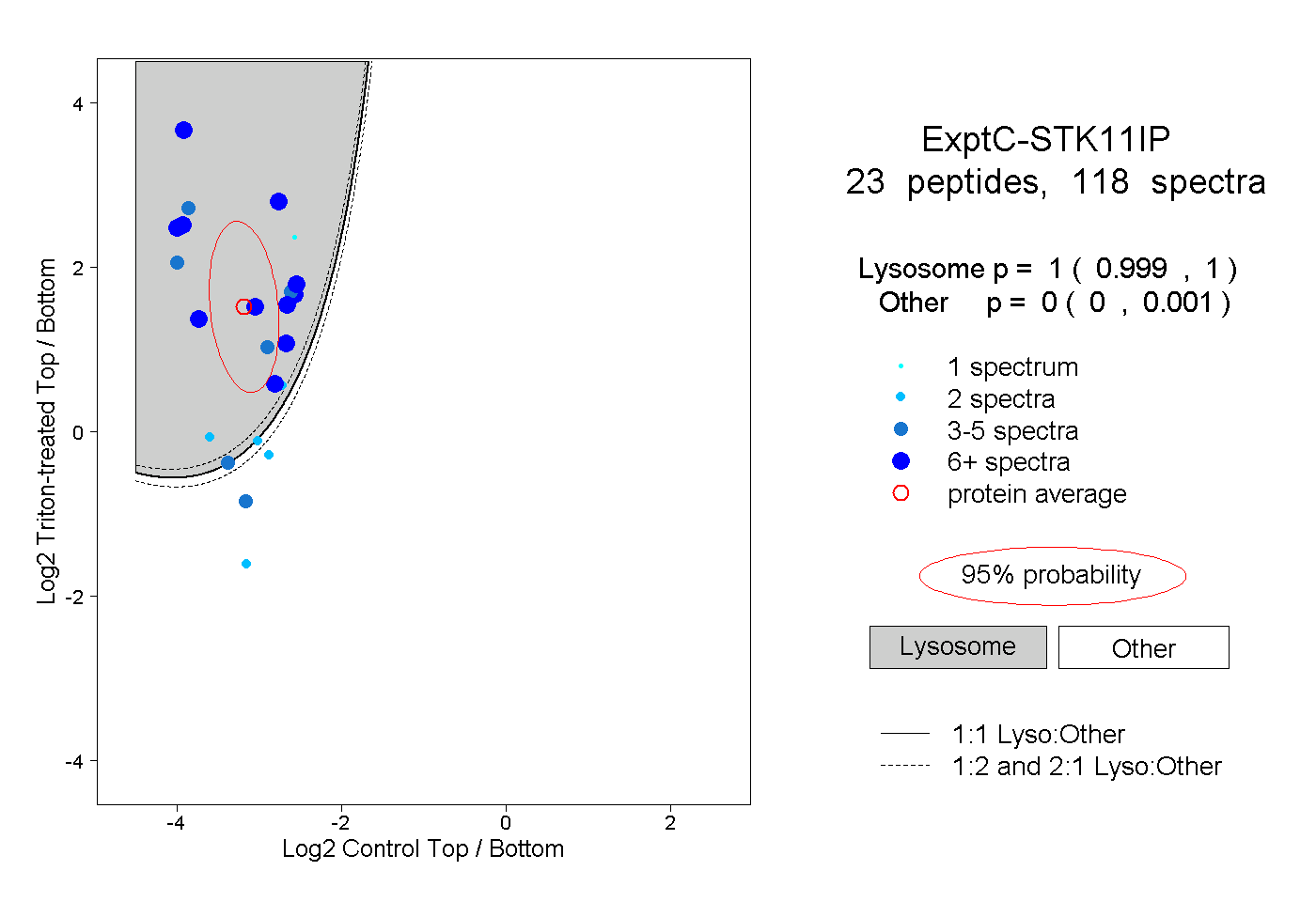
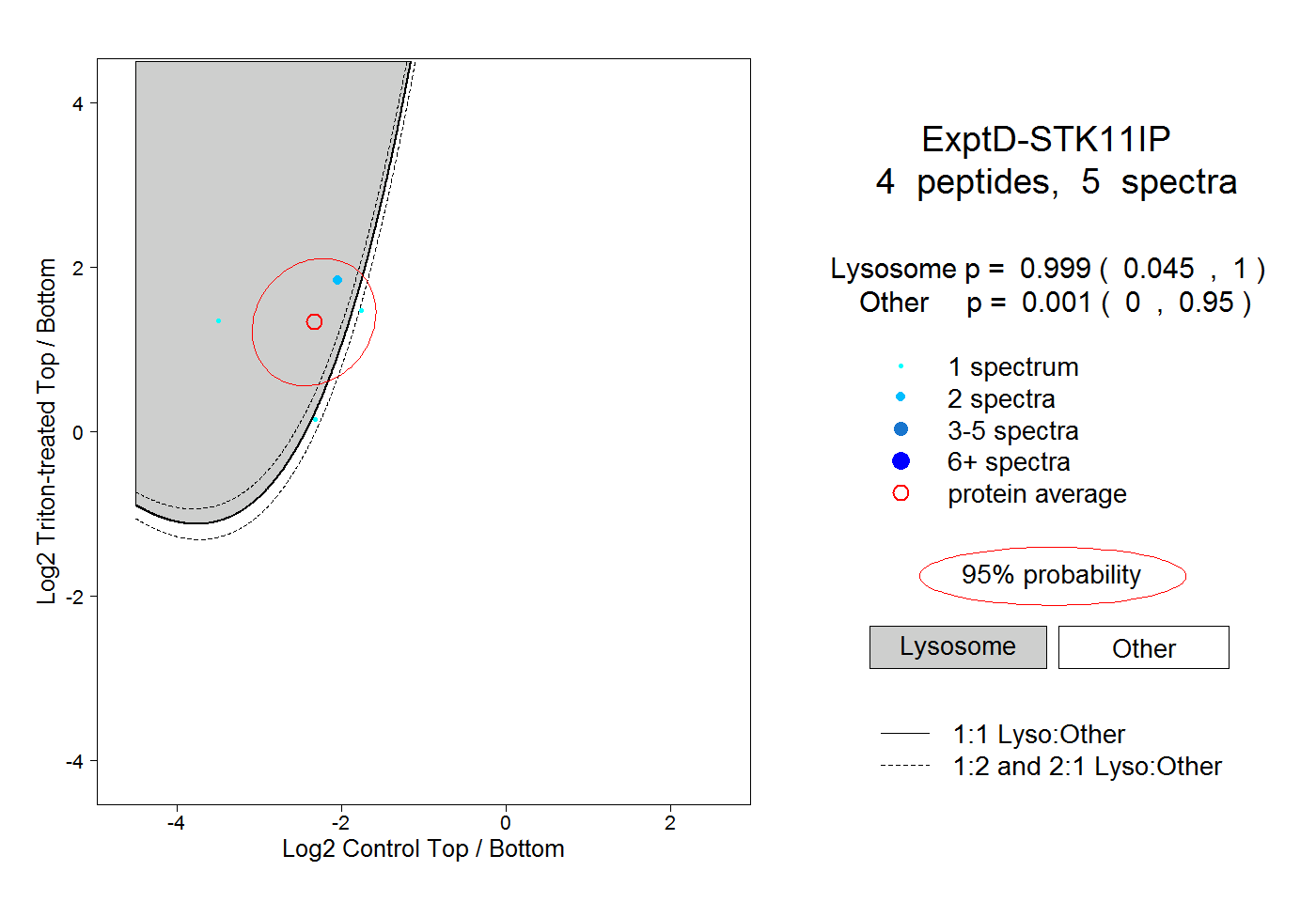
| 6 spectra, MGPSGAALGTLILR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 6 spectra, MLYLLK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 3 spectra, LEWAAGTGHCVLLPR |
|
0.002 |
|
|
|
|
|
|
|
0.998 |
| 14 spectra, DAAHGFLLDGK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, NCISATEETVTPQHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, DQQPGEAK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, ESLCLVVVSDR |
|
0.882 |
|
|
|
|
|
|
|
0.118 |
| 9 spectra, SPPAIGEDTK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 4 spectra, DTSAETPQFFYLR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, VPVVLAGHTR |
|
0.035 |
|
|
|
|
|
|
|
0.965 |
| 8 spectra, LESFWALR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 4 spectra, GVPIHSLCGLR |
|
0.532 |
|
|
|
|
|
|
|
0.468 |
| 2 spectra, FSYICPDR |
|
0.433 |
|
|
|
|
|
|
|
0.567 |
| 4 spectra, LIFYDEVSR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 6 spectra, LWPLLGK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 7 spectra, TSPLDLR |
|
0.974 |
|
|
|
|
|
|
|
0.026 |
| 6 spectra, DLQQTSESSR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 8 spectra, TVTQEALDLDR |
|
0.996 |
|
|
|
|
|
|
|
0.004 |
| 2 spectra, LVHTPGVGLPGPIK |
|
0.991 |
|
|
|
|
|
|
|
0.009 |
| 3 spectra, SLQGLEQLK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 7 spectra, ILSAIR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 4 spectra, ATTAQYLSPR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 1 spectrum, EPWEELFSIGLR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |