peptides
spectra
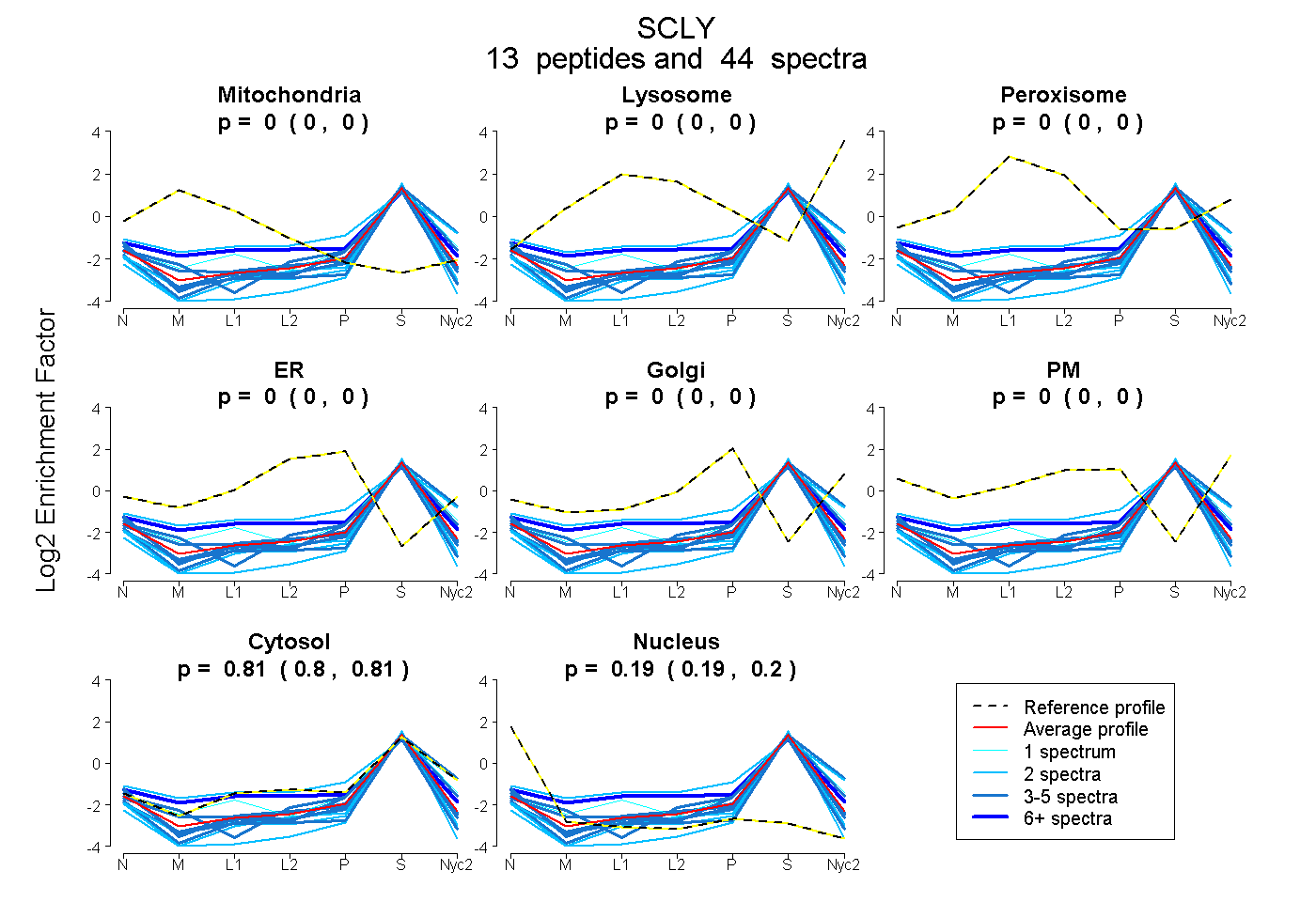
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.802 | 0.813
0.186 | 0.197
peptides
spectra
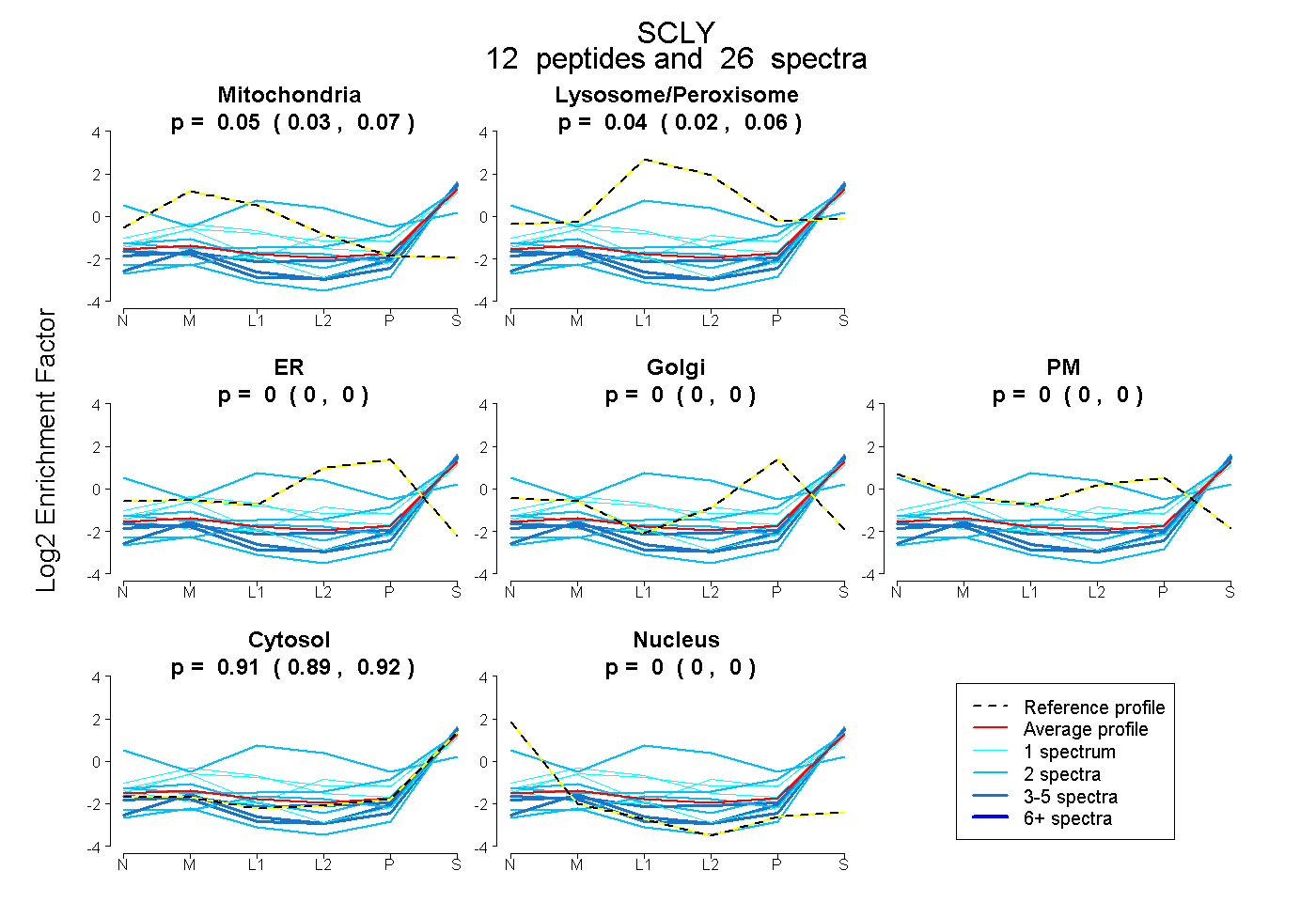
0.028 | 0.065
0.020 | 0.064
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.891 | 0.921
0.000 | 0.004
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
44 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.808 0.802 | 0.813 |
0.192 0.186 | 0.197 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
26 spectra |
 |
0.049 0.028 | 0.065 |
0.043 0.020 | 0.064 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.908 0.891 | 0.921 |
0.000 0.000 | 0.004 |
| 1 spectrum, LPNTCNFSIQGSQLR | 0.107 | 0.000 | 0.000 | 0.000 | 0.000 | 0.840 | 0.053 | |||
| 1 spectrum, AEVDLIVQDLK | 0.214 | 0.143 | 0.000 | 0.000 | 0.000 | 0.642 | 0.000 | |||
| 2 spectra, GSVESPPNR | 0.000 | 0.588 | 0.000 | 0.000 | 0.140 | 0.149 | 0.123 | |||
| 2 spectra, AADLVSENCETYEAHMR | 0.078 | 0.000 | 0.000 | 0.000 | 0.000 | 0.898 | 0.024 | |||
| 4 spectra, AASGLPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, ALGGQLR | 0.000 | 0.098 | 0.071 | 0.000 | 0.000 | 0.831 | 0.000 | |||
| 2 spectra, DYIEER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 3 spectra, DIINTAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.950 | 0.050 | |||
| 1 spectrum, IHLNSR | 0.074 | 0.242 | 0.000 | 0.000 | 0.000 | 0.684 | 0.000 | |||
| 5 spectra, IGALYVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, FPGVER | 0.000 | 0.029 | 0.000 | 0.000 | 0.000 | 0.971 | 0.000 | |||
| 2 spectra, QAVNQLEGPV | 0.000 | 0.146 | 0.000 | 0.083 | 0.000 | 0.771 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
22 spectra |
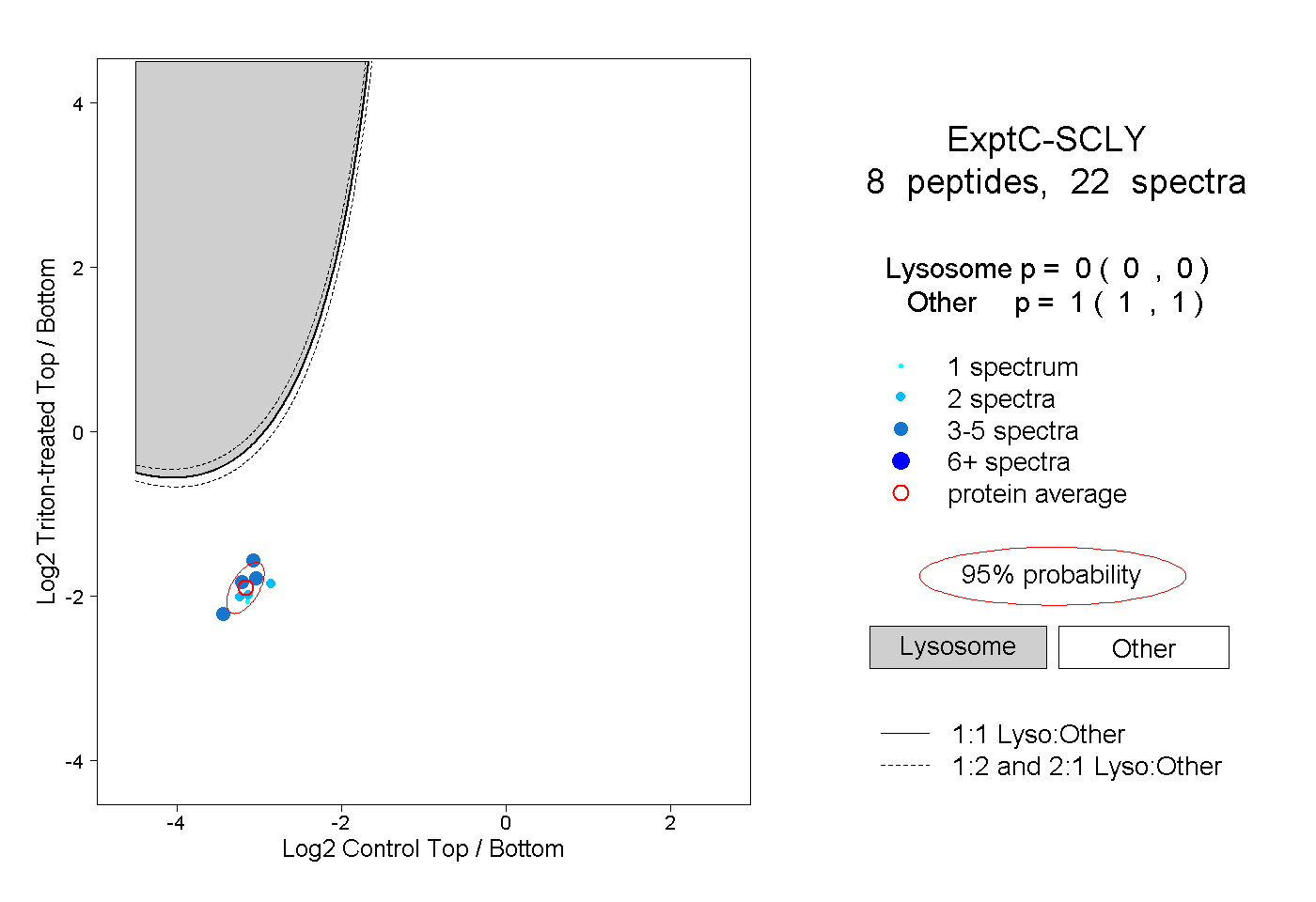 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
2 spectra |
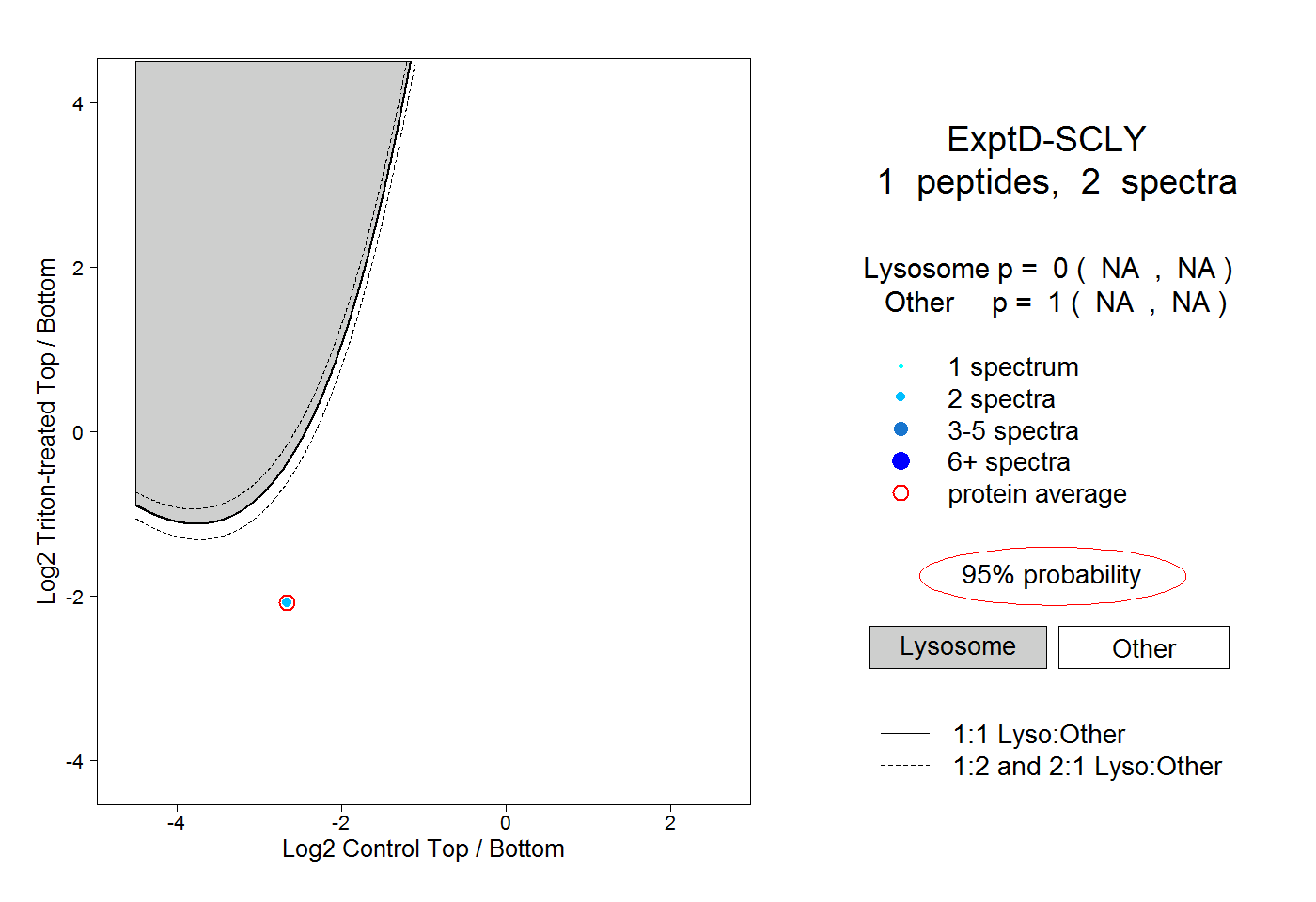 |
0.000 NA | NA |
1.000 NA | NA |