peptides
spectra
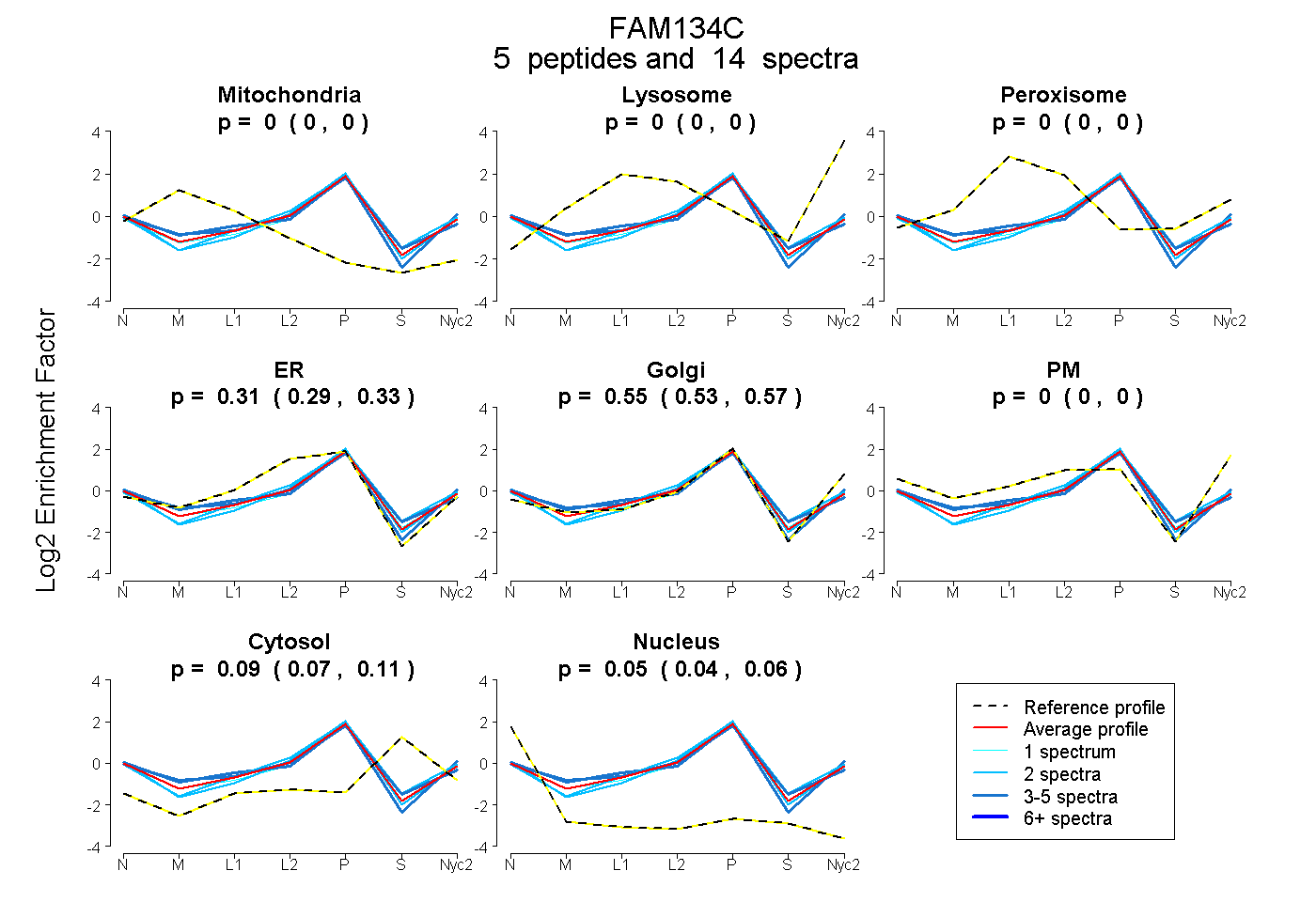
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.290 | 0.327
0.528 | 0.571
0.000 | 0.000
0.071 | 0.107
0.036 | 0.055
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
14 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.310 0.290 | 0.327 |
0.552 0.528 | 0.571 |
0.000 0.000 | 0.000 |
0.091 0.071 | 0.107 |
0.046 0.036 | 0.055 |
| 4 spectra, LDFSVR | 0.033 | 0.000 | 0.006 | 0.230 | 0.678 | 0.000 | 0.000 | 0.053 | ||
| 2 spectra, DQQVEAAQR | 0.000 | 0.000 | 0.000 | 0.256 | 0.622 | 0.000 | 0.051 | 0.071 | ||
| 1 spectrum, ALVEVLGPYEPLLSR | 0.000 | 0.000 | 0.000 | 0.231 | 0.622 | 0.000 | 0.102 | 0.046 | ||
| 2 spectra, LKPALQR | 0.000 | 0.000 | 0.000 | 0.345 | 0.482 | 0.000 | 0.173 | 0.000 | ||
| 5 spectra, VQAALVWERPAR | 0.013 | 0.000 | 0.000 | 0.365 | 0.450 | 0.000 | 0.146 | 0.027 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
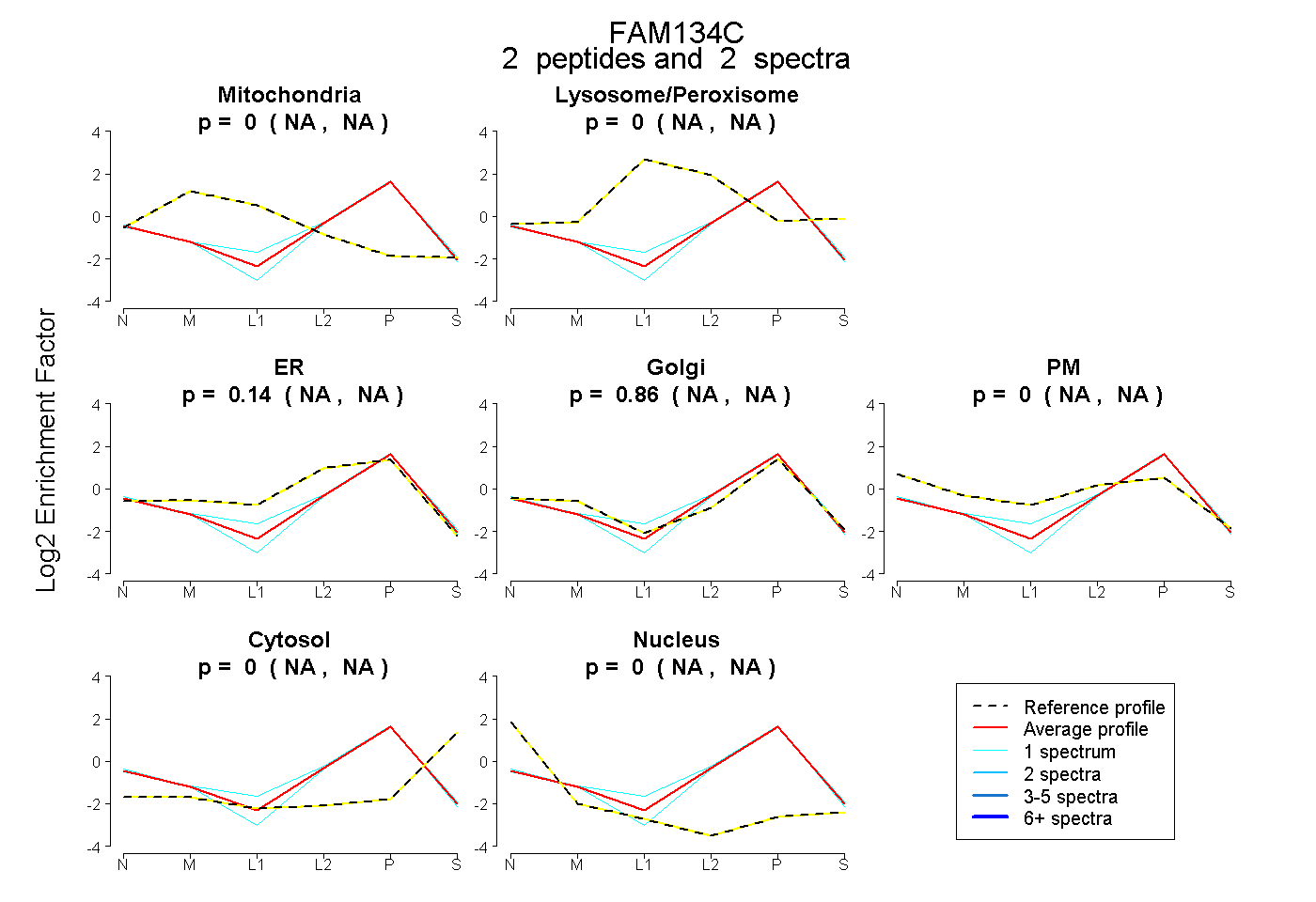 |
0.000 NA | NA |
0.000 NA | NA |
0.138 NA | NA |
0.862 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
10 spectra |
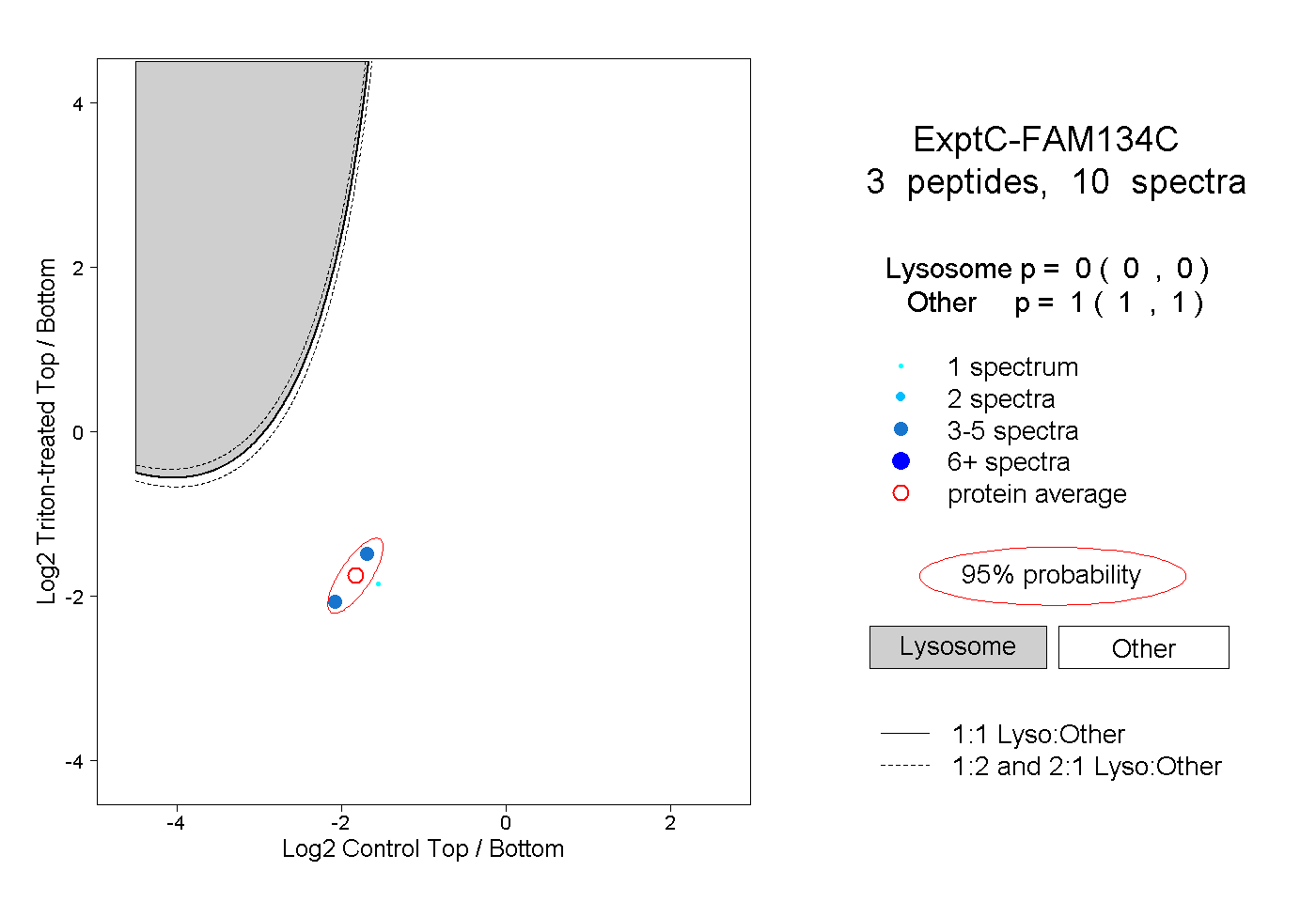 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
2 spectra |
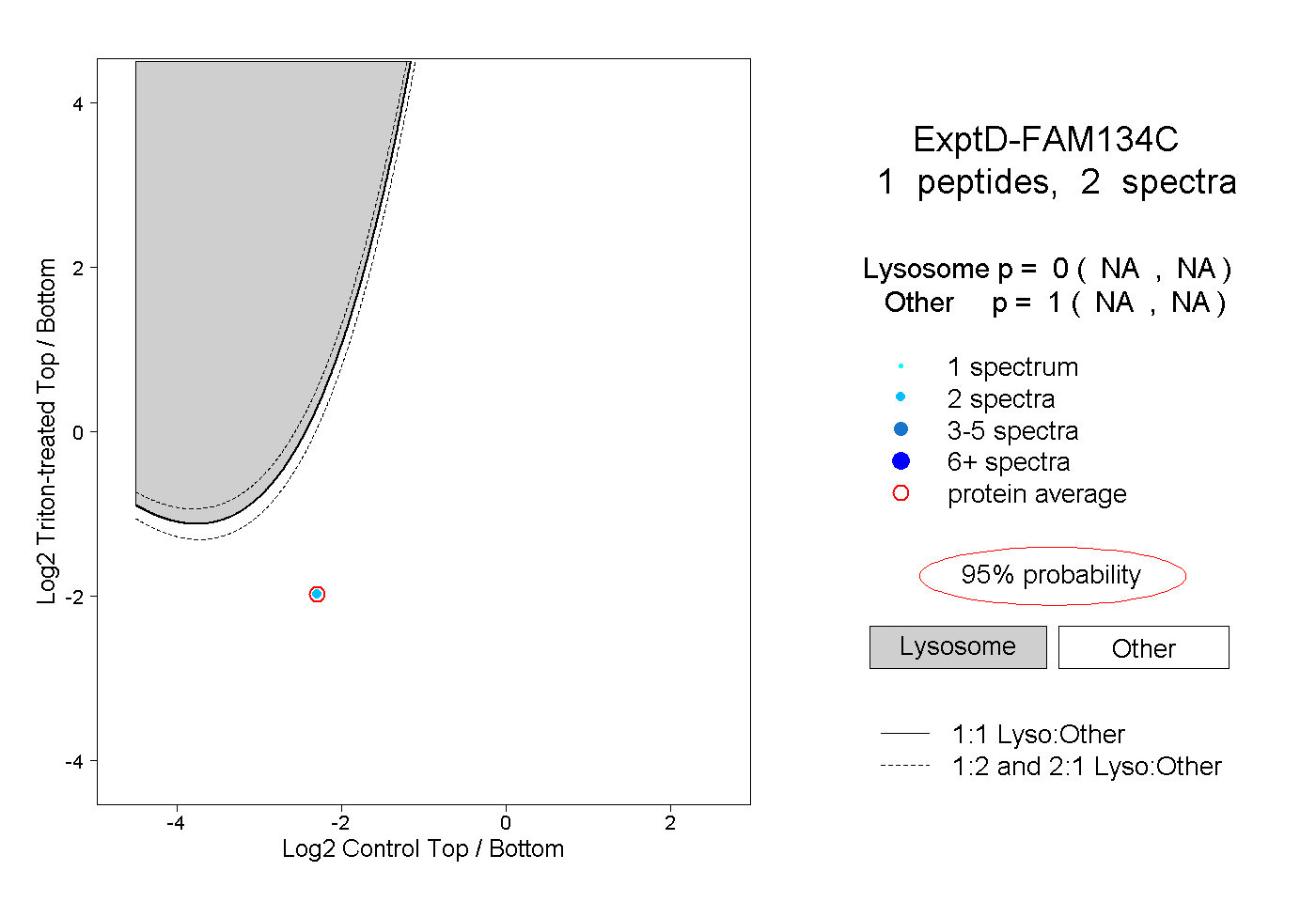 |
0.000 NA | NA |
1.000 NA | NA |