peptides
spectra
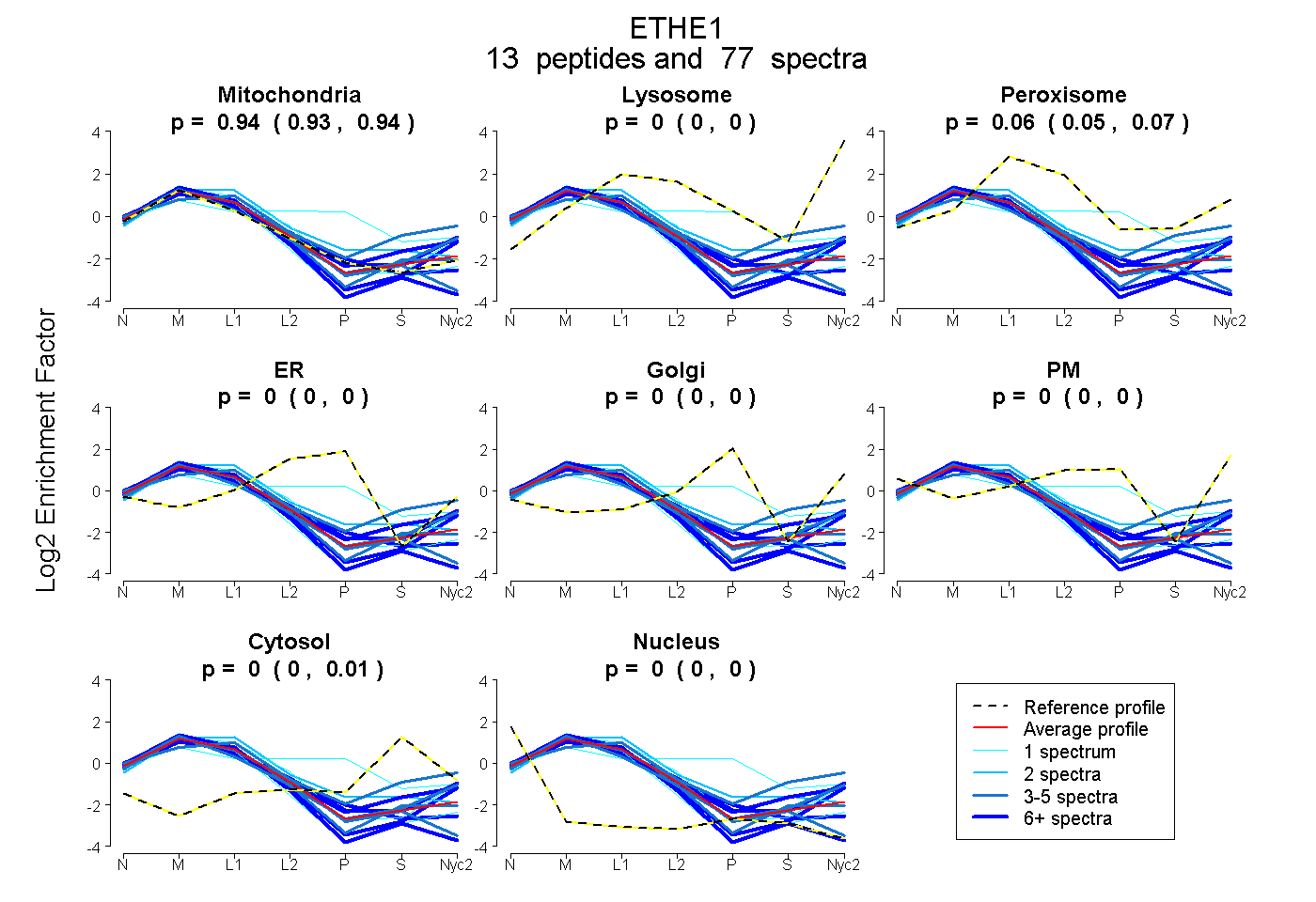
0.926 | 0.942
0.000 | 0.000
0.053 | 0.067
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.008
0.000 | 0.000
peptides
spectra
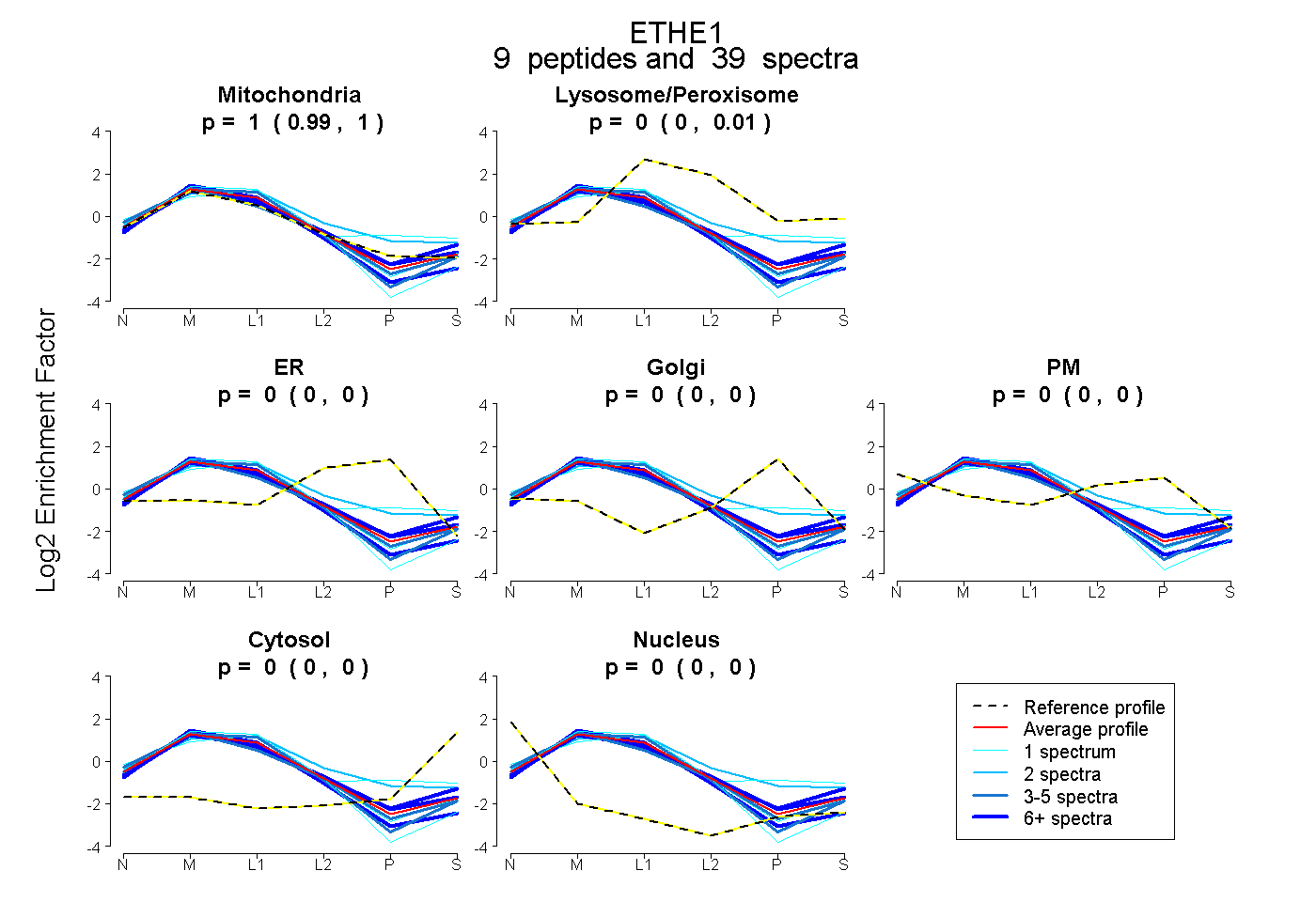
0.988 | 1.000
0.000 | 0.010
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
77 spectra |
 |
0.935 0.926 | 0.942 |
0.000 0.000 | 0.000 |
0.061 0.053 | 0.067 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.004 0.000 | 0.008 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
39 spectra |
 |
0.997 0.988 | 1.000 |
0.003 0.000 | 0.010 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, DAQLIK | 0.721 | 0.266 | 0.000 | 0.011 | 0.002 | 0.000 | 0.000 | |||
| 1 spectrum, TDFQQGCAK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, EAILIDPVLETAHR | 0.906 | 0.045 | 0.000 | 0.000 | 0.000 | 0.049 | 0.000 | |||
| 8 spectra, LSGAQADLHIGEGDSIPFGR | 0.988 | 0.008 | 0.000 | 0.000 | 0.000 | 0.004 | 0.000 | |||
| 1 spectrum, LLYAVNTHCHADHITGSGVLR | 0.680 | 0.243 | 0.000 | 0.038 | 0.000 | 0.026 | 0.012 | |||
| 1 spectrum, SCTYTYLLGDR | 0.982 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.018 | |||
| 3 spectra, LTLSCEEFIK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, FALETR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, SLLPGCQSVISR | 0.993 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.007 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
219 spectra |
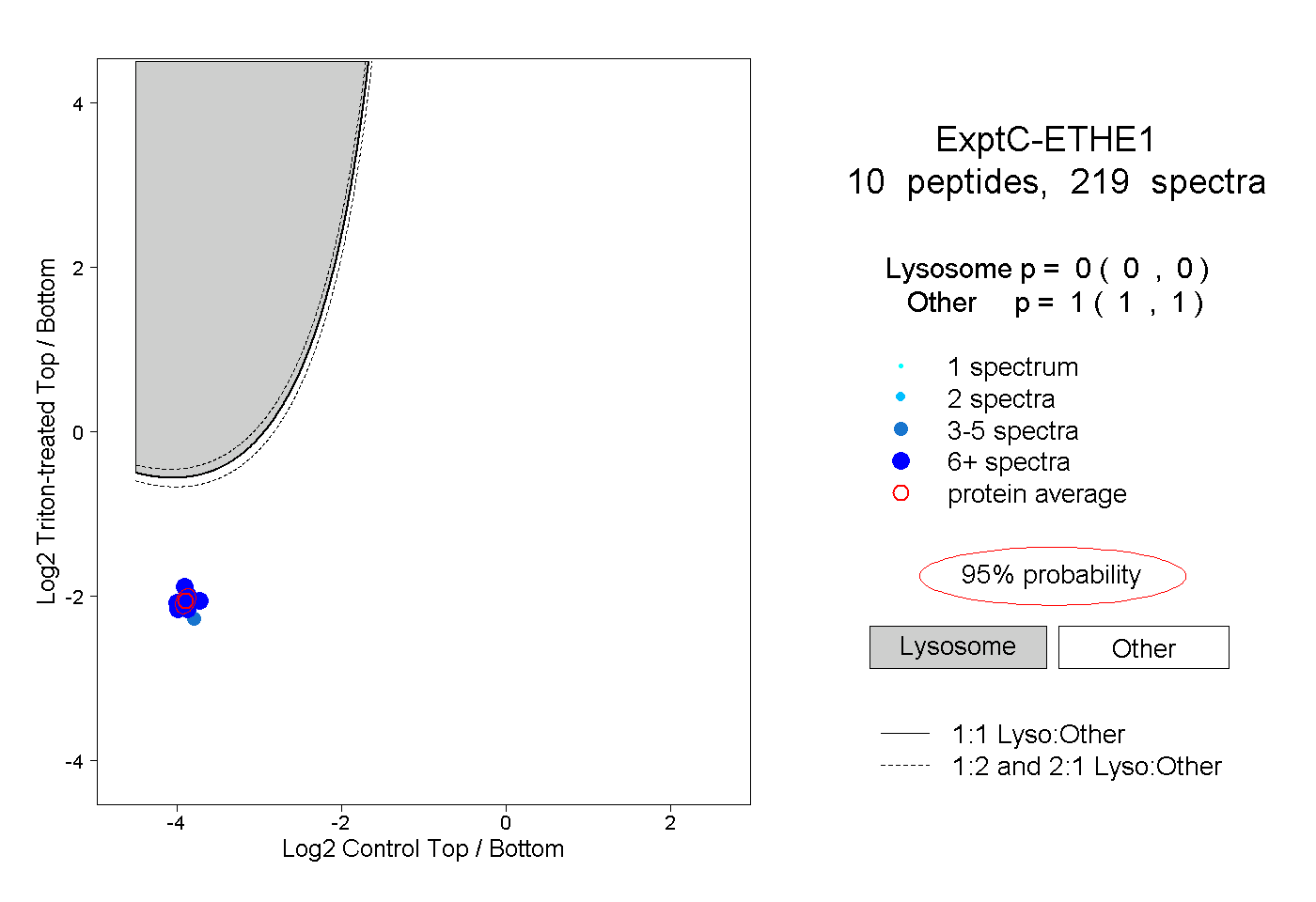 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
36 spectra |
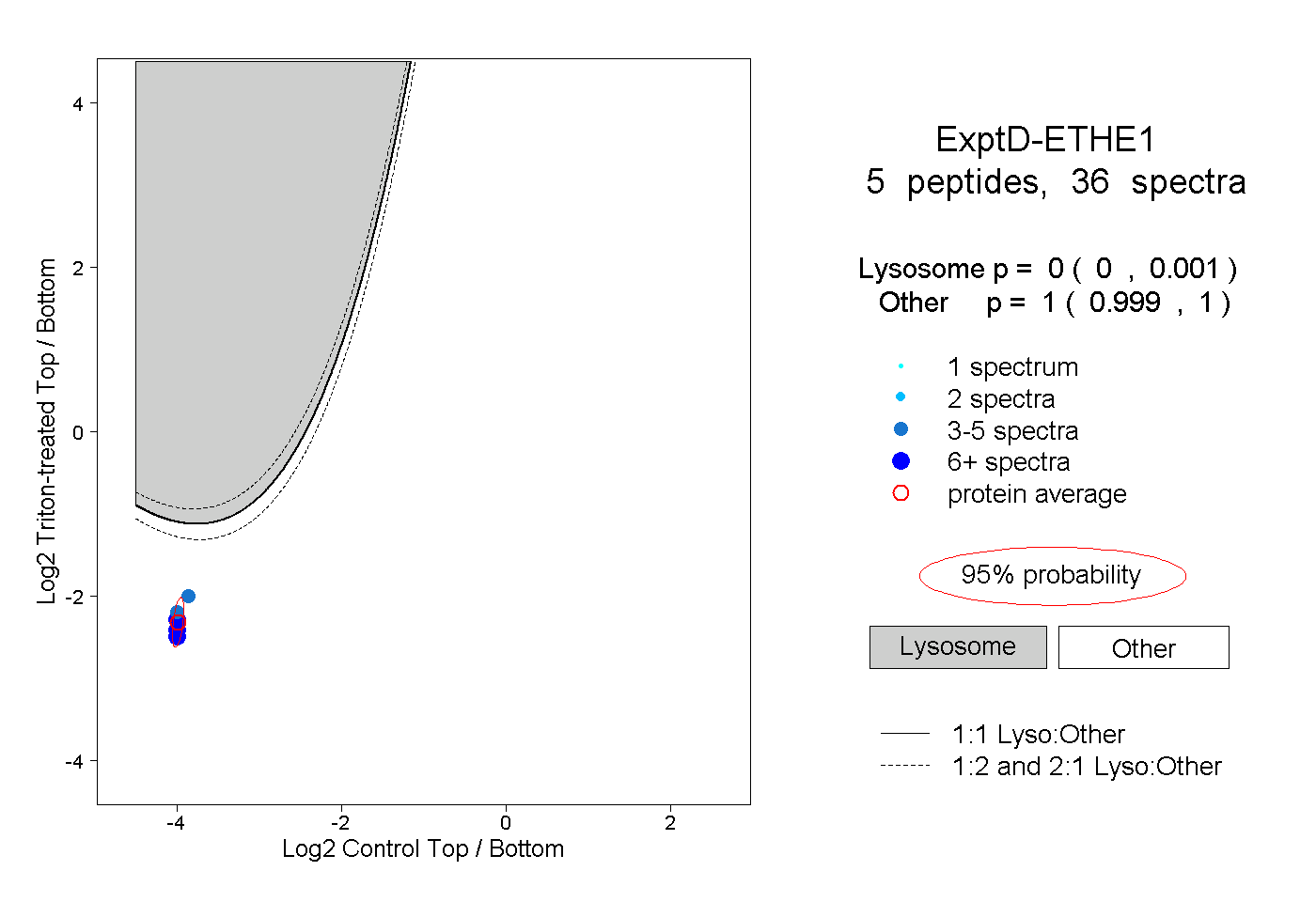 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |