peptides
spectra
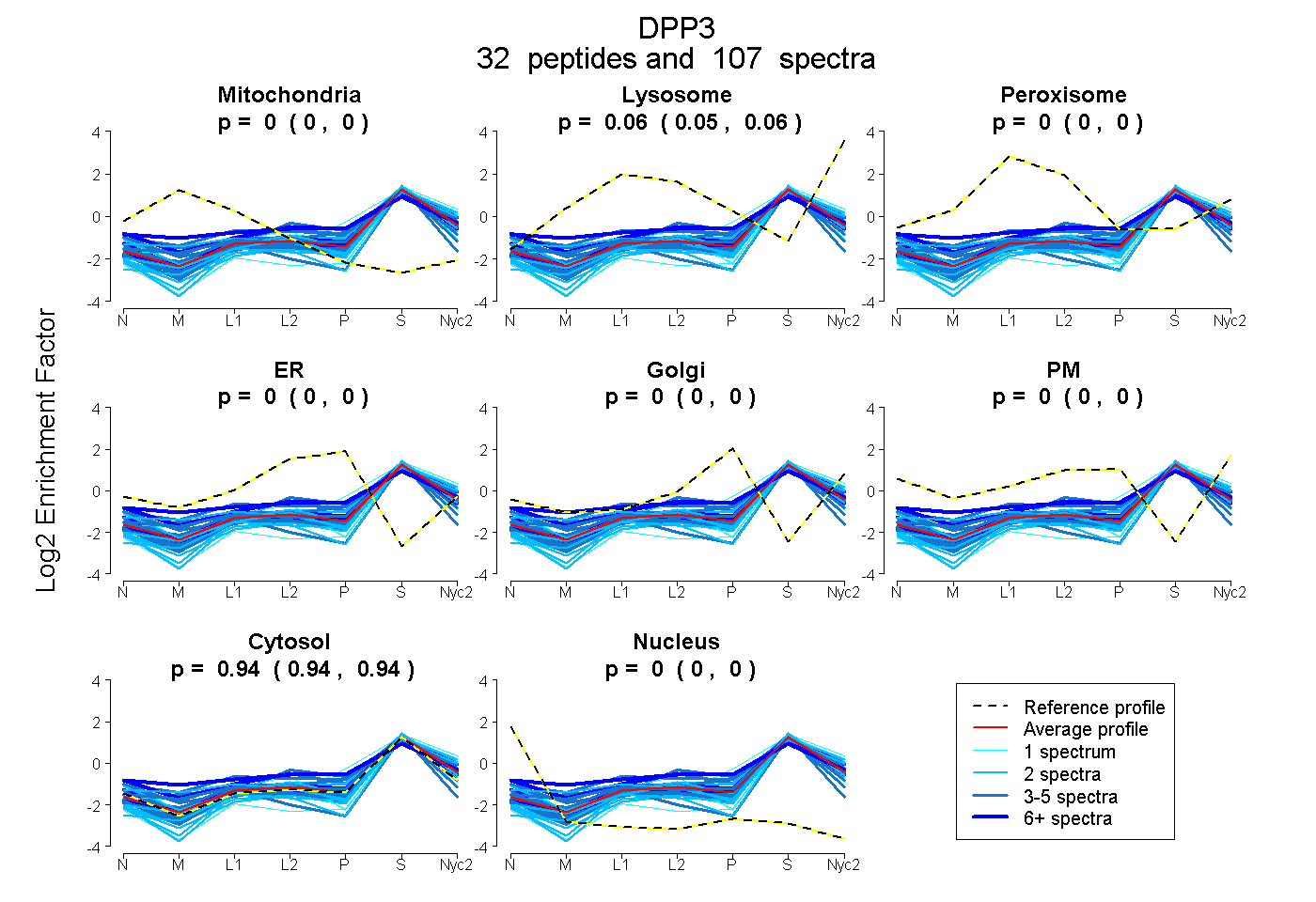
0.000 | 0.000
0.055 | 0.058
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.941 | 0.945
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
107 spectra |
 |
0.000 0.000 | 0.000 |
0.057 0.055 | 0.058 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.943 0.941 | 0.945 |
0.000 0.000 | 0.000 |
| 1 spectrum, NVSLGNVLAVAYATK | 0.000 | 0.131 | 0.000 | 0.000 | 0.000 | 0.000 | 0.869 | 0.000 | ||
| 3 spectra, LYAHHLSR | 0.000 | 0.108 | 0.100 | 0.000 | 0.000 | 0.048 | 0.744 | 0.000 | ||
| 5 spectra, VVGQEGK | 0.013 | 0.112 | 0.000 | 0.000 | 0.000 | 0.000 | 0.874 | 0.000 | ||
| 5 spectra, LVASAEQLLK | 0.000 | 0.066 | 0.000 | 0.000 | 0.000 | 0.000 | 0.934 | 0.000 | ||
| 1 spectrum, FWIQDK | 0.000 | 0.005 | 0.000 | 0.000 | 0.000 | 0.000 | 0.995 | 0.000 | ||
| 2 spectra, LFVQDEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 6 spectra, GEFEGFVAMVNK | 0.000 | 0.110 | 0.000 | 0.000 | 0.000 | 0.000 | 0.890 | 0.000 | ||
| 9 spectra, YHYEVR | 0.023 | 0.001 | 0.183 | 0.000 | 0.083 | 0.042 | 0.667 | 0.000 | ||
| 2 spectra, VILGSK | 0.068 | 0.124 | 0.000 | 0.000 | 0.000 | 0.000 | 0.808 | 0.000 | ||
| 3 spectra, QAHMQAR | 0.000 | 0.047 | 0.038 | 0.000 | 0.000 | 0.000 | 0.915 | 0.000 | ||
| 1 spectrum, LASVLNTEPALDSELTSK | 0.000 | 0.106 | 0.000 | 0.000 | 0.000 | 0.000 | 0.894 | 0.000 | ||
| 3 spectra, SVGKPALER | 0.000 | 0.027 | 0.000 | 0.000 | 0.000 | 0.000 | 0.973 | 0.000 | ||
| 4 spectra, STGDVVAGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 3 spectra, QTEGFK | 0.000 | 0.000 | 0.000 | 0.064 | 0.000 | 0.000 | 0.936 | 0.000 | ||
| 3 spectra, GPIVESYIGFIESYR | 0.130 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.870 | 0.000 | ||
| 6 spectra, SYEFQGNHFQVTR | 0.000 | 0.000 | 0.080 | 0.014 | 0.001 | 0.151 | 0.754 | 0.000 | ||
| 2 spectra, LEGSEVQLVEYEASAAGLIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, AGLLALEFYTPETANWR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.971 | 0.029 | ||
| 4 spectra, LIVQPNTR | 0.000 | 0.029 | 0.000 | 0.000 | 0.000 | 0.000 | 0.971 | 0.000 | ||
| 2 spectra, SFGDTK | 0.000 | 0.116 | 0.000 | 0.000 | 0.000 | 0.000 | 0.884 | 0.000 | ||
| 2 spectra, FVPNLPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 7 spectra, SGETWDSK | 0.000 | 0.018 | 0.000 | 0.000 | 0.000 | 0.000 | 0.982 | 0.000 | ||
| 4 spectra, HLGLGK | 0.000 | 0.050 | 0.000 | 0.000 | 0.000 | 0.000 | 0.950 | 0.000 | ||
| 5 spectra, AAQQHPEEVR | 0.000 | 0.152 | 0.027 | 0.000 | 0.000 | 0.010 | 0.811 | 0.000 | ||
| 2 spectra, ELPWPPAFEK | 0.000 | 0.028 | 0.000 | 0.000 | 0.000 | 0.000 | 0.972 | 0.000 | ||
| 5 spectra, EGVTTYFSGDCAMEDAK | 0.000 | 0.042 | 0.000 | 0.062 | 0.000 | 0.092 | 0.803 | 0.000 | ||
| 2 spectra, VVEHLEK | 0.000 | 0.011 | 0.000 | 0.000 | 0.000 | 0.000 | 0.989 | 0.000 | ||
| 2 spectra, GDYAPILQK | 0.000 | 0.017 | 0.000 | 0.000 | 0.000 | 0.000 | 0.983 | 0.000 | ||
| 2 spectra, VLLEAGEGLVTVTPTTGSDGRPDAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, DQVQEAPSGQA | 0.000 | 0.000 | 0.000 | 0.000 | 0.026 | 0.000 | 0.974 | 0.000 | ||
| 4 spectra, AQDPDQLR | 0.000 | 0.026 | 0.000 | 0.000 | 0.000 | 0.000 | 0.974 | 0.000 | ||
| 5 spectra, FSTIASSYEECR | 0.037 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.951 | 0.013 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
39 spectra |
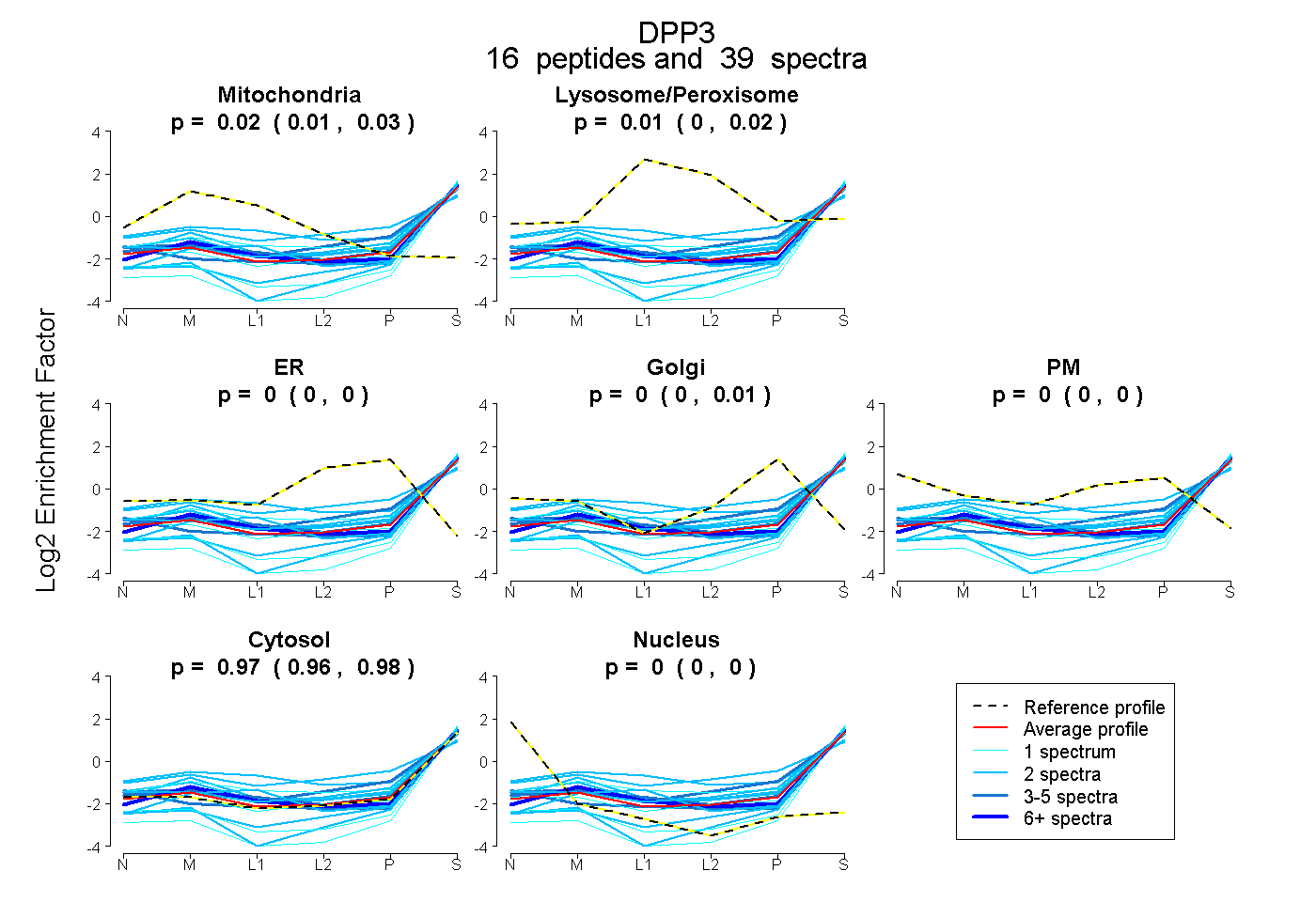 |
0.018 0.006 | 0.026 |
0.011 0.000 | 0.020 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.005 |
0.000 0.000 | 0.000 |
0.971 0.962 | 0.978 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
168 spectra |
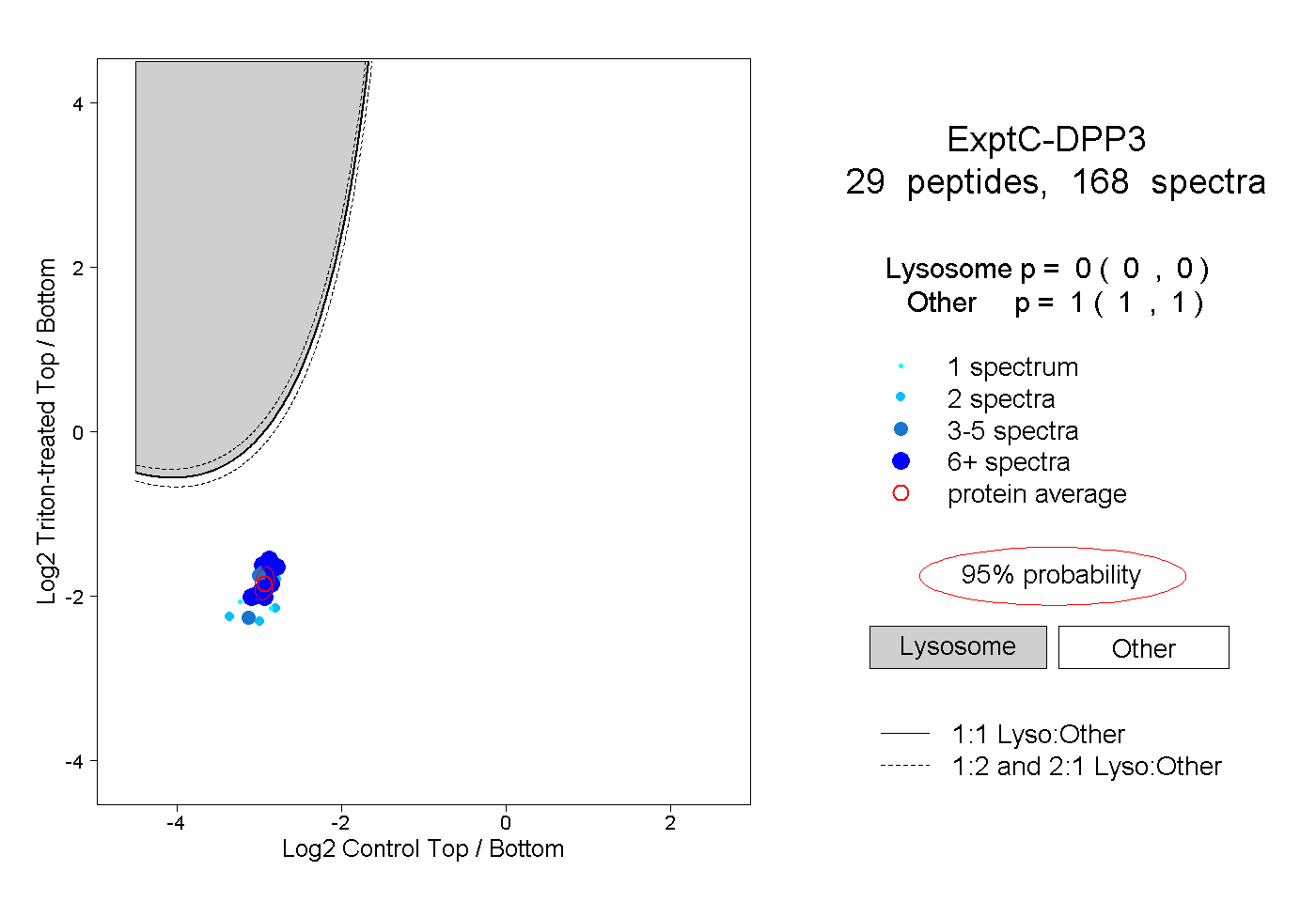 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
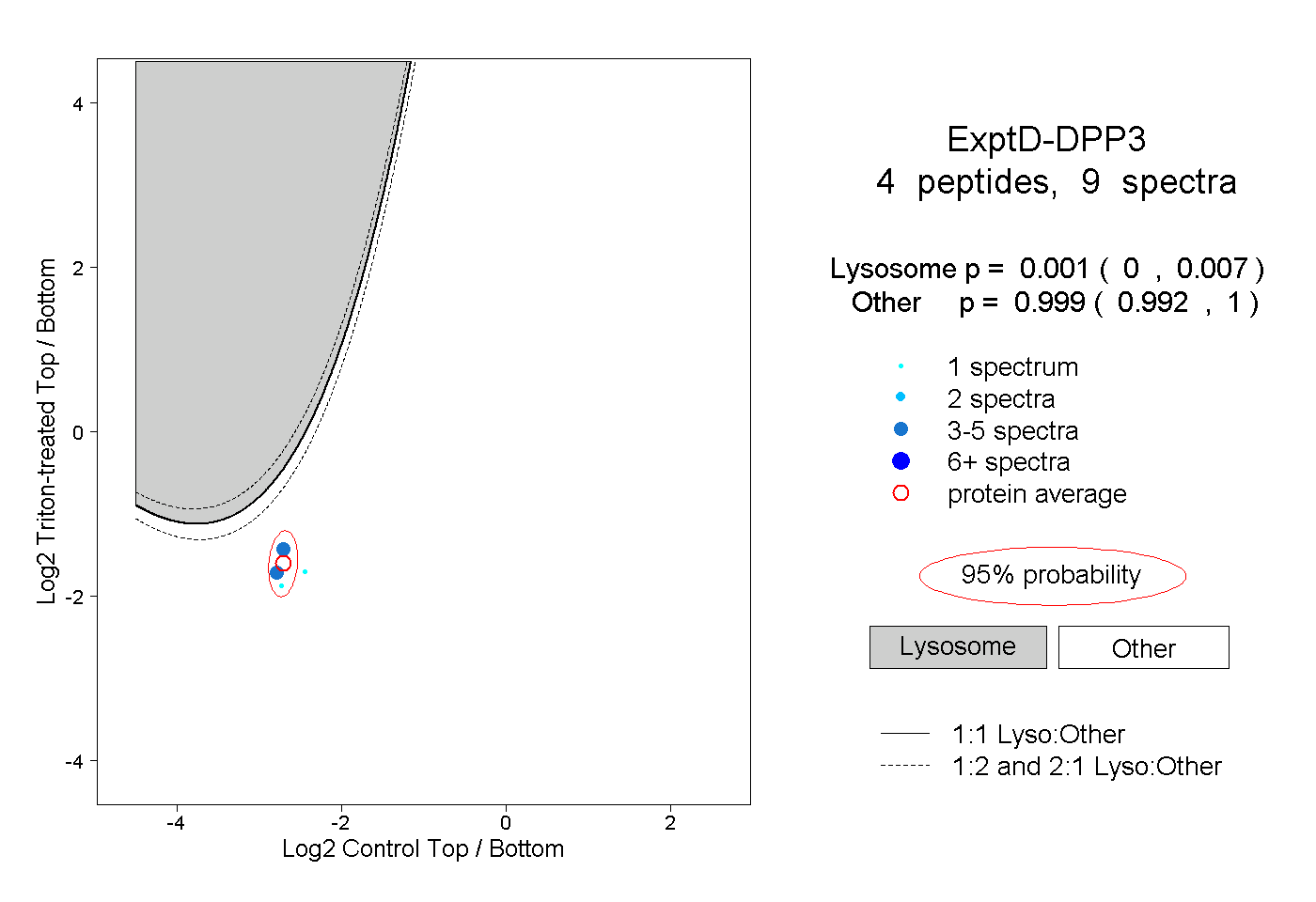 |
0.001 0.000 | 0.007 |
0.999 0.992 | 1.000 |