peptides
spectra
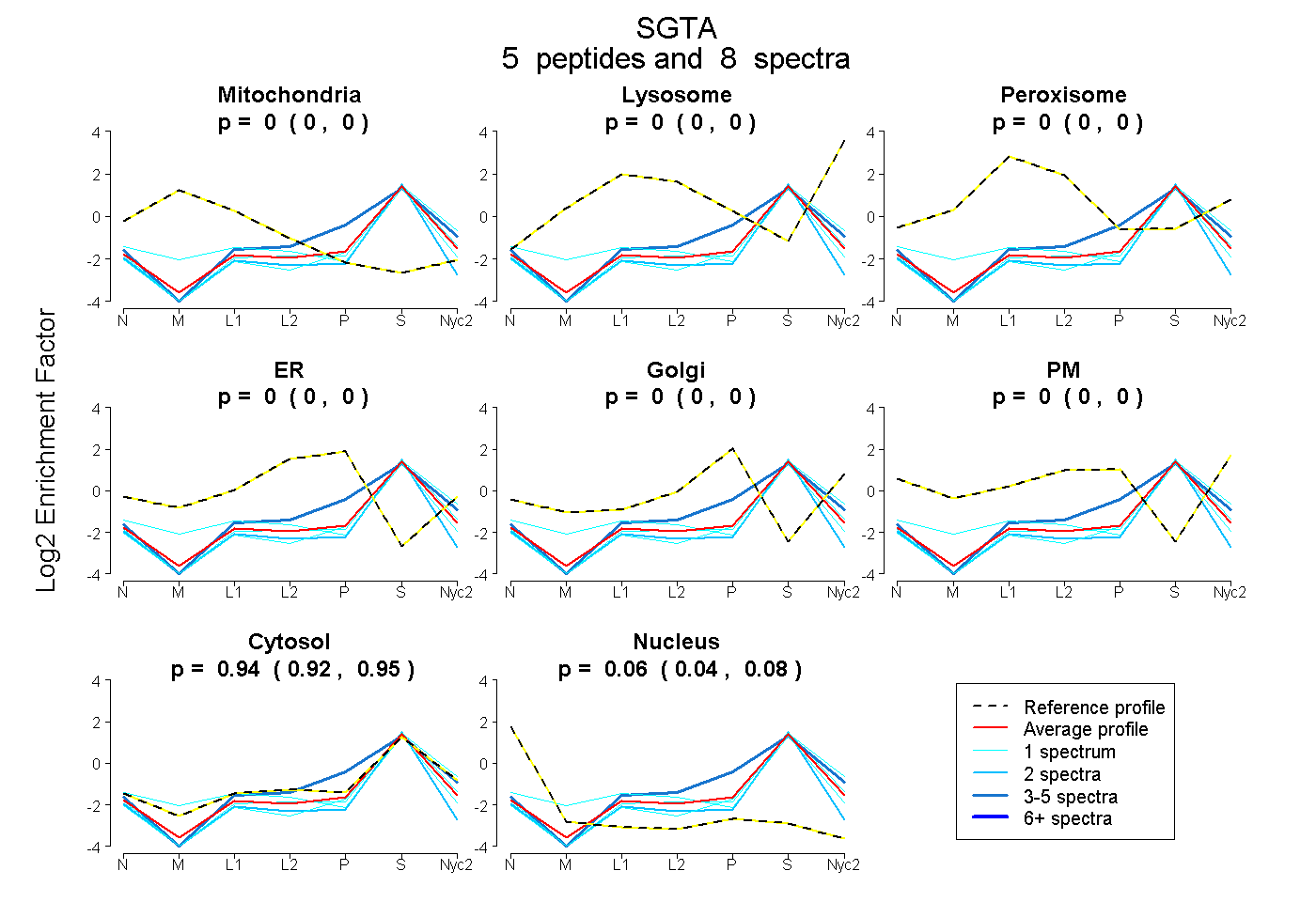
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.915 | 0.953
0.044 | 0.081
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
8 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.937 0.915 | 0.953 |
0.063 0.044 | 0.081 |
| 3 spectra, EMPQDPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.010 | 0.000 | 0.990 | 0.000 | ||
| 1 spectrum, LGNYVGAVQDCER | 0.052 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.871 | 0.077 | ||
| 2 spectra, AIELNPANAVYFCNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.833 | 0.167 | ||
| 1 spectrum, ALELDPDNDTYK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.966 | 0.034 | ||
| 1 spectrum, LENFEAAVHLYGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.961 | 0.039 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
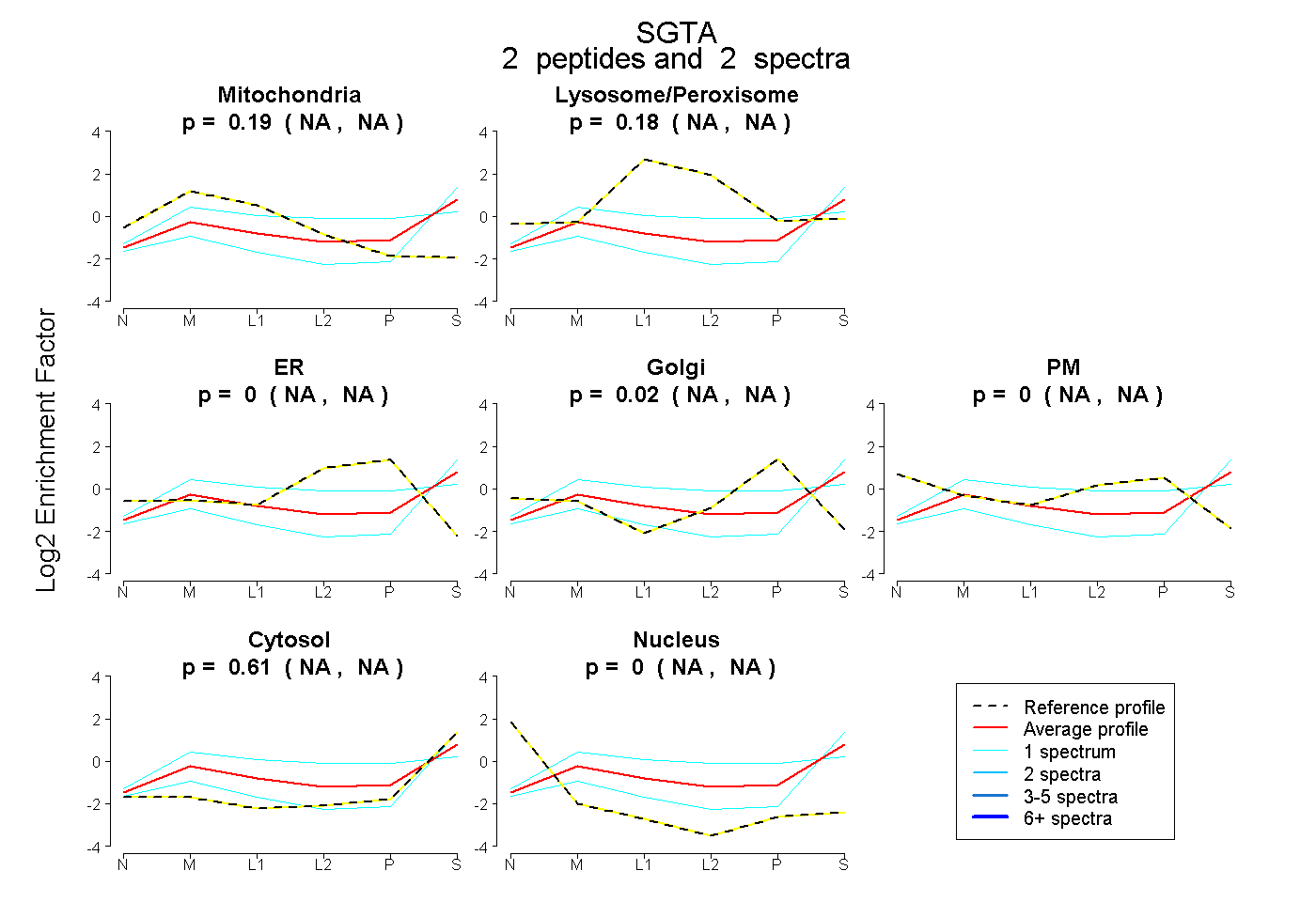 |
0.191 NA | NA |
0.180 NA | NA |
0.000 NA | NA |
0.021 NA | NA |
0.000 NA | NA |
0.609 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
7 spectra |
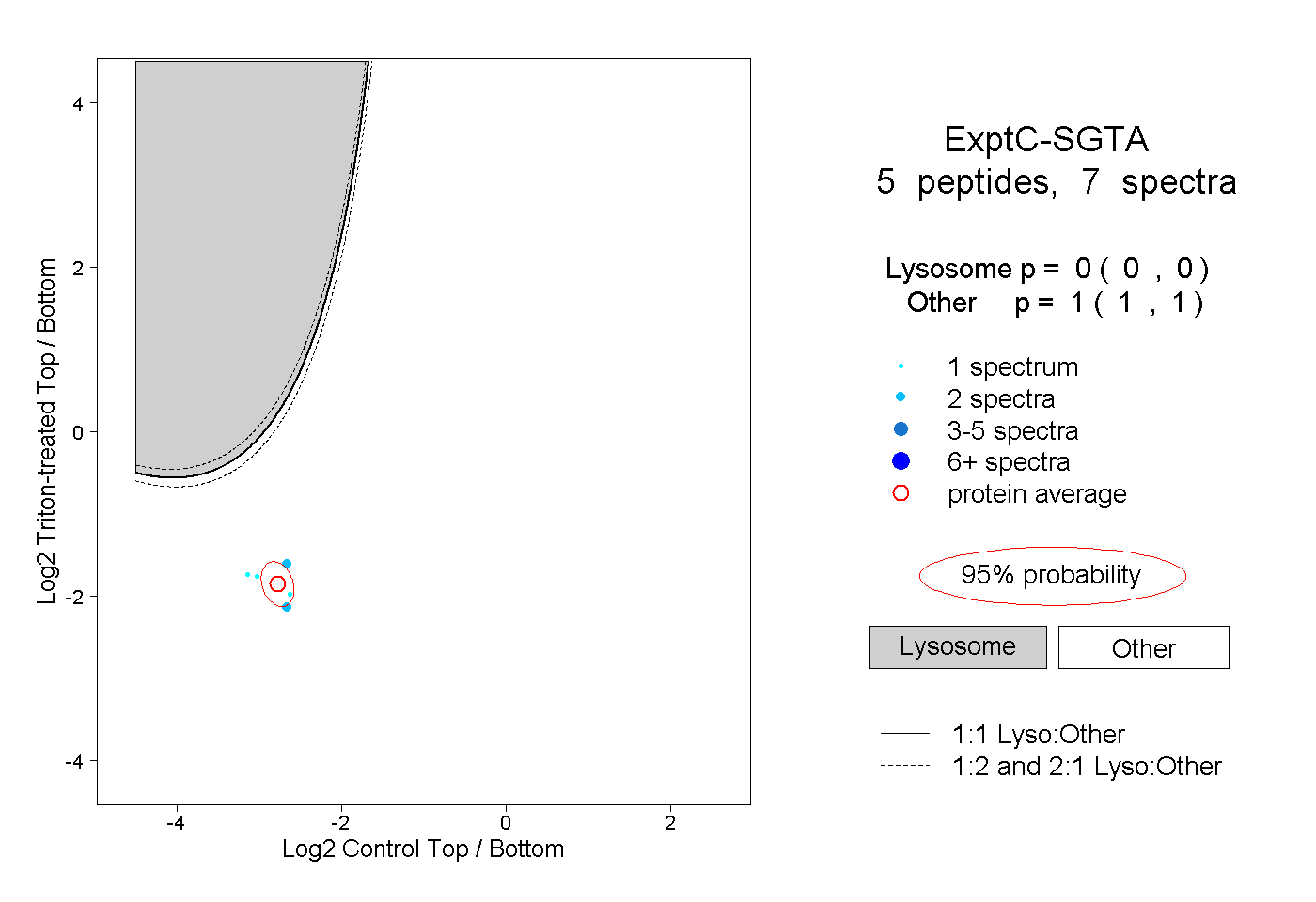 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |