peptides
spectra
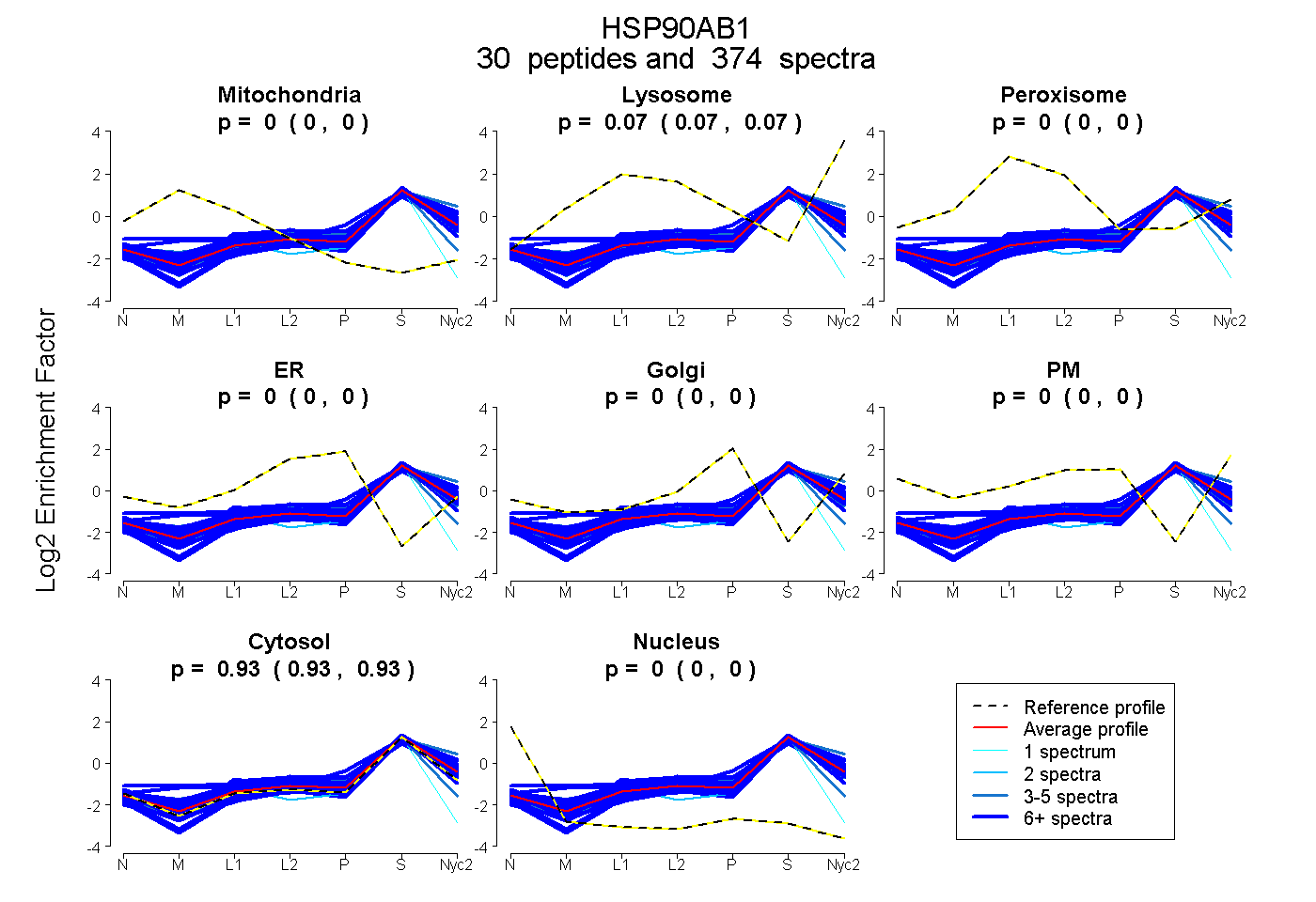
0.000 | 0.000
0.065 | 0.067
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.933 | 0.935
0.000 | 0.000
peptides
spectra
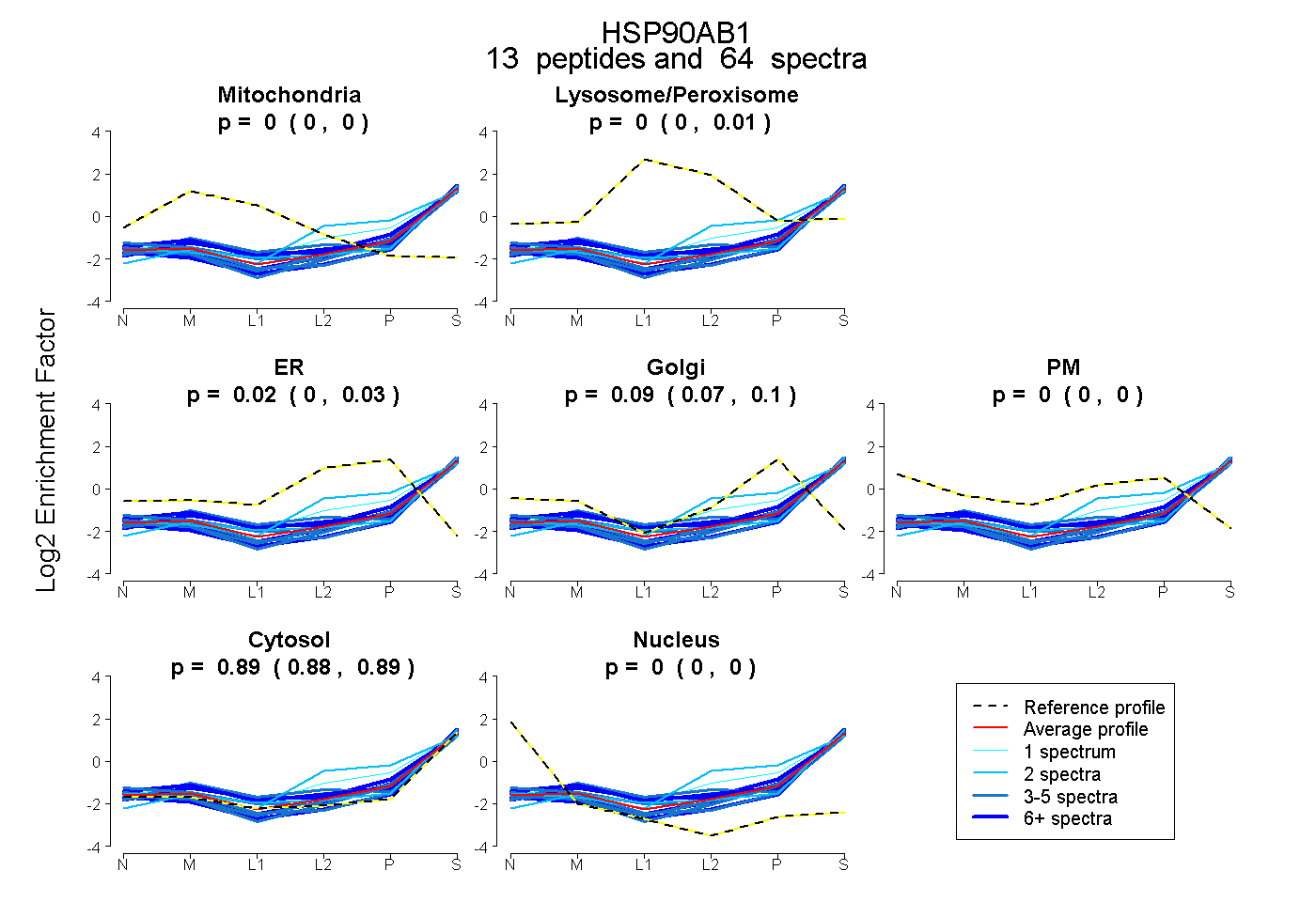
0.000 | 0.000
0.000 | 0.012
0.000 | 0.032
0.071 | 0.104
0.000 | 0.000
0.884 | 0.895
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
374 spectra |
 |
0.000 0.000 | 0.000 |
0.066 0.065 | 0.067 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.934 0.933 | 0.935 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
64 spectra |
 |
0.000 0.000 | 0.000 |
0.004 0.000 | 0.012 |
0.017 0.000 | 0.032 |
0.088 0.071 | 0.104 |
0.000 0.000 | 0.000 |
0.890 0.884 | 0.895 |
0.000 0.000 | 0.000 |
| 3 spectra, HSQFIGYPITLYLEK | 0.030 | 0.113 | 0.025 | 0.000 | 0.000 | 0.832 | 0.000 | |||
| 3 spectra, FYEAFSK | 0.000 | 0.000 | 0.000 | 0.102 | 0.000 | 0.898 | 0.000 | |||
| 3 spectra, SIYYITGESK | 0.000 | 0.000 | 0.000 | 0.113 | 0.000 | 0.887 | 0.000 | |||
| 1 spectrum, APFDLFENK | 0.000 | 0.028 | 0.191 | 0.000 | 0.000 | 0.782 | 0.000 | |||
| 2 spectra, VVVITK | 0.000 | 0.000 | 0.292 | 0.000 | 0.000 | 0.708 | 0.000 | |||
| 3 spectra, IDIIPNPQER | 0.000 | 0.000 | 0.000 | 0.023 | 0.000 | 0.977 | 0.000 | |||
| 8 spectra, ALLFIPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.999 | 0.001 | |||
| 19 spectra, EQVANSAFVER | 0.000 | 0.000 | 0.000 | 0.105 | 0.000 | 0.895 | 0.000 | |||
| 8 spectra, HLEINPDHPIVETLR | 0.000 | 0.082 | 0.000 | 0.108 | 0.000 | 0.810 | 0.000 | |||
| 2 spectra, SLTNDWEDHLAVK | 0.000 | 0.040 | 0.000 | 0.000 | 0.000 | 0.960 | 0.000 | |||
| 3 spectra, NPDDITQEEYGEFYK | 0.000 | 0.016 | 0.000 | 0.091 | 0.031 | 0.862 | 0.000 | |||
| 8 spectra, LGIHEDSTNR | 0.000 | 0.091 | 0.000 | 0.080 | 0.000 | 0.829 | 0.000 | |||
| 1 spectrum, GFEVVYMTEPIDEYCVQQLK | 0.000 | 0.097 | 0.000 | 0.056 | 0.000 | 0.846 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
563 spectra |
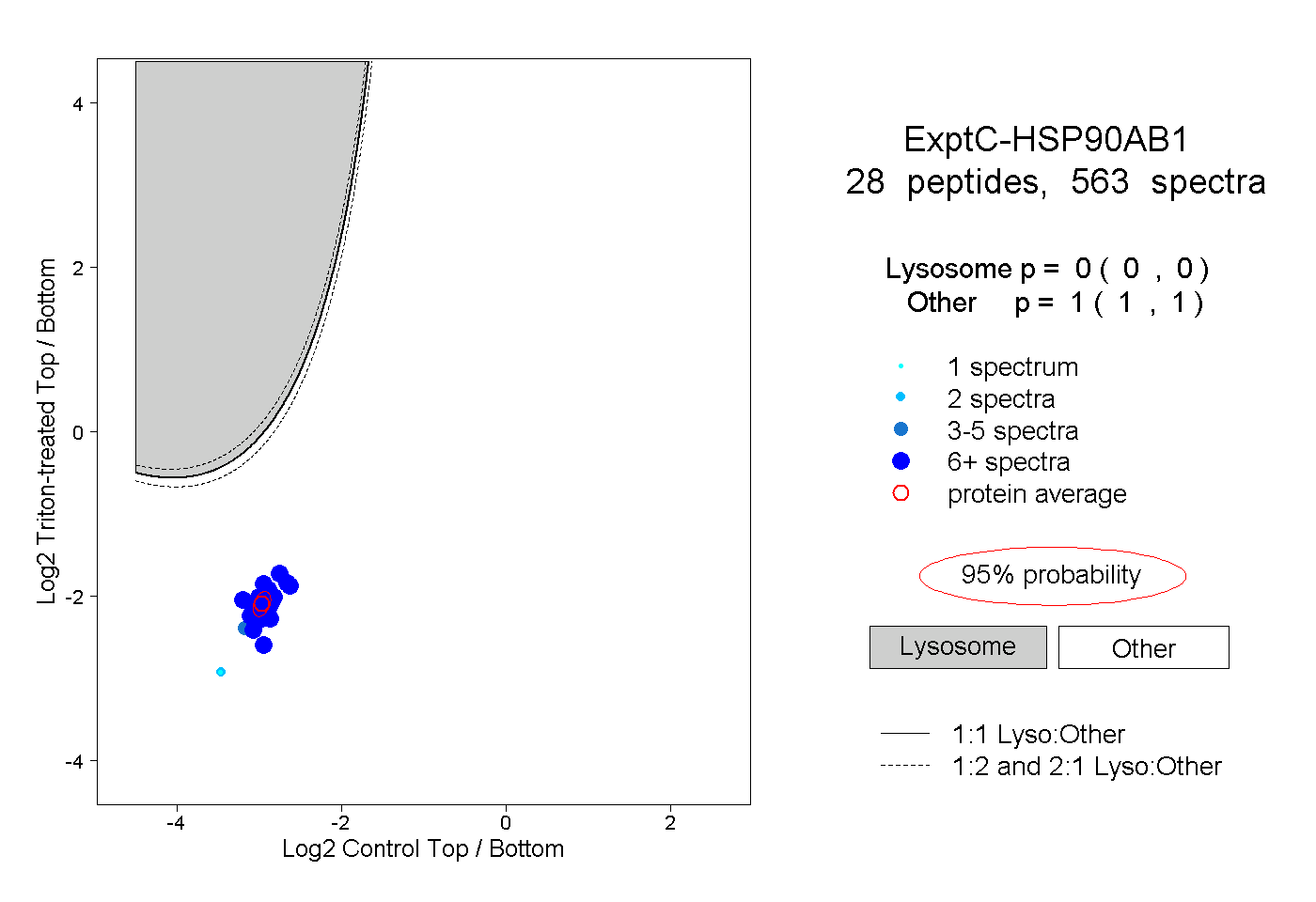 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
36 spectra |
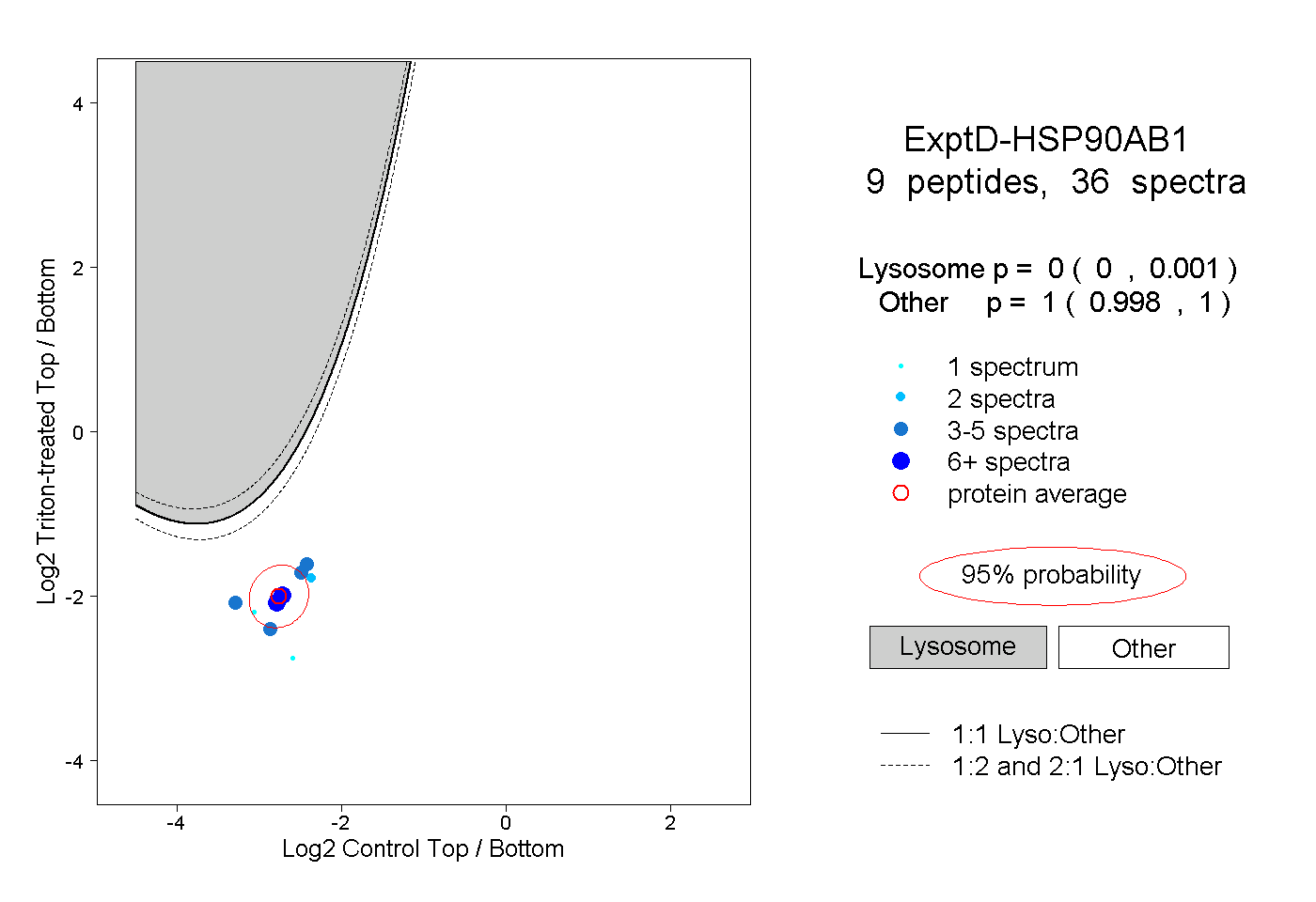 |
0.000 0.000 | 0.001 |
1.000 0.998 | 1.000 |