peptides
spectra
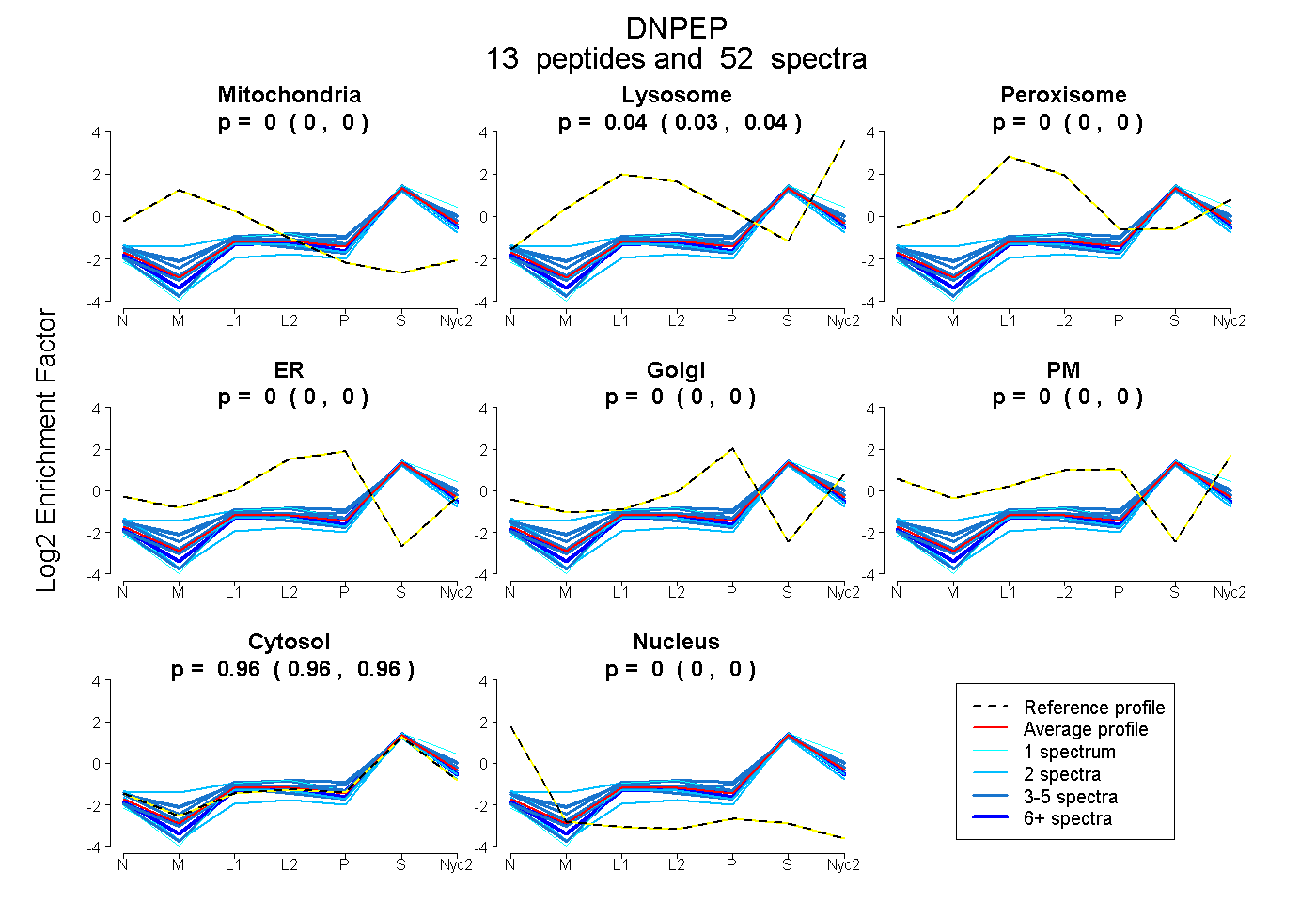
0.000 | 0.000
0.035 | 0.041
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.958 | 0.965
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
52 spectra |
 |
0.000 0.000 | 0.000 |
0.038 0.035 | 0.041 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.962 0.958 | 0.965 |
0.000 0.000 | 0.000 |
| 3 spectra, LLQAGFR | 0.000 | 0.153 | 0.000 | 0.000 | 0.000 | 0.000 | 0.847 | 0.000 | ||
| 7 spectra, FVHIERPILR | 0.000 | 0.015 | 0.000 | 0.000 | 0.000 | 0.000 | 0.985 | 0.000 | ||
| 4 spectra, ISASPQR | 0.000 | 0.041 | 0.000 | 0.000 | 0.000 | 0.000 | 0.959 | 0.000 | ||
| 4 spectra, EAIQATAR | 0.000 | 0.099 | 0.010 | 0.000 | 0.000 | 0.000 | 0.891 | 0.000 | ||
| 2 spectra, CPTSGR | 0.103 | 0.000 | 0.069 | 0.000 | 0.000 | 0.000 | 0.828 | 0.000 | ||
| 1 spectrum, NVNENFGPNTEMHLVPILATAVQEELEK | 0.000 | 0.071 | 0.000 | 0.000 | 0.000 | 0.000 | 0.929 | 0.000 | ||
| 1 spectrum, EVAGQVGVPLQDLMVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 3 spectra, VLDLGSPQLAMHSIR | 0.000 | 0.074 | 0.000 | 0.000 | 0.000 | 0.000 | 0.926 | 0.000 | ||
| 14 spectra, IPHLAIHLQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, ETEGWDILPENK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 4 spectra, YASNAVSESLIR | 0.000 | 0.119 | 0.000 | 0.000 | 0.000 | 0.000 | 0.881 | 0.000 | ||
| 5 spectra, GFFELFPSVSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, LTAFEEAIPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
30 spectra |
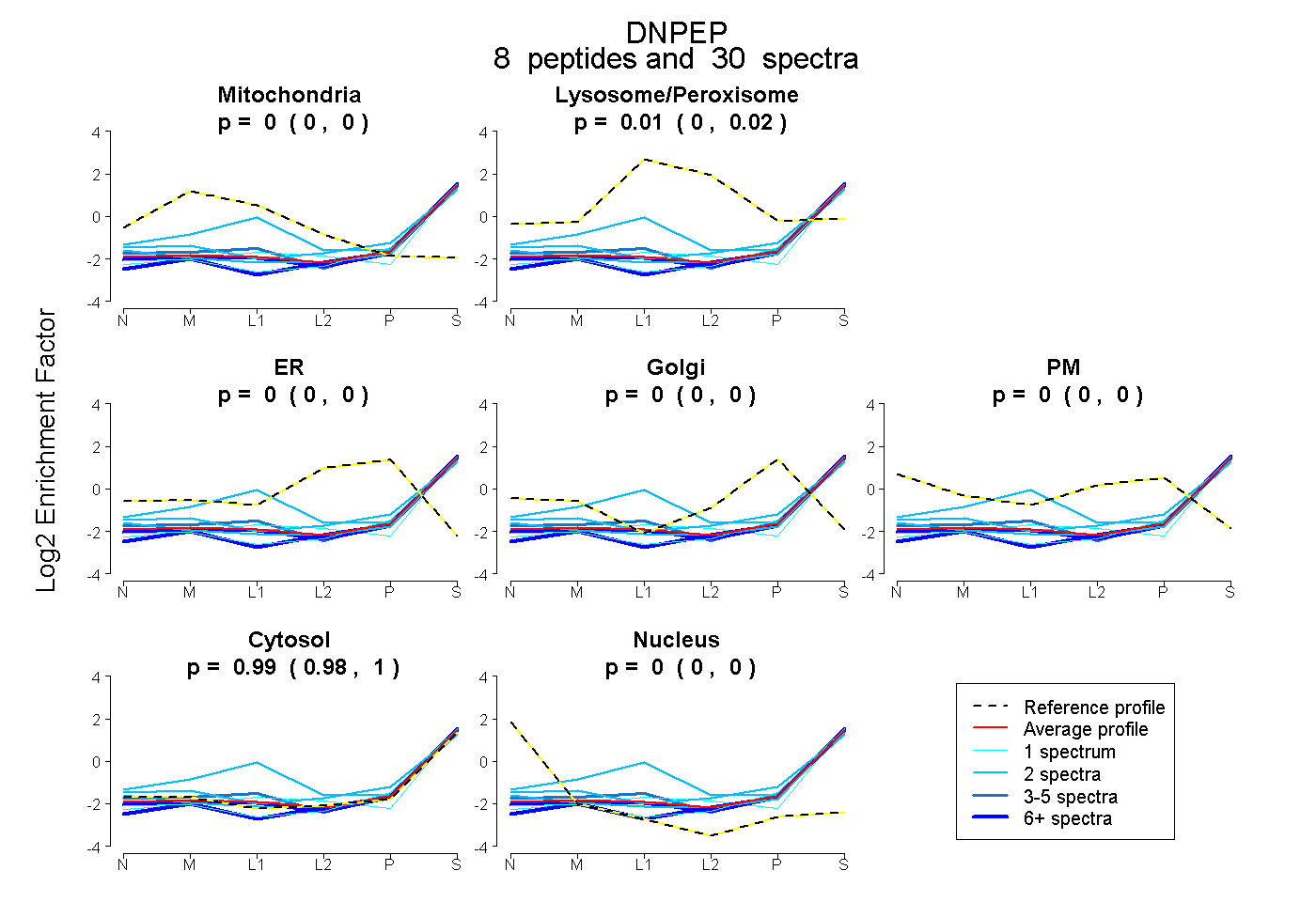 |
0.000 0.000 | 0.000 |
0.014 0.003 | 0.023 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.986 0.975 | 0.995 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
71 spectra |
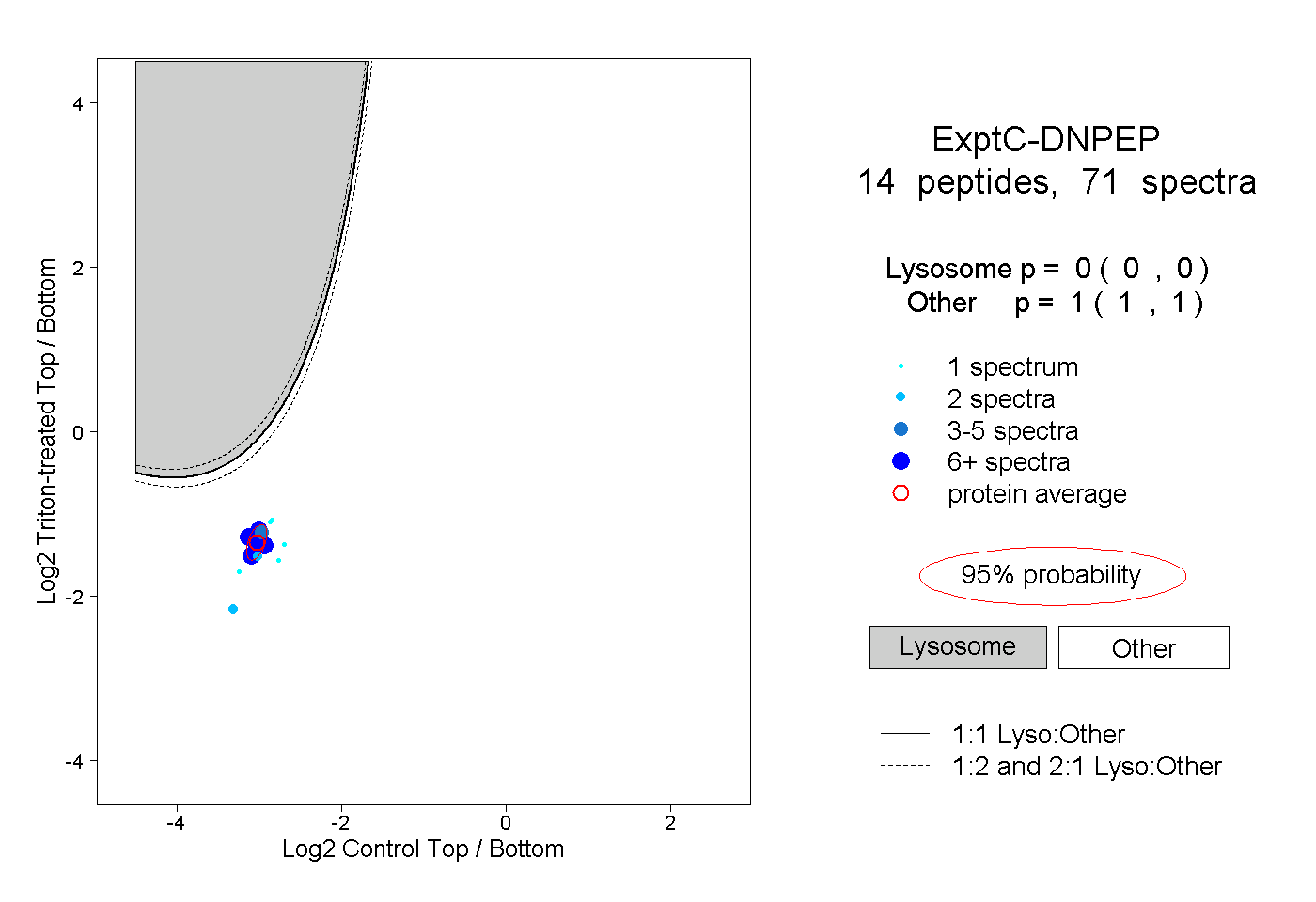 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
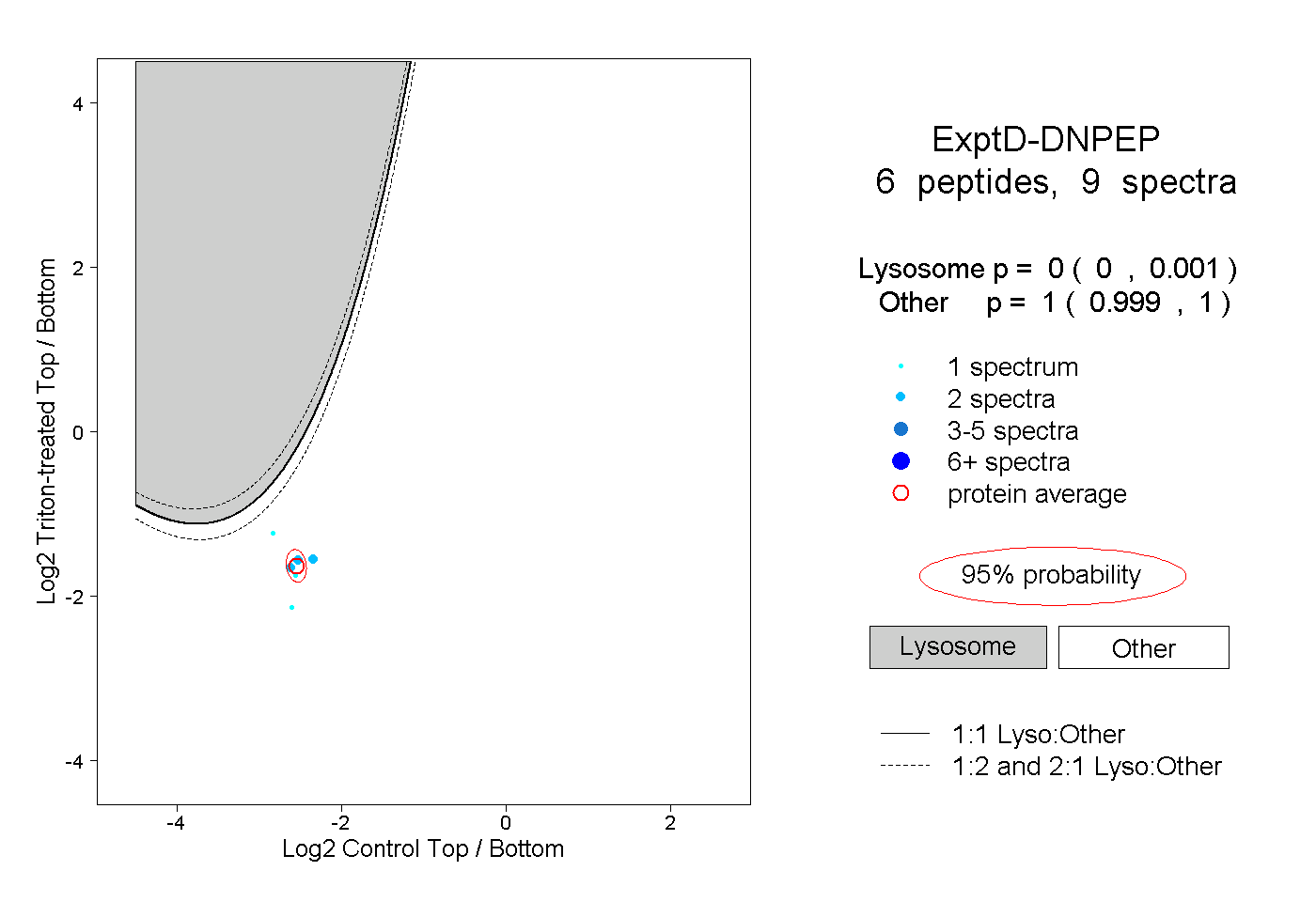 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |