peptides
spectra
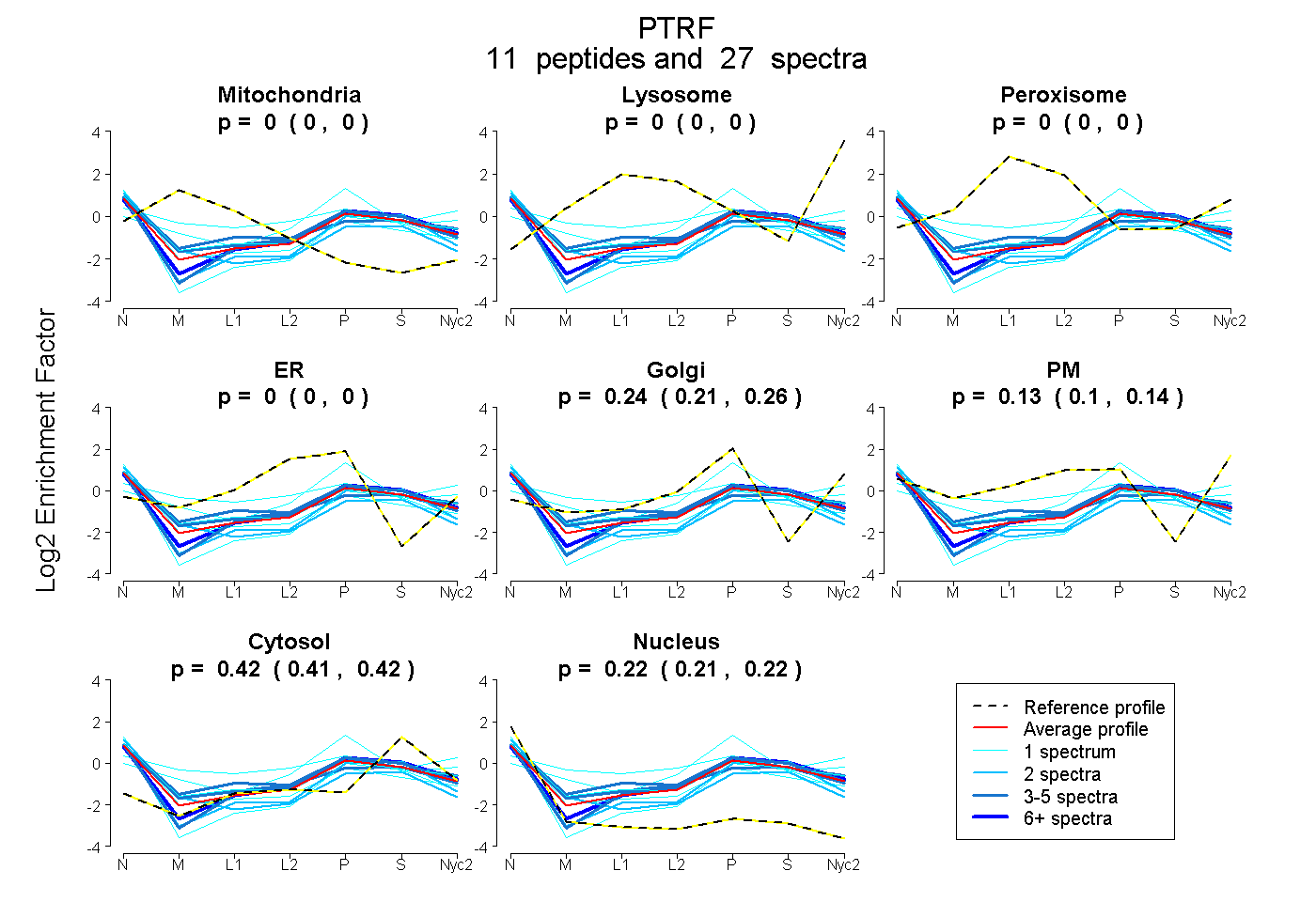
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.211 | 0.258
0.099 | 0.145
0.411 | 0.425
0.213 | 0.225
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
27 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.236 0.211 | 0.258 |
0.125 0.099 | 0.145 |
0.419 0.411 | 0.425 |
0.220 0.213 | 0.225 |
| 1 spectrum, ESEALPEK | 0.081 | 0.000 | 0.015 | 0.000 | 0.000 | 0.530 | 0.375 | 0.000 | ||
| 1 spectrum, ATEEPSGTGSDELIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.211 | 0.000 | 0.405 | 0.383 | ||
| 2 spectra, VMIYQDEVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.217 | 0.000 | 0.486 | 0.298 | ||
| 4 spectra, VPPFTFHVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.316 | 0.005 | 0.478 | 0.200 | ||
| 2 spectra, QAEMEGAVQSIQGELSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.204 | 0.045 | 0.354 | 0.397 | ||
| 4 spectra, QAGQIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.179 | 0.240 | 0.398 | 0.183 | ||
| 7 spectra, EGEVEVLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.307 | 0.030 | 0.477 | 0.186 | ||
| 1 spectrum, QAGEIK | 0.016 | 0.000 | 0.000 | 0.000 | 0.639 | 0.000 | 0.339 | 0.006 | ||
| 1 spectrum, VSVNVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.111 | 0.283 | 0.394 | 0.211 | ||
| 3 spectra, SDQVNGVLVLSLLDK | 0.000 | 0.000 | 0.050 | 0.012 | 0.000 | 0.306 | 0.402 | 0.230 | ||
| 1 spectrum, IIGAVDQIQLTQAQLEER | 0.000 | 0.000 | 0.000 | 0.000 | 0.150 | 0.190 | 0.312 | 0.348 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
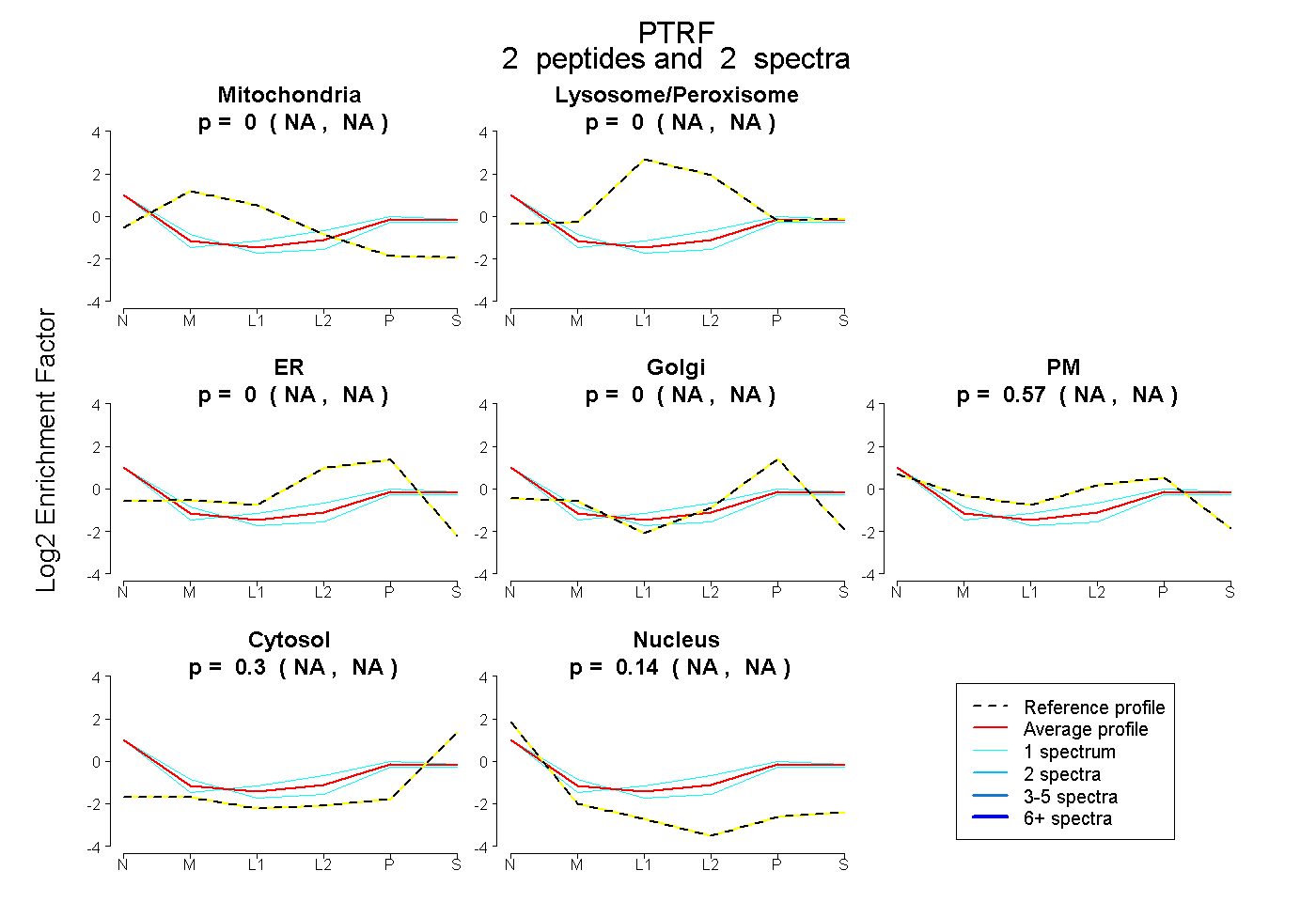 |
0.000 NA | NA |
0.002 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.567 NA | NA |
0.295 NA | NA |
0.137 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
24 spectra |
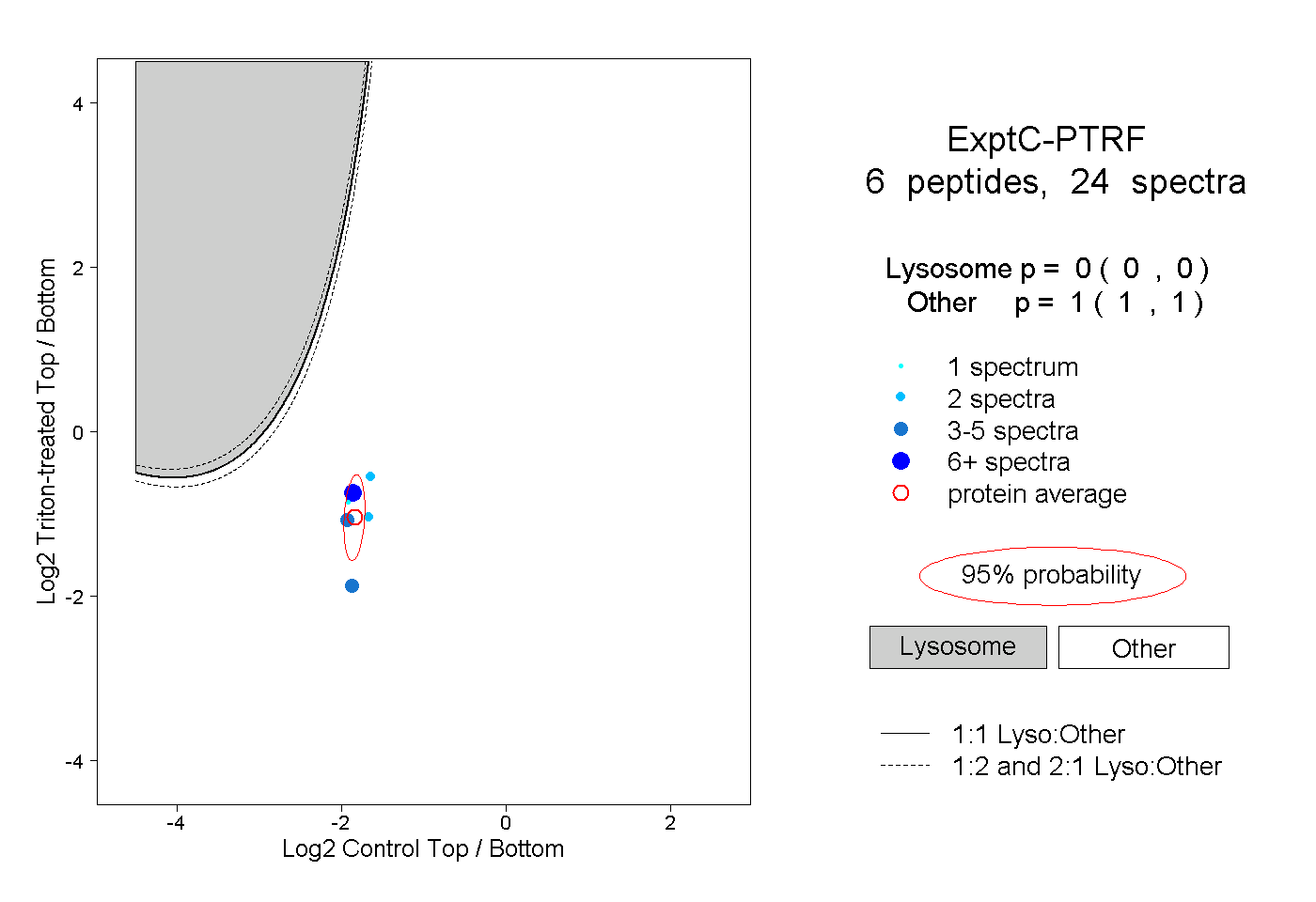 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
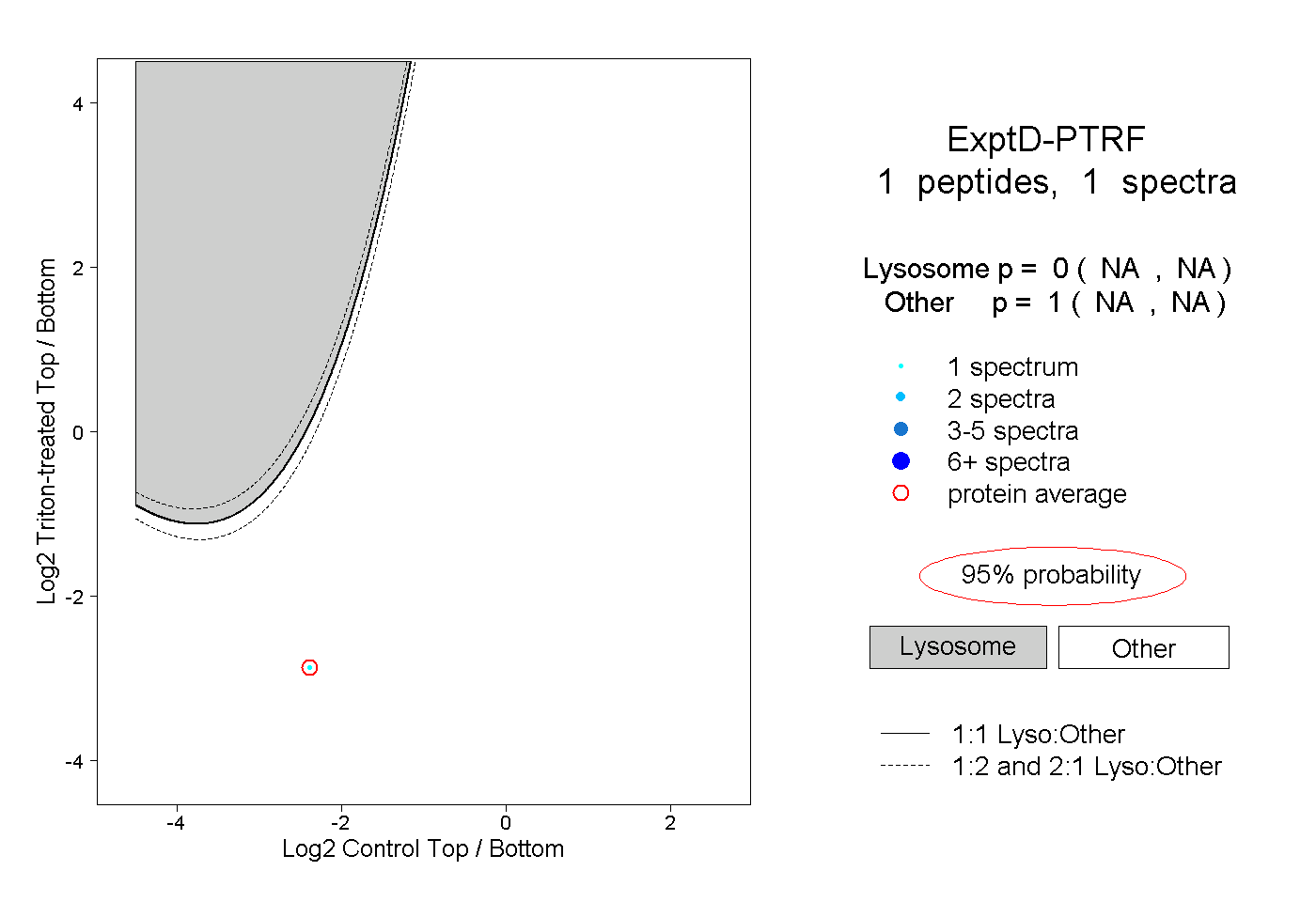 |
0.000 NA | NA |
1.000 NA | NA |