peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.043 | 0.063
0.000 | 0.050
0.000 | 0.000
0.462 | 0.532
0.414 | 0.427
0.000 | 0.000
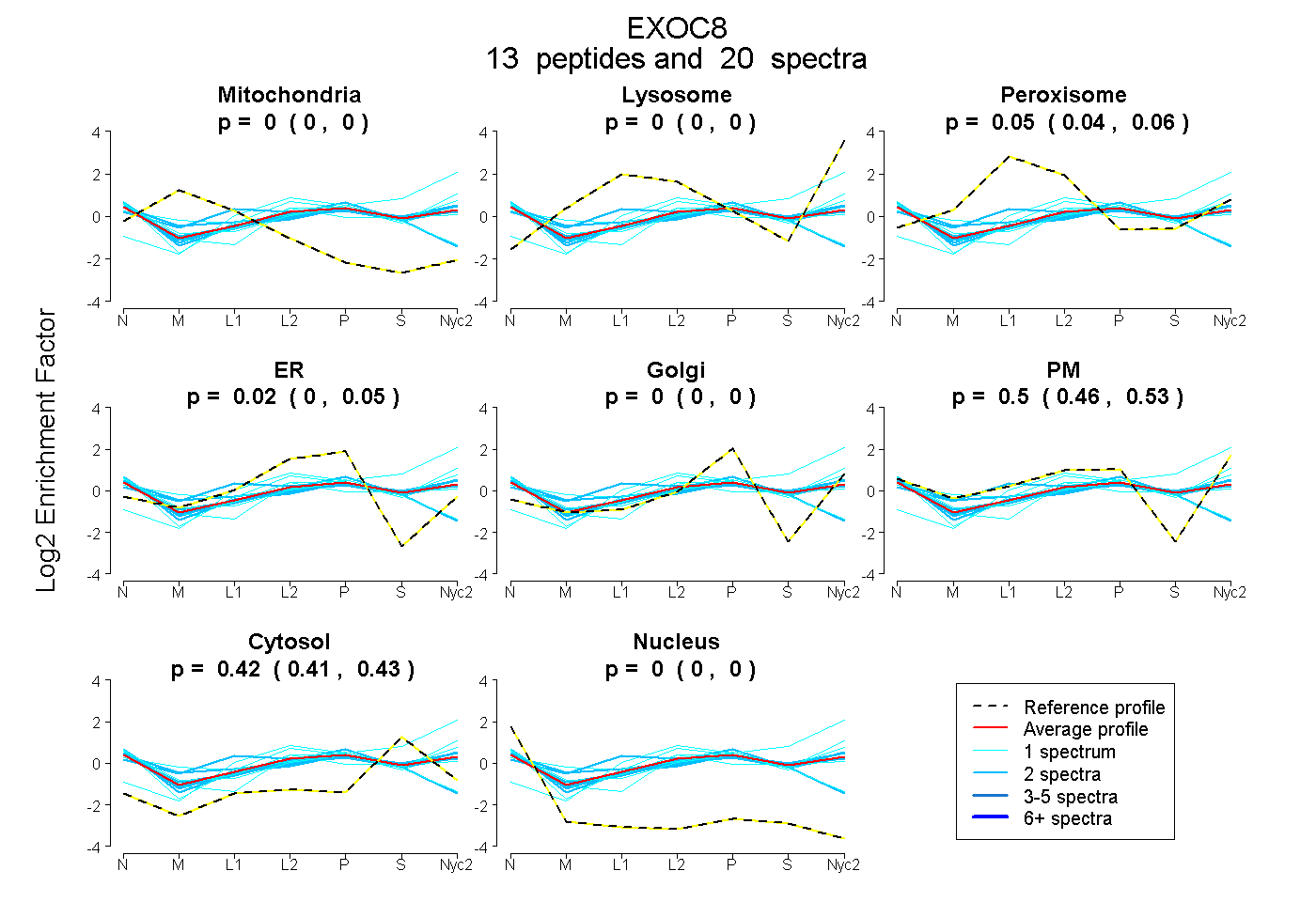
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
20 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.054 0.043 | 0.063 |
0.021 0.000 | 0.050 |
0.000 0.000 | 0.000 |
0.503 0.462 | 0.532 |
0.422 0.414 | 0.427 |
0.000 0.000 | 0.000 |
| 1 spectrum, LGQCTK | 0.007 | 0.000 | 0.120 | 0.406 | 0.000 | 0.000 | 0.323 | 0.143 | ||
| 2 spectra, DFEGAVDLLDK | 0.043 | 0.000 | 0.102 | 0.000 | 0.000 | 0.487 | 0.368 | 0.000 | ||
| 2 spectra, GAAQAGFLPGPAGVPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.559 | 0.441 | 0.000 | ||
| 2 spectra, ACELFLR | 0.000 | 0.000 | 0.092 | 0.452 | 0.000 | 0.000 | 0.345 | 0.111 | ||
| 2 spectra, EIIIEATK | 0.000 | 0.000 | 0.033 | 0.000 | 0.000 | 0.534 | 0.433 | 0.000 | ||
| 1 spectrum, AAAVHTAIR | 0.000 | 0.000 | 0.161 | 0.034 | 0.000 | 0.504 | 0.301 | 0.000 | ||
| 2 spectra, ESLSTAAECVK | 0.000 | 0.000 | 0.293 | 0.000 | 0.094 | 0.286 | 0.326 | 0.000 | ||
| 1 spectrum, EIEDLR | 0.000 | 0.496 | 0.000 | 0.000 | 0.069 | 0.000 | 0.435 | 0.000 | ||
| 1 spectrum, EGPGTGEEGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.503 | 0.448 | 0.050 | ||
| 1 spectrum, QFIETAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.583 | 0.417 | 0.000 | ||
| 1 spectrum, IFQAENAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.644 | 0.356 | 0.000 | ||
| 2 spectra, APPPVTSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.559 | 0.441 | 0.000 | ||
| 2 spectra, EQEEAAALR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.582 | 0.418 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
6 spectra |
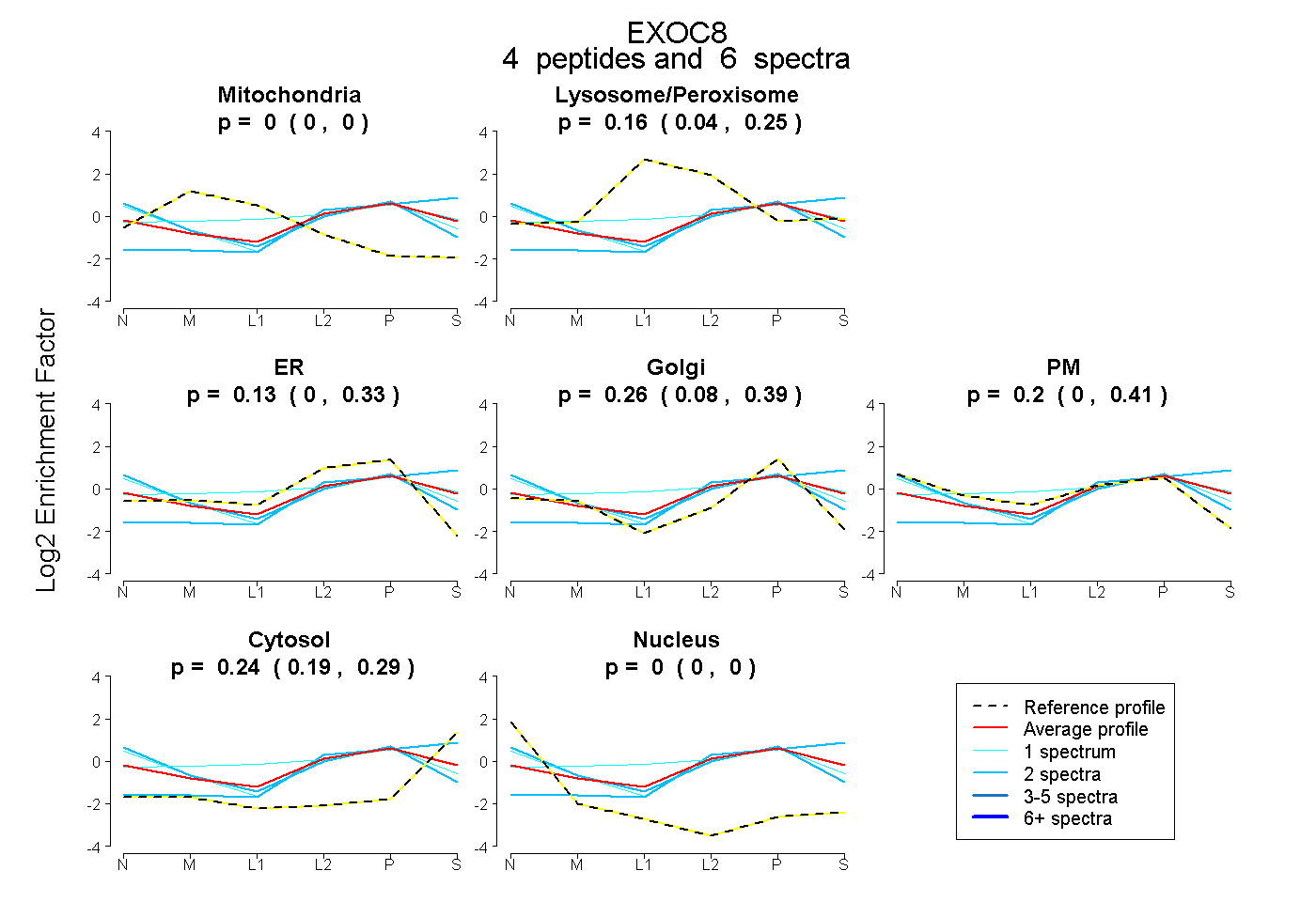 |
0.000 0.000 | 0.000 |
0.164 0.036 | 0.251 |
0.133 0.000 | 0.329 |
0.262 0.081 | 0.388 |
0.200 0.000 | 0.408 |
0.241 0.188 | 0.294 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
35 spectra |
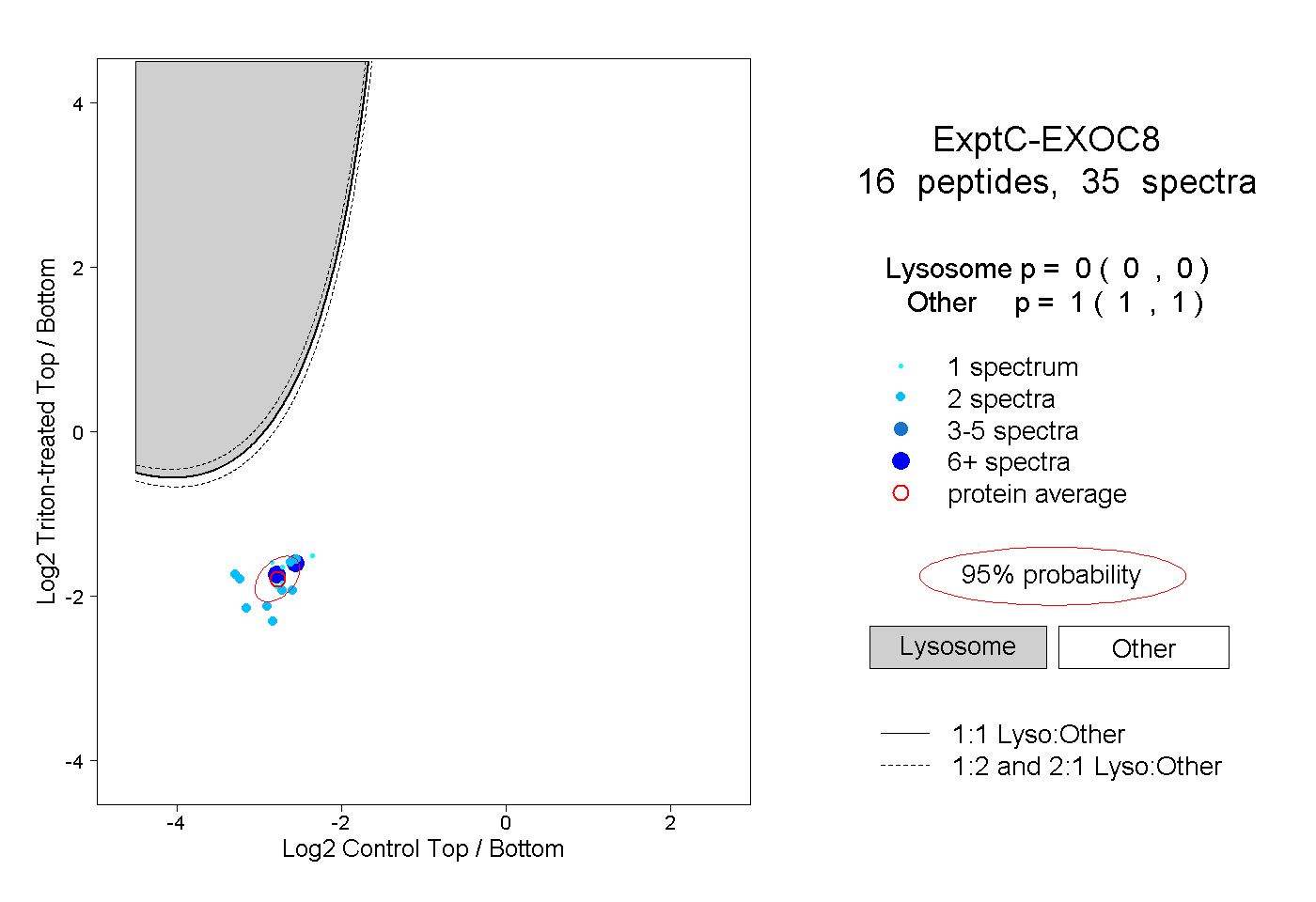 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
3 spectra |
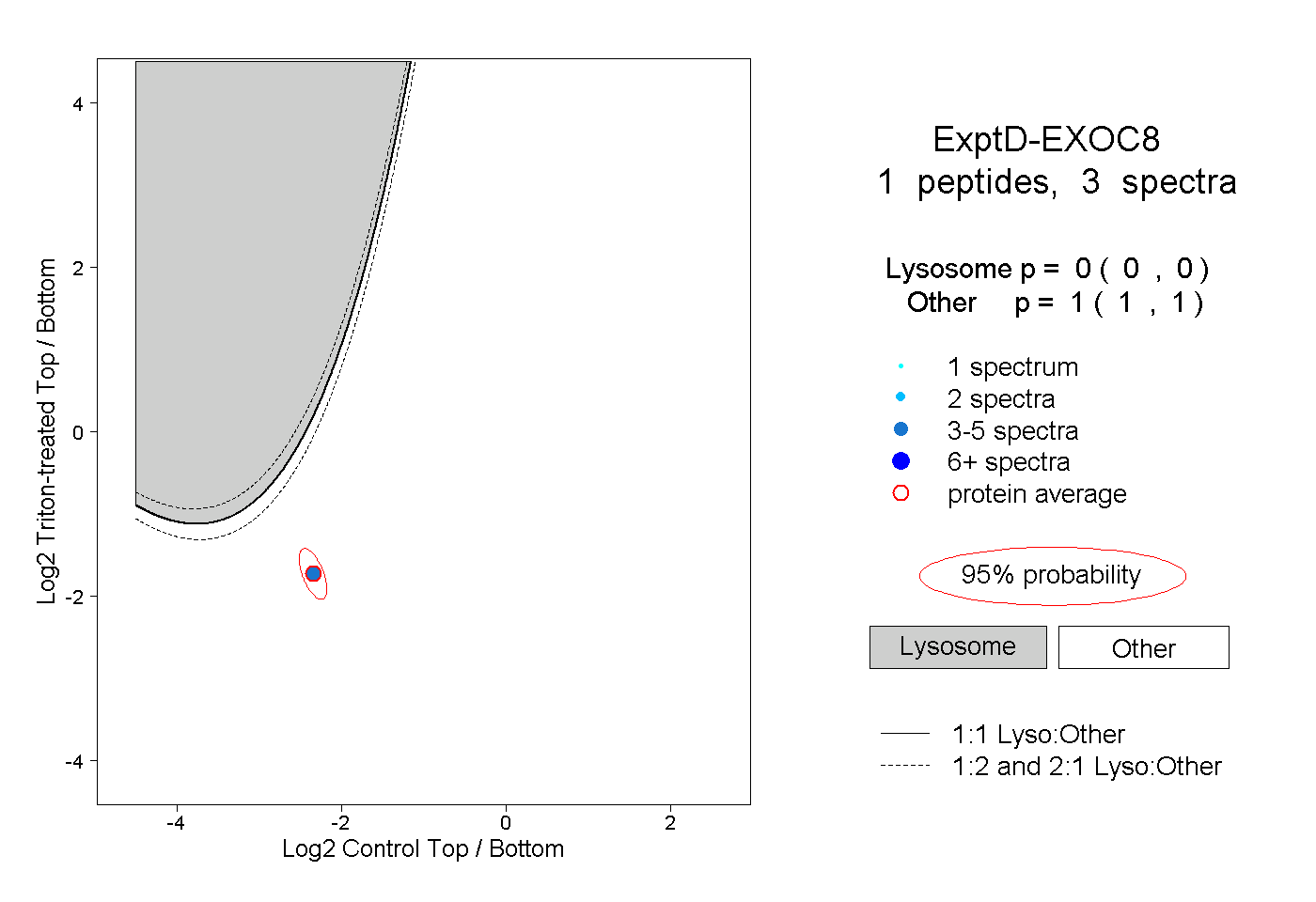 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |