peptides
spectra
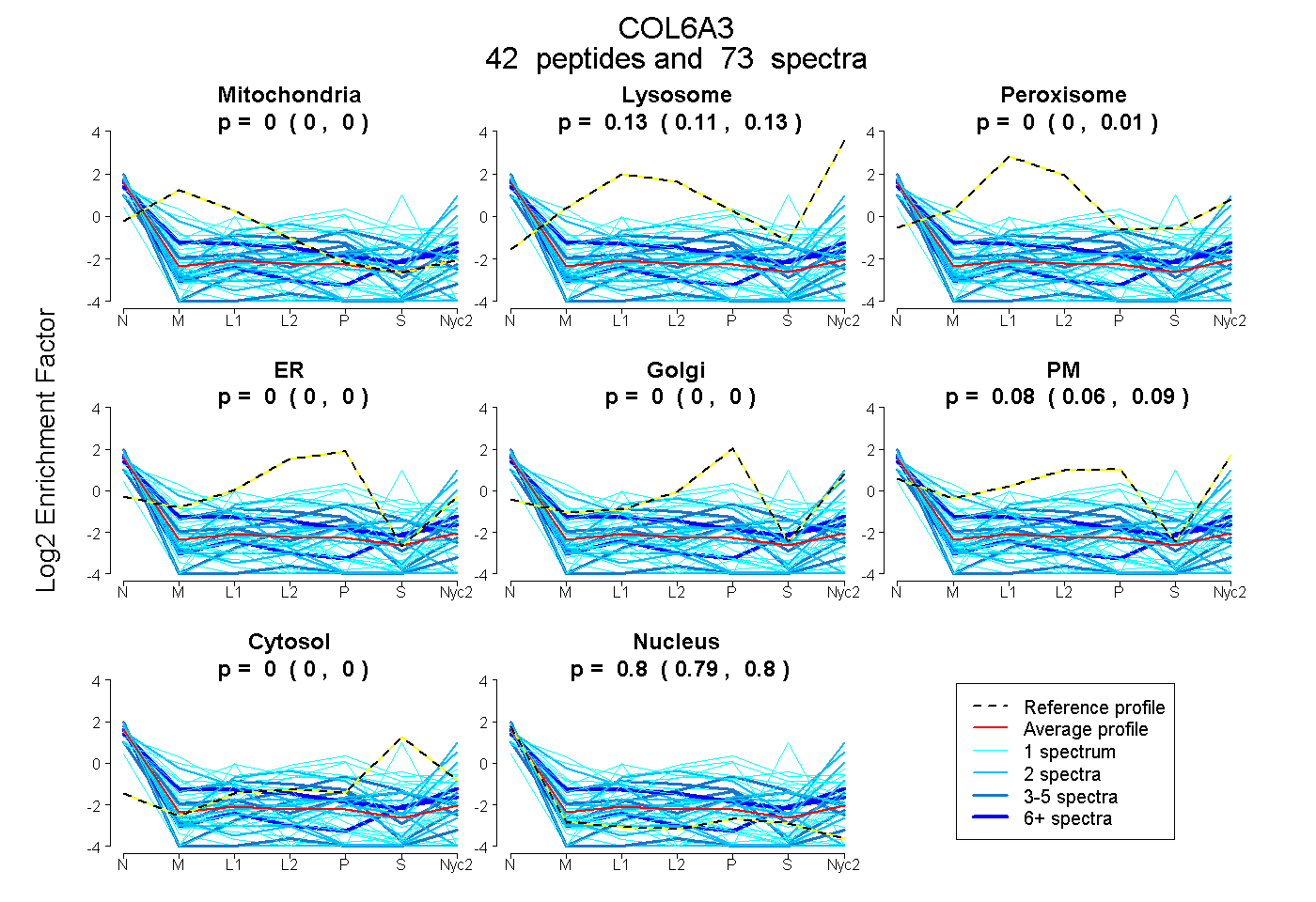
0.000 | 0.000
0.108 | 0.135
0.000 | 0.015
0.000 | 0.000
0.000 | 0.000
0.061 | 0.090
0.000 | 0.000
0.789 | 0.800
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
73 spectra |
 |
0.000 0.000 | 0.000 |
0.126 0.108 | 0.135 |
0.001 0.000 | 0.015 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.077 0.061 | 0.090 |
0.000 0.000 | 0.000 |
0.796 0.789 | 0.800 |
| 1 spectrum, VVIHFTDGADGDMADLYR | 0.260 | 0.000 | 0.098 | 0.000 | 0.000 | 0.322 | 0.166 | 0.154 | ||
| 2 spectra, NIDSEEVGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.101 | 0.243 | 0.656 | ||
| 1 spectrum, VALVQYSDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.159 | 0.000 | 0.841 | ||
| 2 spectra, DQNVFVSQK | 0.000 | 0.381 | 0.000 | 0.000 | 0.000 | 0.066 | 0.000 | 0.553 | ||
| 1 spectrum, STDAVAGPASSLK | 0.025 | 0.000 | 0.058 | 0.091 | 0.000 | 0.344 | 0.231 | 0.251 | ||
| 1 spectrum, QSSPDTVK | 0.000 | 0.000 | 0.000 | 0.185 | 0.000 | 0.357 | 0.312 | 0.146 | ||
| 1 spectrum, LSQIQR | 0.335 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.665 | ||
| 3 spectra, QVYIGNALEYVLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 1 spectrum, ALEFVAR | 0.233 | 0.000 | 0.000 | 0.000 | 0.000 | 0.010 | 0.000 | 0.757 | ||
| 6 spectra, GVIPFIFQAK | 0.081 | 0.093 | 0.102 | 0.000 | 0.000 | 0.159 | 0.000 | 0.565 | ||
| 1 spectrum, VAVVTYNNEVTTEIR | 0.000 | 0.000 | 0.382 | 0.000 | 0.000 | 0.111 | 0.193 | 0.315 | ||
| 1 spectrum, DAITTVR | 0.107 | 0.070 | 0.000 | 0.000 | 0.000 | 0.015 | 0.000 | 0.808 | ||
| 3 spectra, GFMYDRPLR | 0.099 | 0.000 | 0.067 | 0.000 | 0.000 | 0.348 | 0.000 | 0.486 | ||
| 2 spectra, LSVGNQQVR | 0.000 | 0.214 | 0.000 | 0.000 | 0.000 | 0.090 | 0.000 | 0.695 | ||
| 1 spectrum, DFLVNVLER | 0.000 | 0.125 | 0.000 | 0.000 | 0.000 | 0.359 | 0.012 | 0.504 | ||
| 1 spectrum, VFAVGVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.058 | 0.345 | 0.597 | ||
| 1 spectrum, IEDGVPQHLVLFLGGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 1 spectrum, DVVFLIDGSEGVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.482 | 0.518 | ||
| 3 spectra, AEILNLVK | 0.000 | 0.000 | 0.000 | 0.081 | 0.145 | 0.000 | 0.000 | 0.774 | ||
| 1 spectrum, LSDAGITPLFLTSQEDR | 0.000 | 0.000 | 0.000 | 0.509 | 0.000 | 0.000 | 0.000 | 0.491 | ||
| 2 spectra, LVFTVR | 0.000 | 0.000 | 0.000 | 0.016 | 0.000 | 0.000 | 0.024 | 0.960 | ||
| 1 spectrum, EQLEEAQR | 0.167 | 0.000 | 0.000 | 0.000 | 0.000 | 0.152 | 0.221 | 0.461 | ||
| 1 spectrum, SQDDVSR | 0.600 | 0.000 | 0.000 | 0.000 | 0.000 | 0.081 | 0.000 | 0.319 | ||
| 7 spectra, GSIMALVIGSR | 0.000 | 0.081 | 0.000 | 0.000 | 0.000 | 0.000 | 0.123 | 0.797 | ||
| 2 spectra, NILTSSTGSR | 0.493 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.507 | ||
| 1 spectrum, SADEVDDSAVELK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 2 spectra, IIEELDVKPDGTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 2 spectra, STELNEEPLMR | 0.000 | 0.058 | 0.000 | 0.000 | 0.000 | 0.590 | 0.000 | 0.353 | ||
| 1 spectrum, FNEHQTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.485 | 0.090 | 0.425 | ||
| 3 spectra, GGPGQPGFEGEQGTR | 0.000 | 0.000 | 0.000 | 0.245 | 0.000 | 0.000 | 0.252 | 0.502 | ||
| 1 spectrum, VAIAQFSDDVR | 0.000 | 0.122 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.878 | ||
| 1 spectrum, VGLVQYNSDPTDEFFLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 2 spectra, DVVFLIDGSQNAGAEFQHIR | 0.000 | 0.000 | 0.063 | 0.000 | 0.000 | 0.195 | 0.010 | 0.732 | ||
| 3 spectra, GDVGIR | 0.000 | 0.000 | 0.081 | 0.000 | 0.000 | 0.115 | 0.171 | 0.632 | ||
| 1 spectrum, VGIEHLLK | 0.000 | 0.000 | 0.103 | 0.000 | 0.000 | 0.000 | 0.000 | 0.897 | ||
| 1 spectrum, LMQVEFGR | 0.000 | 0.036 | 0.000 | 0.000 | 0.000 | 0.000 | 0.257 | 0.708 | ||
| 1 spectrum, GLNLGLALDHALR | 0.000 | 0.000 | 0.000 | 0.000 | 0.055 | 0.000 | 0.023 | 0.922 | ||
| 1 spectrum, DEVQNAVR | 0.000 | 0.141 | 0.000 | 0.000 | 0.000 | 0.235 | 0.000 | 0.624 | ||
| 1 spectrum, ACCGVPCK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 2 spectra, VPQIAFVITGGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 1 spectrum, ISLSPEYVFSVSTFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 2 spectra, NIFQRPLGSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.374 | 0.000 | 0.626 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
17 spectra |
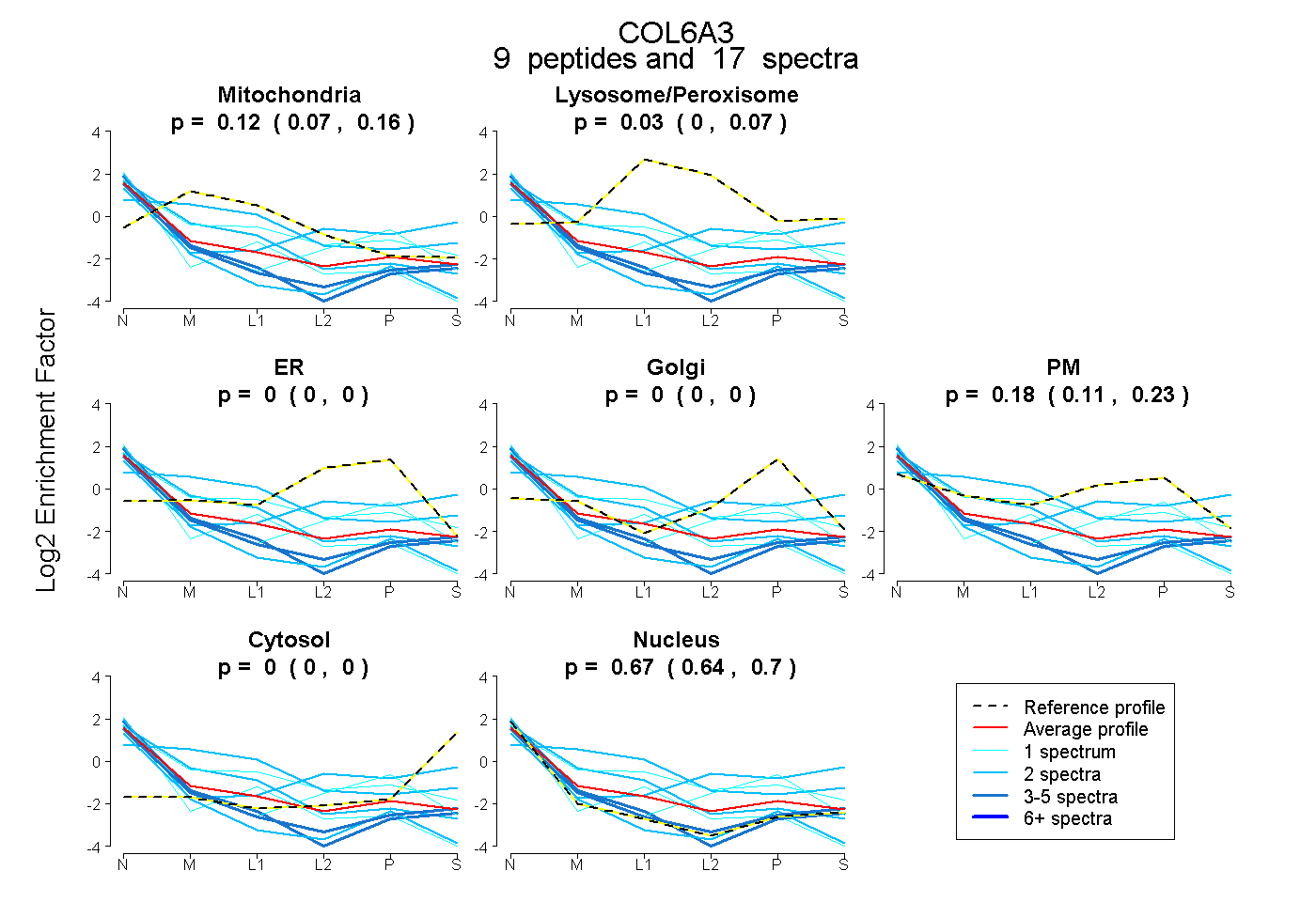 |
0.121 0.073 | 0.158 |
0.028 0.000 | 0.072 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.181 0.113 | 0.225 |
0.000 0.000 | 0.000 |
0.670 0.638 | 0.700 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
48 spectra |
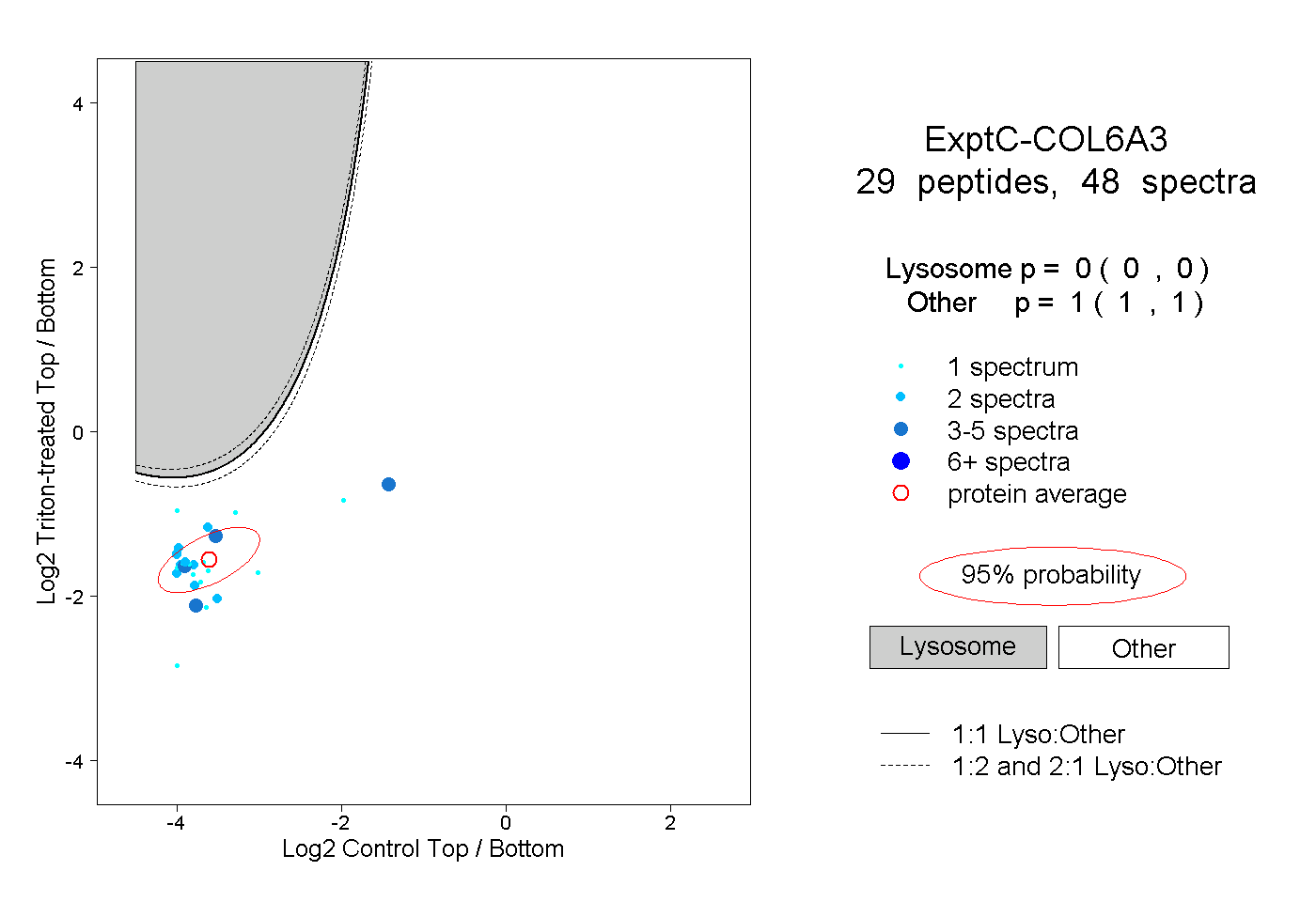 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
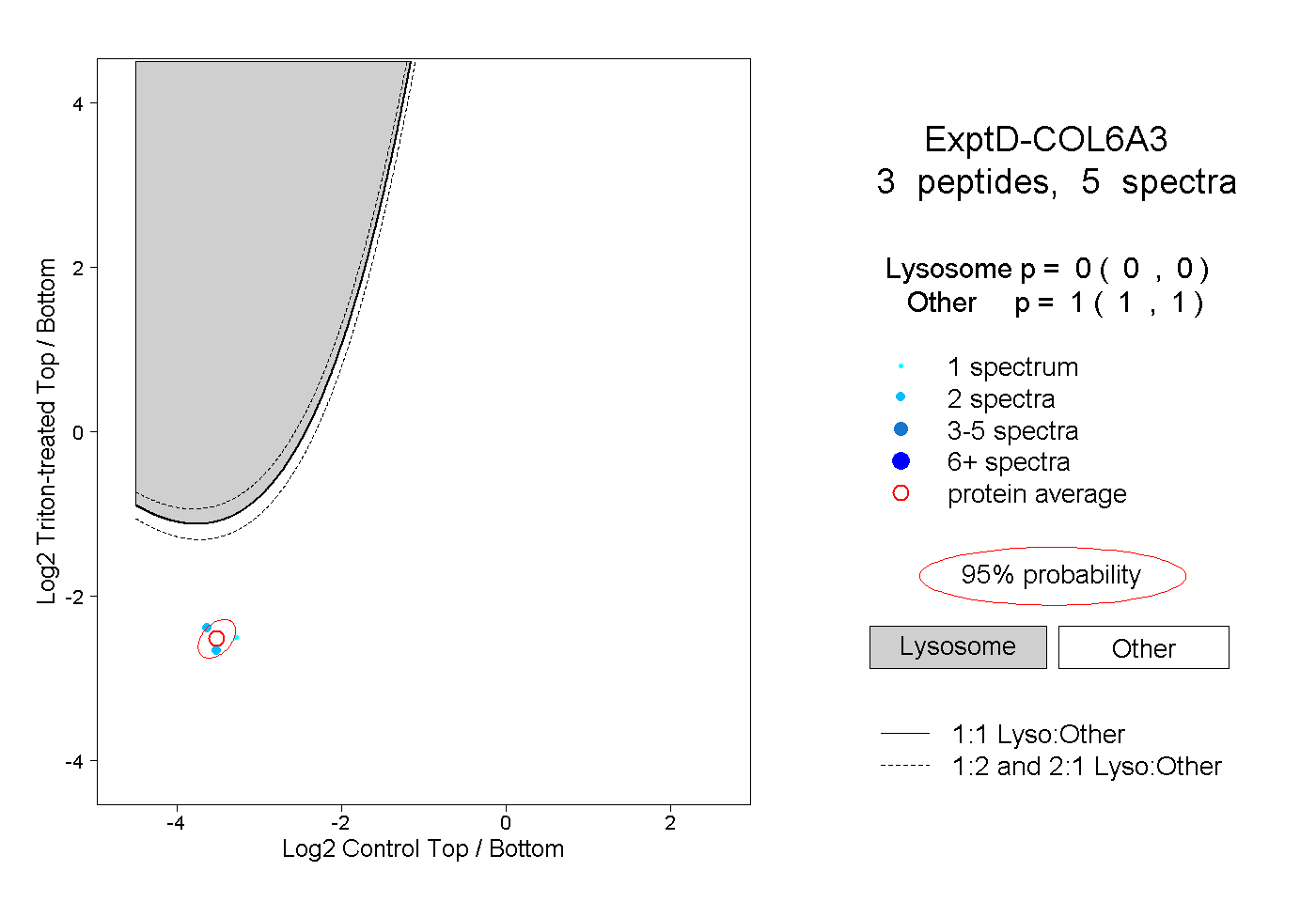 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |