peptides
spectra
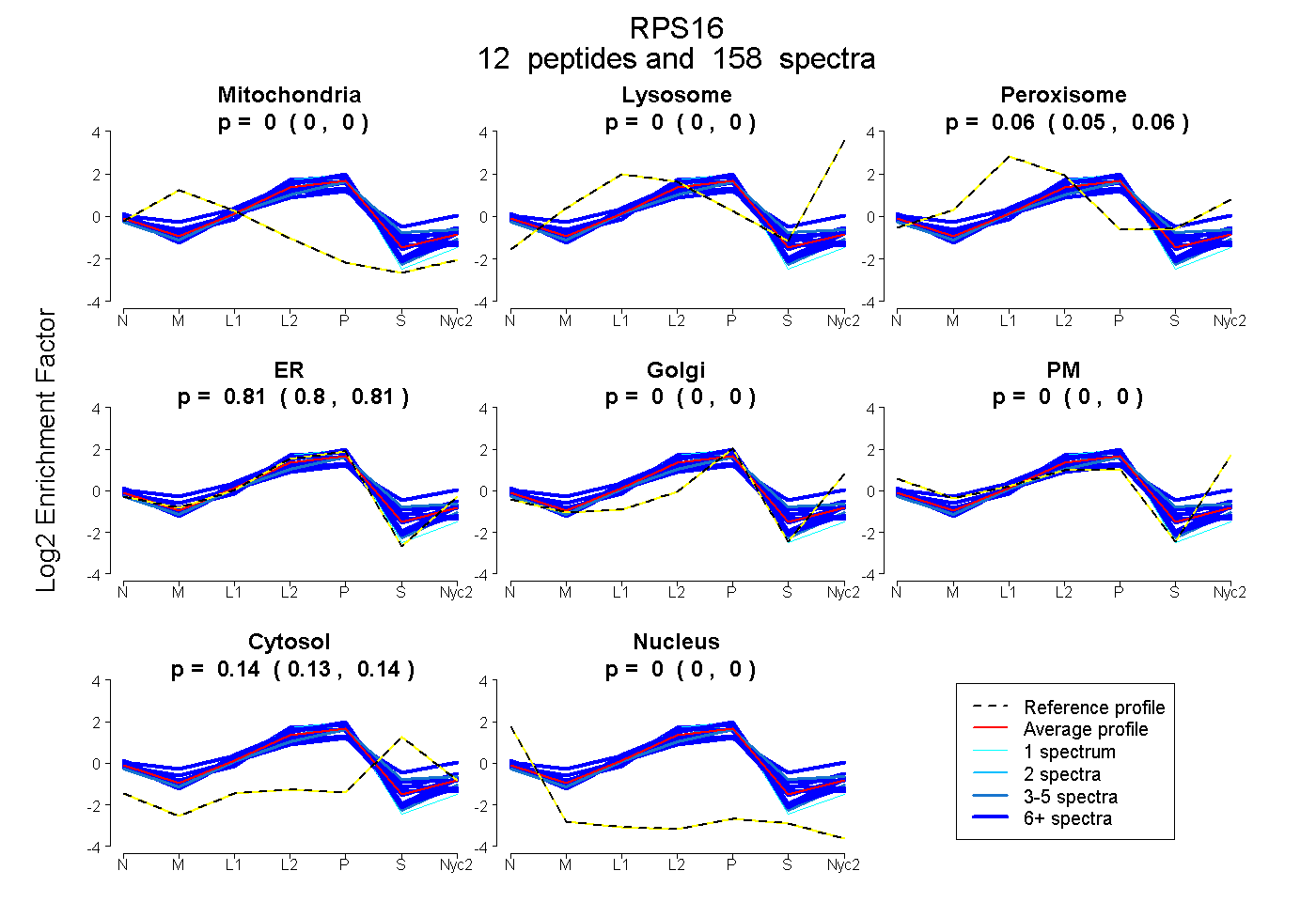
0.000 | 0.000
0.000 | 0.000
0.052 | 0.058
0.803 | 0.812
0.000 | 0.000
0.000 | 0.000
0.134 | 0.139
0.000 | 0.000
peptides
spectra
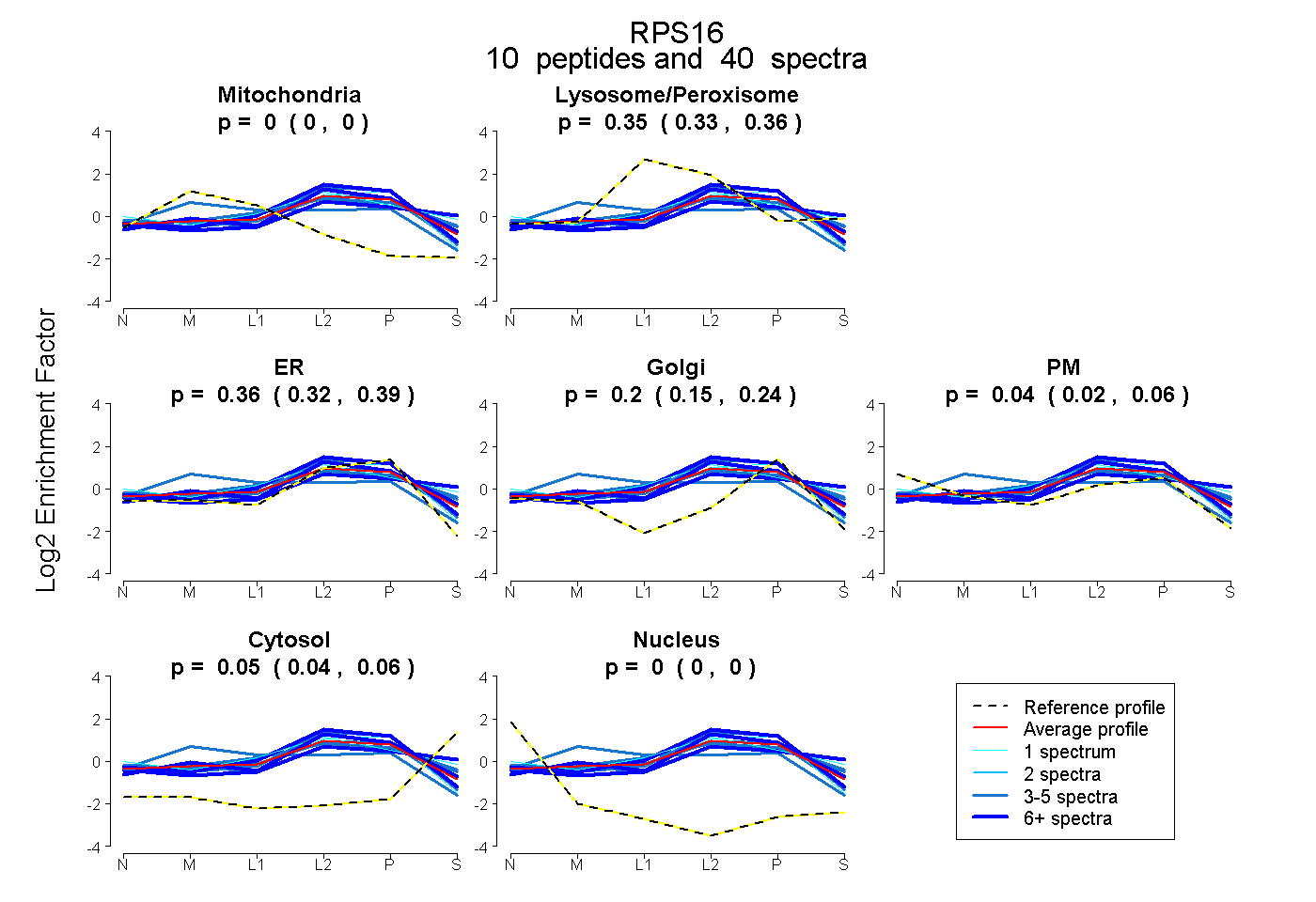
0.000 | 0.000
0.327 | 0.362
0.319 | 0.394
0.151 | 0.238
0.020 | 0.061
0.042 | 0.063
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
158 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.055 0.052 | 0.058 |
0.808 0.803 | 0.812 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.137 0.134 | 0.139 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
40 spectra |
 |
0.000 0.000 | 0.000 |
0.346 0.327 | 0.362 |
0.359 0.319 | 0.394 |
0.200 0.151 | 0.238 |
0.042 0.020 | 0.061 |
0.053 0.042 | 0.063 |
0.000 0.000 | 0.000 |
| 3 spectra, ALVAYYQK | 0.000 | 0.291 | 0.346 | 0.185 | 0.175 | 0.003 | 0.000 | |||
| 5 spectra, GPLQSVQVFGR | 0.000 | 0.506 | 0.065 | 0.384 | 0.000 | 0.045 | 0.000 | |||
| 1 spectrum, TATAVAHCK | 0.000 | 0.432 | 0.179 | 0.044 | 0.227 | 0.118 | 0.000 | |||
| 8 spectra, LLEPVLLLGK | 0.000 | 0.286 | 0.714 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, GGGHVAQIYAIR | 0.000 | 0.327 | 0.297 | 0.106 | 0.021 | 0.249 | 0.000 | |||
| 6 spectra, VNGRPLEMIEPR | 0.000 | 0.247 | 0.640 | 0.000 | 0.000 | 0.113 | 0.000 | |||
| 4 spectra, FGGPGAR | 0.333 | 0.184 | 0.356 | 0.091 | 0.035 | 0.000 | 0.000 | |||
| 1 spectrum, GNGLIK | 0.000 | 0.221 | 0.607 | 0.099 | 0.073 | 0.000 | 0.000 | |||
| 3 spectra, DILIQYDR | 0.000 | 0.332 | 0.268 | 0.264 | 0.000 | 0.136 | 0.000 | |||
| 3 spectra, FAGVDIR | 0.000 | 0.220 | 0.758 | 0.007 | 0.009 | 0.006 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
177 spectra |
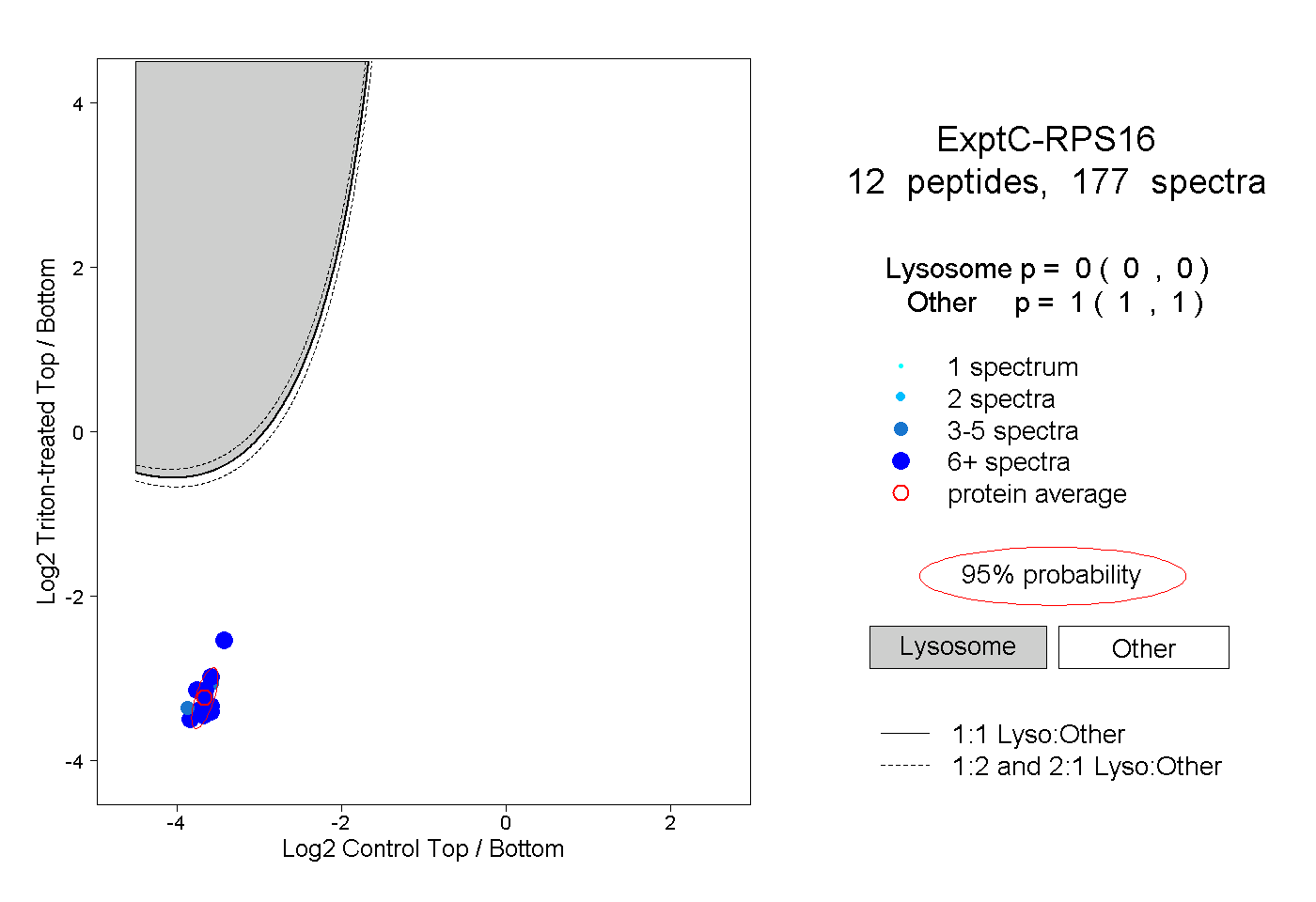 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
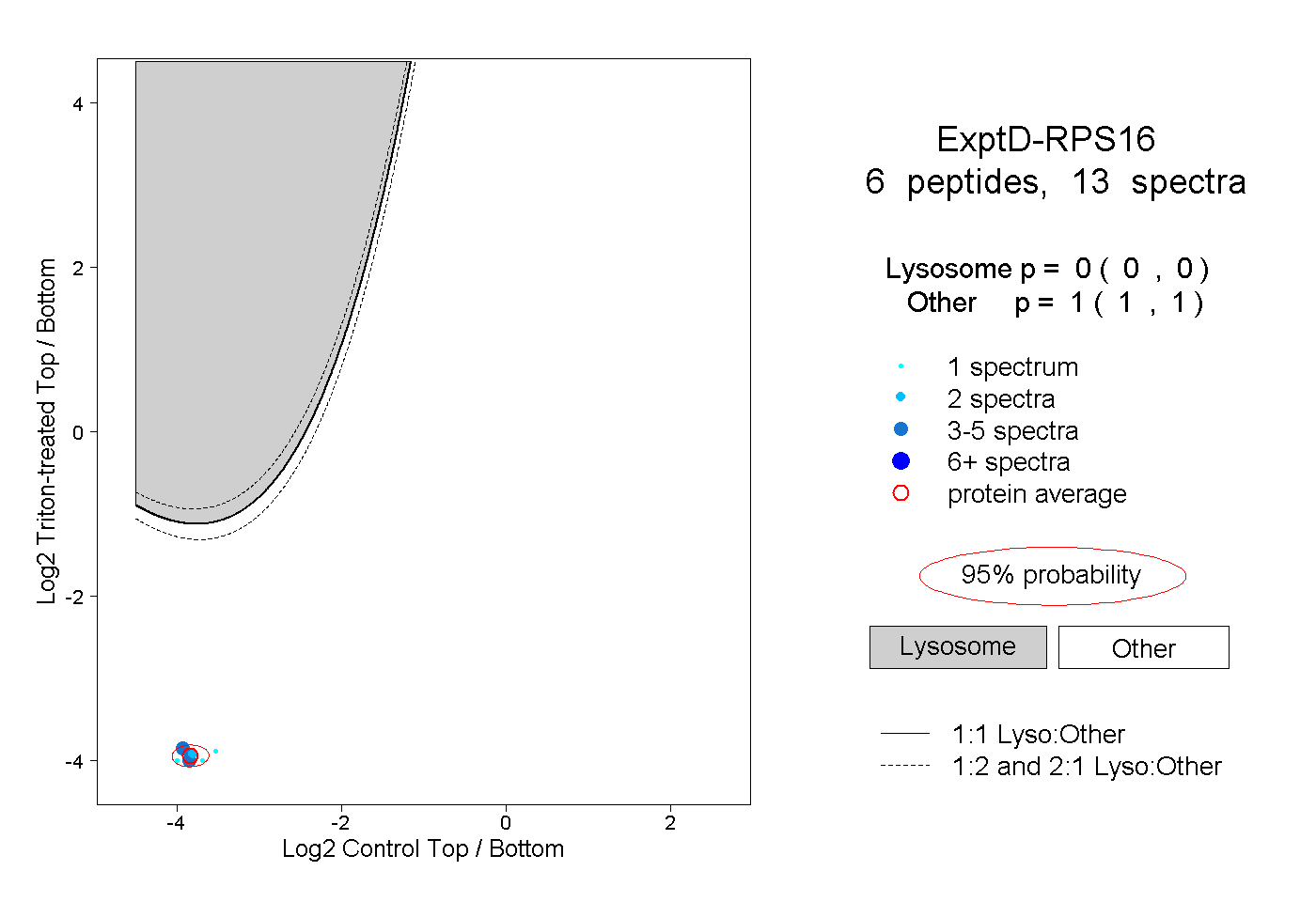 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |