peptides
spectra
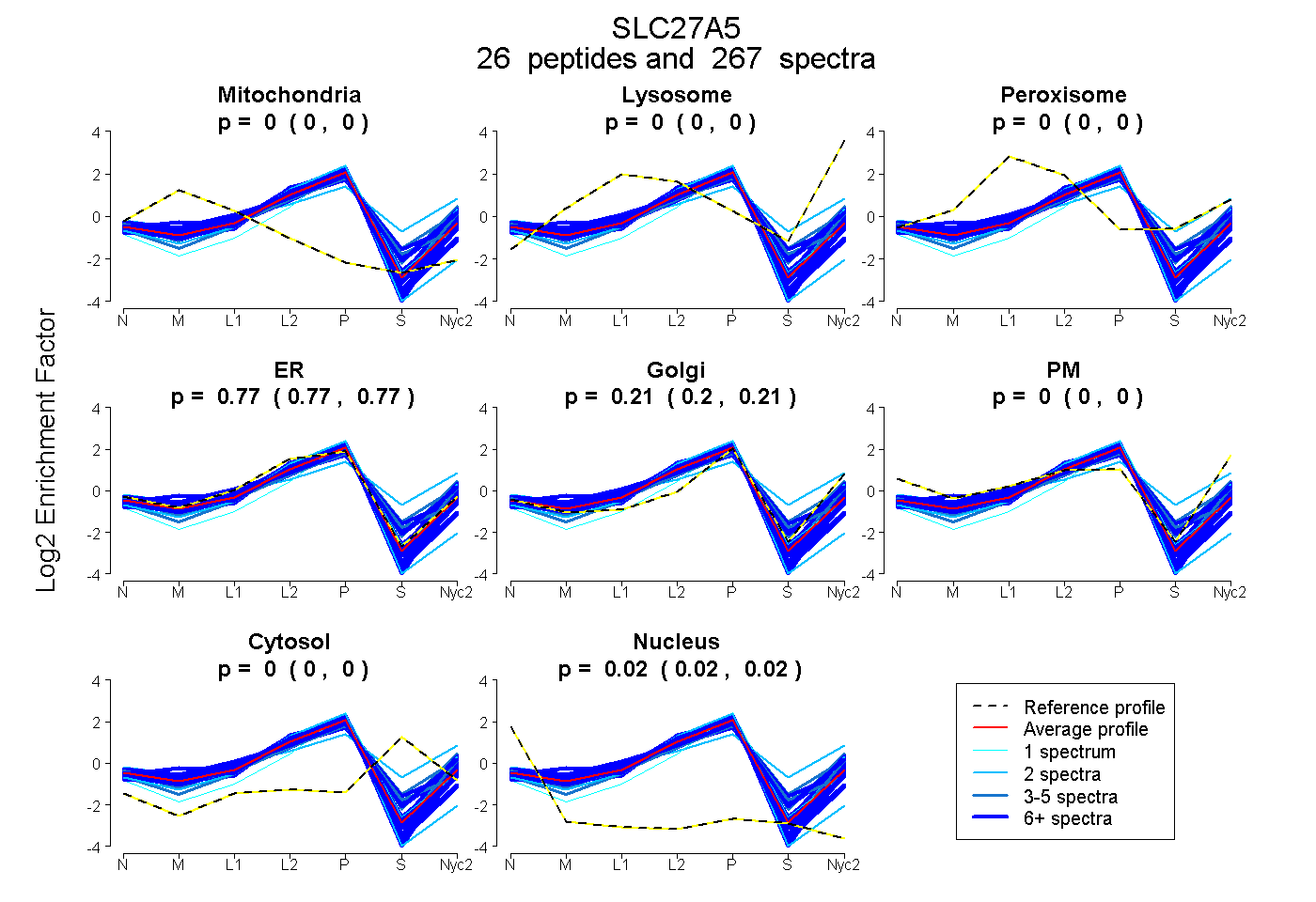
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.767 | 0.774
0.204 | 0.213
0.000 | 0.000
0.000 | 0.000
0.019 | 0.022
peptides
spectra
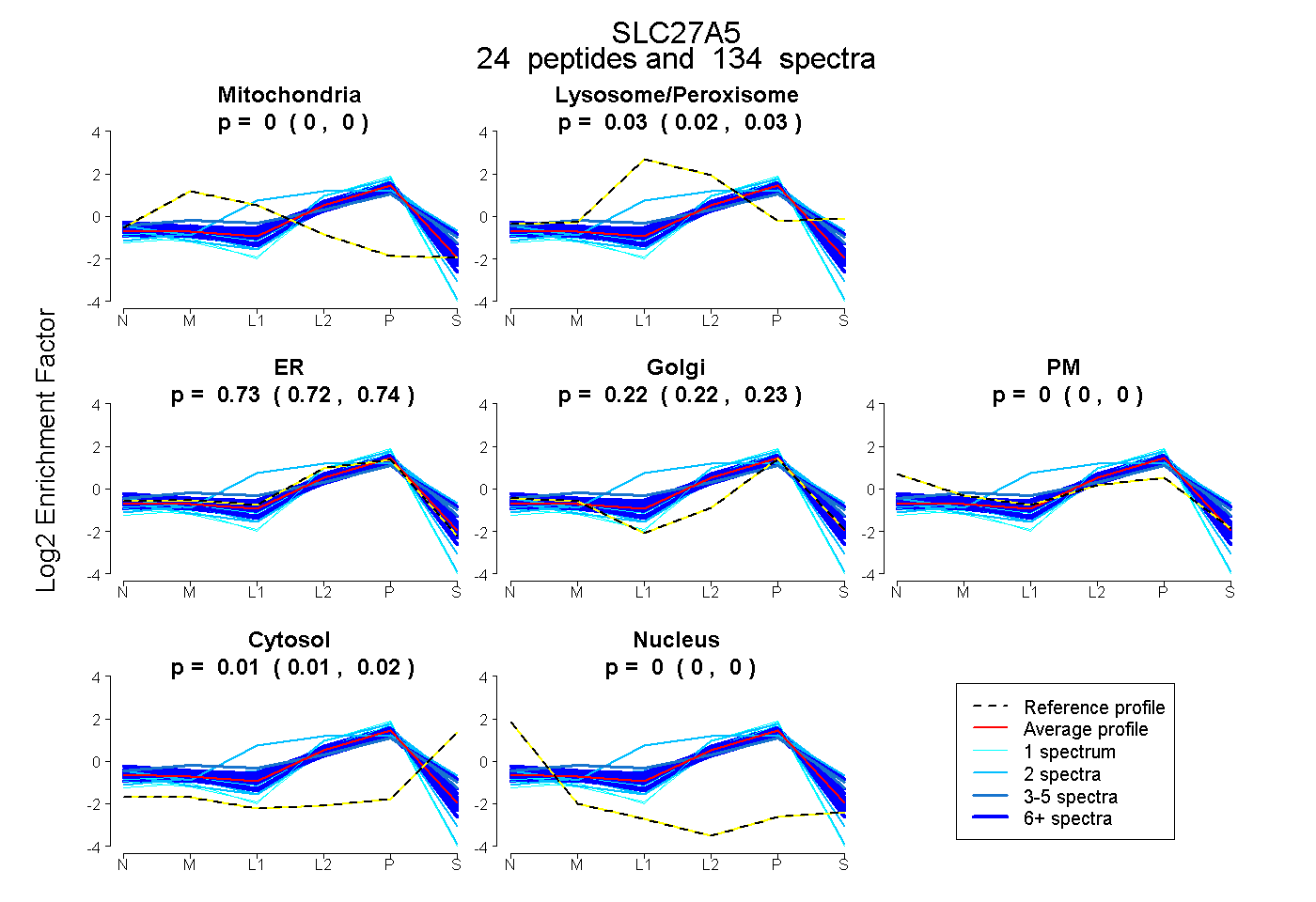
0.000 | 0.000
0.021 | 0.031
0.725 | 0.744
0.217 | 0.230
0.000 | 0.000
0.011 | 0.016
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
267 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.771 0.767 | 0.774 |
0.209 0.204 | 0.213 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.021 0.019 | 0.022 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
134 spectra |
 |
0.000 0.000 | 0.000 |
0.027 0.021 | 0.031 |
0.735 0.725 | 0.744 |
0.225 0.217 | 0.230 |
0.000 0.000 | 0.000 |
0.014 0.011 | 0.016 |
0.000 0.000 | 0.000 |
| 3 spectra, YWAECR | 0.000 | 0.375 | 0.024 | 0.601 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VIQMSNVLSFCGR | 0.000 | 0.000 | 0.785 | 0.215 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, GATAILVLPSK | 0.000 | 0.000 | 0.834 | 0.130 | 0.000 | 0.036 | 0.000 | |||
| 7 spectra, ACQAAWALK | 0.000 | 0.188 | 0.387 | 0.325 | 0.100 | 0.000 | 0.000 | |||
| 2 spectra, YLCNVPGQPEDK | 0.000 | 0.490 | 0.337 | 0.174 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, SISALSVFLGLAK | 0.000 | 0.000 | 0.665 | 0.335 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, VGMAAVK | 0.000 | 0.092 | 0.554 | 0.354 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, FALGNGLR | 0.000 | 0.000 | 0.804 | 0.196 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TFDGQK | 0.000 | 0.000 | 0.836 | 0.164 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, ADVWENFQQR | 0.000 | 0.112 | 0.531 | 0.356 | 0.000 | 0.001 | 0.000 | |||
| 10 spectra, LVANVR | 0.000 | 0.000 | 0.763 | 0.237 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, IGDTFR | 0.000 | 0.000 | 0.891 | 0.064 | 0.000 | 0.000 | 0.046 | |||
| 14 spectra, LYQHVR | 0.007 | 0.074 | 0.726 | 0.193 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, TSCFIR | 0.000 | 0.000 | 0.673 | 0.327 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, SPAIFIYTSGTTGLPKPAILSHER | 0.000 | 0.000 | 0.651 | 0.163 | 0.000 | 0.186 | 0.000 | |||
| 1 spectrum, EATIQEDK | 0.000 | 0.000 | 0.899 | 0.101 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, SWLPAYATPHFIR | 0.000 | 0.201 | 0.248 | 0.463 | 0.000 | 0.089 | 0.000 | |||
| 1 spectrum, IQDSLEITNTYK | 0.000 | 0.000 | 0.662 | 0.338 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LLFYGLNLR | 0.000 | 0.000 | 0.871 | 0.129 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, EGFDVGVIADPLYILDNK | 0.000 | 0.039 | 0.782 | 0.057 | 0.000 | 0.121 | 0.000 | |||
| 8 spectra, ILAEGGIR | 0.000 | 0.000 | 0.636 | 0.315 | 0.000 | 0.048 | 0.000 | |||
| 7 spectra, LGCPVAWINPHSR | 0.000 | 0.115 | 0.615 | 0.268 | 0.000 | 0.002 | 0.000 | |||
| 8 spectra, NQPFLGYR | 0.000 | 0.000 | 0.794 | 0.206 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, DVAFAFK | 0.000 | 0.150 | 0.534 | 0.275 | 0.000 | 0.042 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
387 spectra |
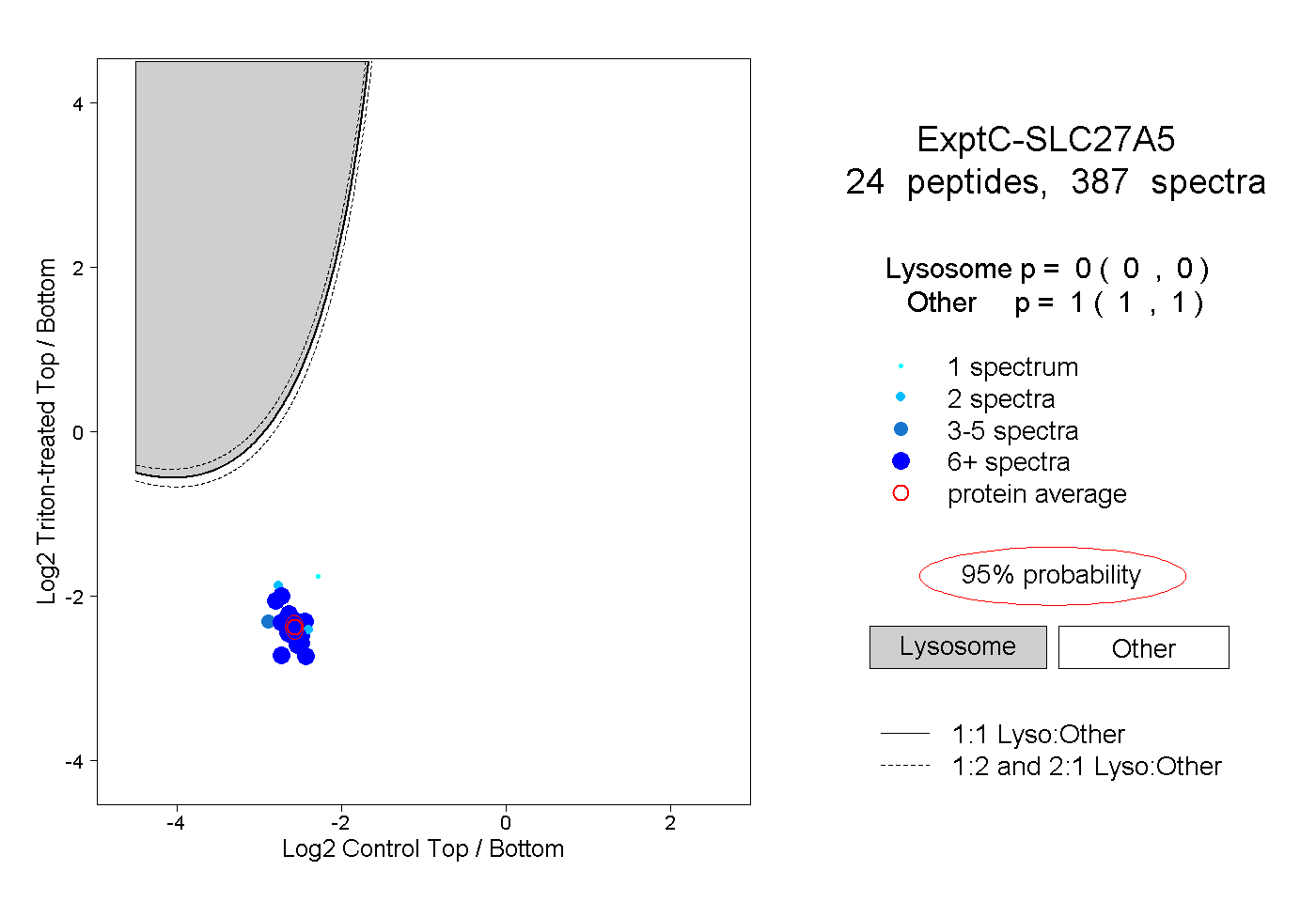 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
57 spectra |
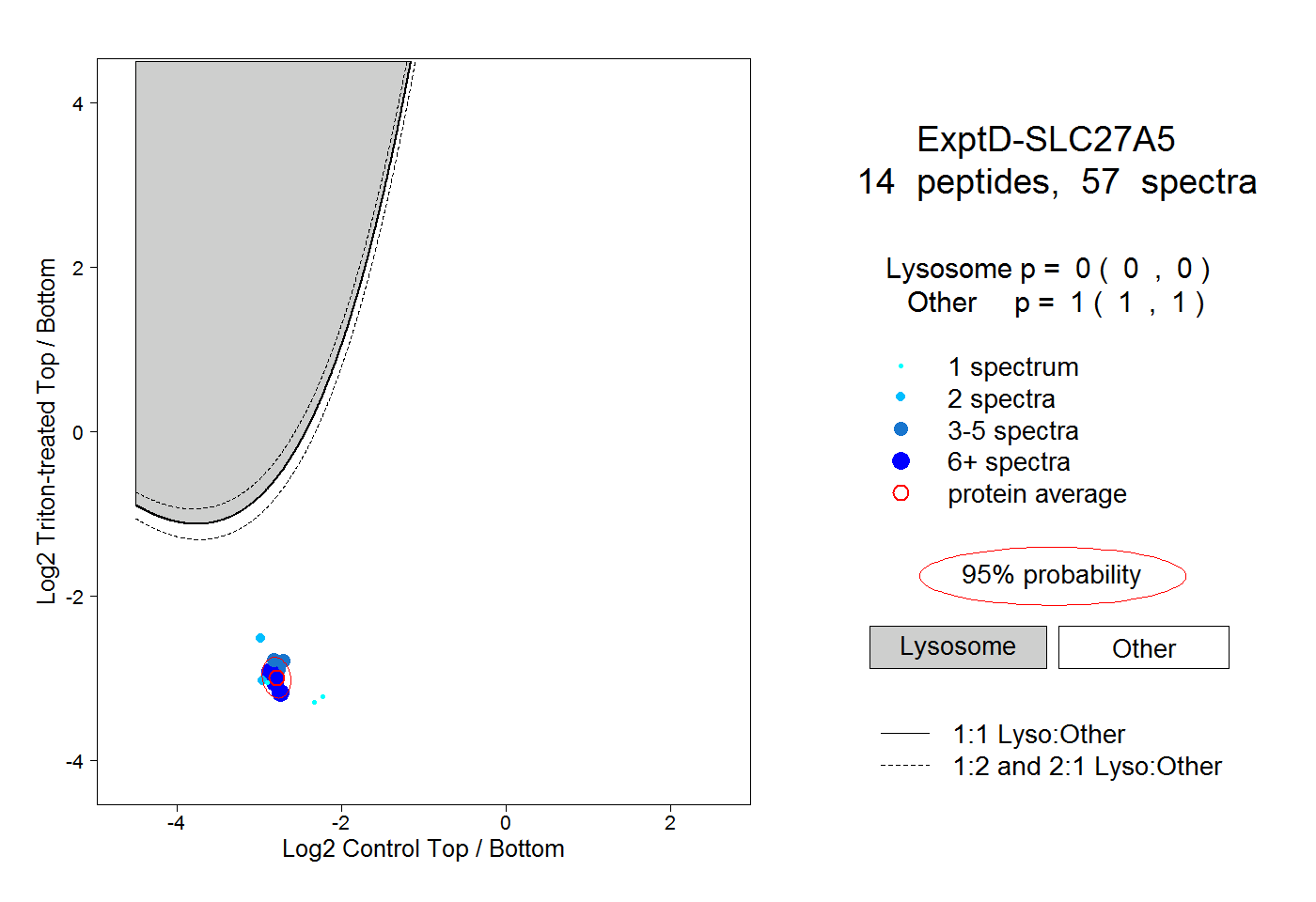 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |