peptides
spectra
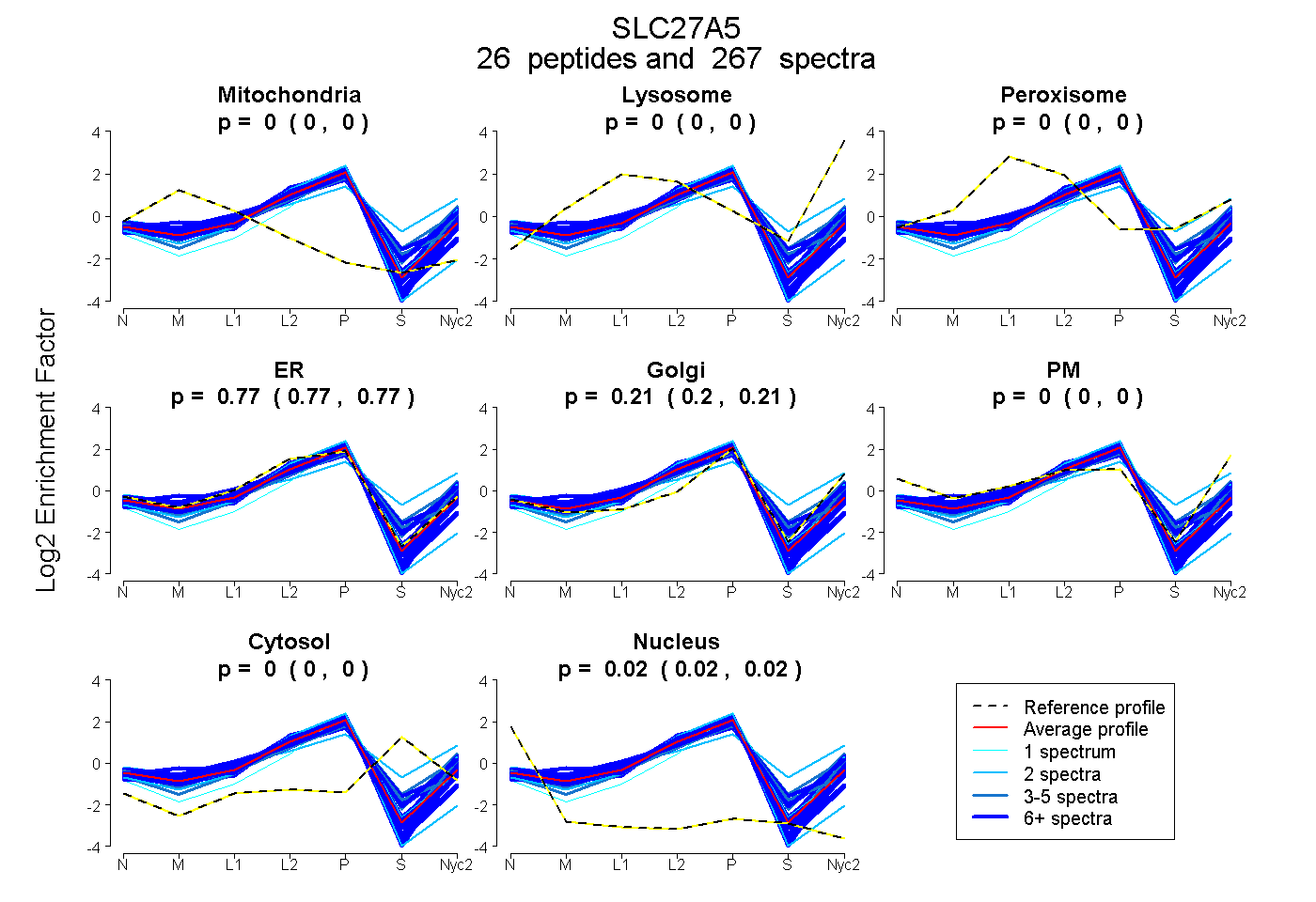
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.767 | 0.774
0.204 | 0.213
0.000 | 0.000
0.000 | 0.000
0.019 | 0.022
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
267 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.771 0.767 | 0.774 |
0.209 0.204 | 0.213 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.021 0.019 | 0.022 |
| 11 spectra, YWAECR | 0.007 | 0.000 | 0.000 | 0.931 | 0.000 | 0.000 | 0.000 | 0.063 | ||
| 39 spectra, VIQMSNVLSFCGR | 0.000 | 0.000 | 0.000 | 0.952 | 0.000 | 0.000 | 0.000 | 0.048 | ||
| 2 spectra, GATAILVLPSK | 0.000 | 0.043 | 0.236 | 0.000 | 0.529 | 0.069 | 0.123 | 0.000 | ||
| 10 spectra, ACQAAWALK | 0.026 | 0.000 | 0.000 | 0.774 | 0.186 | 0.000 | 0.002 | 0.012 | ||
| 2 spectra, YLCNVPGQPEDK | 0.000 | 0.000 | 0.000 | 0.901 | 0.000 | 0.000 | 0.000 | 0.099 | ||
| 1 spectrum, SISALSVFLGLAK | 0.000 | 0.000 | 0.000 | 0.413 | 0.517 | 0.000 | 0.012 | 0.058 | ||
| 3 spectra, GSQDETK | 0.000 | 0.044 | 0.000 | 0.485 | 0.453 | 0.000 | 0.017 | 0.000 | ||
| 8 spectra, VGMAAVK | 0.000 | 0.000 | 0.000 | 0.844 | 0.132 | 0.000 | 0.000 | 0.024 | ||
| 3 spectra, MLTPLELVQFDIETAEPVR | 0.000 | 0.000 | 0.000 | 0.628 | 0.372 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, SLMPDVYQAVCEGTWK | 0.000 | 0.000 | 0.000 | 0.734 | 0.109 | 0.000 | 0.147 | 0.010 | ||
| 8 spectra, FALGNGLR | 0.000 | 0.005 | 0.000 | 0.718 | 0.210 | 0.000 | 0.067 | 0.000 | ||
| 8 spectra, TFDGQK | 0.000 | 0.000 | 0.000 | 0.823 | 0.147 | 0.000 | 0.000 | 0.030 | ||
| 10 spectra, ADVWENFQQR | 0.000 | 0.000 | 0.000 | 0.795 | 0.183 | 0.000 | 0.000 | 0.021 | ||
| 26 spectra, LVANVR | 0.000 | 0.000 | 0.000 | 0.794 | 0.206 | 0.000 | 0.000 | 0.000 | ||
| 6 spectra, IGDTFR | 0.099 | 0.000 | 0.000 | 0.747 | 0.154 | 0.000 | 0.000 | 0.000 | ||
| 28 spectra, LYQHVR | 0.005 | 0.000 | 0.018 | 0.654 | 0.264 | 0.000 | 0.060 | 0.000 | ||
| 20 spectra, TSCFIR | 0.000 | 0.000 | 0.000 | 0.951 | 0.000 | 0.000 | 0.000 | 0.049 | ||
| 5 spectra, EATIQEDK | 0.000 | 0.056 | 0.000 | 0.592 | 0.215 | 0.000 | 0.137 | 0.000 | ||
| 8 spectra, SWLPAYATPHFIR | 0.000 | 0.000 | 0.084 | 0.492 | 0.403 | 0.000 | 0.020 | 0.000 | ||
| 2 spectra, IQDSLEITNTYK | 0.000 | 0.007 | 0.000 | 0.721 | 0.265 | 0.007 | 0.000 | 0.000 | ||
| 8 spectra, LLFYGLNLR | 0.000 | 0.000 | 0.000 | 0.758 | 0.242 | 0.000 | 0.000 | 0.000 | ||
| 19 spectra, NQPFLGYR | 0.000 | 0.000 | 0.000 | 0.826 | 0.167 | 0.000 | 0.000 | 0.006 | ||
| 10 spectra, ILAEGGIR | 0.007 | 0.000 | 0.000 | 0.490 | 0.449 | 0.053 | 0.000 | 0.000 | ||
| 6 spectra, LGCPVAWINPHSR | 0.005 | 0.000 | 0.088 | 0.691 | 0.101 | 0.000 | 0.115 | 0.000 | ||
| 7 spectra, GENVSTR | 0.000 | 0.000 | 0.000 | 0.740 | 0.227 | 0.000 | 0.000 | 0.033 | ||
| 14 spectra, DVAFAFK | 0.026 | 0.000 | 0.000 | 0.807 | 0.138 | 0.000 | 0.000 | 0.029 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
134 spectra |
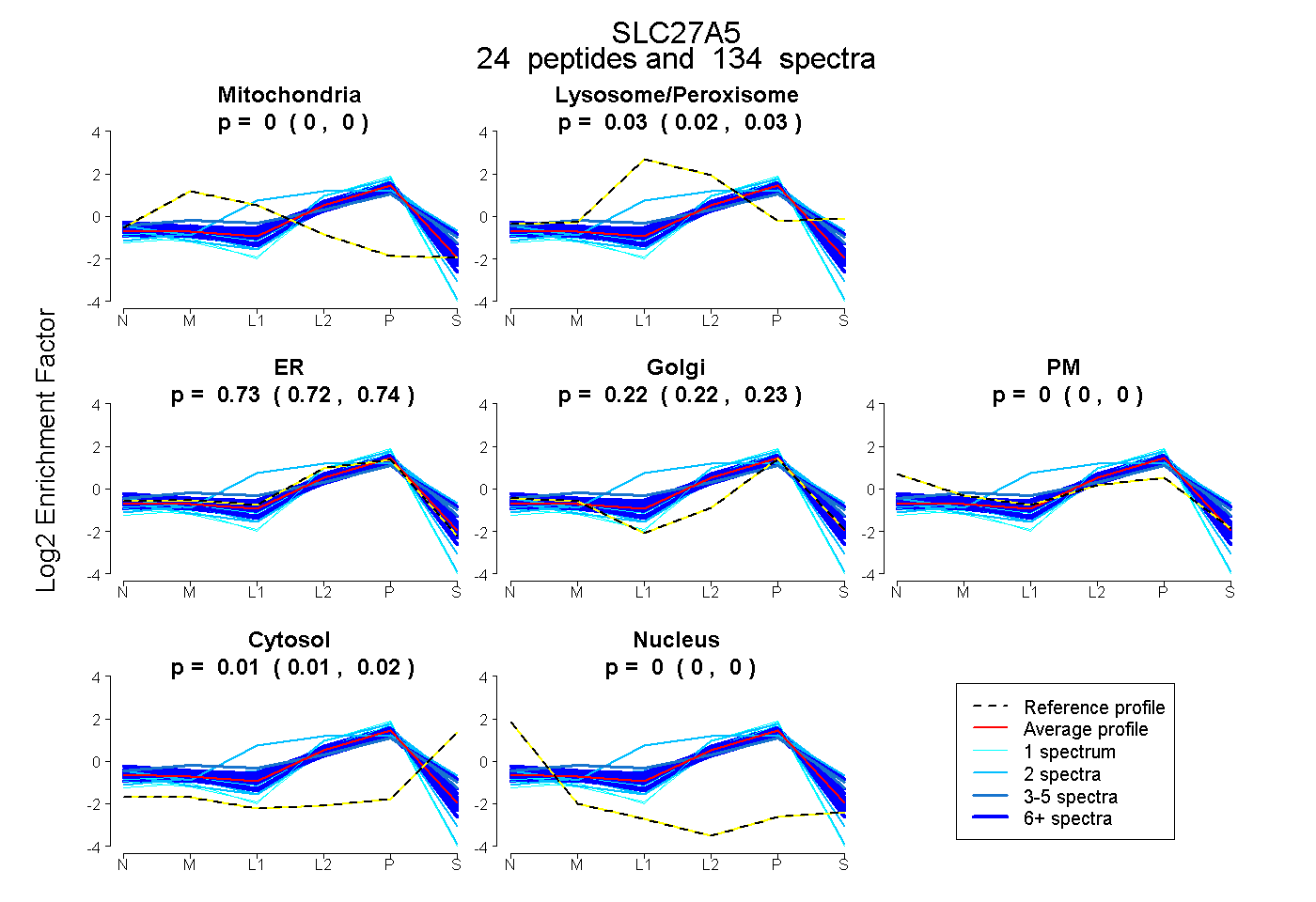 |
0.000 0.000 | 0.000 |
0.027 0.021 | 0.031 |
0.735 0.725 | 0.744 |
0.225 0.217 | 0.230 |
0.000 0.000 | 0.000 |
0.014 0.011 | 0.016 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
387 spectra |
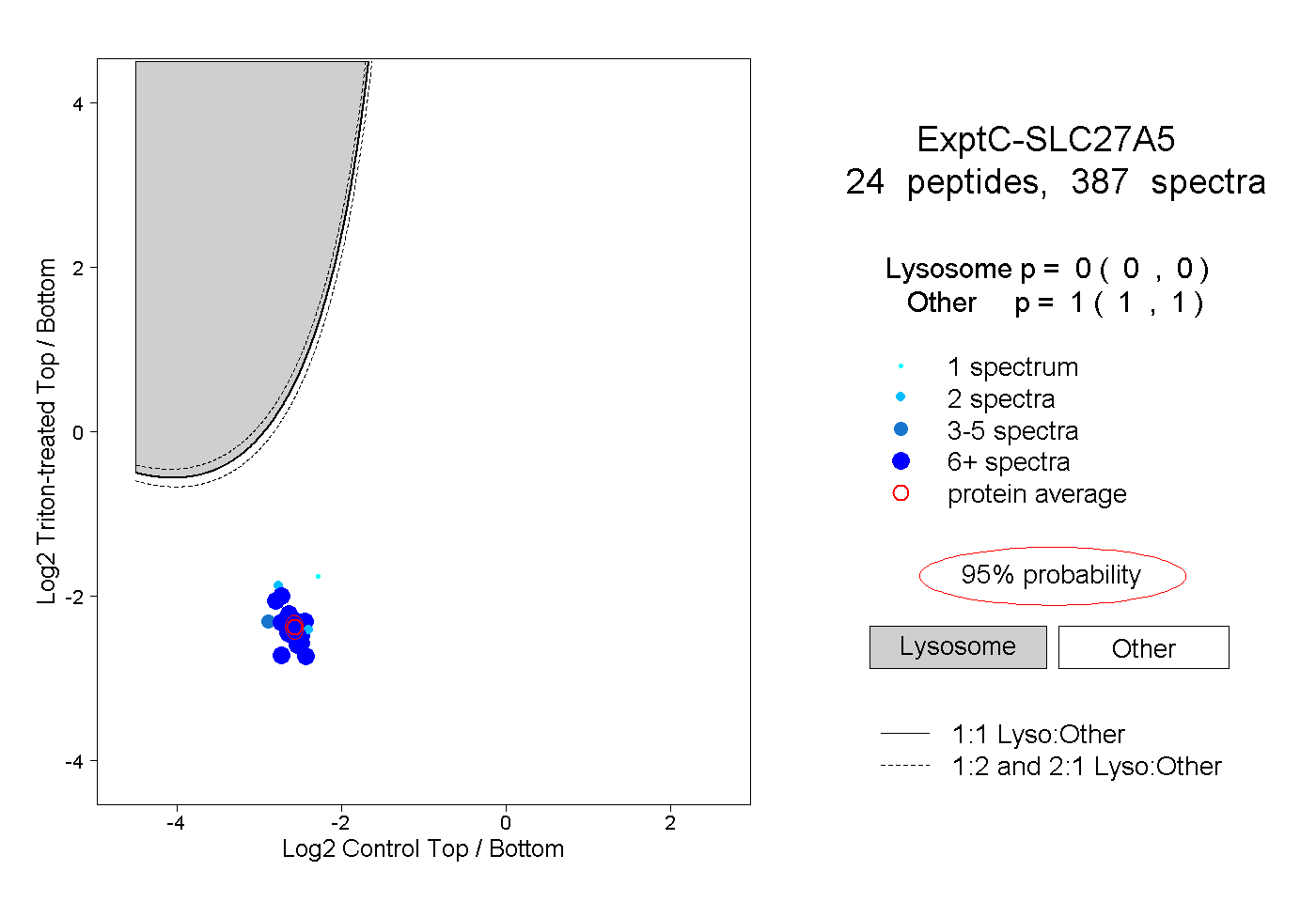 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
57 spectra |
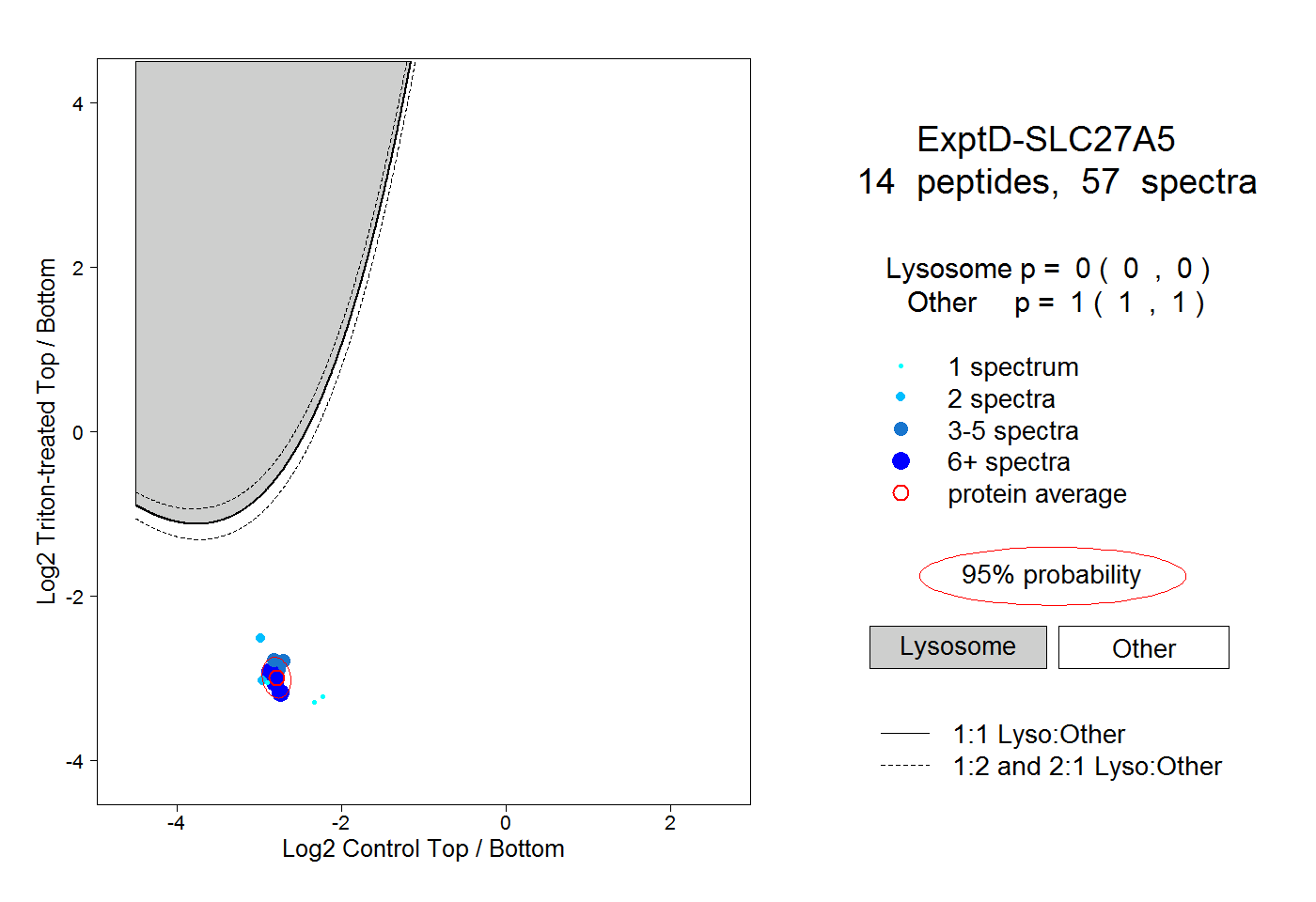 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |