peptides
spectra
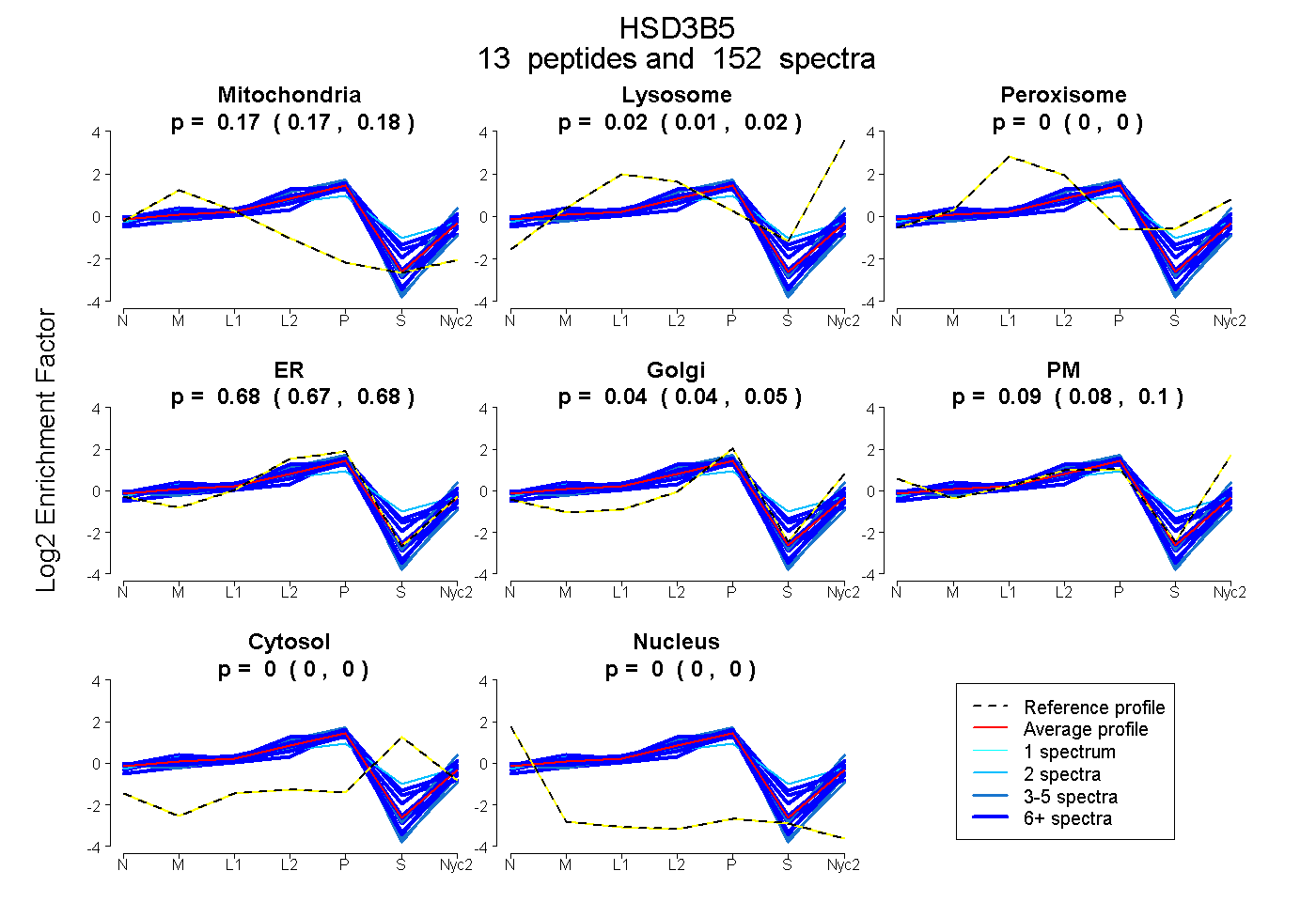
0.172 | 0.176
0.011 | 0.020
0.000 | 0.000
0.669 | 0.681
0.036 | 0.047
0.084 | 0.099
0.000 | 0.000
0.000 | 0.000
peptides
spectra
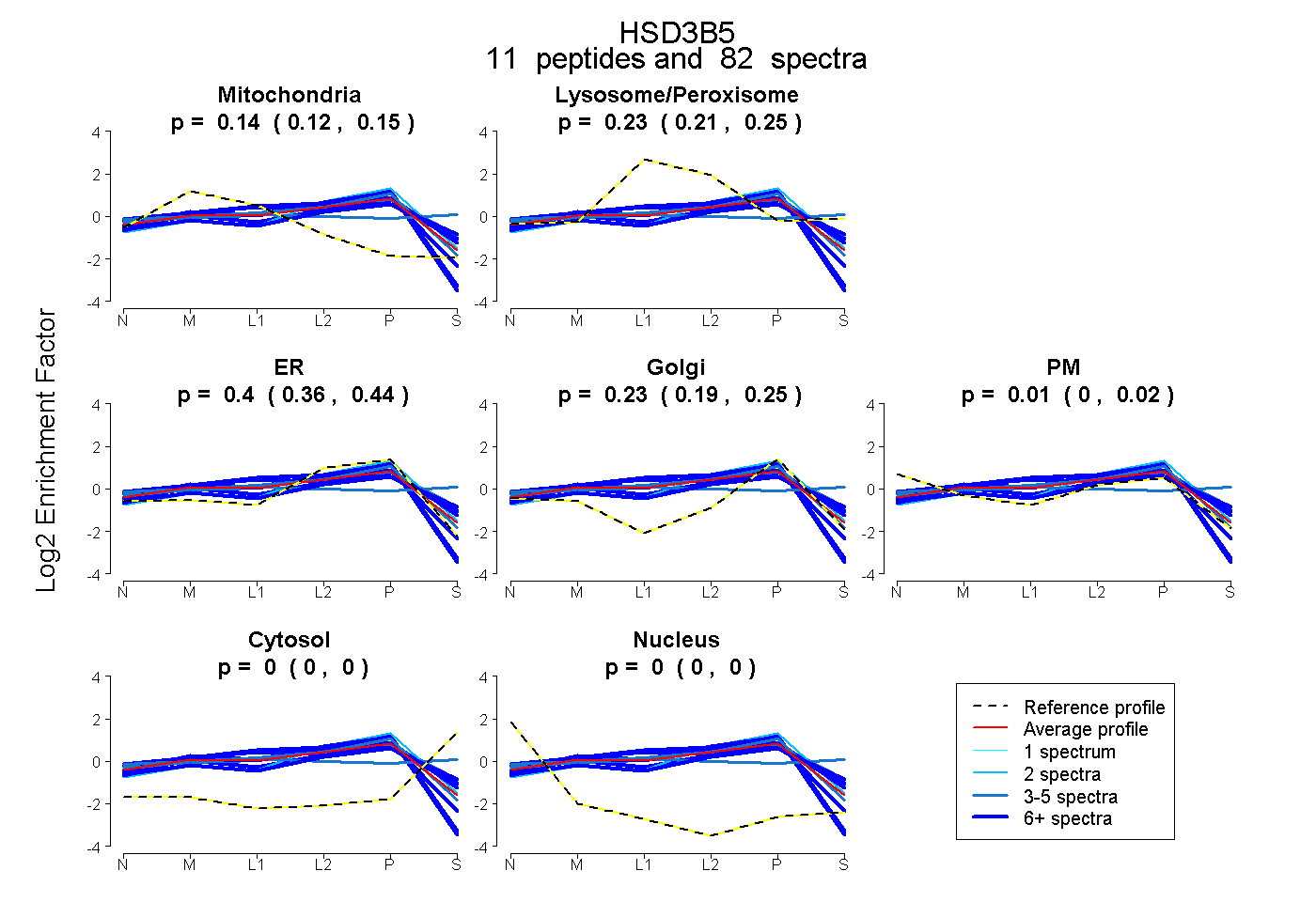
0.122 | 0.148
0.205 | 0.250
0.358 | 0.439
0.186 | 0.254
0.000 | 0.018
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
152 spectra |
 |
0.174 0.172 | 0.176 |
0.016 0.011 | 0.020 |
0.000 0.000 | 0.000 |
0.676 0.669 | 0.681 |
0.042 0.036 | 0.047 |
0.092 0.084 | 0.099 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
82 spectra |
 |
0.136 0.122 | 0.148 |
0.232 0.205 | 0.250 |
0.400 0.358 | 0.439 |
0.226 0.186 | 0.254 |
0.006 0.000 | 0.018 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 3 spectra, ESTWSNPYPYSK | 0.000 | 0.452 | 0.000 | 0.495 | 0.053 | 0.000 | 0.000 | |||
| 12 spectra, IVQMLVQEK | 0.078 | 0.321 | 0.301 | 0.300 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, ELQEVR | 0.184 | 0.000 | 0.816 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, TSEWIGTLVEQHR | 0.024 | 0.338 | 0.071 | 0.482 | 0.000 | 0.086 | 0.000 | |||
| 5 spectra, QTILDVNVK | 0.107 | 0.203 | 0.489 | 0.165 | 0.036 | 0.000 | 0.000 | |||
| 2 spectra, ETILNDR | 0.000 | 0.200 | 0.537 | 0.263 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, PGWSCLVTGAGGFLGQR | 0.033 | 0.371 | 0.000 | 0.047 | 0.298 | 0.251 | 0.000 | |||
| 12 spectra, GDIVDAQFLR | 0.183 | 0.000 | 0.817 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, NGGTLHTCALR | 0.068 | 0.425 | 0.064 | 0.247 | 0.196 | 0.000 | 0.000 | |||
| 7 spectra, AVLAANGSILK | 0.234 | 0.102 | 0.590 | 0.000 | 0.074 | 0.000 | 0.000 | |||
| 12 spectra, DLGYEPLVSWEEAK | 0.041 | 0.379 | 0.000 | 0.580 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
427 spectra |
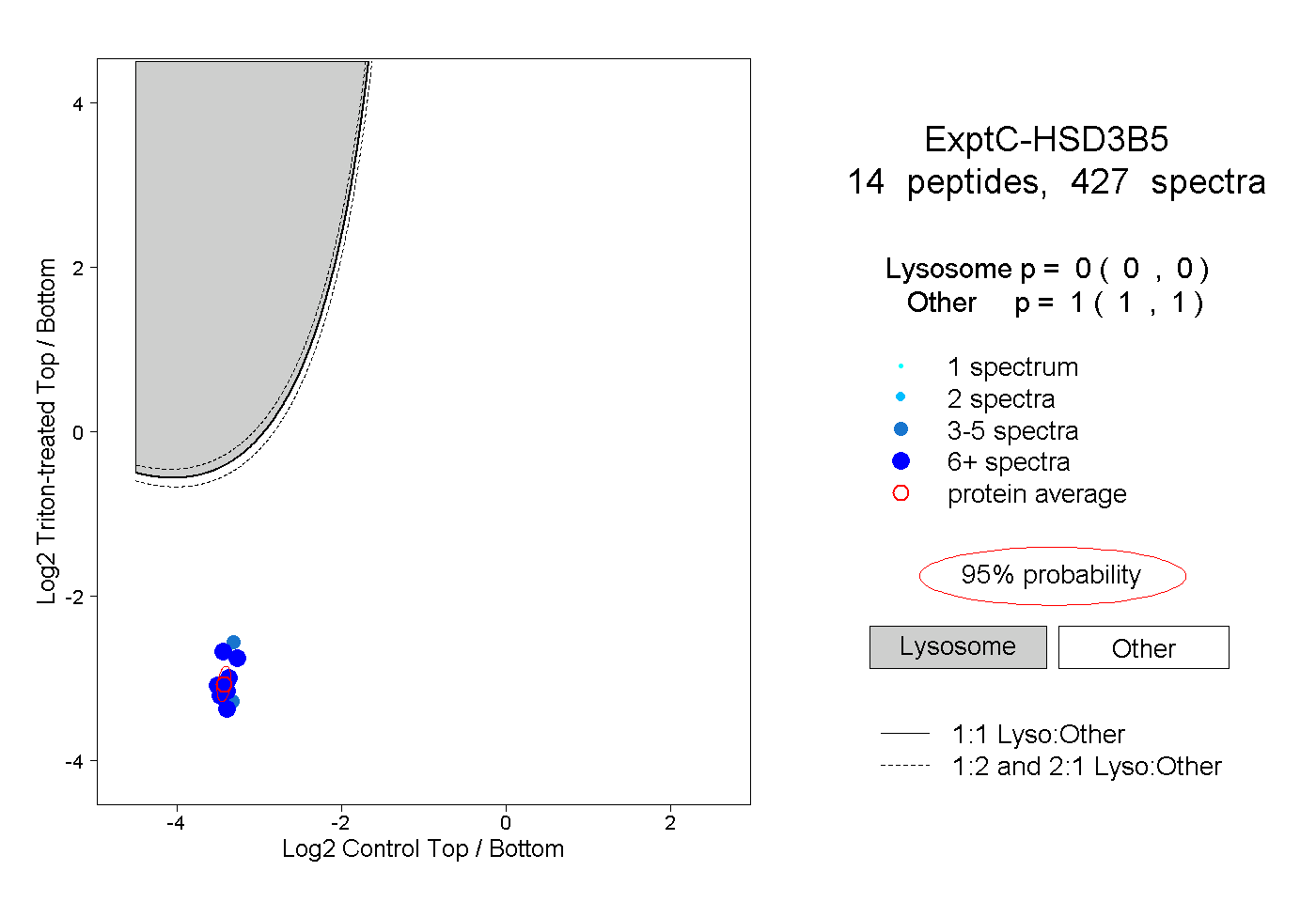 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
41 spectra |
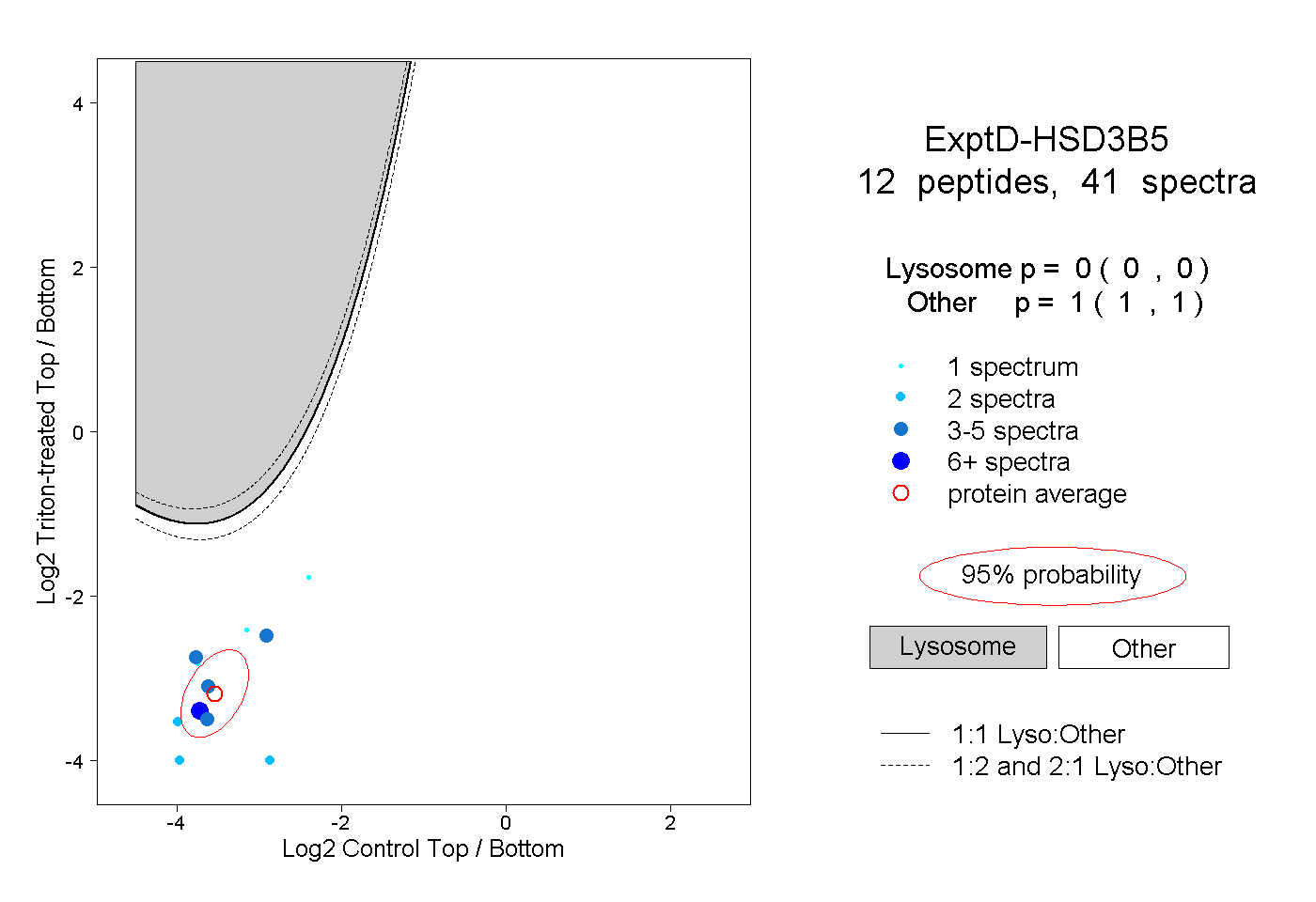 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |