peptides
spectra
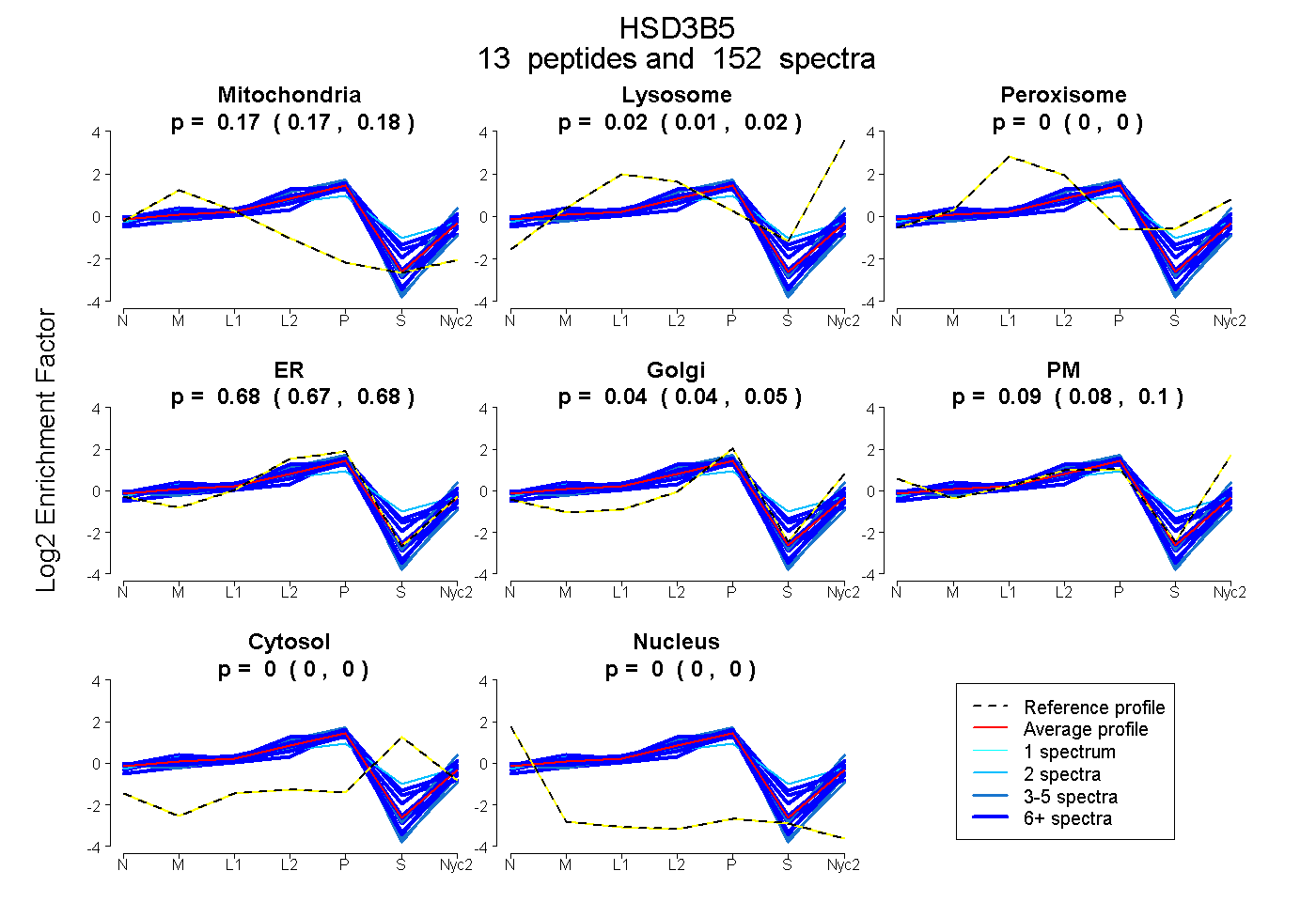
0.172 | 0.176
0.011 | 0.020
0.000 | 0.000
0.669 | 0.681
0.036 | 0.047
0.084 | 0.099
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
152 spectra |
 |
0.174 0.172 | 0.176 |
0.016 0.011 | 0.020 |
0.000 0.000 | 0.000 |
0.676 0.669 | 0.681 |
0.042 0.036 | 0.047 |
0.092 0.084 | 0.099 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 5 spectra, ESTWSNPYPYSK | 0.206 | 0.000 | 0.000 | 0.794 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 11 spectra, IVQMLVQEK | 0.177 | 0.080 | 0.000 | 0.715 | 0.028 | 0.000 | 0.000 | 0.000 | ||
| 24 spectra, ELQEVR | 0.171 | 0.000 | 0.000 | 0.799 | 0.000 | 0.030 | 0.000 | 0.000 | ||
| 3 spectra, ETLDTK | 0.080 | 0.015 | 0.000 | 0.429 | 0.210 | 0.266 | 0.000 | 0.000 | ||
| 17 spectra, TSEWIGTLVEQHR | 0.127 | 0.000 | 0.151 | 0.298 | 0.367 | 0.057 | 0.000 | 0.000 | ||
| 7 spectra, QTILDVNVK | 0.186 | 0.017 | 0.000 | 0.616 | 0.020 | 0.161 | 0.000 | 0.000 | ||
| 8 spectra, NNSIIK | 0.152 | 0.000 | 0.000 | 0.651 | 0.000 | 0.196 | 0.000 | 0.000 | ||
| 6 spectra, ETILNDR | 0.124 | 0.036 | 0.000 | 0.606 | 0.002 | 0.231 | 0.000 | 0.000 | ||
| 2 spectra, PGWSCLVTGAGGFLGQR | 0.130 | 0.000 | 0.268 | 0.261 | 0.251 | 0.000 | 0.090 | 0.000 | ||
| 17 spectra, GDIVDAQFLR | 0.174 | 0.000 | 0.000 | 0.795 | 0.000 | 0.031 | 0.000 | 0.000 | ||
| 40 spectra, NGGTLHTCALR | 0.091 | 0.000 | 0.161 | 0.549 | 0.104 | 0.000 | 0.095 | 0.000 | ||
| 5 spectra, AVLAANGSILK | 0.139 | 0.000 | 0.000 | 0.861 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 7 spectra, DLGYEPLVSWEEAK | 0.142 | 0.000 | 0.033 | 0.568 | 0.143 | 0.000 | 0.113 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
82 spectra |
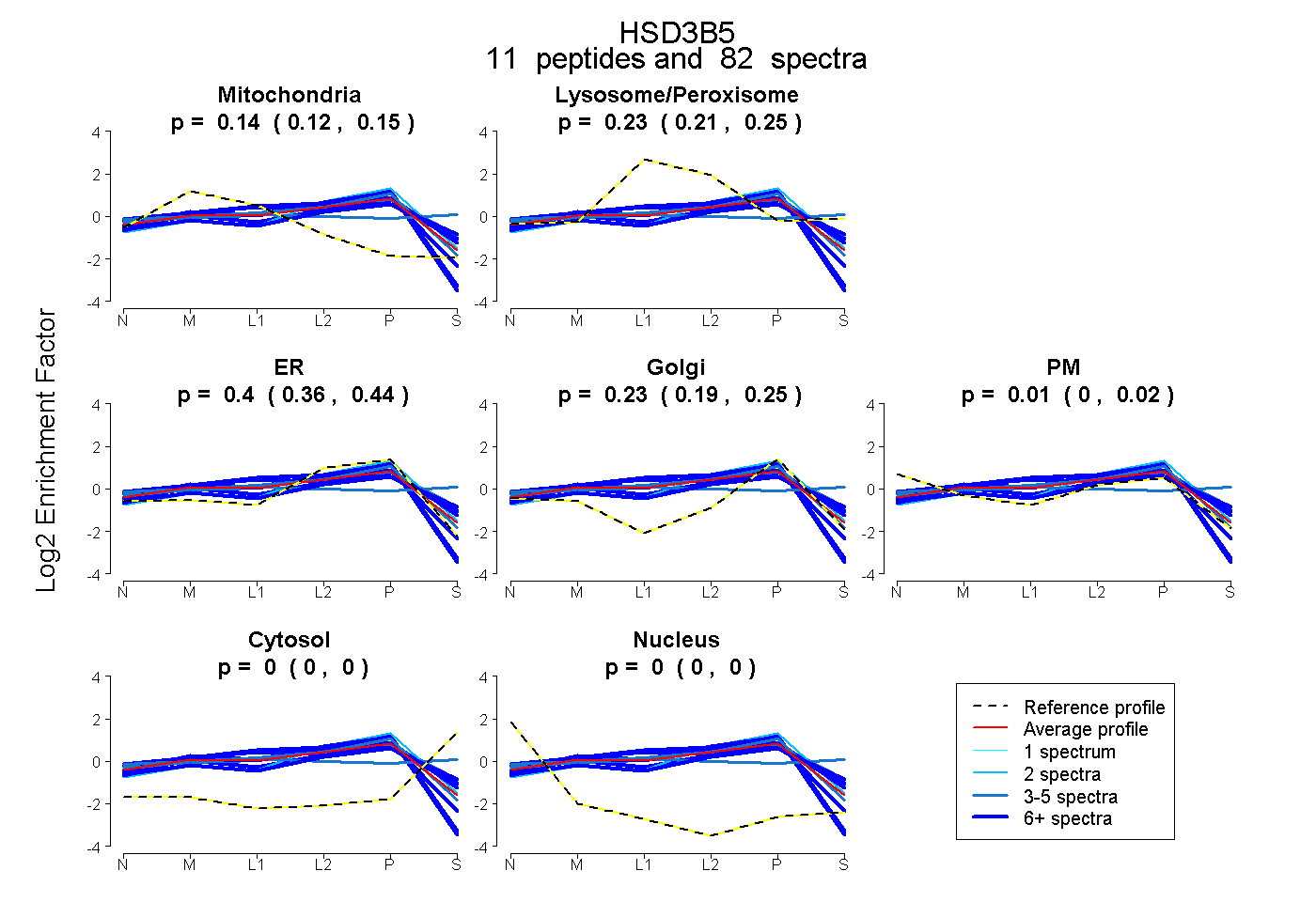 |
0.136 0.122 | 0.148 |
0.232 0.205 | 0.250 |
0.400 0.358 | 0.439 |
0.226 0.186 | 0.254 |
0.006 0.000 | 0.018 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
427 spectra |
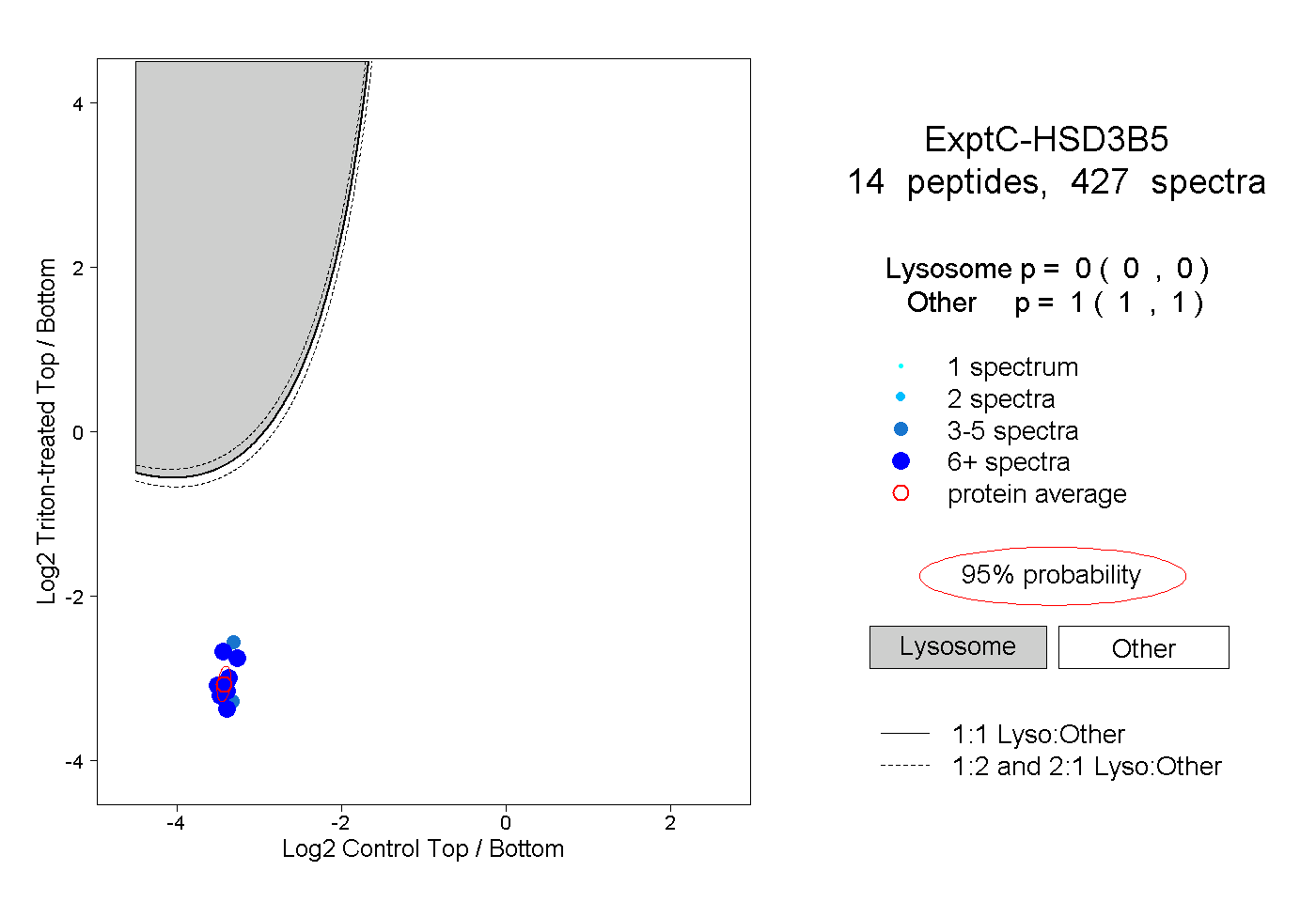 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
41 spectra |
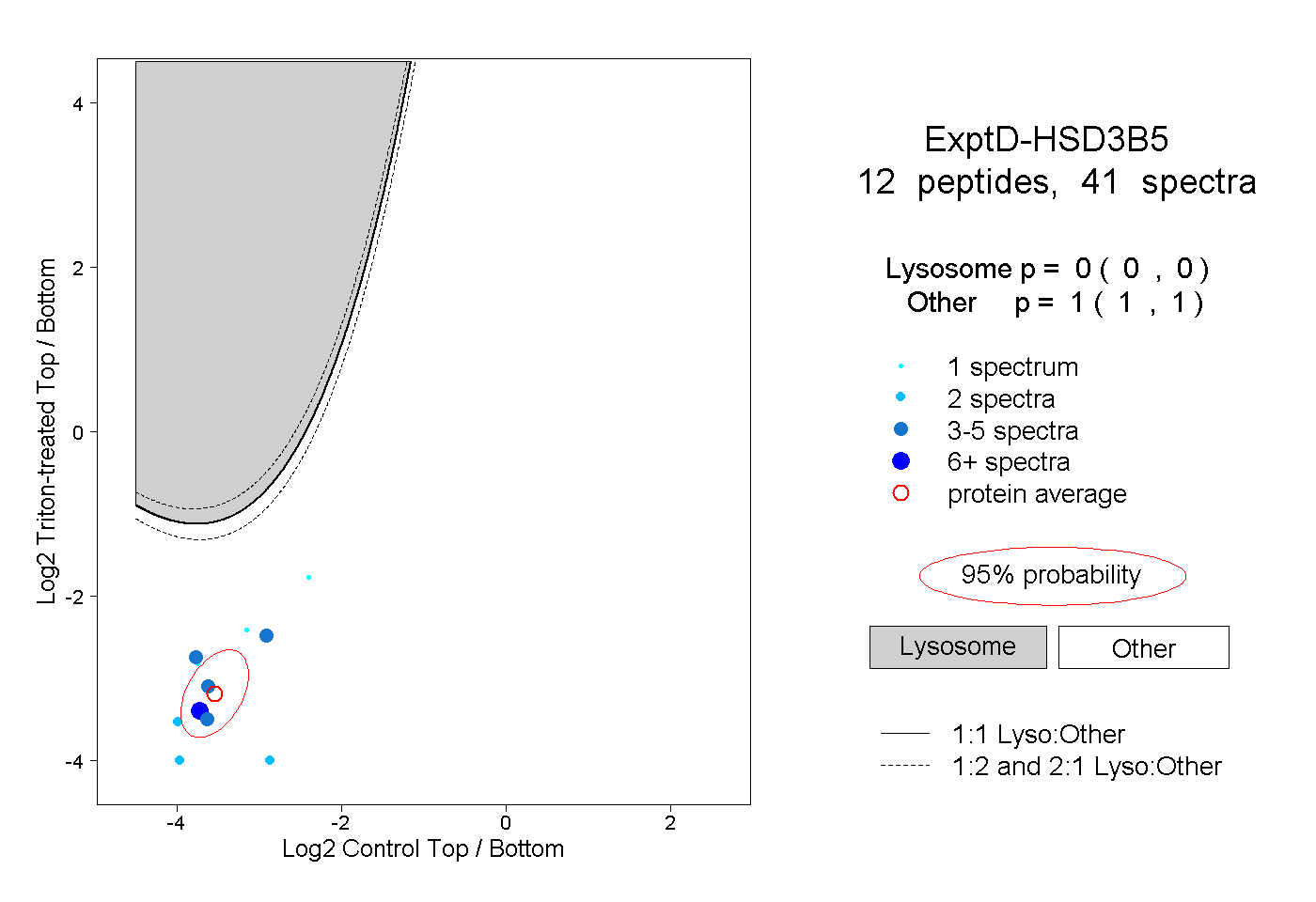 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |