peptides
spectra
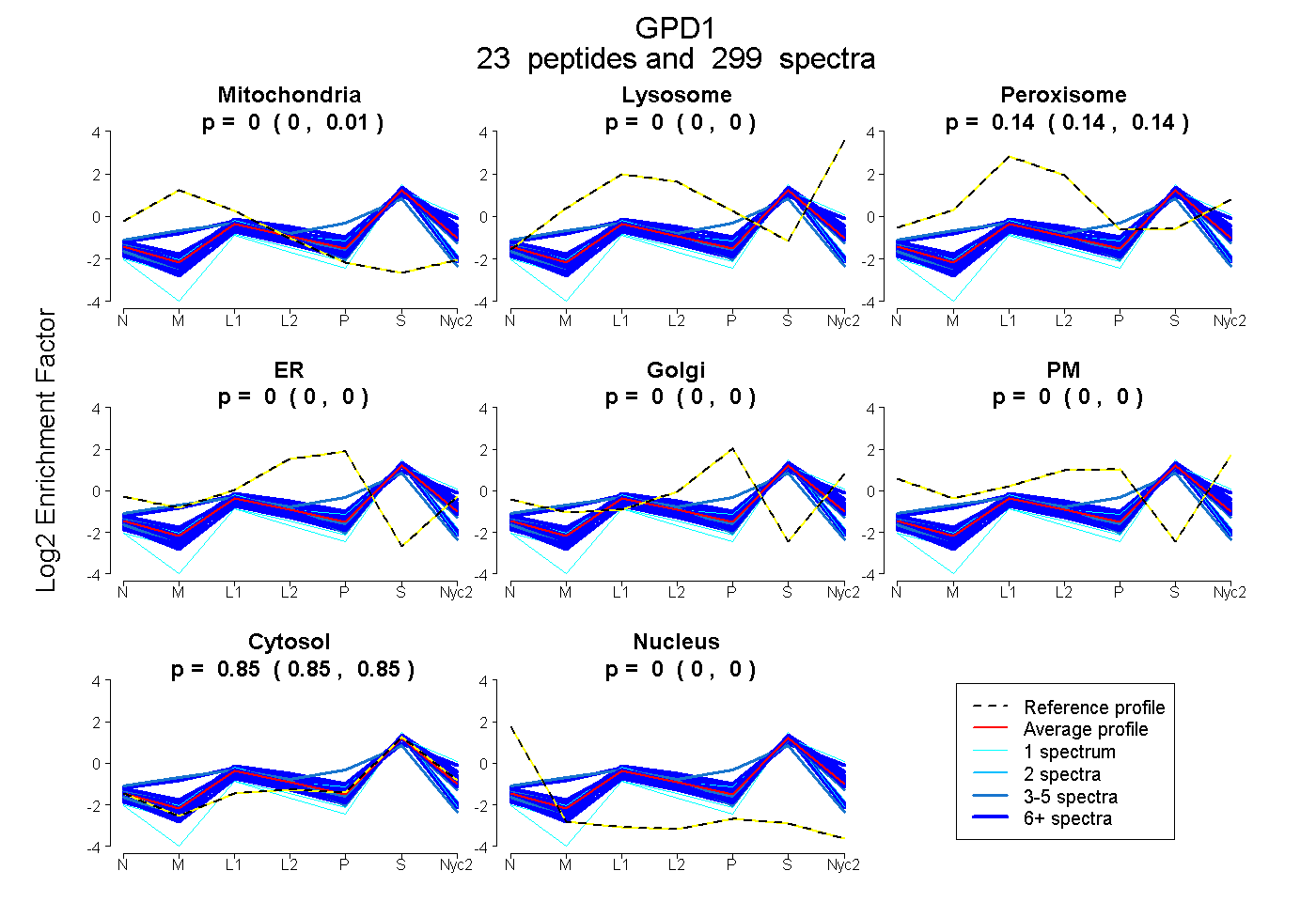
0.003 | 0.006
0.000 | 0.000
0.140 | 0.143
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.852 | 0.855
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
299 spectra |
 |
0.005 0.003 | 0.006 |
0.000 0.000 | 0.000 |
0.142 0.140 | 0.143 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.854 0.852 | 0.855 |
0.000 0.000 | 0.000 |
| 22 spectra, LGLMEMIAFAK | 0.000 | 0.000 | 0.192 | 0.000 | 0.000 | 0.000 | 0.808 | 0.000 | ||
| 22 spectra, GIDEGPDGLK | 0.000 | 0.000 | 0.177 | 0.000 | 0.000 | 0.000 | 0.823 | 0.000 | ||
| 4 spectra, VCIVGSGNWGSAIAK | 0.093 | 0.000 | 0.111 | 0.000 | 0.000 | 0.000 | 0.797 | 0.000 | ||
| 1 spectrum, NIVAVGAGFCDGLGFGDNTK | 0.000 | 0.120 | 0.100 | 0.000 | 0.000 | 0.000 | 0.780 | 0.000 | ||
| 42 spectra, LQGPQTAR | 0.000 | 0.000 | 0.104 | 0.000 | 0.000 | 0.000 | 0.896 | 0.000 | ||
| 12 spectra, GIDEGPNGLK | 0.000 | 0.000 | 0.232 | 0.000 | 0.000 | 0.000 | 0.768 | 0.000 | ||
| 1 spectrum, LPPNVVAVPDVVQAATGADILVFVVPHQFIGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.949 | 0.051 | ||
| 8 spectra, EMLNGQK | 0.000 | 0.000 | 0.154 | 0.000 | 0.000 | 0.000 | 0.846 | 0.000 | ||
| 3 spectra, VCYEGQPVGEFICCLQNHPEHM | 0.241 | 0.000 | 0.054 | 0.087 | 0.000 | 0.000 | 0.618 | 0.000 | ||
| 18 spectra, ELMQTPNFR | 0.000 | 0.000 | 0.128 | 0.000 | 0.000 | 0.000 | 0.872 | 0.000 | ||
| 24 spectra, ELHSILQHK | 0.000 | 0.000 | 0.199 | 0.000 | 0.000 | 0.000 | 0.801 | 0.000 | ||
| 1 spectrum, FCETTIGCK | 0.017 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.981 | 0.002 | ||
| 7 spectra, IVGSNASQLAHFDPR | 0.083 | 0.104 | 0.171 | 0.000 | 0.000 | 0.000 | 0.643 | 0.000 | ||
| 9 spectra, SIEQLEK | 0.012 | 0.000 | 0.138 | 0.000 | 0.000 | 0.000 | 0.850 | 0.000 | ||
| 6 spectra, FPLFTAVYK | 0.000 | 0.015 | 0.031 | 0.000 | 0.000 | 0.000 | 0.955 | 0.000 | ||
| 11 spectra, DPAQGQLLK | 0.000 | 0.000 | 0.138 | 0.000 | 0.000 | 0.000 | 0.862 | 0.000 | ||
| 29 spectra, VTMWVFEEDIGGR | 0.000 | 0.000 | 0.083 | 0.000 | 0.000 | 0.000 | 0.917 | 0.000 | ||
| 17 spectra, VAEAFAR | 0.000 | 0.000 | 0.105 | 0.000 | 0.000 | 0.000 | 0.878 | 0.017 | ||
| 9 spectra, ANTIGISLIK | 0.000 | 0.000 | 0.172 | 0.000 | 0.000 | 0.000 | 0.828 | 0.000 | ||
| 9 spectra, ICDQLK | 0.080 | 0.000 | 0.030 | 0.000 | 0.000 | 0.000 | 0.890 | 0.000 | ||
| 32 spectra, YLPGHK | 0.058 | 0.000 | 0.154 | 0.000 | 0.000 | 0.000 | 0.788 | 0.000 | ||
| 3 spectra, LTEIINTQHENVK | 0.000 | 0.000 | 0.097 | 0.000 | 0.000 | 0.000 | 0.903 | 0.000 | ||
| 9 spectra, ITVVQEVDTVEICGALK | 0.059 | 0.000 | 0.024 | 0.000 | 0.000 | 0.000 | 0.903 | 0.014 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
116 spectra |
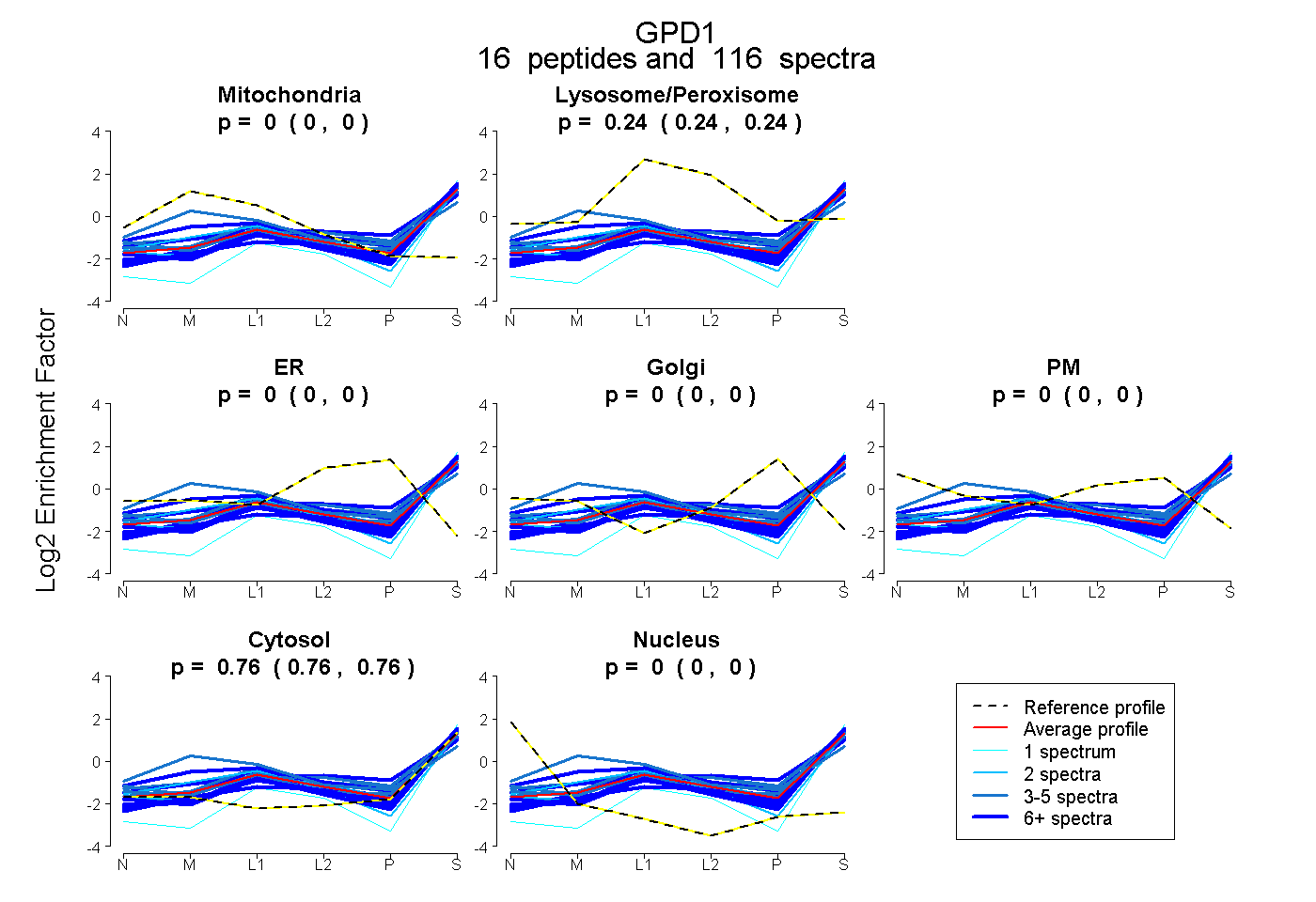 |
0.000 0.000 | 0.000 |
0.242 0.240 | 0.244 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.758 0.756 | 0.760 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
721 spectra |
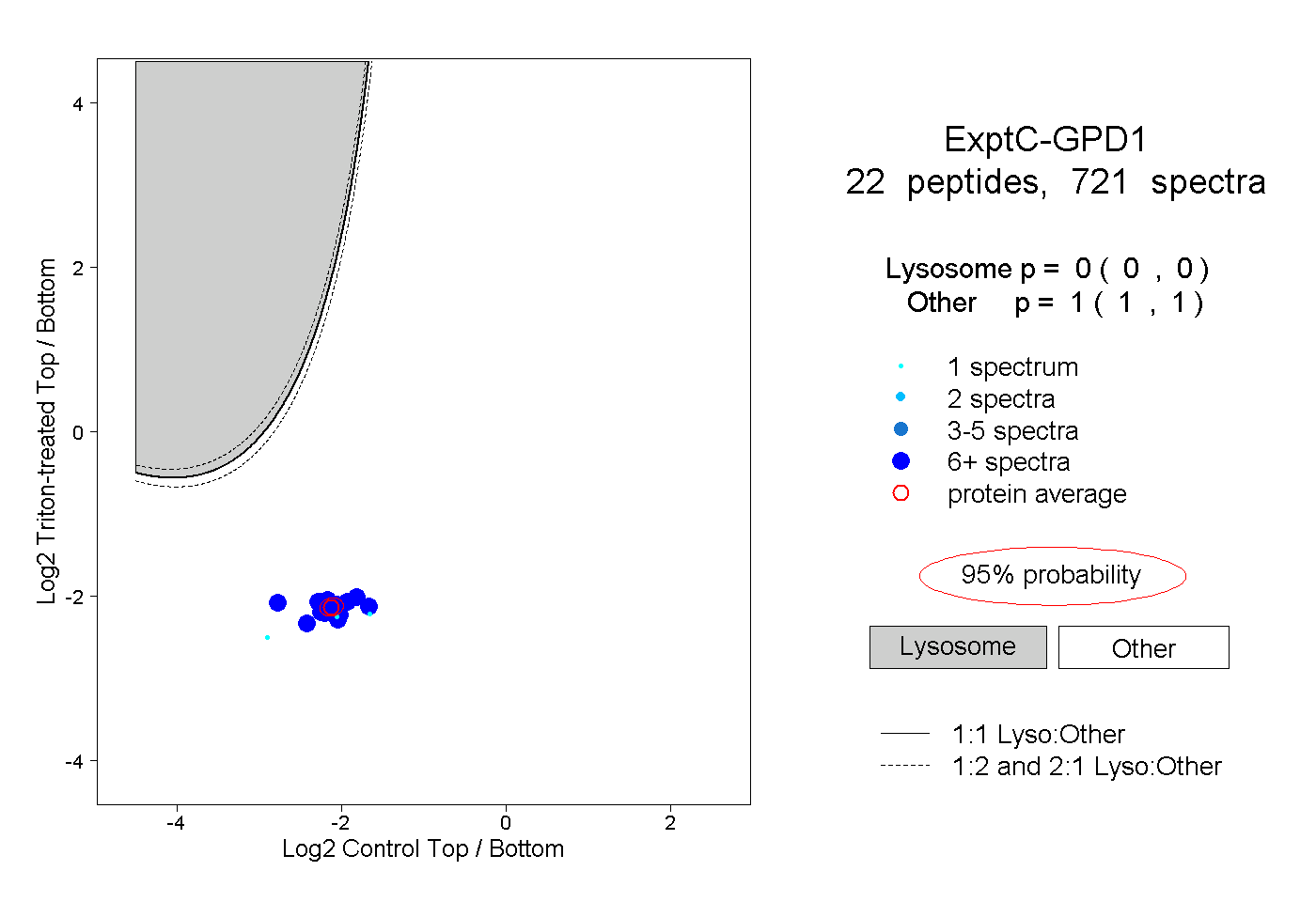 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
85 spectra |
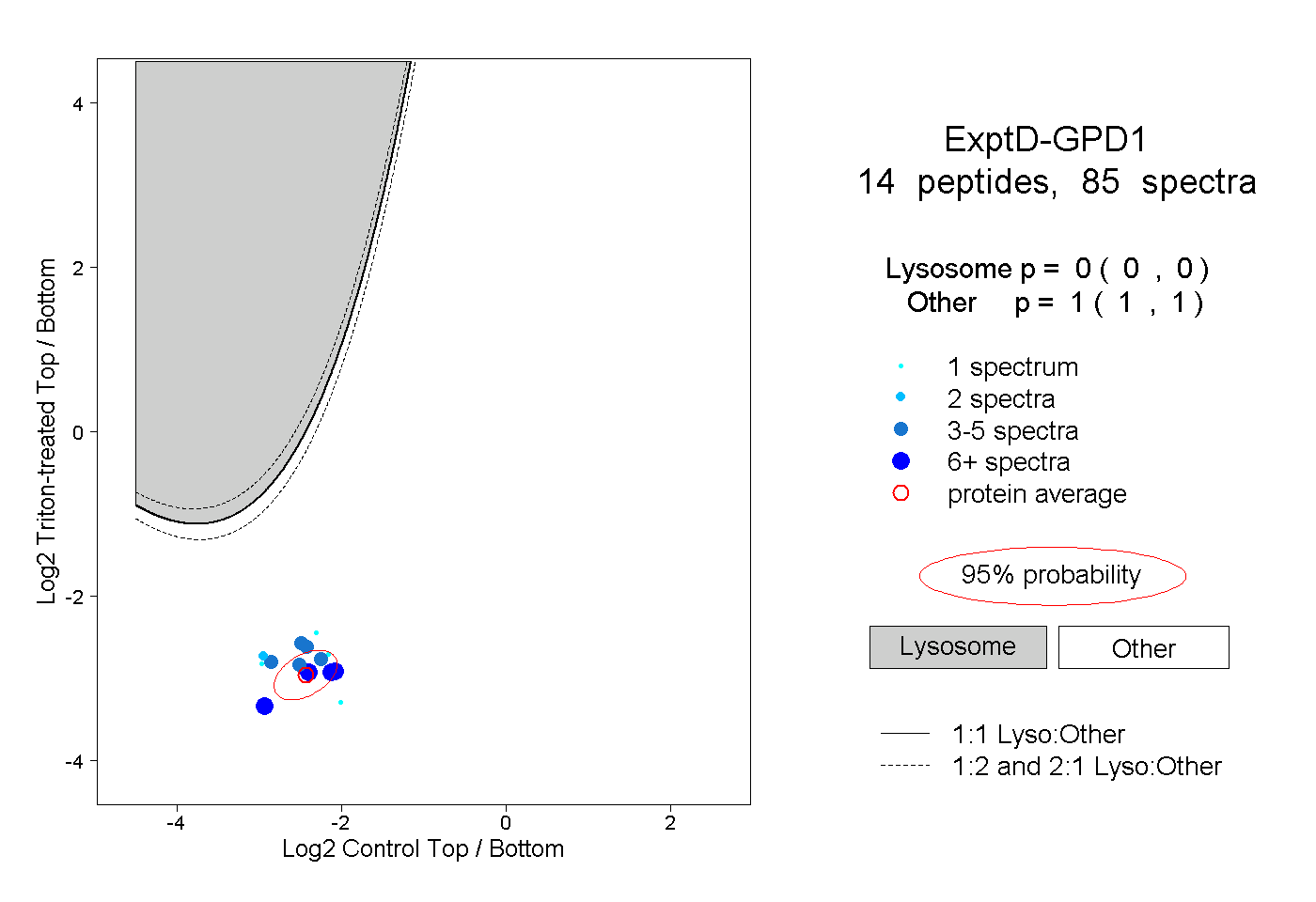 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |