HMGCS2
[ENSRNOP00000026122]
Main page
| | | Plot |
Mito |
Lyso |
|
Perox |
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt A |
 22
22
peptides |
633
spectra |
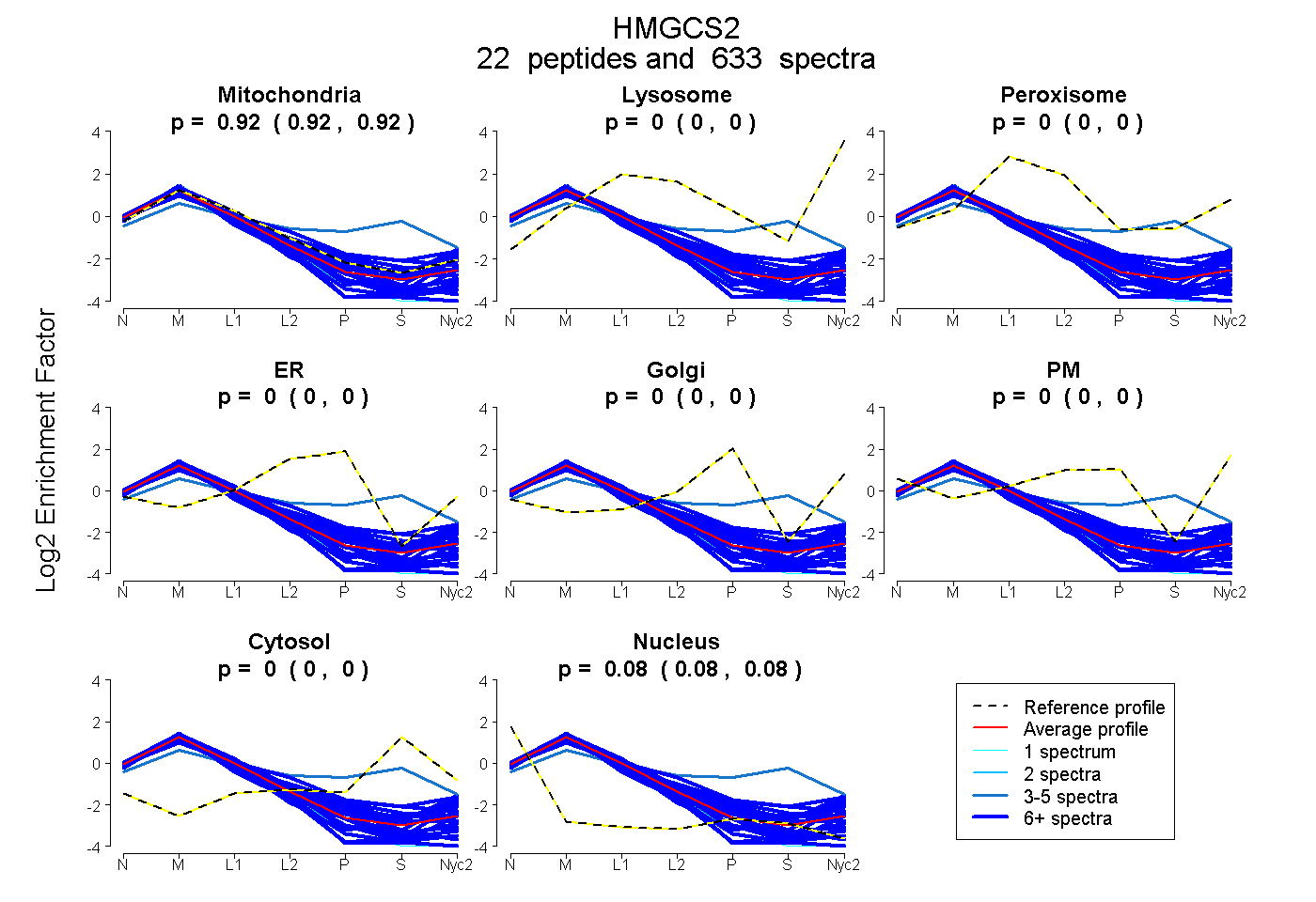 |
0.919
0.918 | 0.919 |
0.000
0.000 | 0.000 |
|
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.081
0.081 | 0.082 |
|
| | | Plot |
Mito |
|
Lyso or Perox |
|
ER |
Golgi |
PM |
Cytosol |
Nucleus |
|
| Expt B |
 20
20
peptides |
313
spectra |
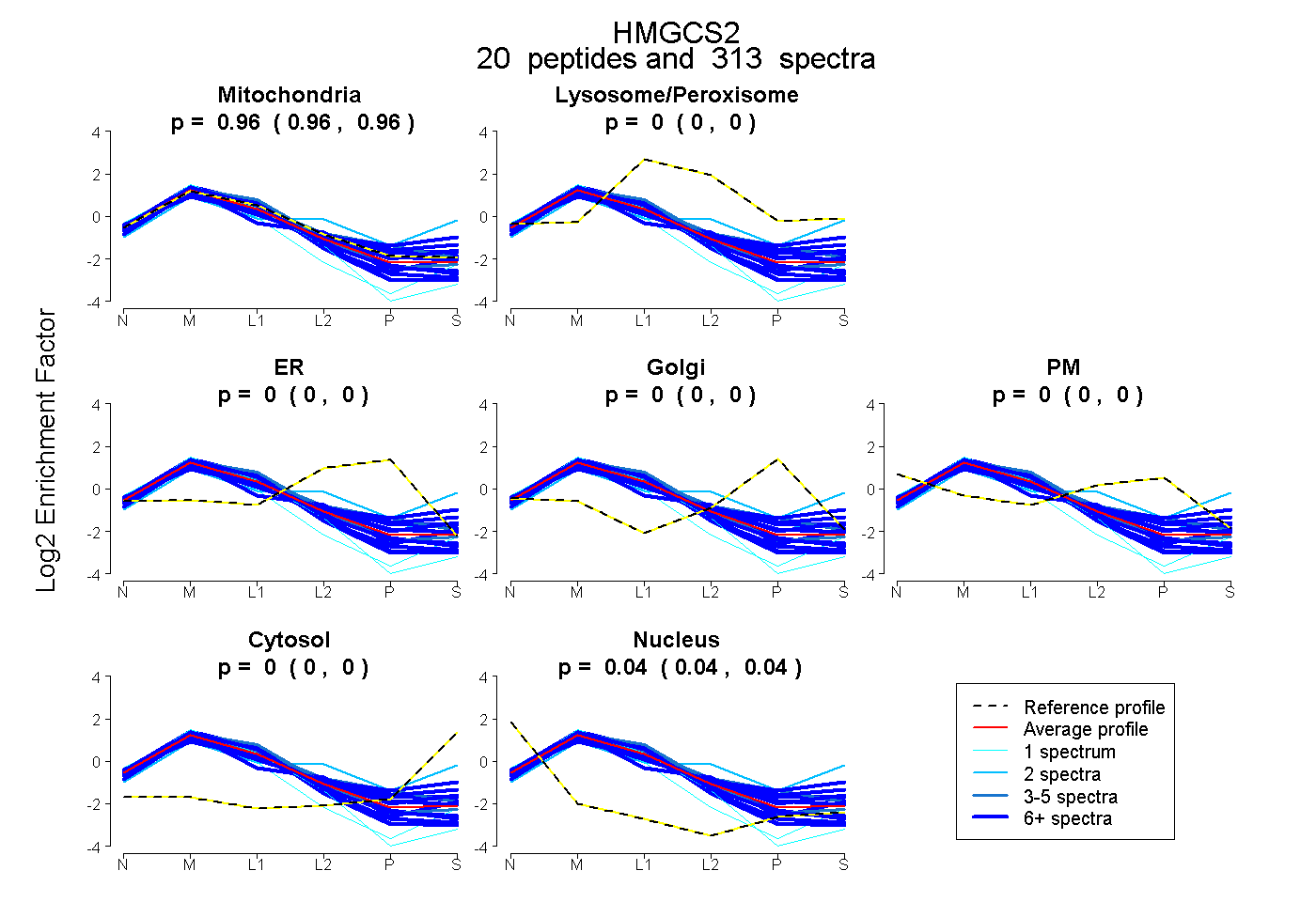 |
0.961
0.960 | 0.962 |
|
0.000
0.000 | 0.000 |
|
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.000
0.000 | 0.000 |
0.039
0.038 | 0.040 |
|
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
| Expt C |
 25
25
peptides |
2120
spectra |
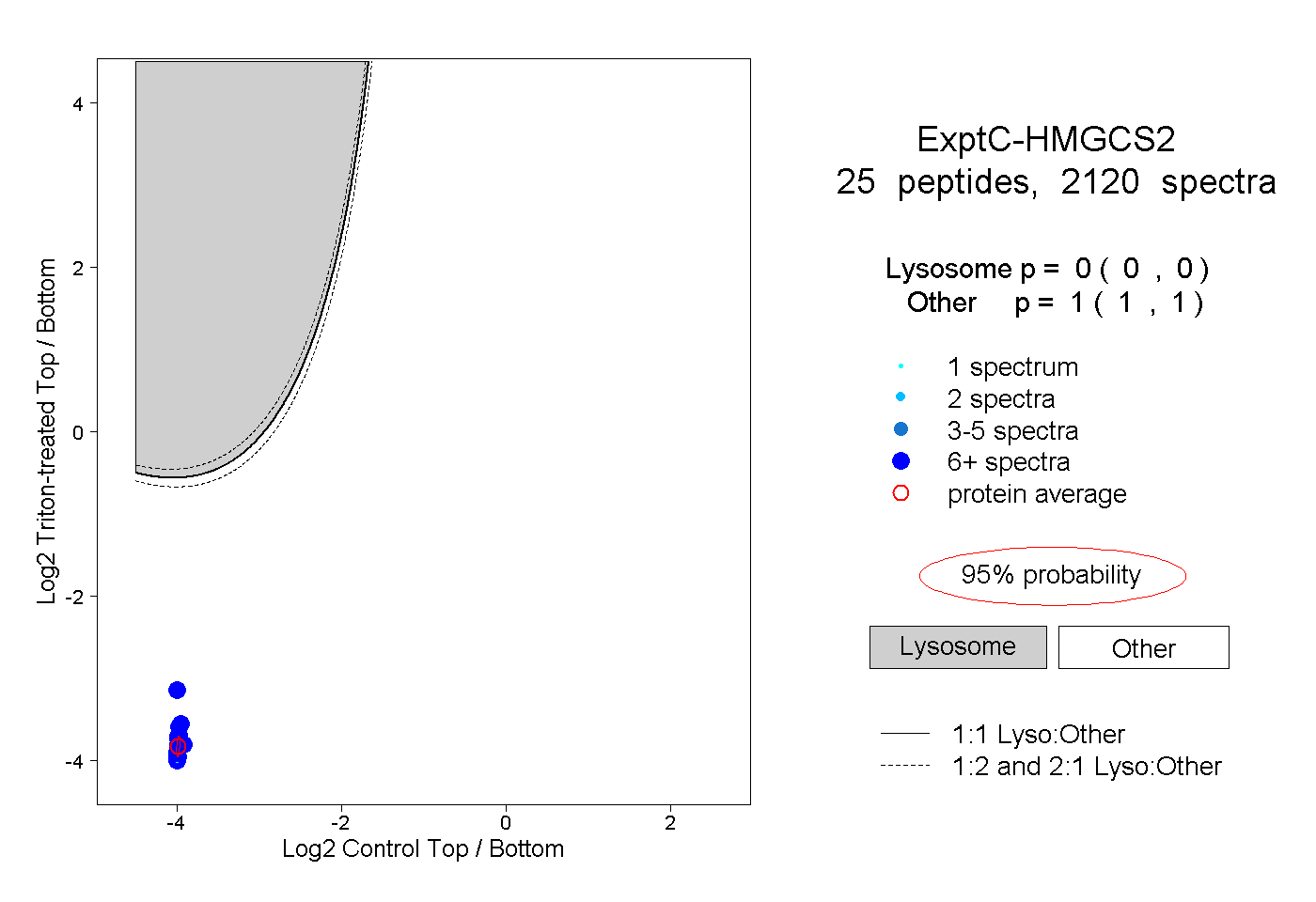 |
|
0.000
0.000 | 0.000 |
|
|
|
|
|
|
|
1.000
1.000 | 1.000 |
| | | Plot |
|
Lyso |
|
|
|
|
|
|
|
Other |
| Expt D |
 18
18
peptides |
170
spectra |
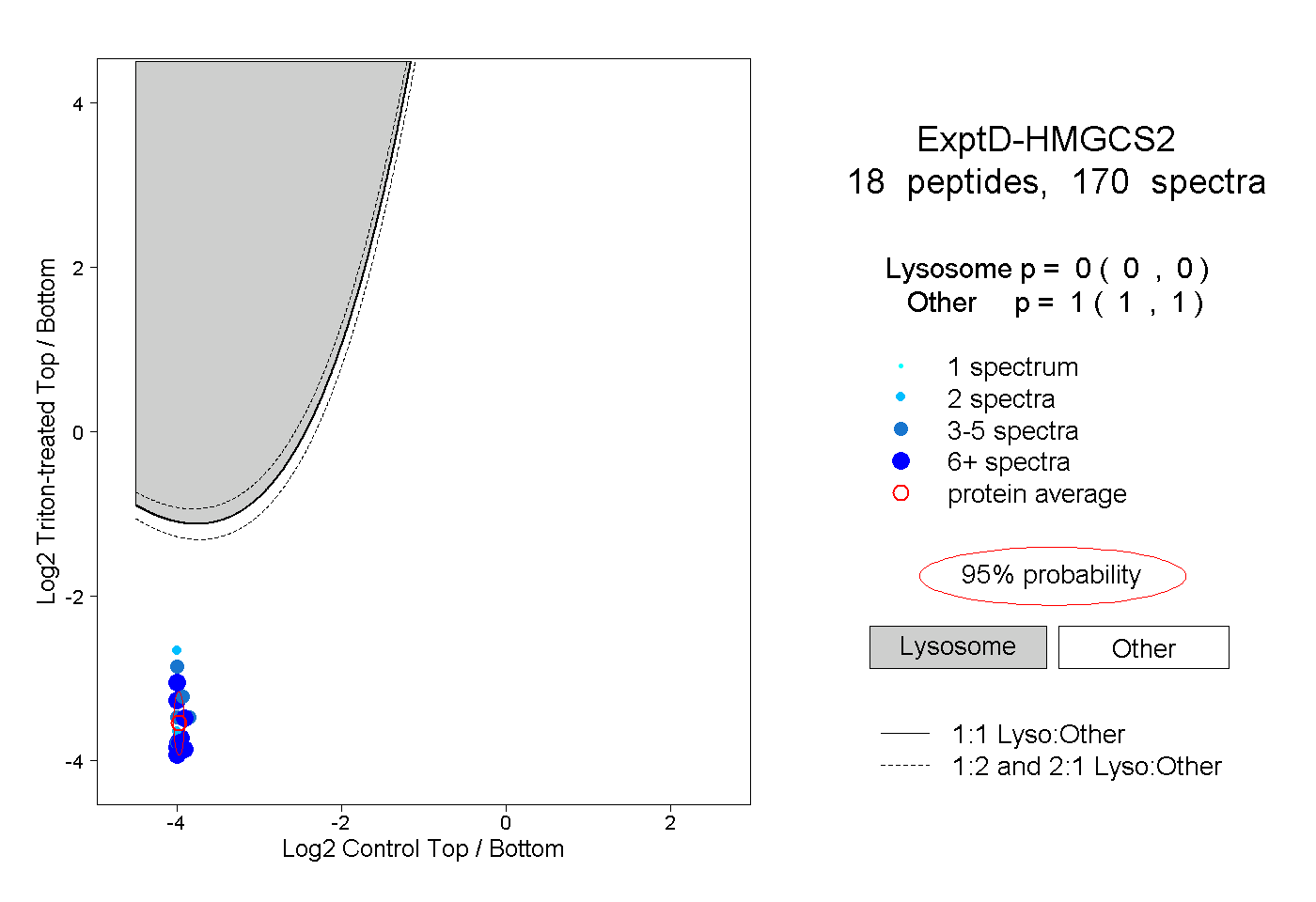 |
|
0.000
0.000 | 0.000 |
|
|
|
|
|
|
|
1.000
1.000 | 1.000 |
| 4 spectra, FNNVEAGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, TDTWPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, QNNLYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, CYAAYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, MSPEEFTEIMNQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, DASPGSPLEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 23 spectra, APLVLEQGLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, LVSSVSDLPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 15 spectra, VDEMHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, LMFNDFLSSSSDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, IQNQWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 25 spectra, YTVGLGQTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, ASLDMFNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LEETYTNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, GLEAFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, EQFYHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, LPWDAVGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, LEVGTETIIDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |



