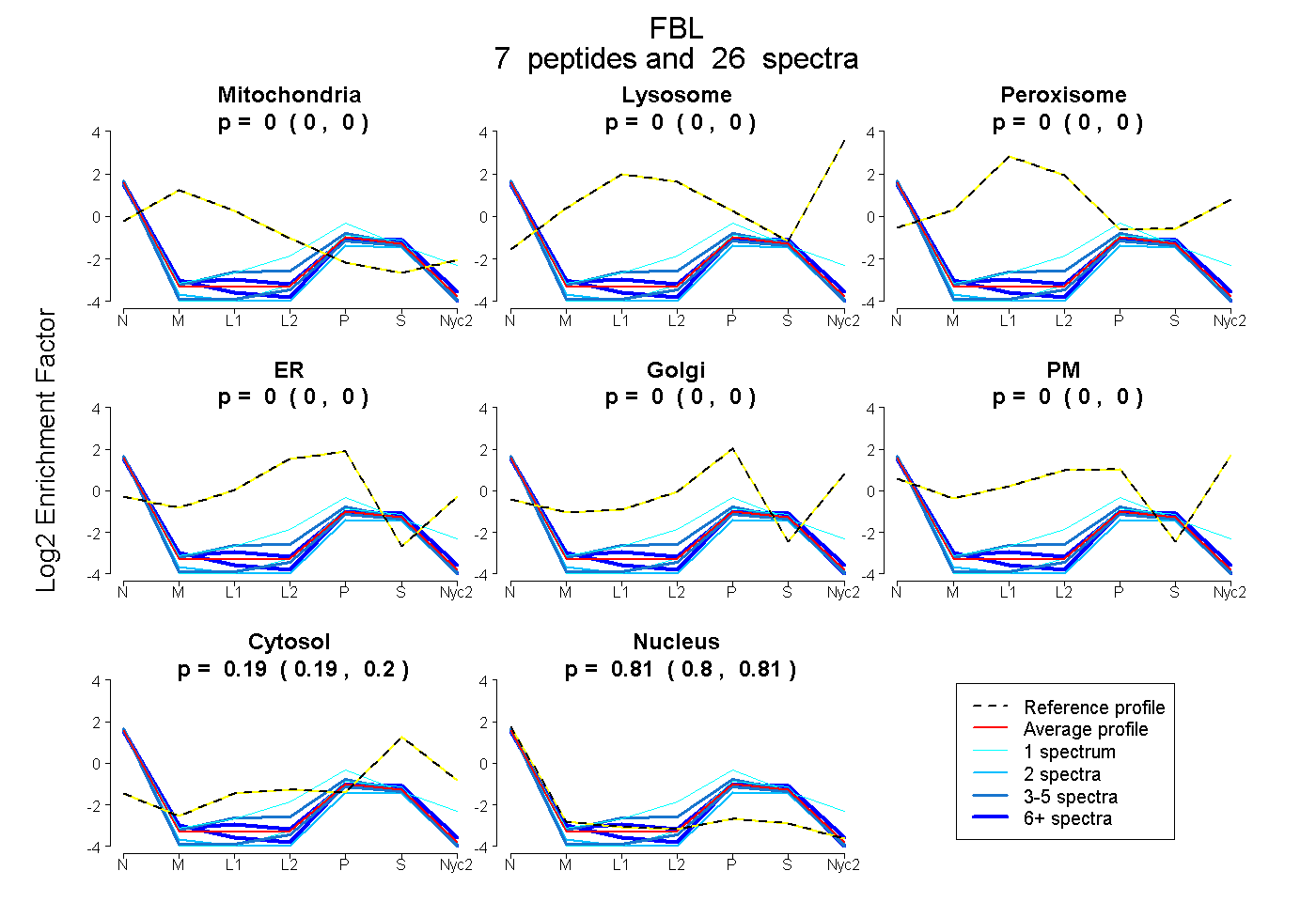
peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.186 | 0.198
0.801 | 0.813
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
26 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.192 0.186 | 0.198 |
0.808 0.801 | 0.813 |
| 1 spectrum, HEGVFICR | 0.000 | 0.000 | 0.000 | 0.000 | 0.247 | 0.000 | 0.178 | 0.575 | ||
| 1 spectrum, NGGHFVISIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.165 | 0.835 | ||
| 7 spectra, AWNPFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.145 | 0.855 | ||
| 2 spectra, IVALNAHTFLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.083 | 0.917 | ||
| 8 spectra, DHAVVVGVYRPPPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.244 | 0.756 | ||
| 4 spectra, DLINLAK | 0.000 | 0.000 | 0.000 | 0.065 | 0.000 | 0.000 | 0.189 | 0.746 | ||
| 3 spectra, TNIIPVIEDAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.125 | 0.875 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
10 spectra |
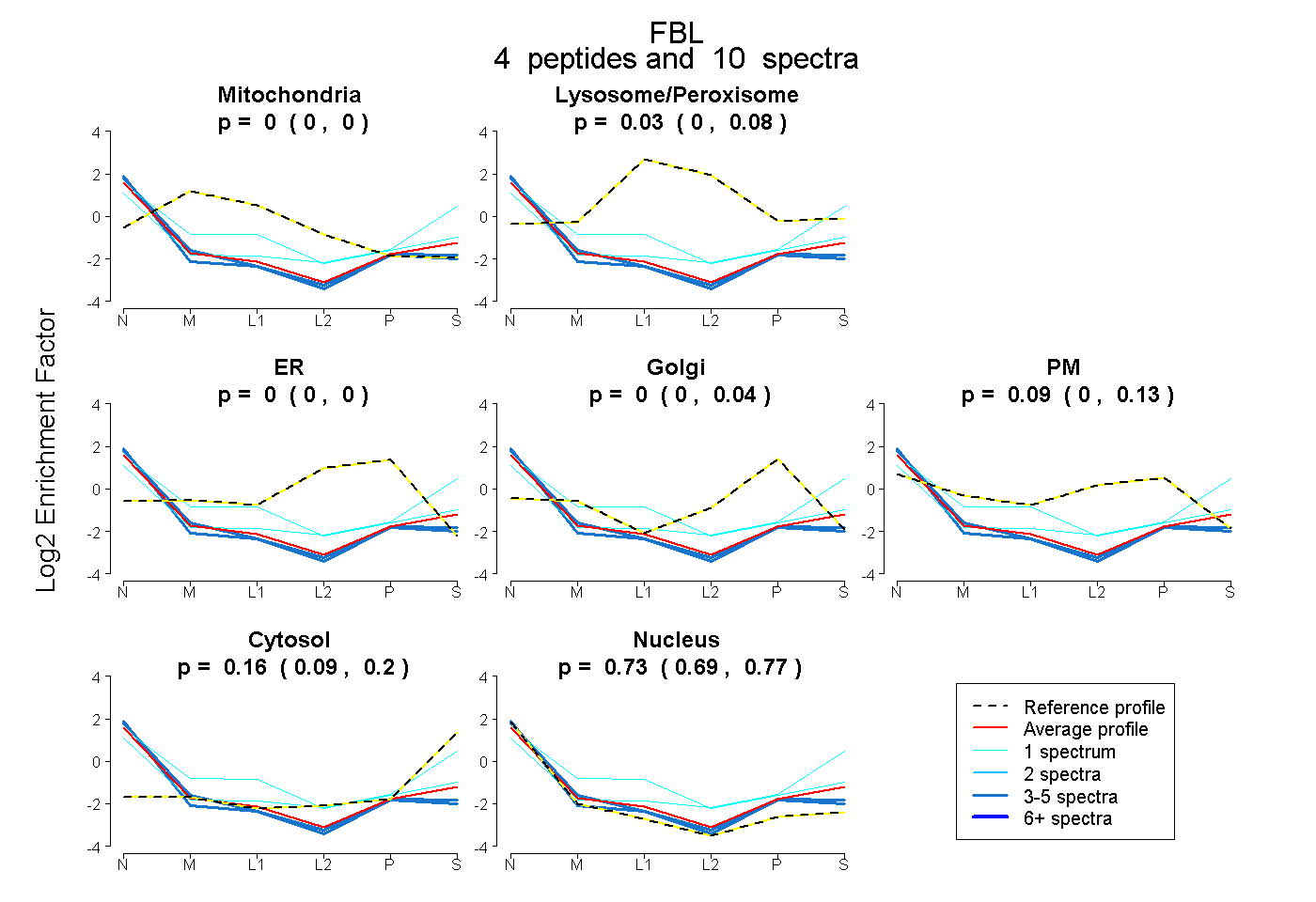 |
0.000 0.000 | 0.000 |
0.030 0.000 | 0.076 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.042 |
0.086 0.000 | 0.128 |
0.157 0.087 | 0.202 |
0.727 0.691 | 0.769 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
2 spectra |
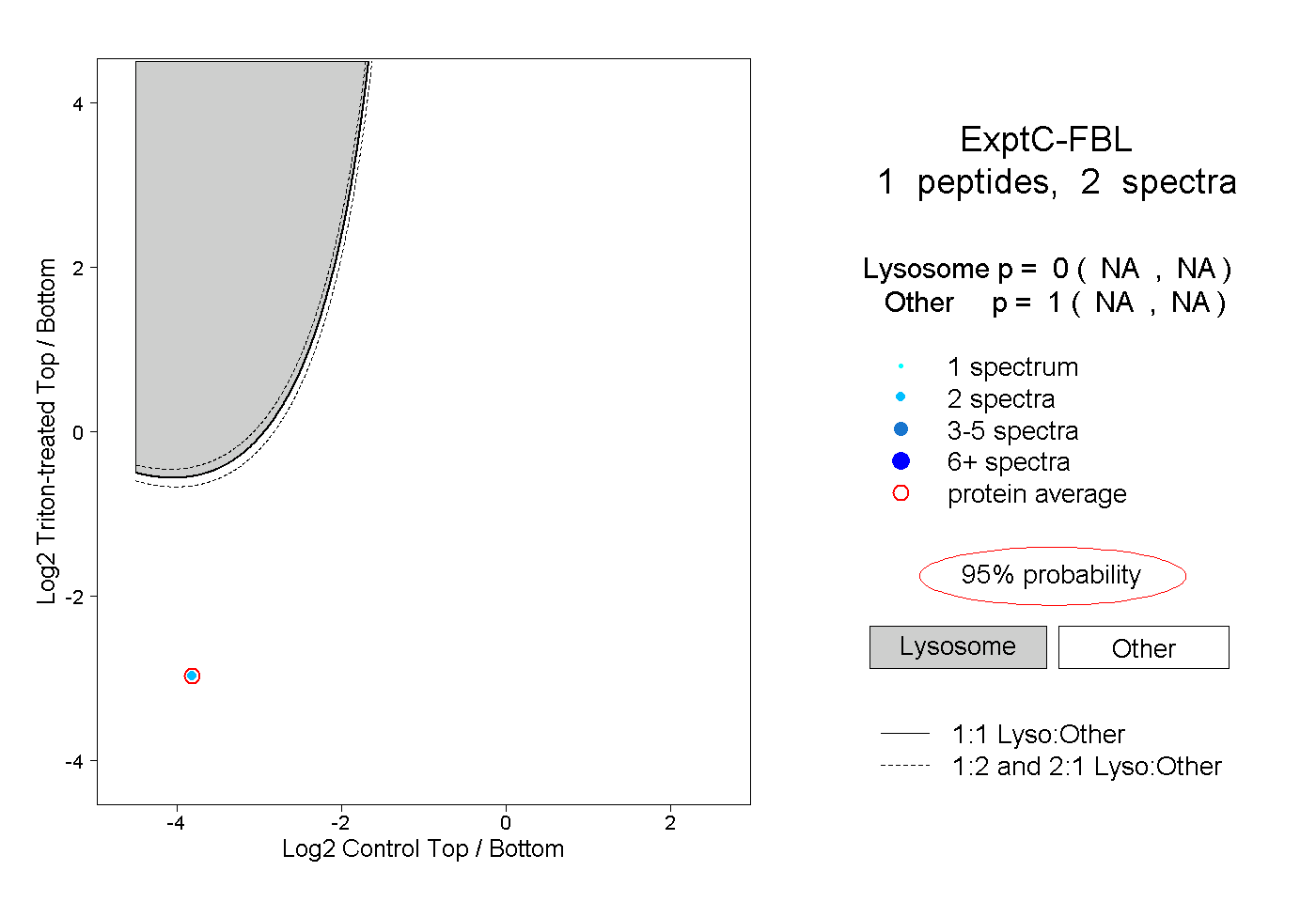 |
0.000 NA | NA |
1.000 NA | NA |