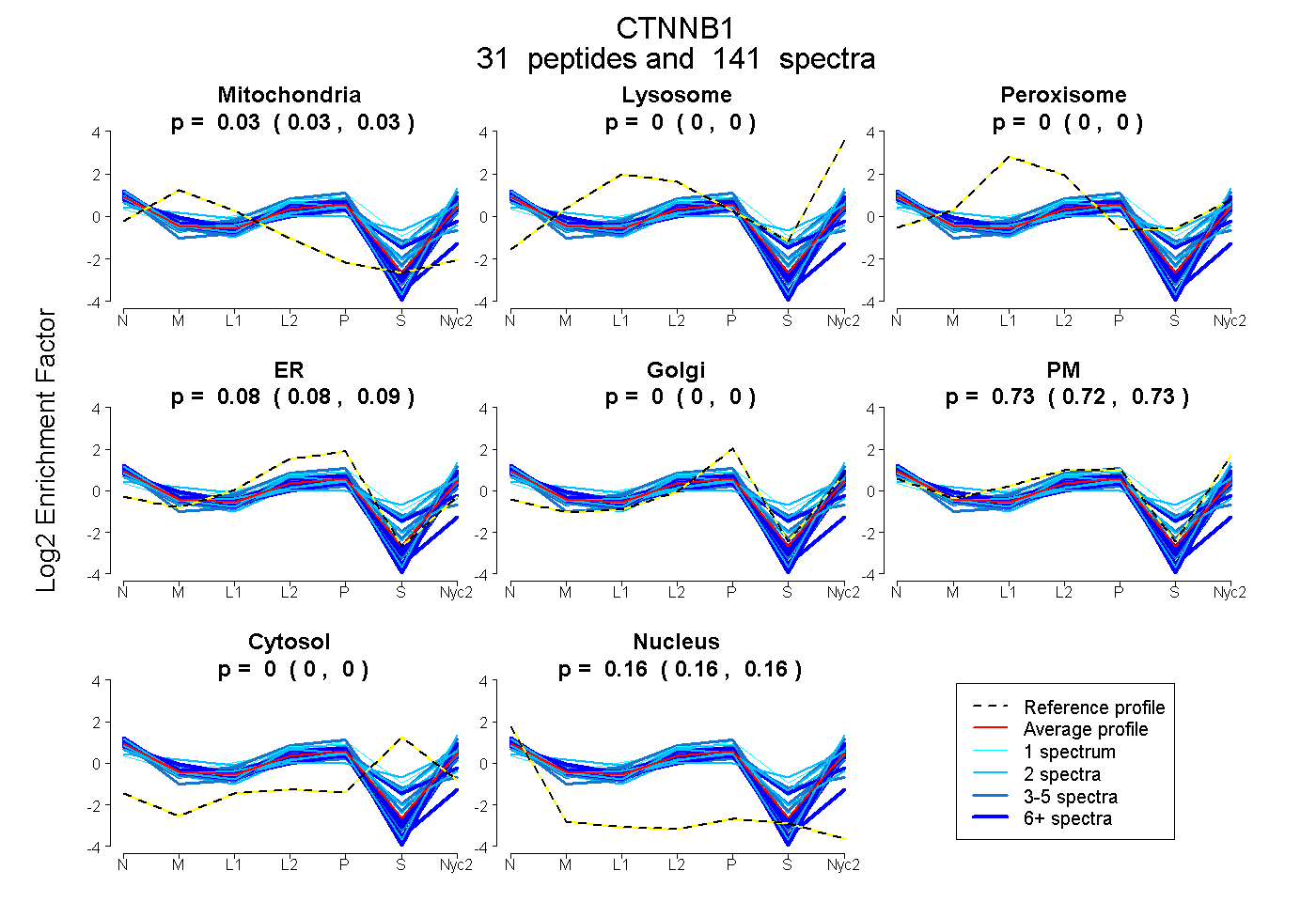
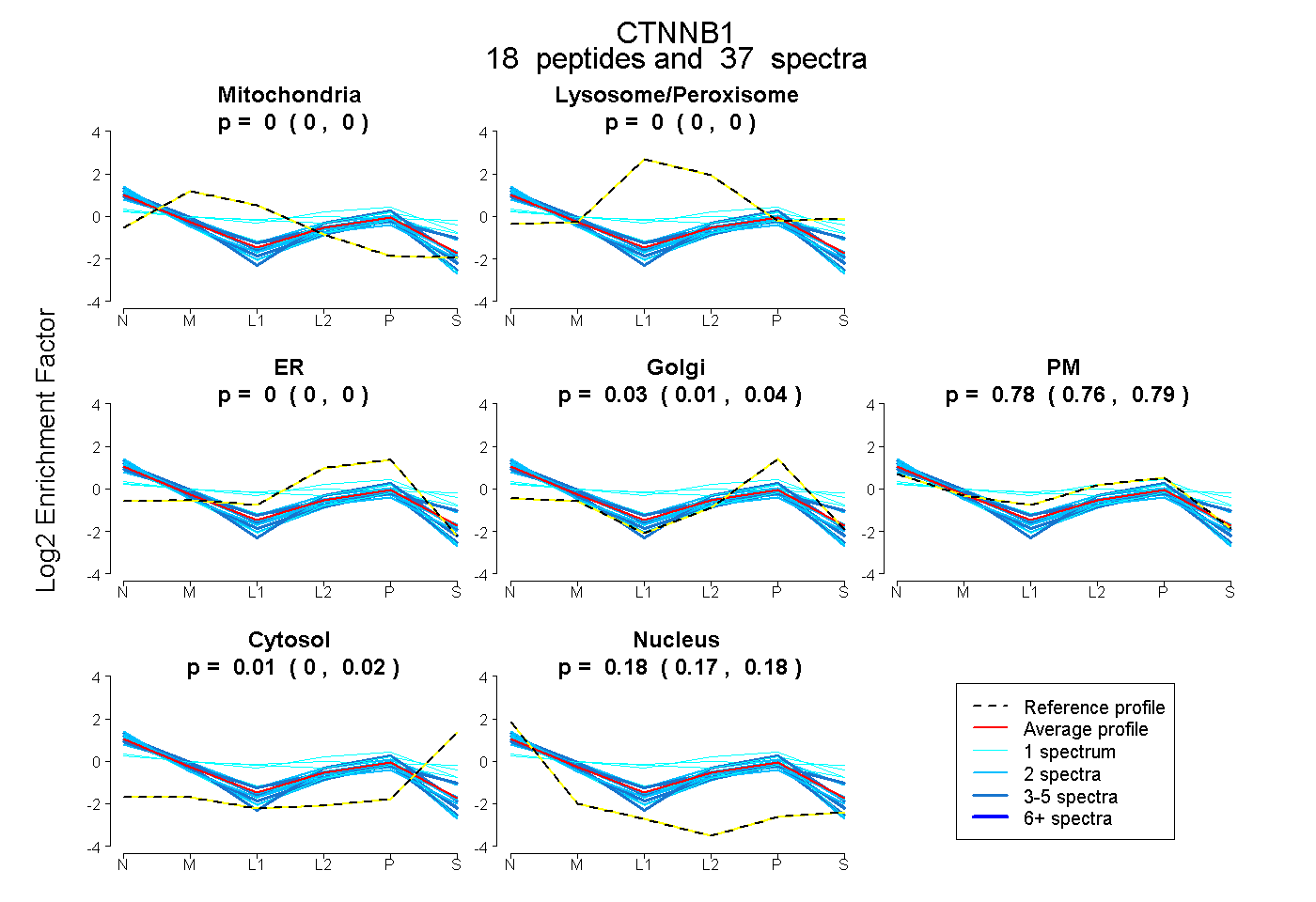
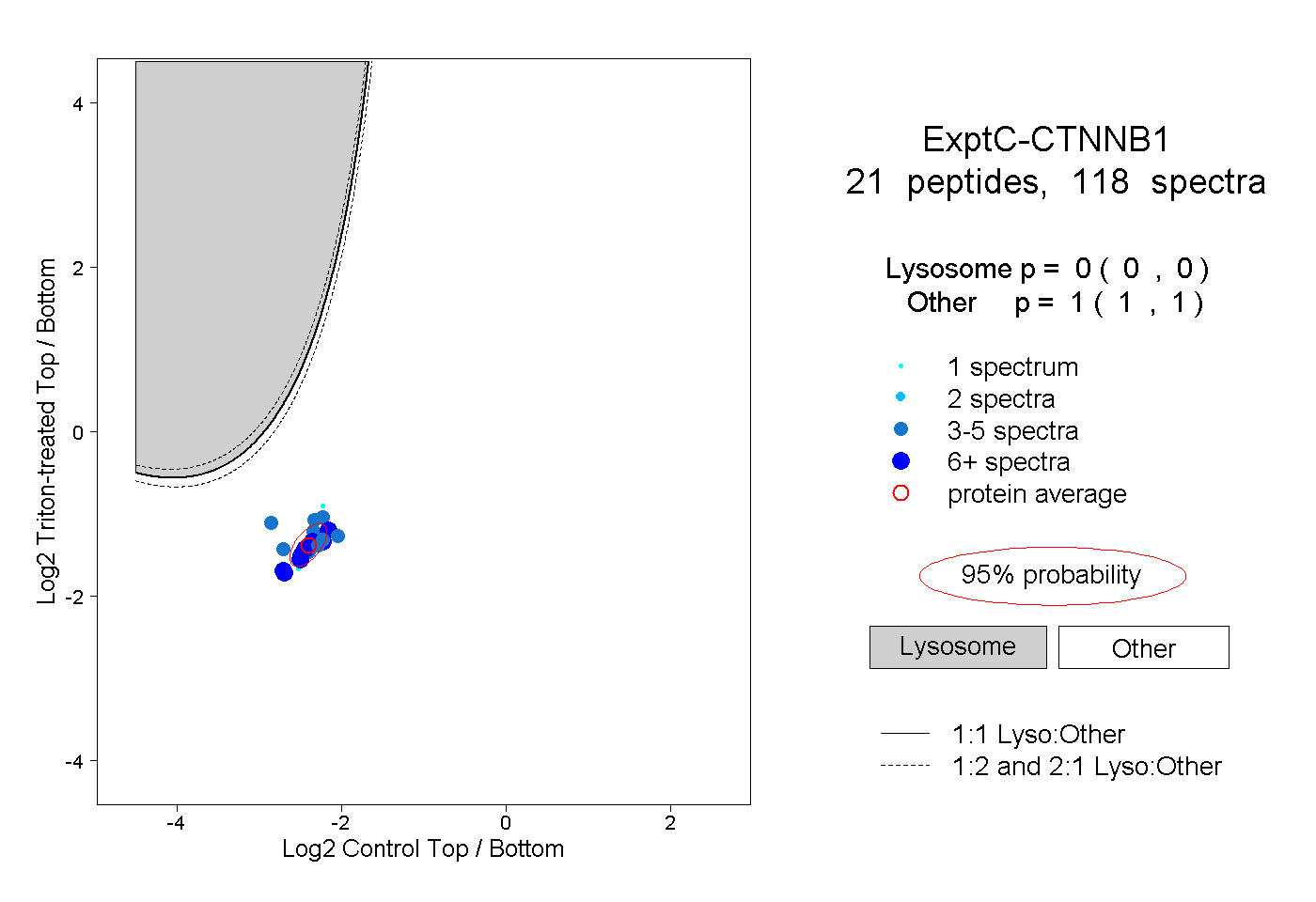
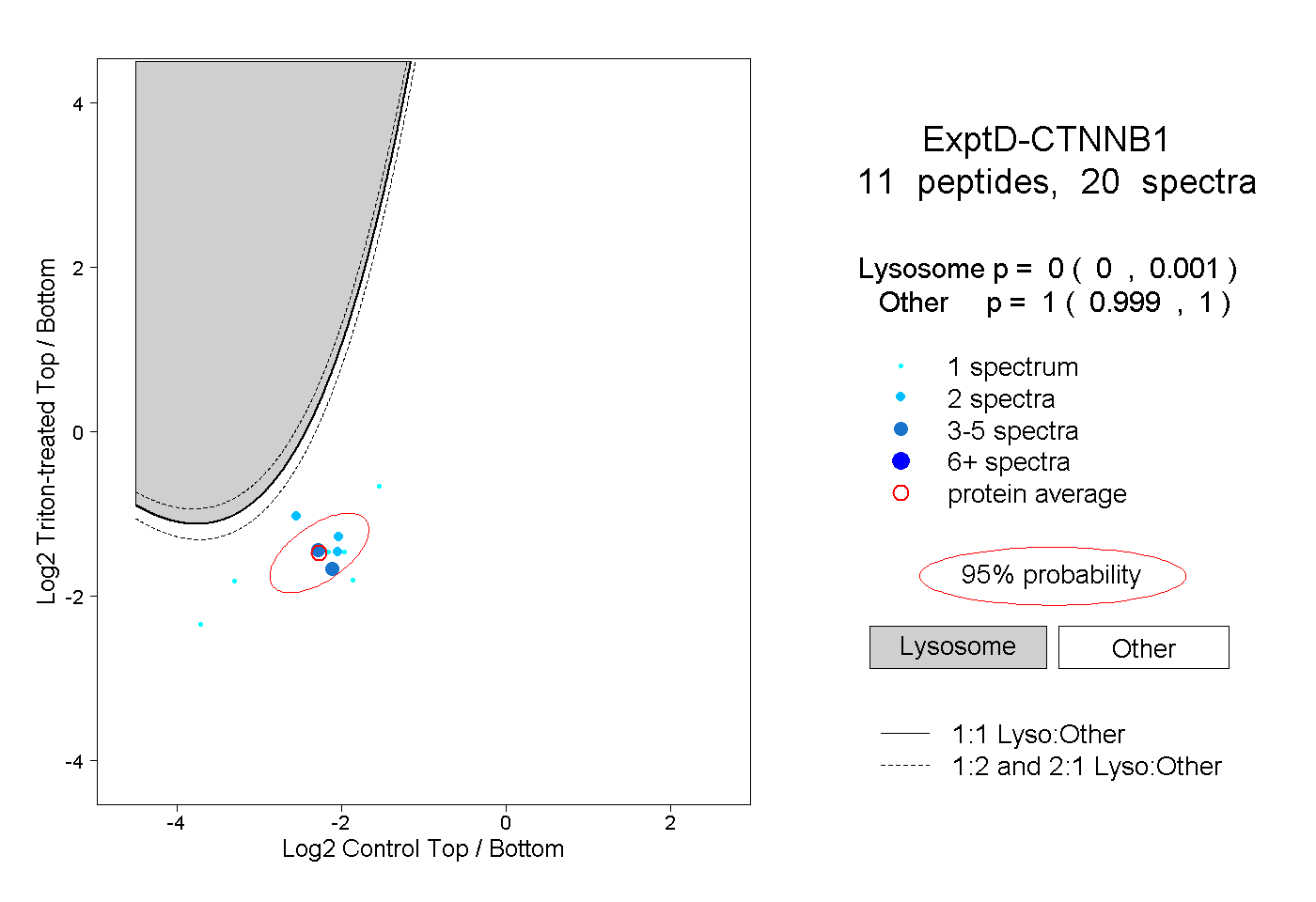
| 4 spectra, SPQMVSAIVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, SGGIPALVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, MMVCQVGGIEALVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LLHPPSHWPLIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, TSMGGTQQQFVEGVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LVQLLVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, MSEDKPQDYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, ATVGLIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, LAEPSQMLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, TYTYEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LHYGLPVVVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LAGGLQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, MVALLNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LLNDEDQVVVNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, AAVMVHQLSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, HAVVNLINYQDDAELATR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, HQEAEMAQNAVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, EQGAIPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, NEGVATYAAAVLFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, TMQNTNDVETAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, NLSDAATK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |