peptides
spectra
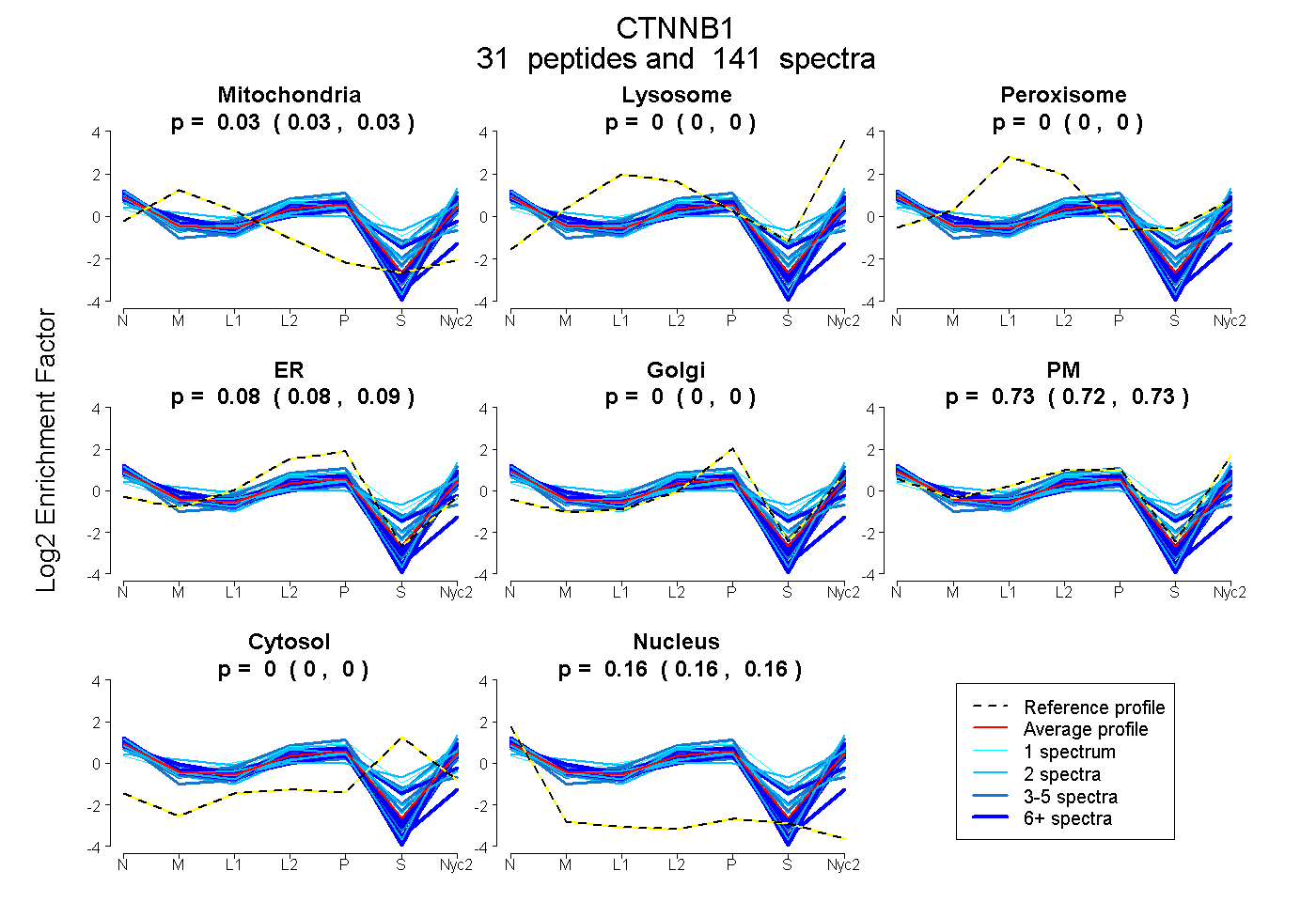
0.029 | 0.033
0.000 | 0.000
0.000 | 0.000
0.076 | 0.085
0.000 | 0.000
0.721 | 0.733
0.000 | 0.000
0.159 | 0.161
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
141 spectra |
 |
0.031 0.029 | 0.033 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.081 0.076 | 0.085 |
0.000 0.000 | 0.000 |
0.727 0.721 | 0.733 |
0.000 0.000 | 0.000 |
0.161 0.159 | 0.161 |
| 9 spectra, SPQMVSAIVR | 0.009 | 0.000 | 0.000 | 0.000 | 0.000 | 0.847 | 0.000 | 0.144 | ||
| 2 spectra, SGGIPALVK | 0.087 | 0.000 | 0.000 | 0.000 | 0.000 | 0.594 | 0.308 | 0.010 | ||
| 4 spectra, LLHPPSHWPLIK | 0.000 | 0.000 | 0.000 | 0.044 | 0.000 | 0.774 | 0.000 | 0.182 | ||
| 2 spectra, LVQLLVR | 0.000 | 0.000 | 0.000 | 0.041 | 0.000 | 0.787 | 0.000 | 0.172 | ||
| 4 spectra, ATVGLIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.819 | 0.000 | 0.181 | ||
| 2 spectra, VAAGVLCELAQDK | 0.058 | 0.000 | 0.063 | 0.251 | 0.000 | 0.420 | 0.000 | 0.207 | ||
| 4 spectra, MEEIVEGCTGALHILAR | 0.124 | 0.000 | 0.031 | 0.241 | 0.000 | 0.290 | 0.193 | 0.121 | ||
| 9 spectra, NLALCPANHAPLR | 0.119 | 0.000 | 0.000 | 0.135 | 0.000 | 0.490 | 0.140 | 0.116 | ||
| 4 spectra, LHYGLPVVVK | 0.180 | 0.000 | 0.000 | 0.028 | 0.008 | 0.624 | 0.057 | 0.103 | ||
| 2 spectra, LAGGLQK | 0.000 | 0.000 | 0.000 | 0.228 | 0.000 | 0.640 | 0.000 | 0.132 | ||
| 3 spectra, LLNDEDQVVVNK | 0.000 | 0.000 | 0.000 | 0.180 | 0.000 | 0.664 | 0.000 | 0.156 | ||
| 1 spectrum, CTAGTLHNLSHHR | 0.000 | 0.000 | 0.153 | 0.096 | 0.189 | 0.390 | 0.173 | 0.000 | ||
| 6 spectra, AAVMVHQLSK | 0.000 | 0.000 | 0.000 | 0.096 | 0.000 | 0.750 | 0.000 | 0.154 | ||
| 2 spectra, ALPELTK | 0.000 | 0.000 | 0.000 | 0.000 | 0.006 | 0.760 | 0.040 | 0.194 | ||
| 5 spectra, HQEAEMAQNAVR | 0.000 | 0.000 | 0.006 | 0.000 | 0.000 | 0.761 | 0.180 | 0.053 | ||
| 4 spectra, LSVELTSSLFR | 0.000 | 0.000 | 0.000 | 0.117 | 0.006 | 0.819 | 0.000 | 0.058 | ||
| 1 spectrum, NEGVATYAAAVLFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.841 | 0.000 | 0.159 | ||
| 12 spectra, TMQNTNDVETAR | 0.000 | 0.000 | 0.000 | 0.027 | 0.000 | 0.825 | 0.000 | 0.148 | ||
| 4 spectra, QDDPSYR | 0.000 | 0.000 | 0.000 | 0.111 | 0.110 | 0.600 | 0.000 | 0.178 | ||
| 2 spectra, TSMGGTQQQFVEGVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.870 | 0.000 | 0.130 | ||
| 1 spectrum, MSEDKPQDYK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.915 | 0.000 | 0.085 | ||
| 3 spectra, LAEPSQMLK | 0.063 | 0.000 | 0.000 | 0.137 | 0.043 | 0.635 | 0.000 | 0.122 | ||
| 6 spectra, EGLLAIFK | 0.021 | 0.000 | 0.000 | 0.058 | 0.000 | 0.709 | 0.000 | 0.212 | ||
| 2 spectra, TYTYEK | 0.039 | 0.000 | 0.000 | 0.000 | 0.000 | 0.714 | 0.173 | 0.074 | ||
| 8 spectra, MVALLNK | 0.149 | 0.000 | 0.000 | 0.025 | 0.014 | 0.701 | 0.000 | 0.112 | ||
| 13 spectra, LLWTTSR | 0.063 | 0.000 | 0.000 | 0.000 | 0.000 | 0.793 | 0.000 | 0.144 | ||
| 2 spectra, HAVVNLINYQDDAELATR | 0.163 | 0.000 | 0.000 | 0.018 | 0.080 | 0.739 | 0.000 | 0.000 | ||
| 8 spectra, EQGAIPR | 0.015 | 0.000 | 0.000 | 0.035 | 0.000 | 0.764 | 0.000 | 0.186 | ||
| 10 spectra, LVQNCLWTLR | 0.126 | 0.000 | 0.000 | 0.517 | 0.000 | 0.123 | 0.000 | 0.234 | ||
| 2 spectra, EDITEPAICALR | 0.061 | 0.000 | 0.010 | 0.138 | 0.000 | 0.593 | 0.126 | 0.072 | ||
| 4 spectra, NLSDAATK | 0.000 | 0.000 | 0.000 | 0.066 | 0.000 | 0.765 | 0.000 | 0.169 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
37 spectra |
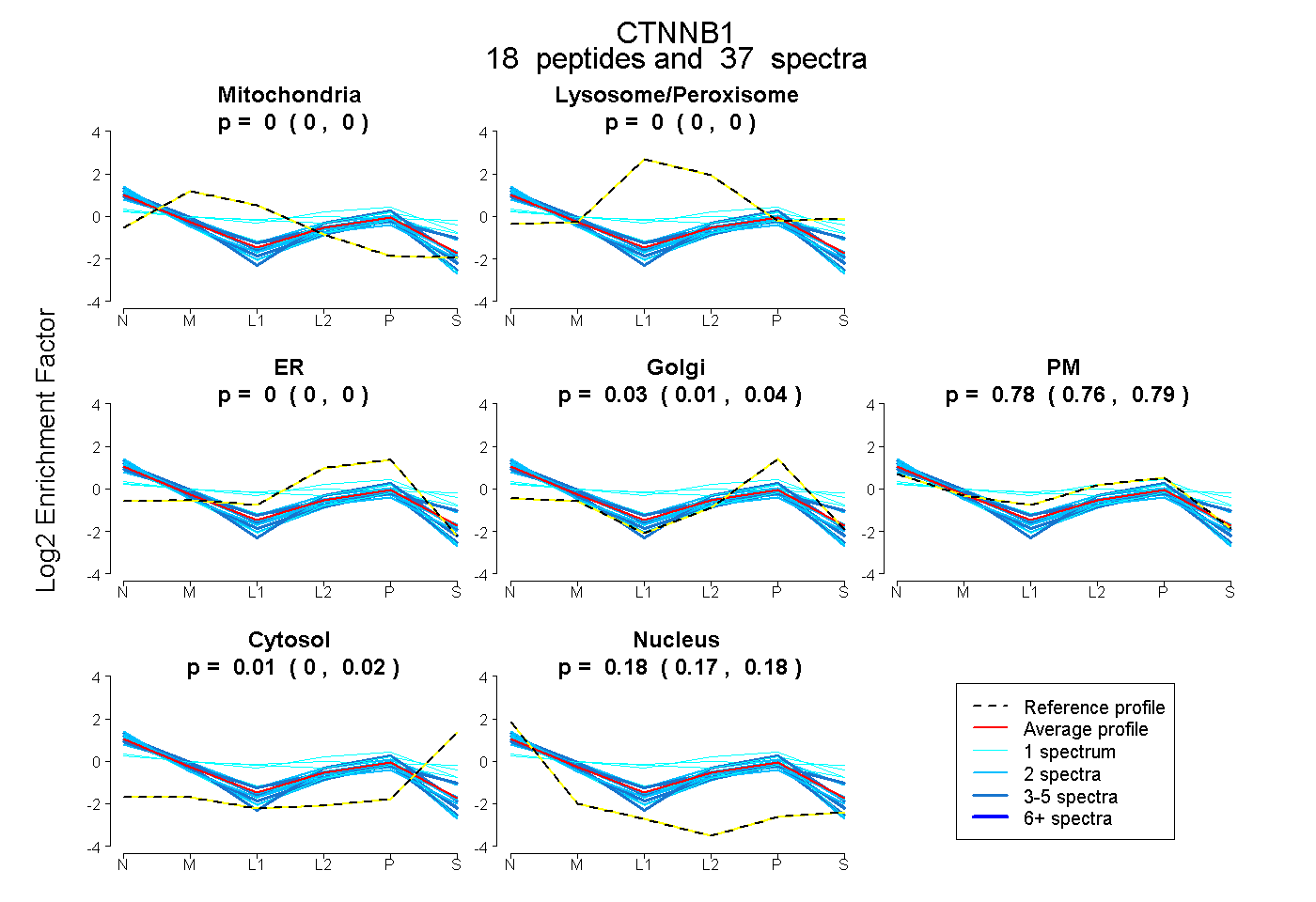 |
0.000 0.000 | 0.001 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.029 0.013 | 0.042 |
0.780 0.764 | 0.792 |
0.015 0.003 | 0.024 |
0.177 0.170 | 0.183 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
118 spectra |
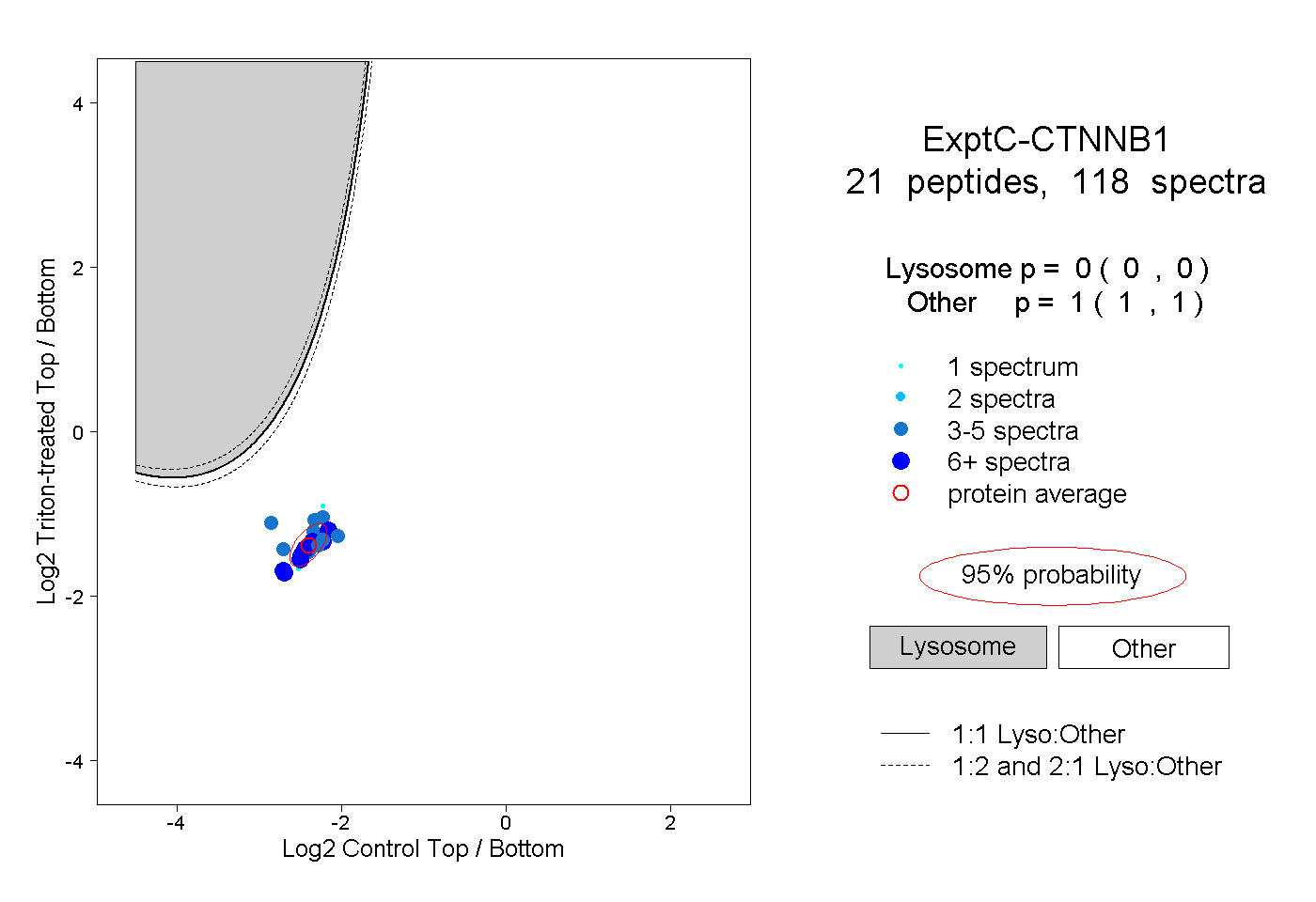 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
20 spectra |
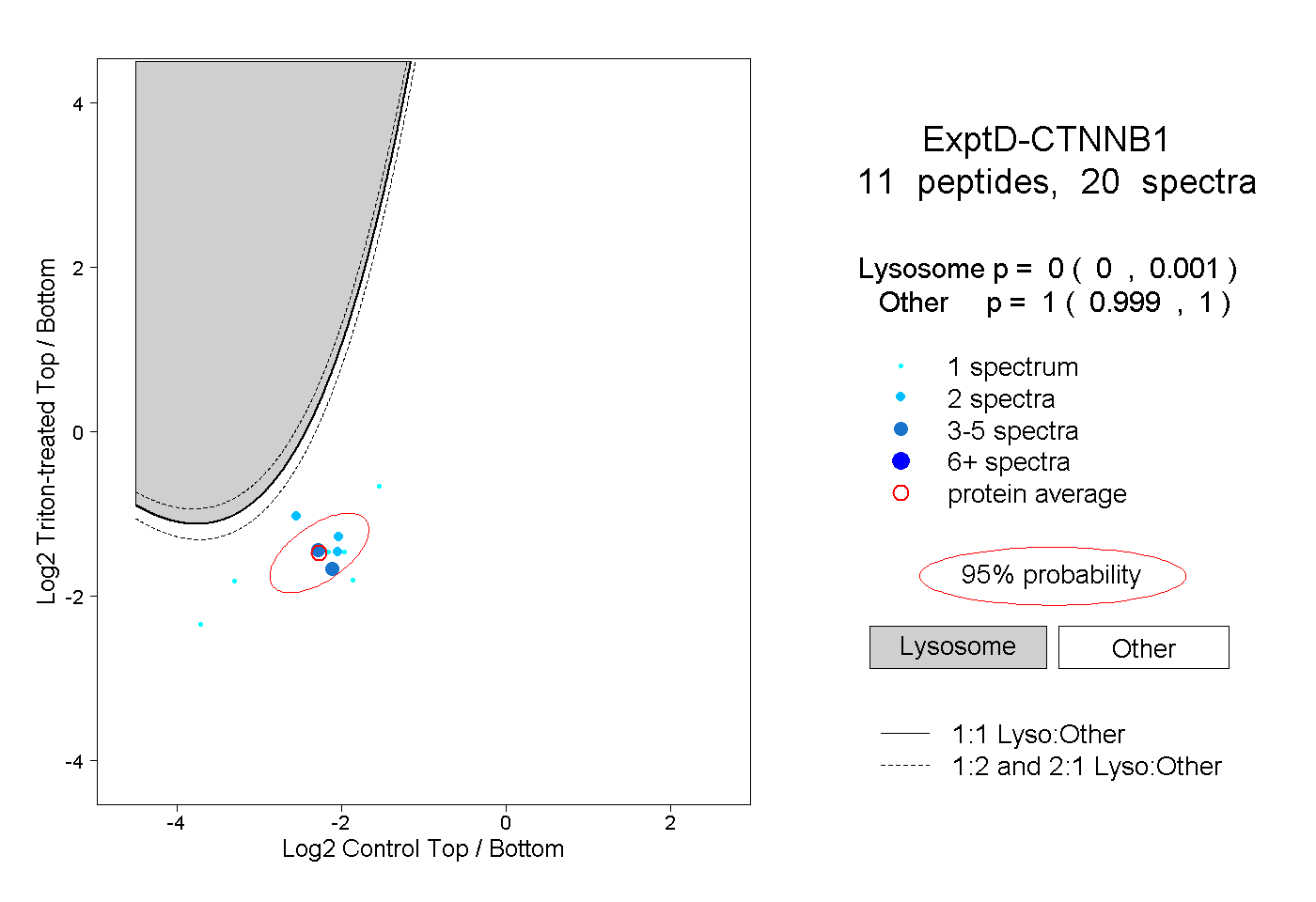 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |