peptides
spectra
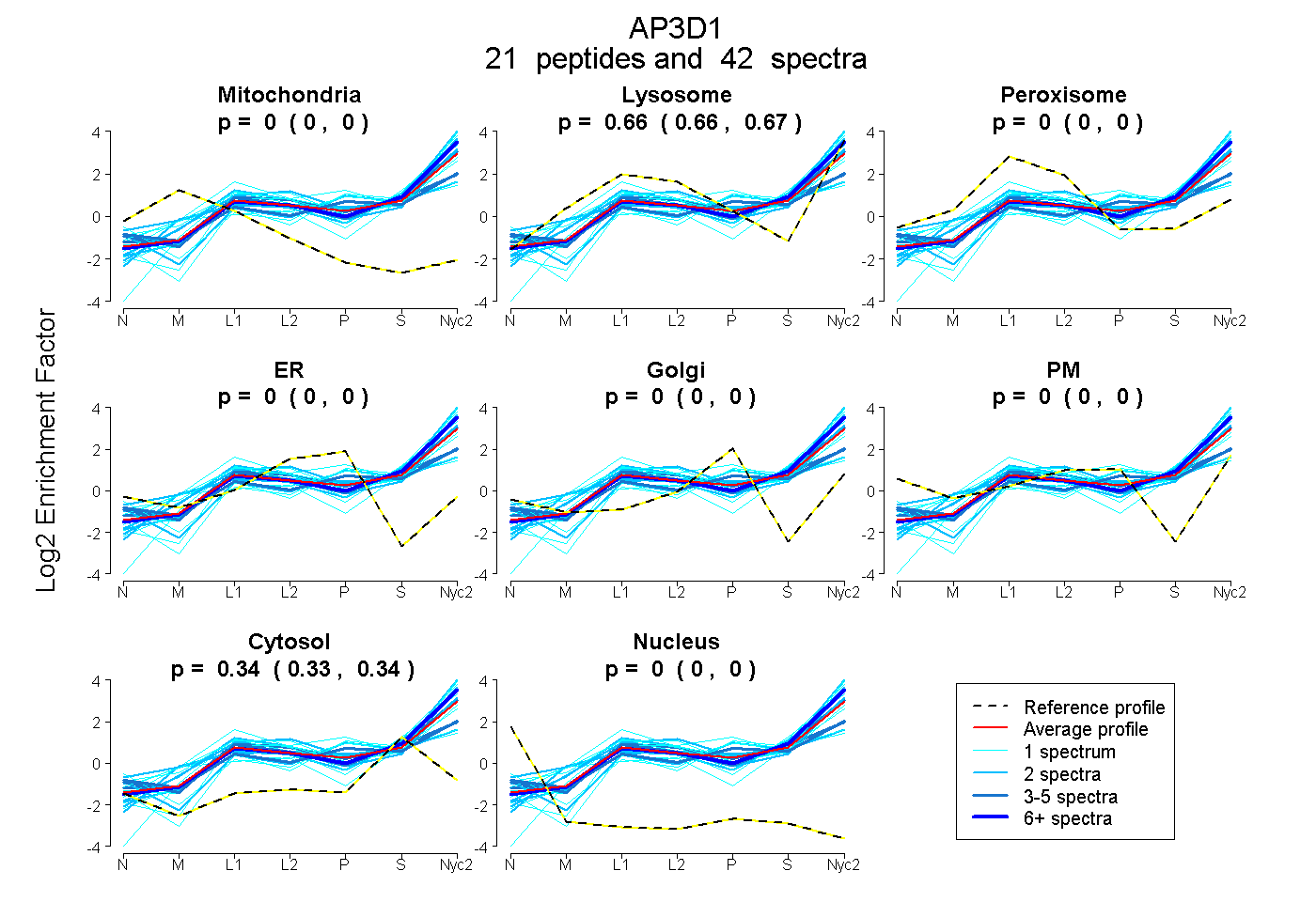
0.000 | 0.000
0.656 | 0.668
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.332 | 0.342
0.000 | 0.000
peptides
spectra
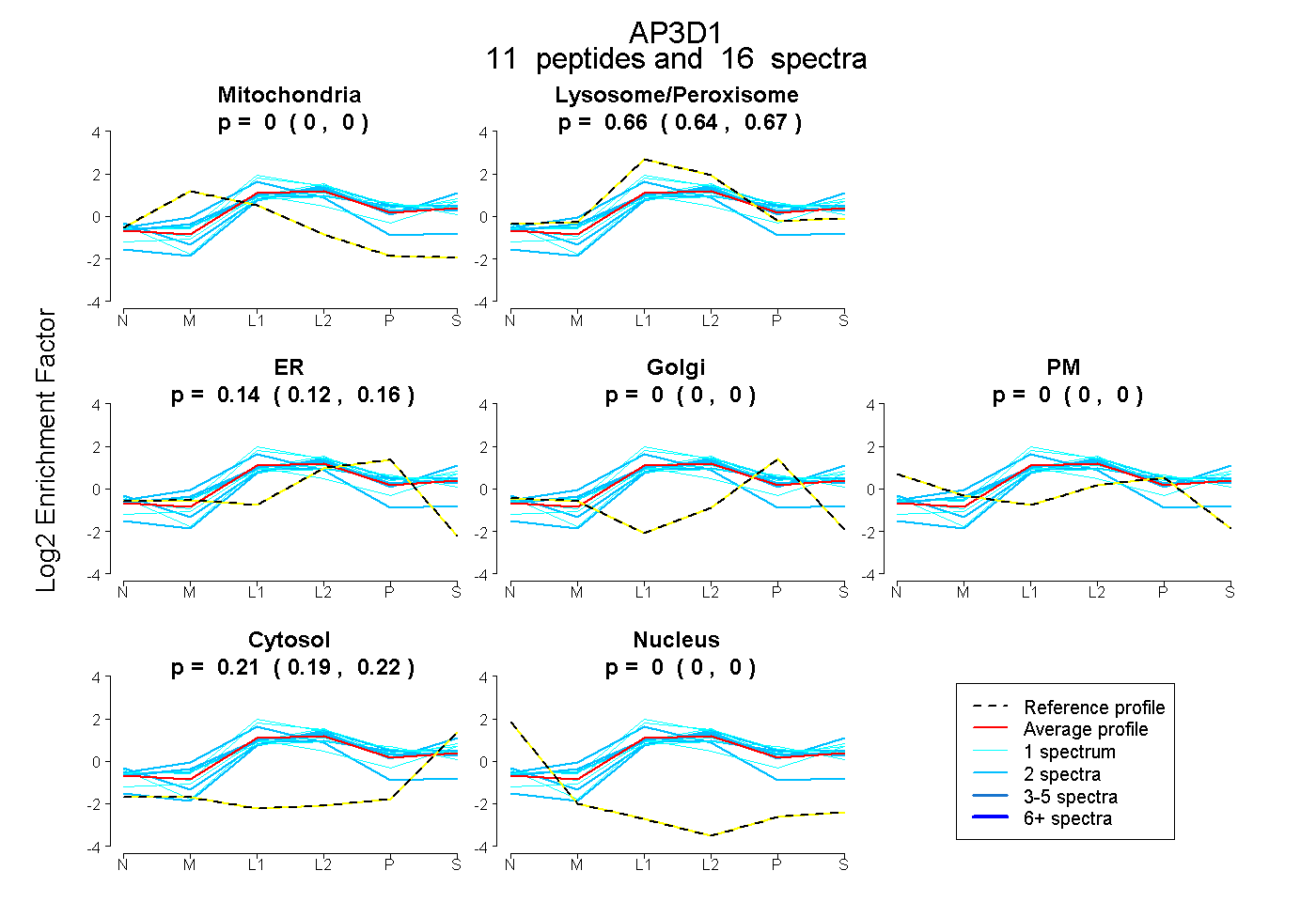
0.000 | 0.000
0.640 | 0.668
0.115 | 0.156
0.000 | 0.000
0.000 | 0.000
0.194 | 0.217
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
42 spectra |
 |
0.000 0.000 | 0.000 |
0.662 0.656 | 0.668 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.338 0.332 | 0.342 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
16 spectra |
 |
0.000 0.000 | 0.000 |
0.655 0.640 | 0.668 |
0.138 0.115 | 0.156 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.207 0.194 | 0.217 |
0.000 0.000 | 0.000 |
| 1 spectrum, NYLSLAPLFFK | 0.000 | 0.658 | 0.000 | 0.033 | 0.000 | 0.310 | 0.000 | |||
| 1 spectrum, NLQDLVR | 0.000 | 0.788 | 0.076 | 0.037 | 0.000 | 0.099 | 0.000 | |||
| 2 spectra, YPESLRPAFPR | 0.000 | 0.665 | 0.119 | 0.049 | 0.000 | 0.167 | 0.000 | |||
| 1 spectrum, VTYDVQASLQK | 0.000 | 0.624 | 0.000 | 0.284 | 0.000 | 0.092 | 0.000 | |||
| 2 spectra, AIFHEEEPR | 0.000 | 0.596 | 0.215 | 0.000 | 0.000 | 0.189 | 0.000 | |||
| 2 spectra, ILIEDSDQNLK | 0.000 | 0.655 | 0.000 | 0.215 | 0.000 | 0.130 | 0.000 | |||
| 1 spectrum, VDGISISFQNLLAK | 0.000 | 0.617 | 0.126 | 0.000 | 0.000 | 0.257 | 0.000 | |||
| 1 spectrum, ASCILQLVK | 0.000 | 0.849 | 0.000 | 0.043 | 0.000 | 0.108 | 0.000 | |||
| 2 spectra, CSDATLLSSLLEEMK | 0.000 | 0.631 | 0.026 | 0.000 | 0.000 | 0.343 | 0.000 | |||
| 1 spectrum, ALDLLYGMVSK | 0.000 | 0.676 | 0.079 | 0.000 | 0.000 | 0.244 | 0.000 | |||
| 2 spectra, LFGALTPLEPR | 0.305 | 0.605 | 0.027 | 0.000 | 0.000 | 0.047 | 0.016 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
142 spectra |
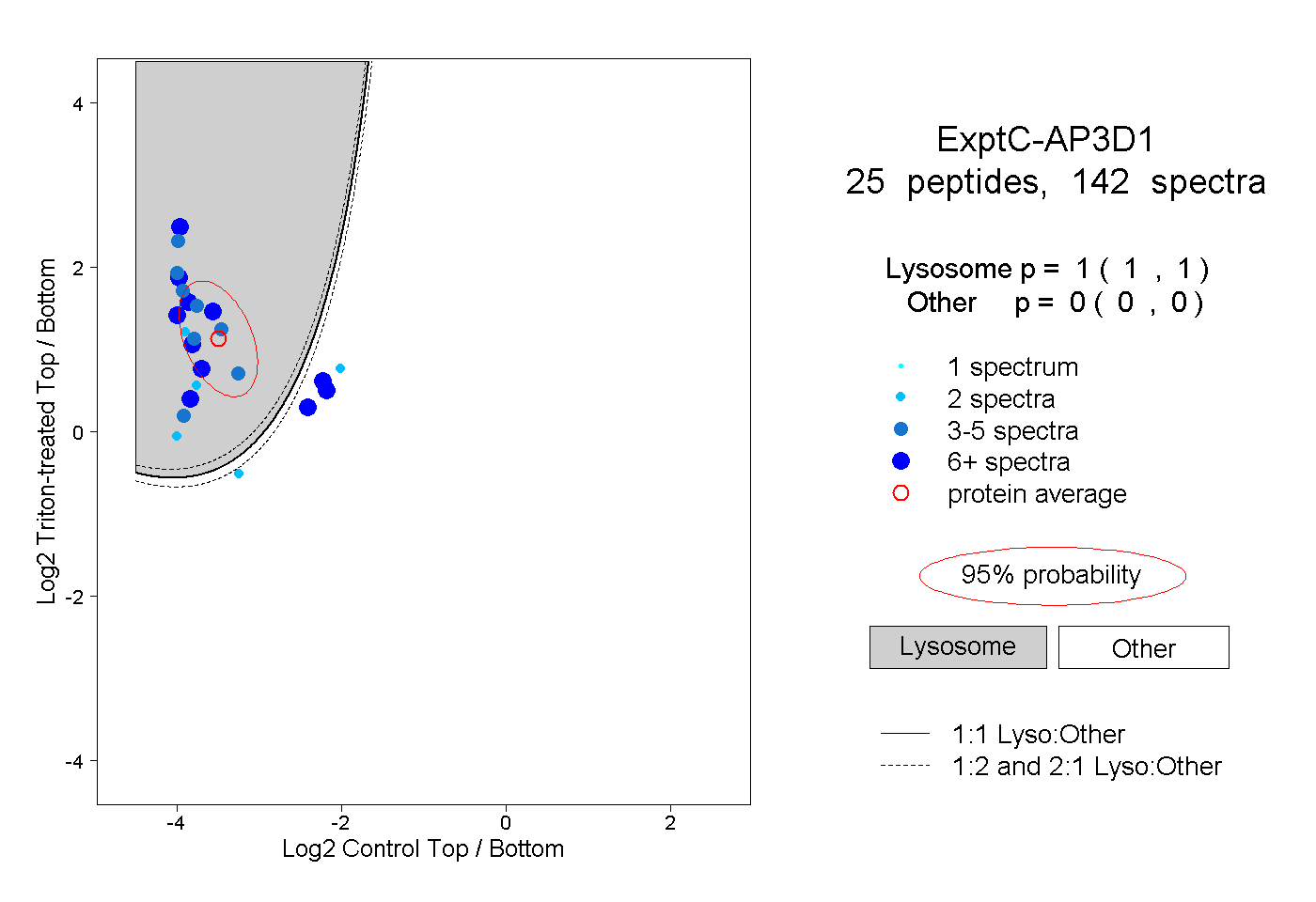 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
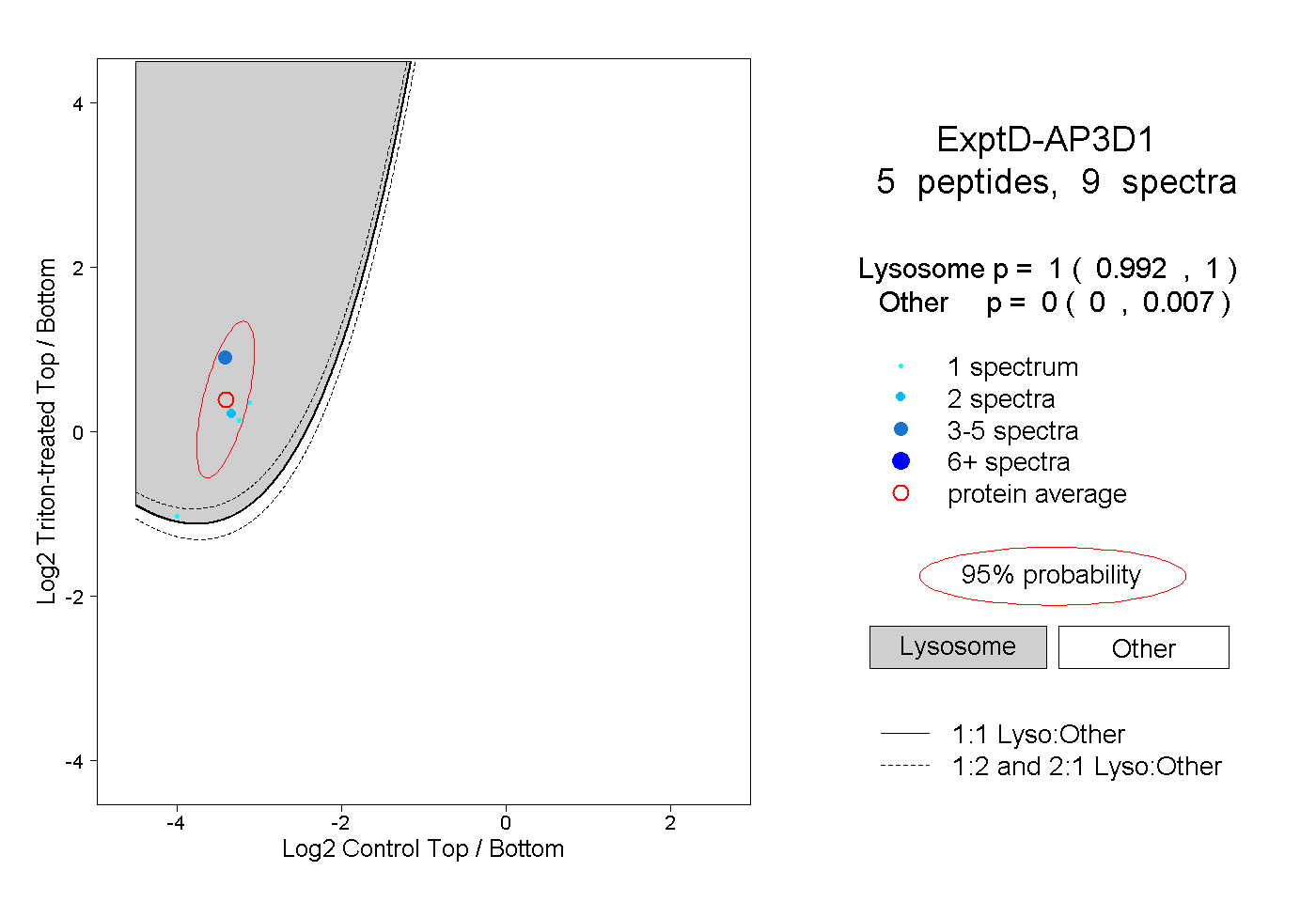 |
1.000 0.992 | 1.000 |
0.000 0.000 | 0.007 |