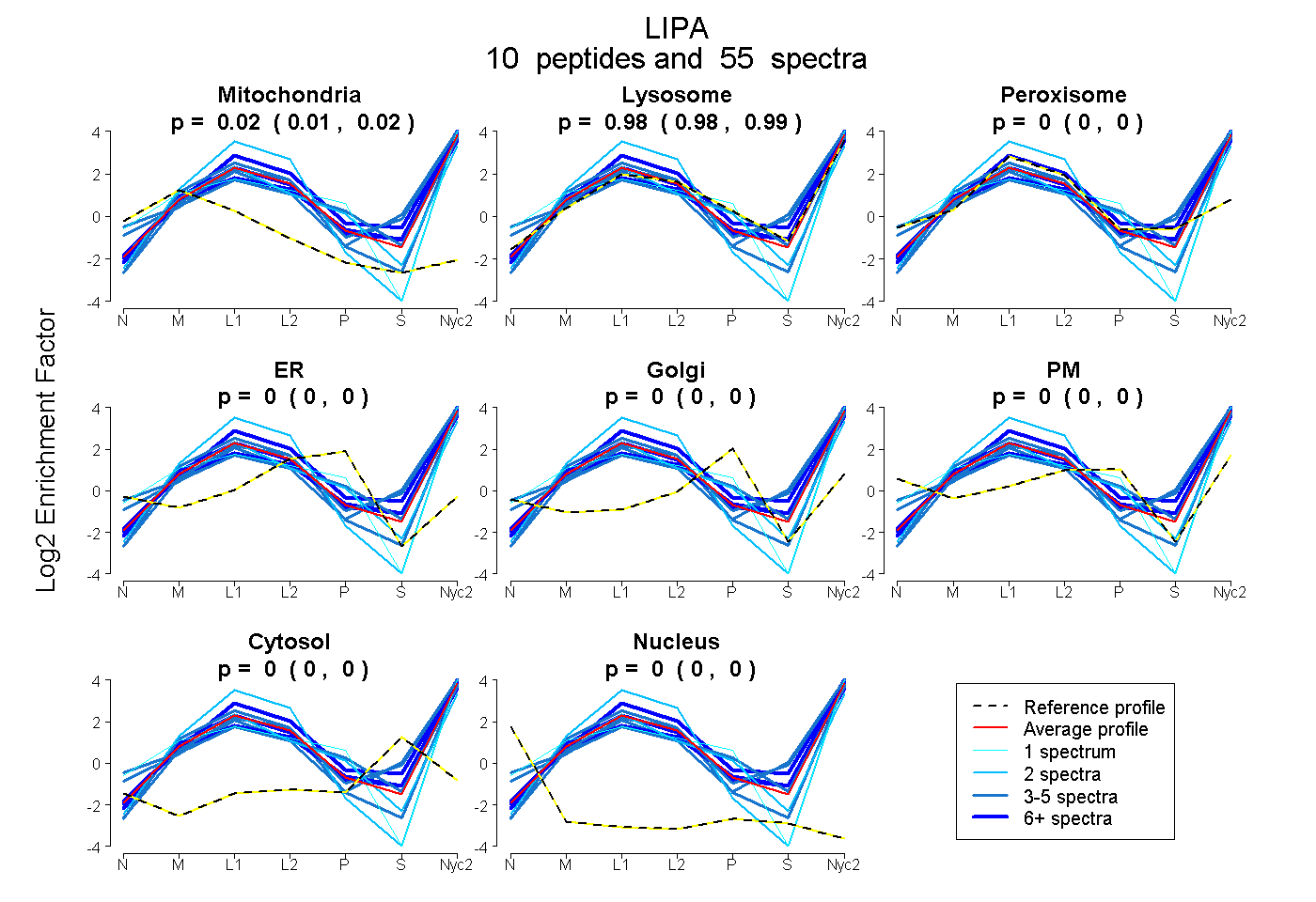
peptides
spectra
0.012 | 0.021
0.978 | 0.987
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
55 spectra |
 |
0.017 0.012 | 0.021 |
0.983 0.978 | 0.987 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, WLSTHICTHVIMK | 0.080 | 0.920 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, TLSVSQDEYWAFSFDEMAK | 0.000 | 0.793 | 0.000 | 0.000 | 0.000 | 0.207 | 0.000 | 0.000 | ||
| 3 spectra, LPDLLLEDLFGQK | 0.000 | 0.865 | 0.064 | 0.000 | 0.000 | 0.000 | 0.071 | 0.000 | ||
| 1 spectrum, YDLPASINYILNK | 0.000 | 0.628 | 0.000 | 0.000 | 0.000 | 0.372 | 0.000 | 0.000 | ||
| 17 spectra, LYNEVVSLMK | 0.061 | 0.939 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 10 spectra, GNTWSR | 0.000 | 0.991 | 0.009 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 4 spectra, QFLPQSAMVK | 0.000 | 0.985 | 0.000 | 0.000 | 0.000 | 0.000 | 0.015 | 0.000 | ||
| 5 spectra, LQAFDWGSSDK | 0.058 | 0.942 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, NIPEWDHLDFIWGLDAPWR | 0.016 | 0.984 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 8 spectra, DMQLPTALWSGGK | 0.002 | 0.998 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
24 spectra |
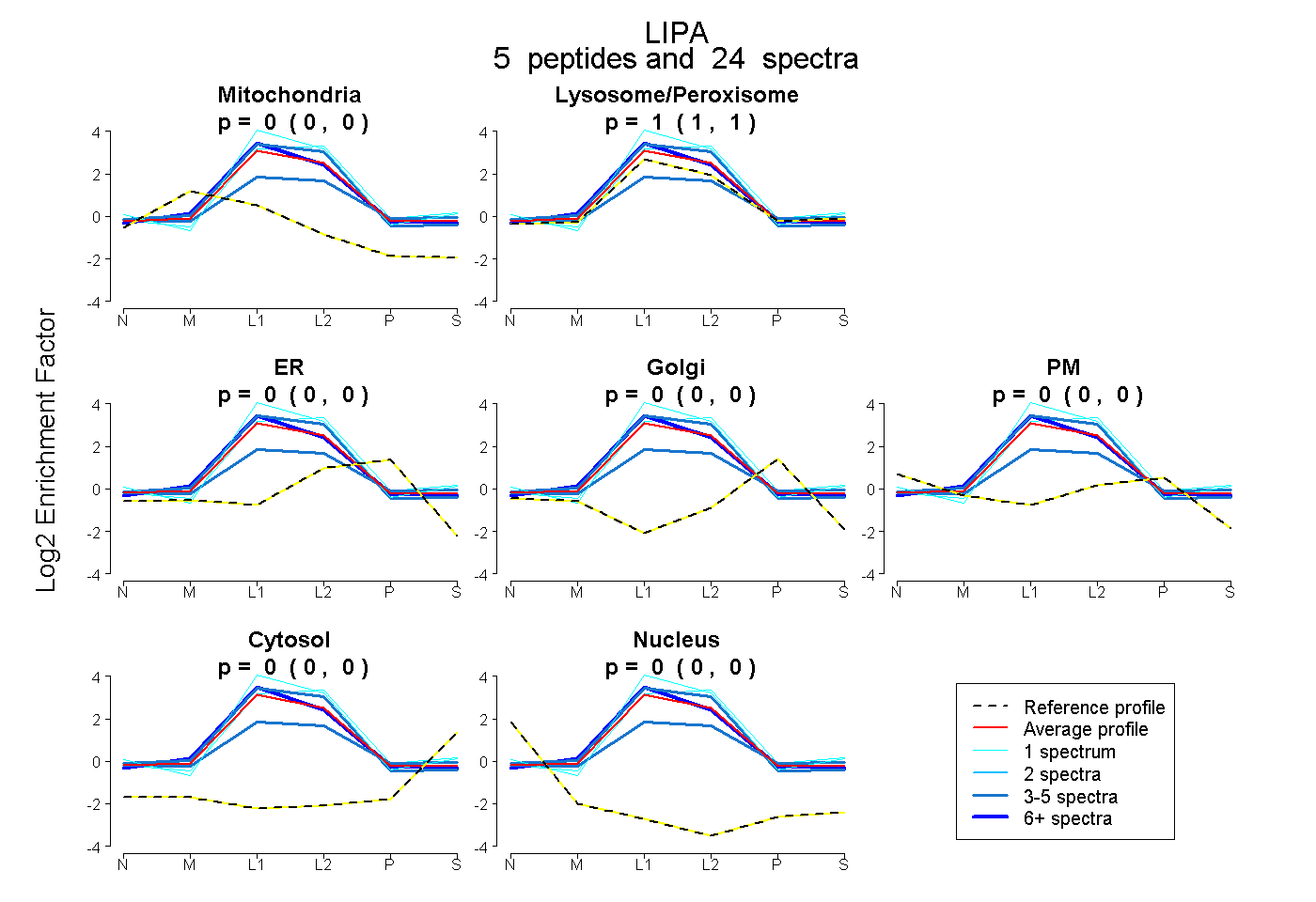 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
75 spectra |
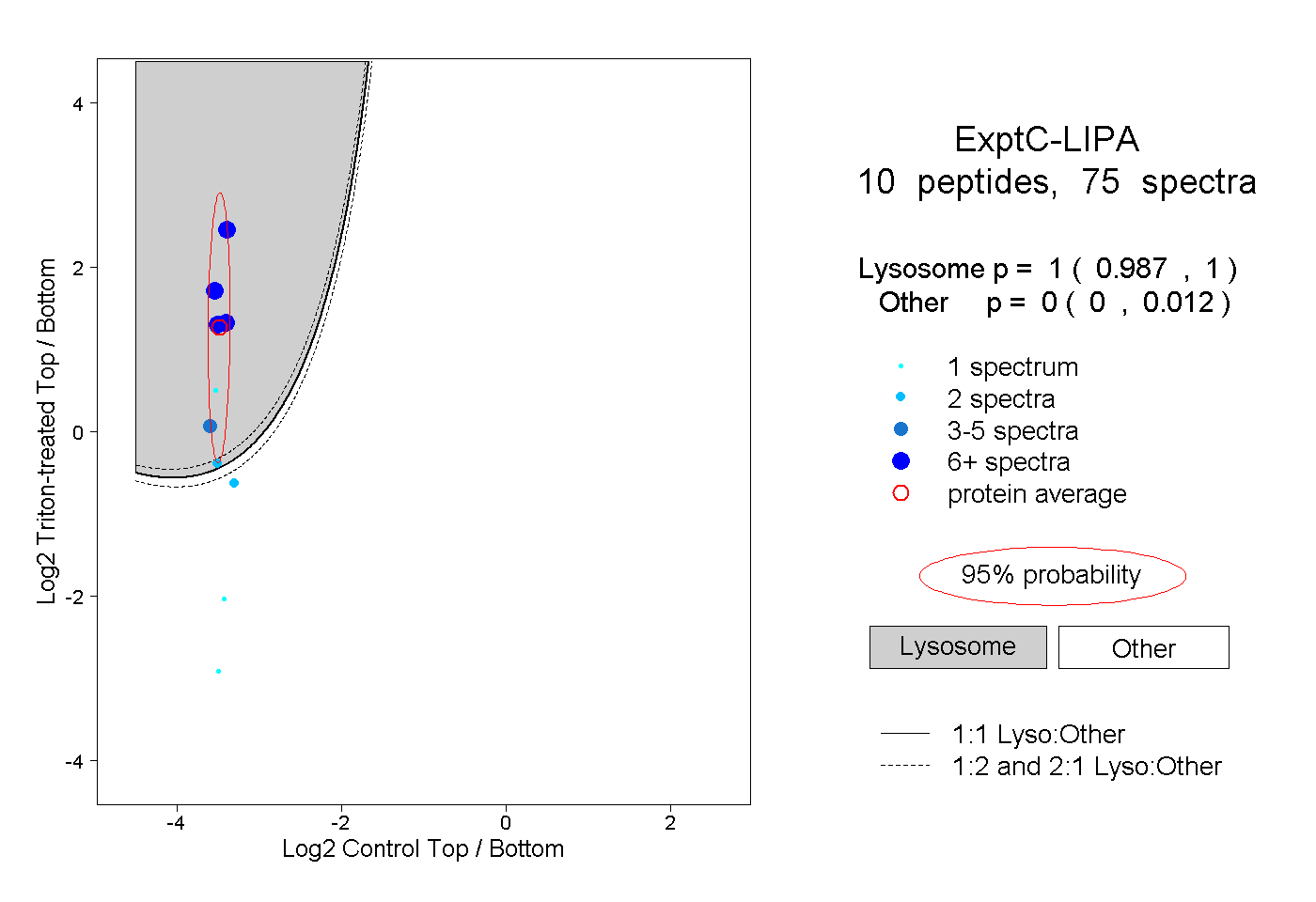 |
1.000 0.987 | 1.000 |
0.000 0.000 | 0.012 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
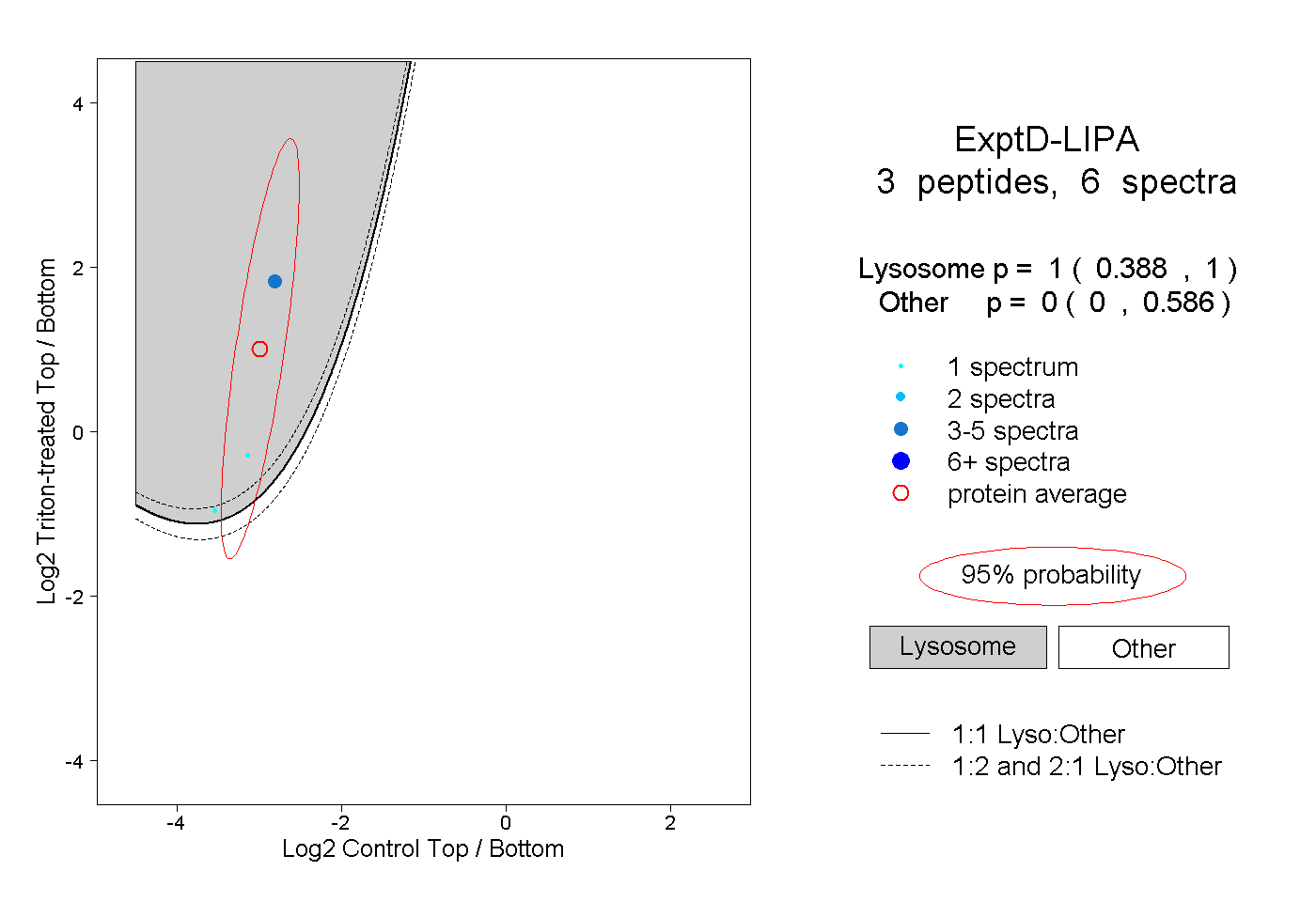 |
1.000 0.388 | 1.000 |
0.000 0.000 | 0.586 |