peptides
spectra
0.000 | 0.000
0.086 | 0.185
0.000 | 0.000
0.020 | 0.130
0.000 | 0.098
0.646 | 0.812
0.000 | 0.000
0.000 | 0.000
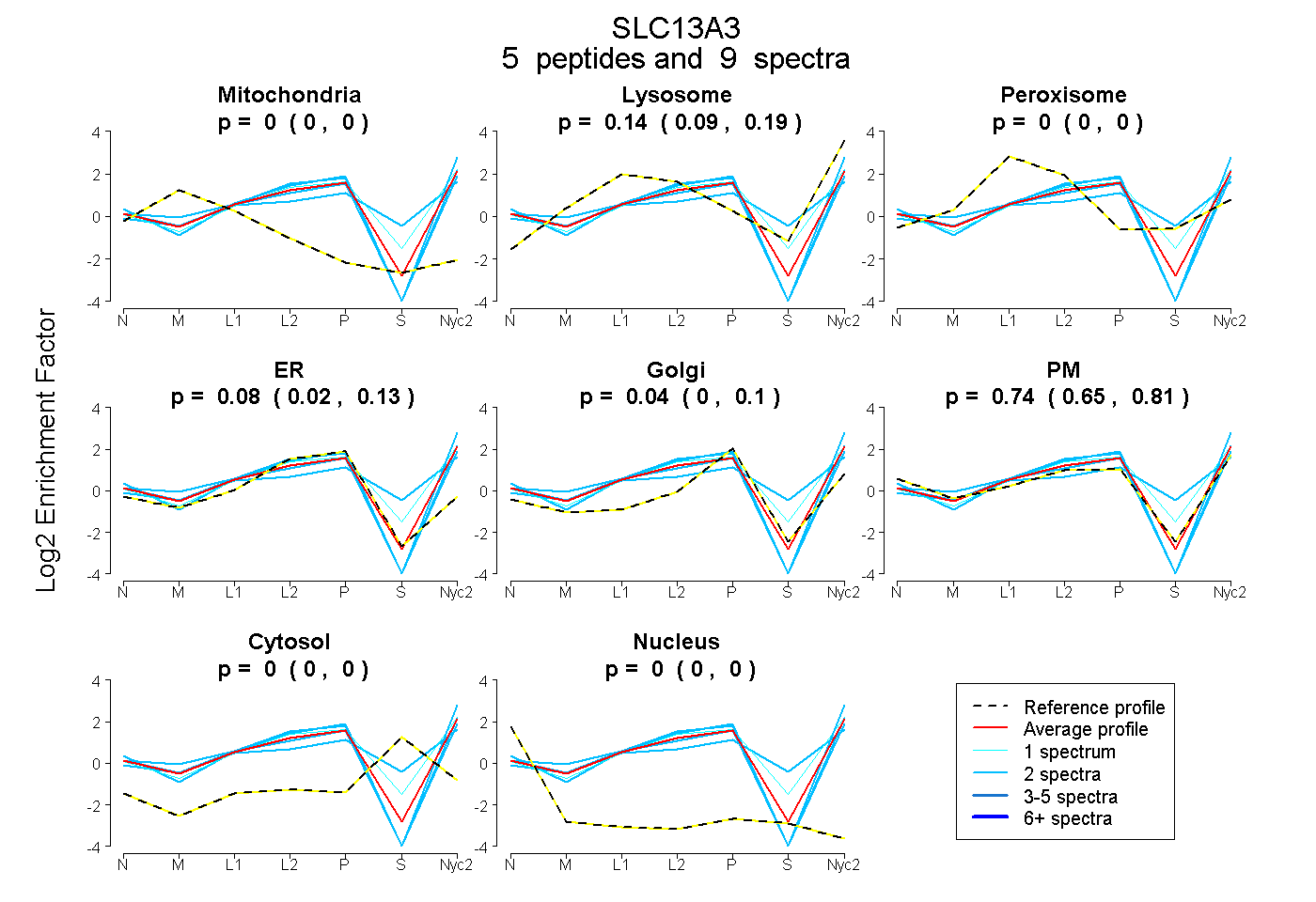
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
9 spectra |
 |
0.000 0.000 | 0.000 |
0.137 0.086 | 0.185 |
0.000 0.000 | 0.000 |
0.082 0.020 | 0.130 |
0.042 0.000 | 0.098 |
0.739 0.646 | 0.812 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, SLFGQR | 0.000 | 0.274 | 0.000 | 0.066 | 0.155 | 0.505 | 0.000 | 0.000 | ||
| 2 spectra, APNSETEPLLSWK | 0.000 | 0.249 | 0.108 | 0.000 | 0.161 | 0.316 | 0.166 | 0.000 | ||
| 2 spectra, EGEDSTAAVR | 0.000 | 0.000 | 0.000 | 0.217 | 0.000 | 0.783 | 0.000 | 0.000 | ||
| 2 spectra, VLMLVGVQPAR | 0.000 | 0.093 | 0.000 | 0.000 | 0.000 | 0.907 | 0.000 | 0.000 | ||
| 2 spectra, WWFDFK | 0.000 | 0.033 | 0.000 | 0.035 | 0.000 | 0.932 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
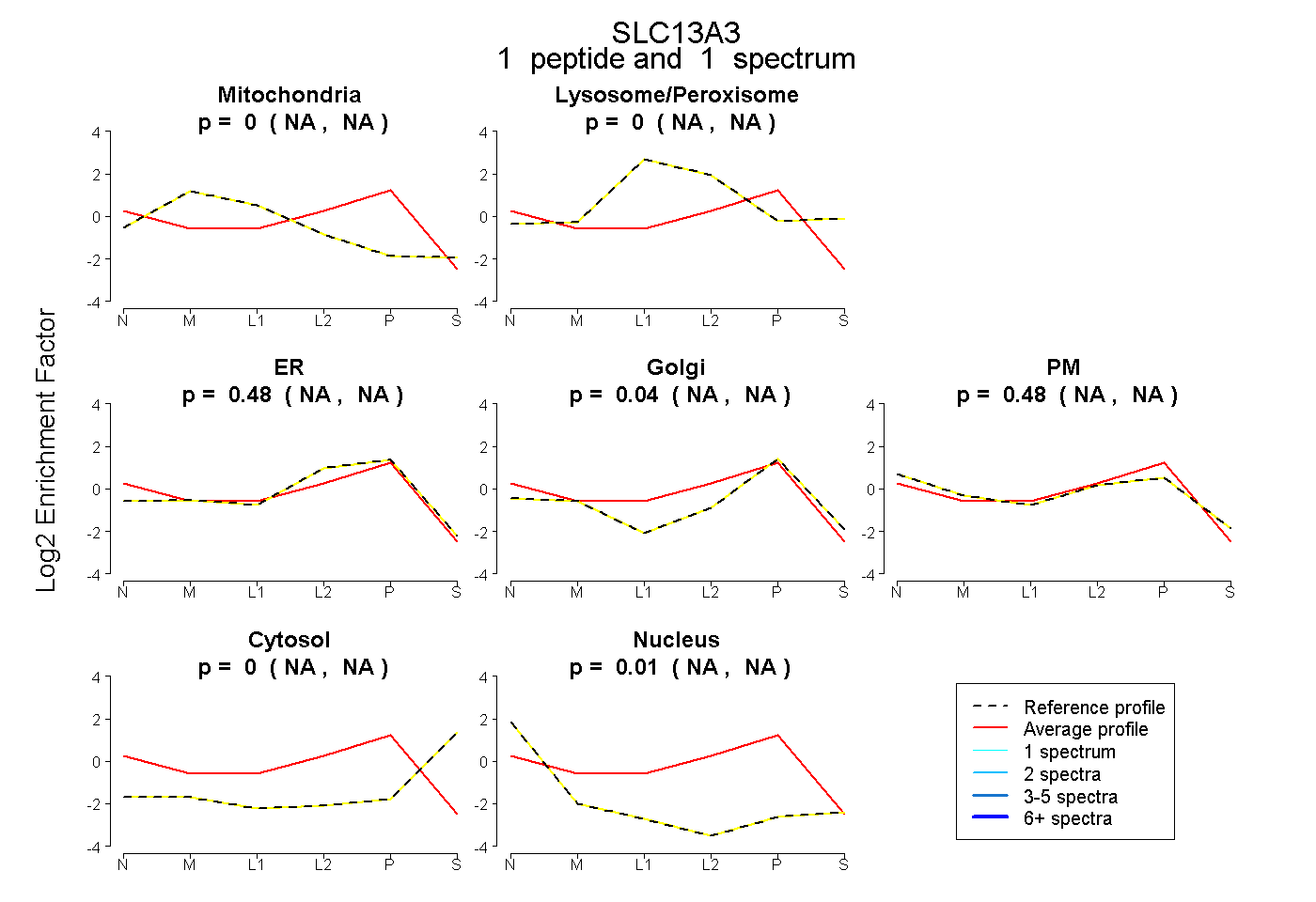 |
0.000 NA | NA |
0.000 NA | NA |
0.477 NA | NA |
0.035 NA | NA |
0.477 NA | NA |
0.000 NA | NA |
0.011 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
9 spectra |
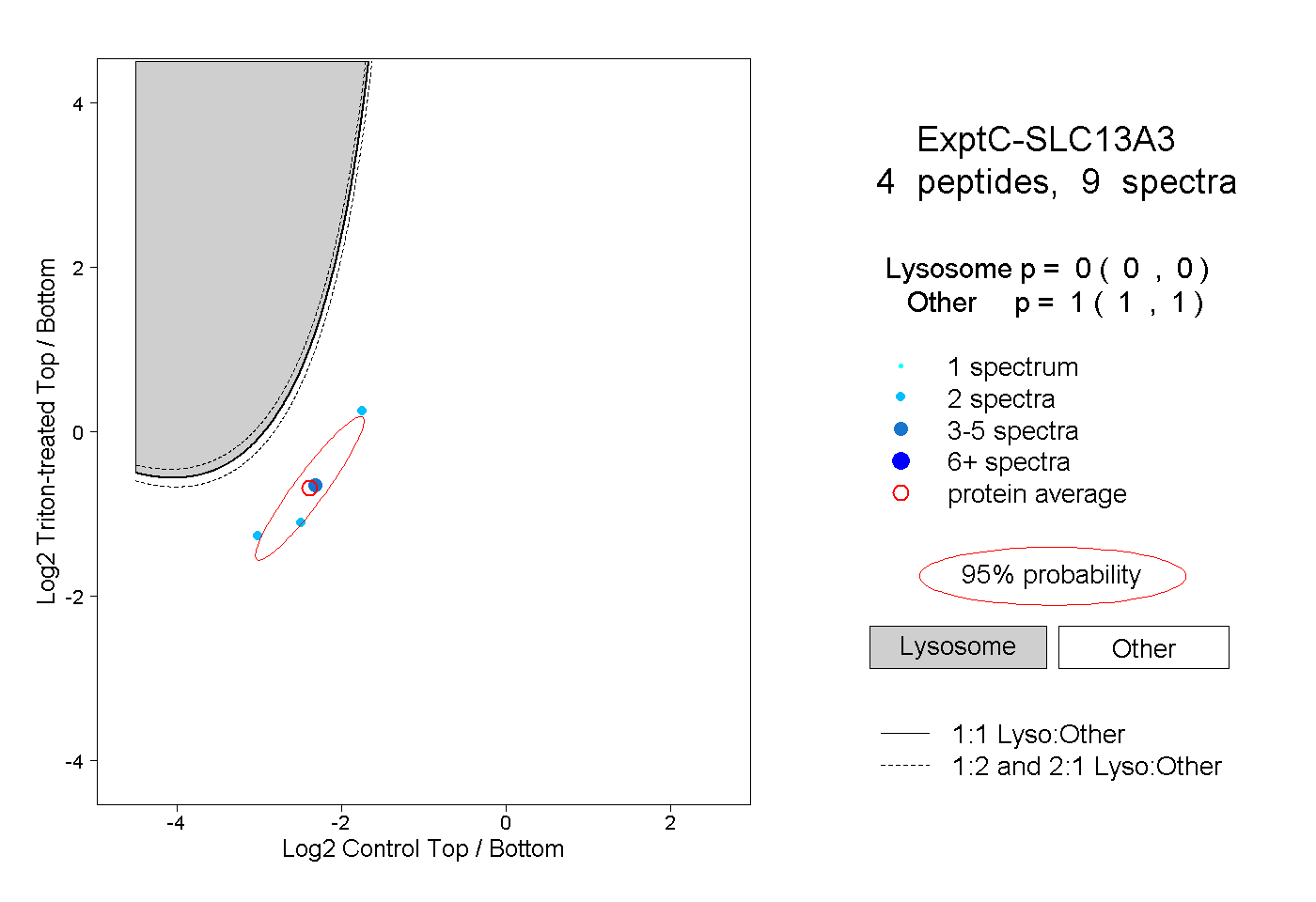 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
3 spectra |
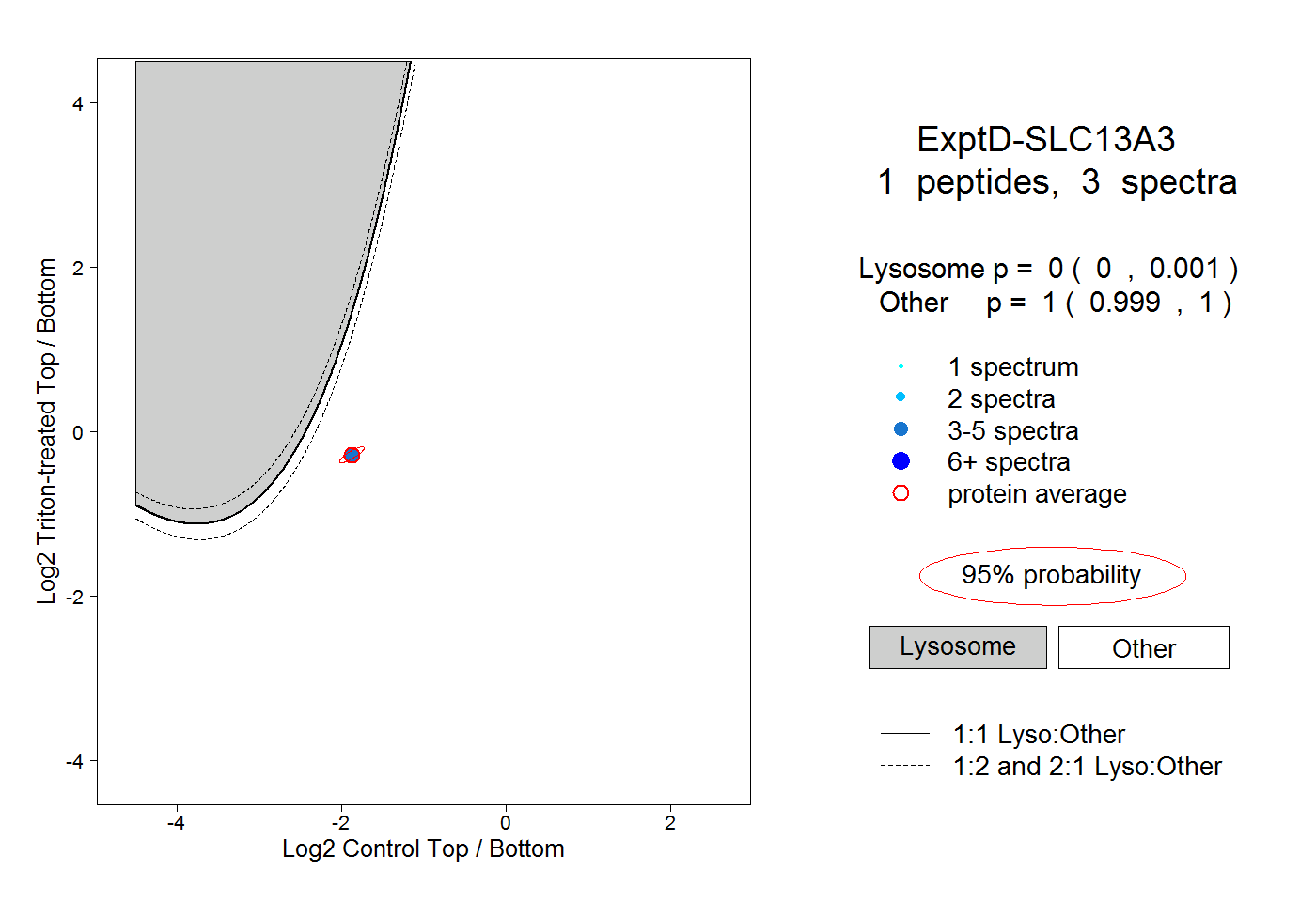 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |