peptides
spectra
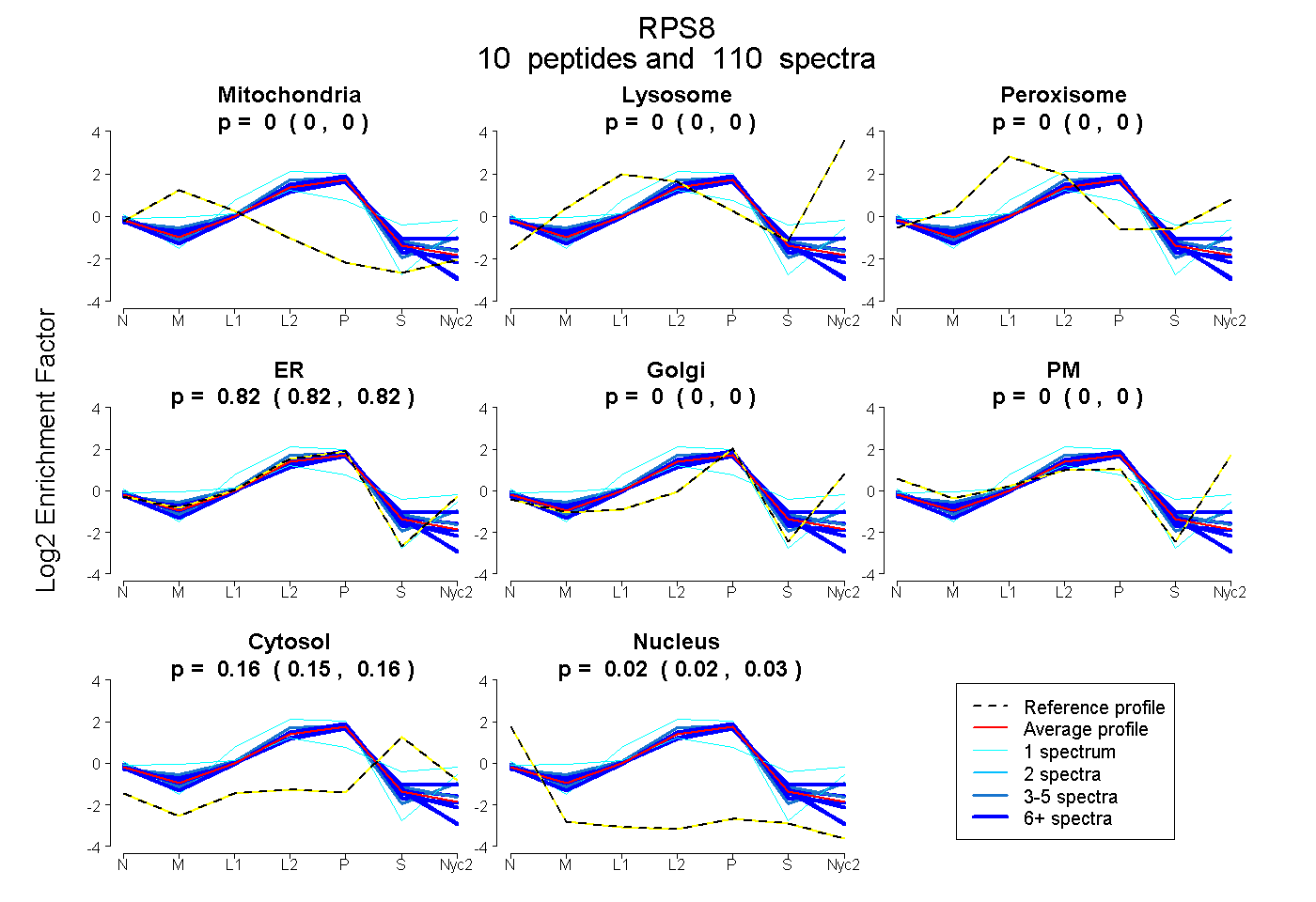
0.000 | 0.005
0.000 | 0.000
0.000 | 0.000
0.816 | 0.821
0.000 | 0.000
0.000 | 0.000
0.153 | 0.159
0.019 | 0.026
peptides
spectra
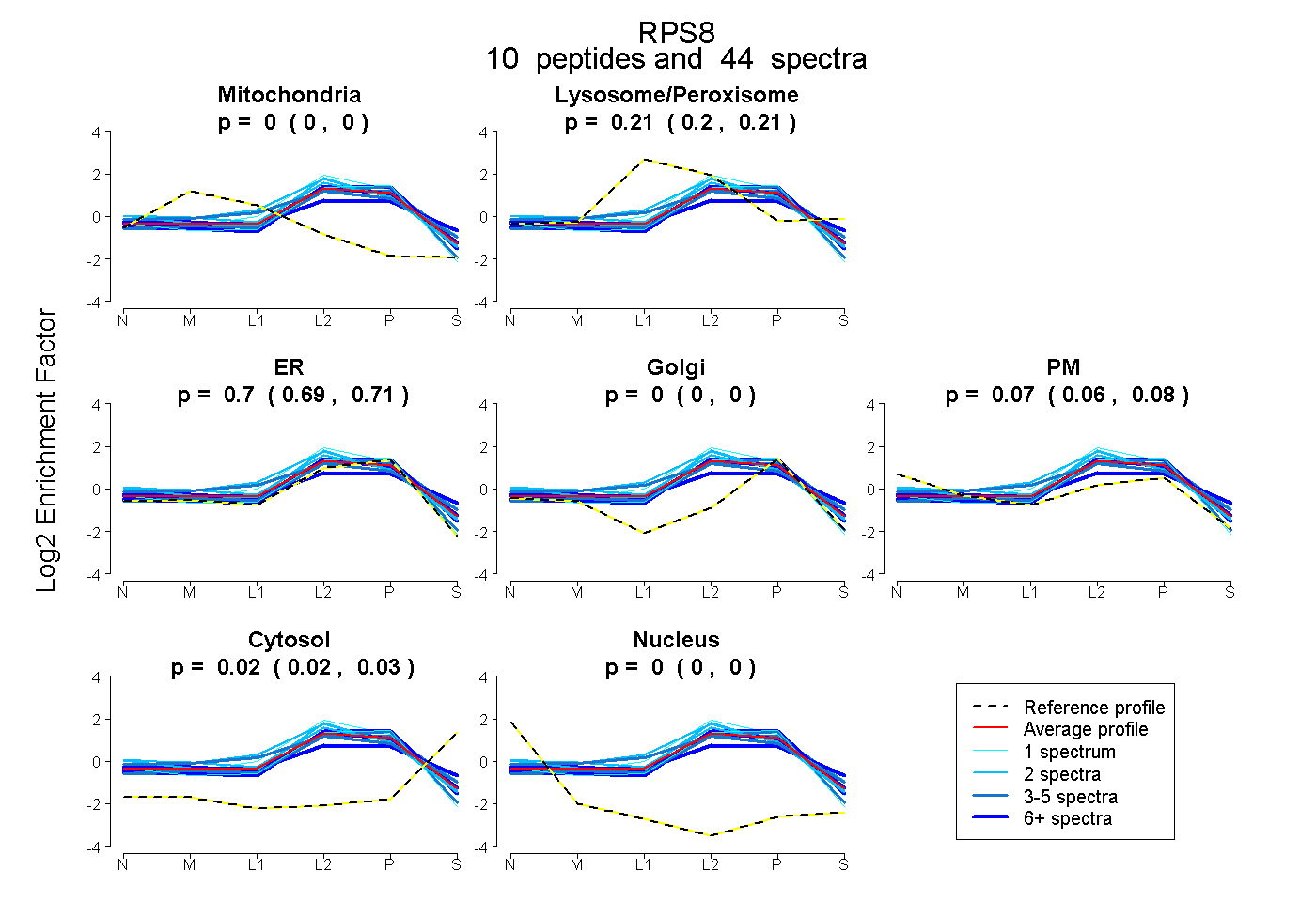
0.000 | 0.000
0.199 | 0.211
0.687 | 0.713
0.000 | 0.000
0.056 | 0.082
0.018 | 0.028
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
110 spectra |
 |
0.002 0.000 | 0.005 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.819 0.816 | 0.821 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.157 0.153 | 0.159 |
0.023 0.019 | 0.026 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
44 spectra |
 |
0.000 0.000 | 0.000 |
0.205 0.199 | 0.211 |
0.701 0.687 | 0.713 |
0.000 0.000 | 0.000 |
0.071 0.056 | 0.082 |
0.023 0.018 | 0.028 |
0.000 0.000 | 0.000 |
| 2 spectra, NCIVLIDSTPYR | 0.000 | 0.224 | 0.564 | 0.000 | 0.212 | 0.000 | 0.000 | |||
| 4 spectra, LTPEEEEILNK | 0.000 | 0.070 | 0.930 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, IIDVVYNASNNELVR | 0.000 | 0.308 | 0.284 | 0.211 | 0.097 | 0.099 | 0.000 | |||
| 4 spectra, ADGYVLEGK | 0.000 | 0.202 | 0.713 | 0.000 | 0.000 | 0.086 | 0.000 | |||
| 1 spectrum, YELGRPAANTK | 0.000 | 0.049 | 0.951 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, QWYESHYALPLGR | 0.000 | 0.371 | 0.352 | 0.111 | 0.166 | 0.000 | 0.000 | |||
| 4 spectra, LDVGNFSWGSECCTR | 0.000 | 0.308 | 0.533 | 0.000 | 0.159 | 0.000 | 0.000 | |||
| 1 spectrum, DNWHK | 0.000 | 0.252 | 0.748 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, ELEFYLR | 0.000 | 0.102 | 0.880 | 0.000 | 0.000 | 0.019 | 0.000 | |||
| 9 spectra, ISSLLEEQFQQGK | 0.000 | 0.191 | 0.679 | 0.000 | 0.104 | 0.025 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
157 spectra |
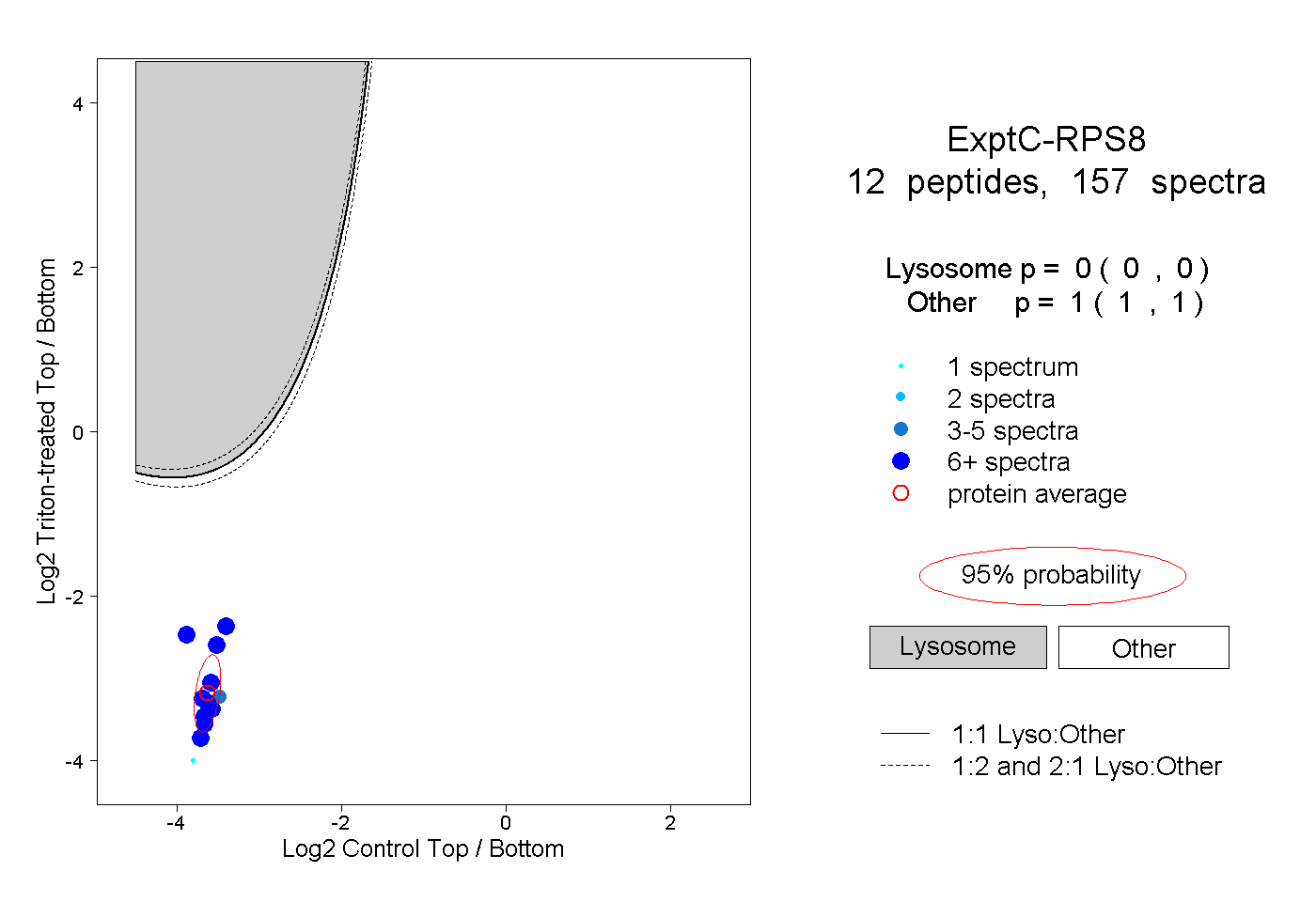 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
16 spectra |
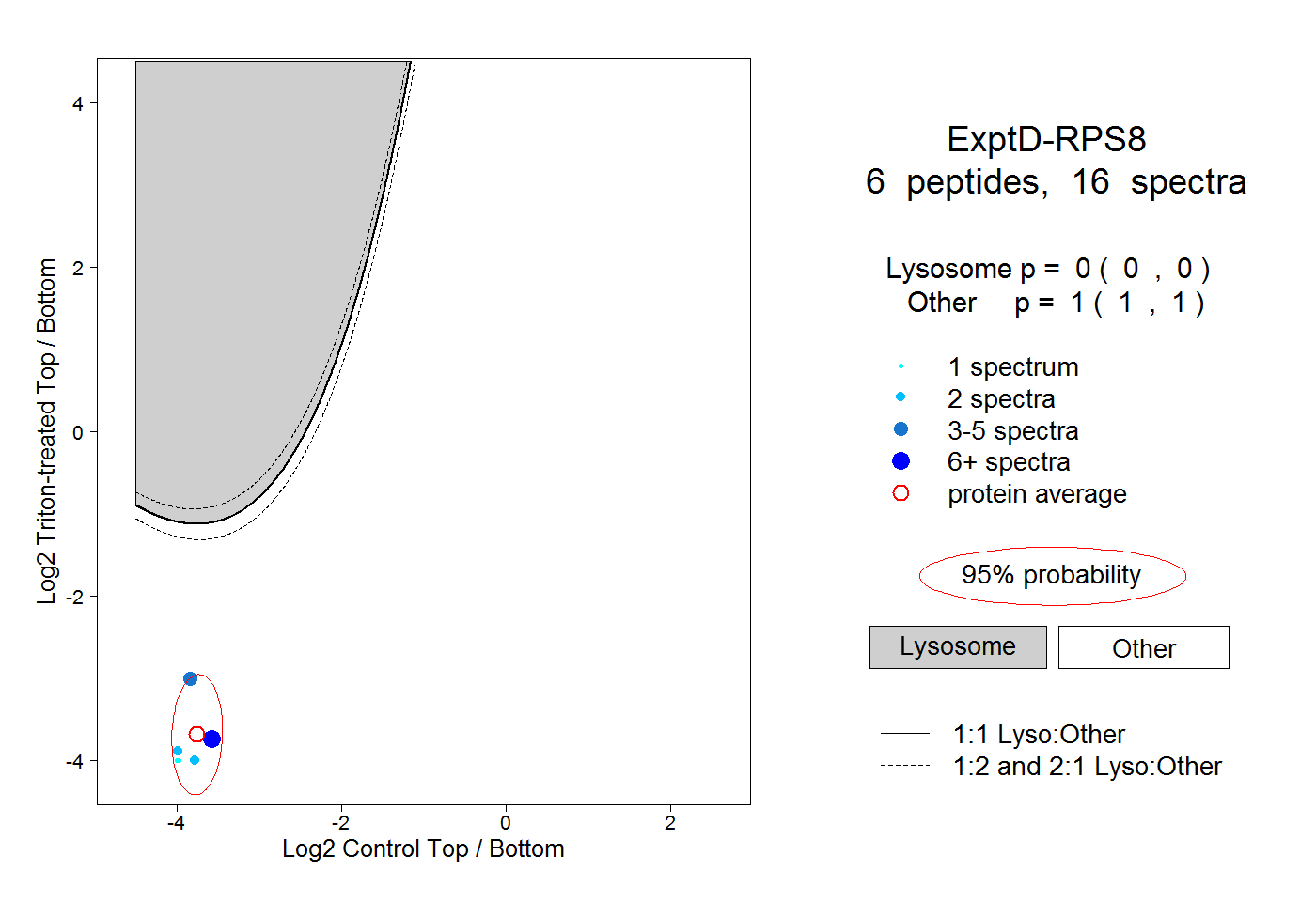 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |