peptides
spectra
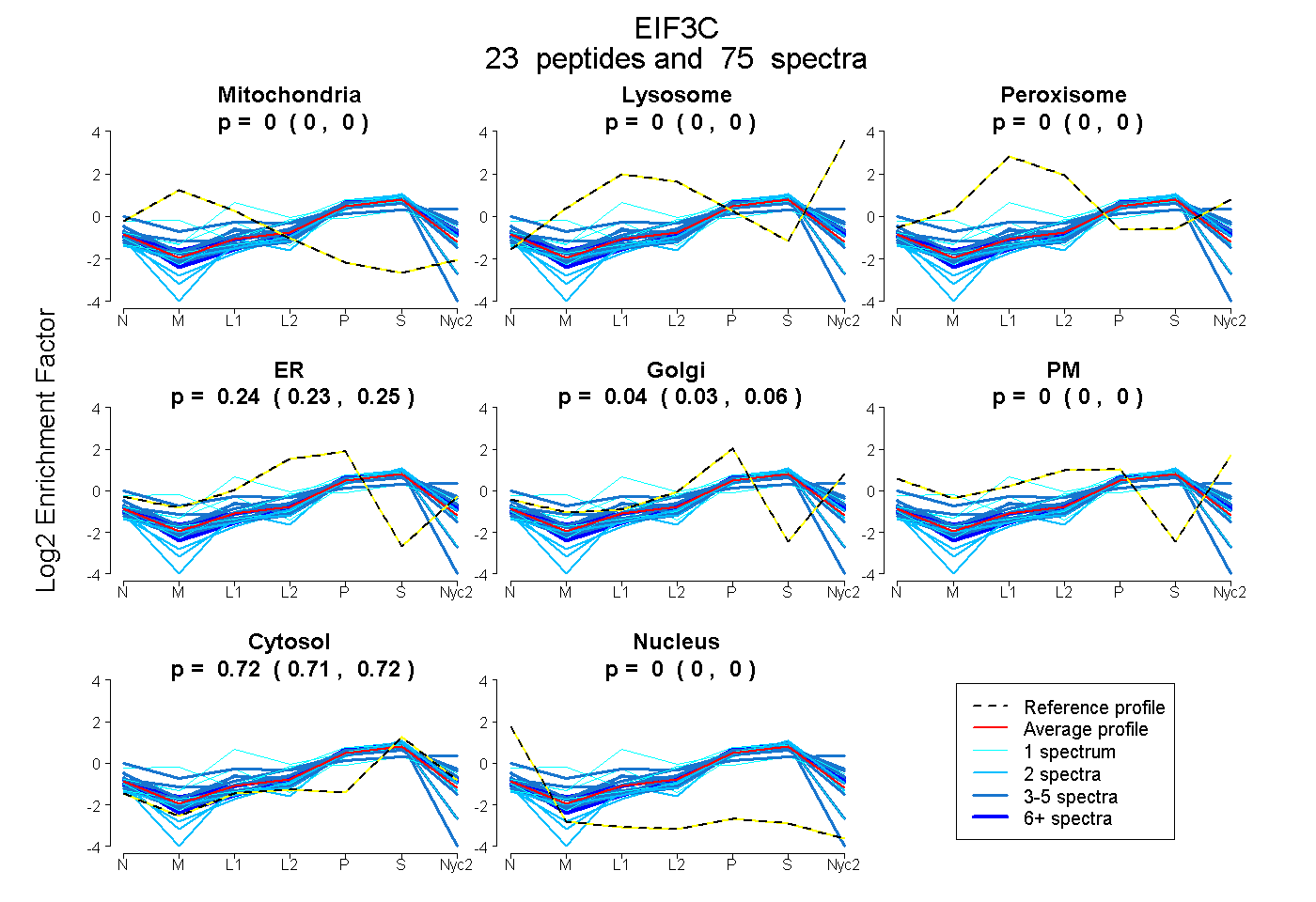
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.225 | 0.252
0.026 | 0.059
0.000 | 0.000
0.713 | 0.719
0.000 | 0.000
peptides
spectra
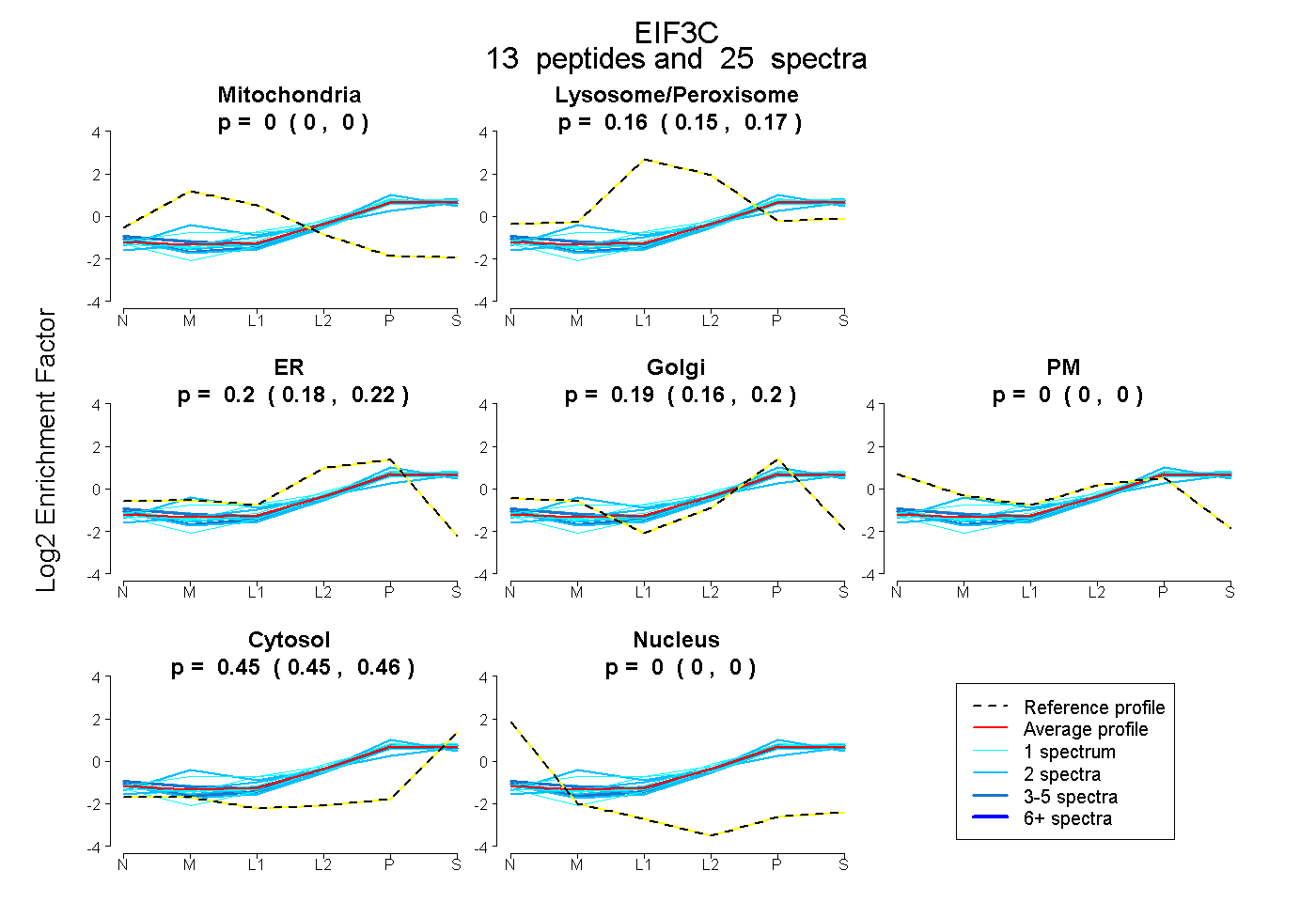
0.000 | 0.000
0.146 | 0.167
0.177 | 0.223
0.164 | 0.204
0.000 | 0.000
0.446 | 0.462
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
75 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.240 0.225 | 0.252 |
0.044 0.026 | 0.059 |
0.000 0.000 | 0.000 |
0.716 0.713 | 0.719 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
25 spectra |
 |
0.000 0.000 | 0.000 |
0.157 0.146 | 0.167 |
0.203 0.177 | 0.223 |
0.185 0.164 | 0.204 |
0.000 0.000 | 0.000 |
0.455 0.446 | 0.462 |
0.000 0.000 | 0.000 |
| 1 spectrum, NQEQEK | 0.000 | 0.291 | 0.000 | 0.338 | 0.000 | 0.371 | 0.000 | |||
| 2 spectra, GTTEEICQIYLR | 0.000 | 0.075 | 0.270 | 0.115 | 0.000 | 0.540 | 0.000 | |||
| 2 spectra, GGVPLVK | 0.000 | 0.133 | 0.155 | 0.280 | 0.000 | 0.431 | 0.000 | |||
| 2 spectra, DAHNALLDIQSSGR | 0.000 | 0.294 | 0.000 | 0.295 | 0.000 | 0.411 | 0.000 | |||
| 5 spectra, FEELTNLIR | 0.000 | 0.087 | 0.321 | 0.076 | 0.000 | 0.516 | 0.000 | |||
| 1 spectrum, ELLGQGLLLR | 0.000 | 0.071 | 0.419 | 0.000 | 0.000 | 0.510 | 0.000 | |||
| 2 spectra, ALSTLR | 0.000 | 0.169 | 0.095 | 0.317 | 0.000 | 0.419 | 0.000 | |||
| 1 spectrum, IQEESLR | 0.000 | 0.121 | 0.274 | 0.176 | 0.000 | 0.429 | 0.000 | |||
| 2 spectra, QFHHQLR | 0.000 | 0.154 | 0.251 | 0.183 | 0.000 | 0.413 | 0.000 | |||
| 1 spectrum, CLEEFELLGK | 0.000 | 0.257 | 0.152 | 0.160 | 0.000 | 0.431 | 0.000 | |||
| 1 spectrum, VWDLFPEADK | 0.000 | 0.128 | 0.375 | 0.000 | 0.000 | 0.497 | 0.000 | |||
| 4 spectra, LGSLVENNER | 0.000 | 0.203 | 0.069 | 0.321 | 0.000 | 0.407 | 0.000 | |||
| 1 spectrum, LNEILQVR | 0.000 | 0.053 | 0.396 | 0.000 | 0.000 | 0.551 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
67 spectra |
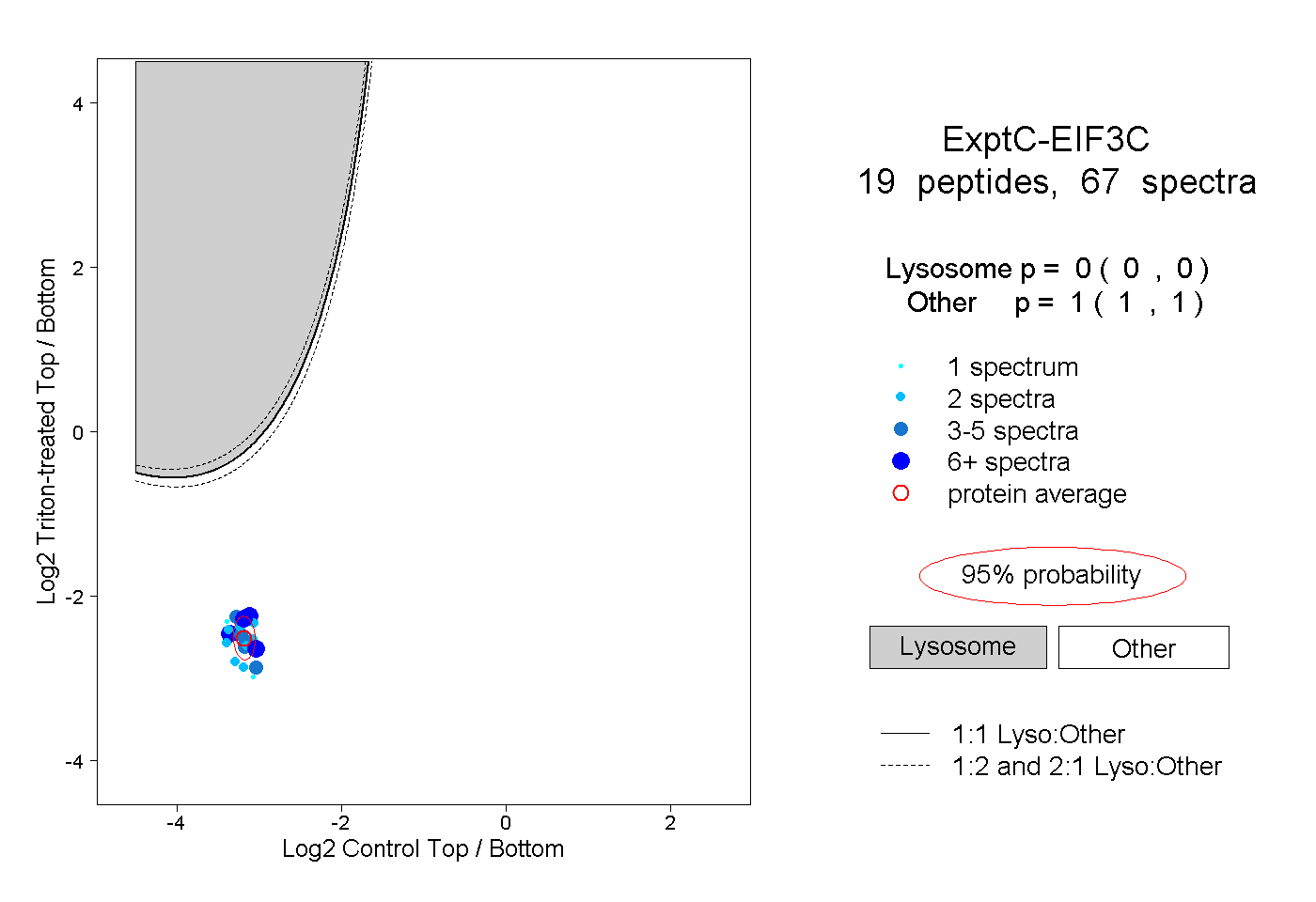 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
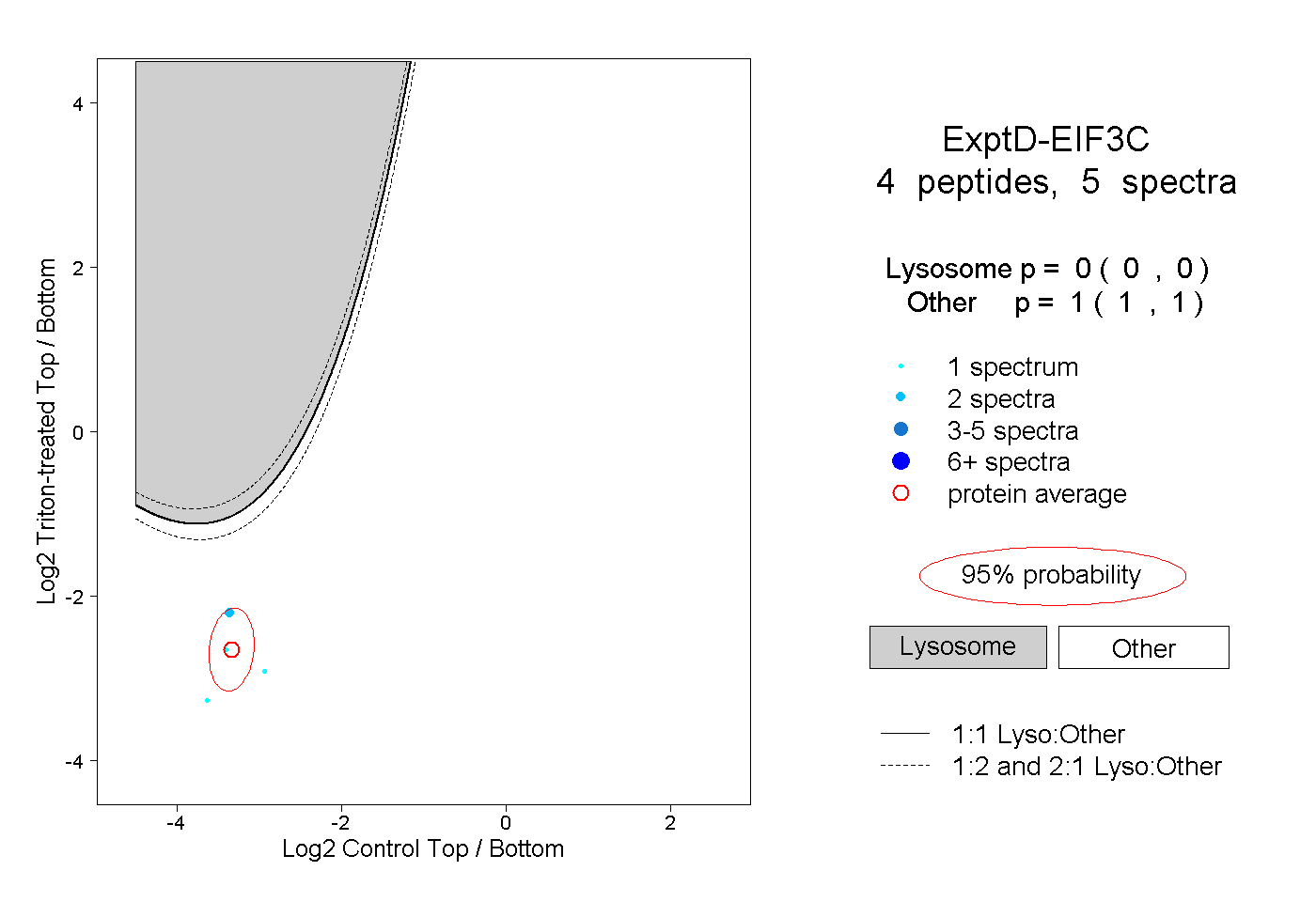 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |