peptides
spectra
0.000 | 0.000
0.016 | 0.022
0.000 | 0.000
0.000 | 0.000
0.036 | 0.042
0.000 | 0.000
0.938 | 0.943
0.000 | 0.000
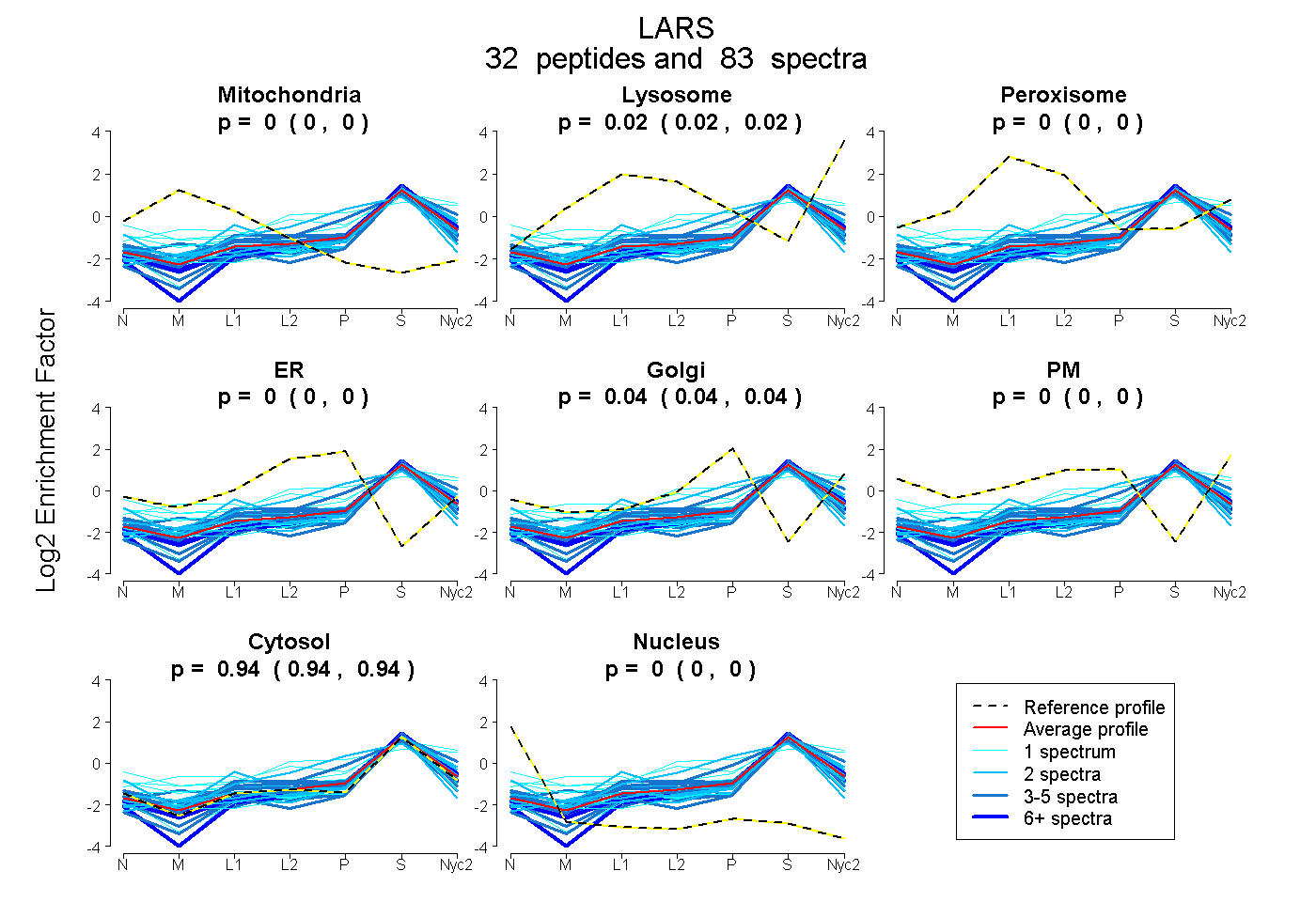
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
83 spectra |
 |
0.000 0.000 | 0.000 |
0.020 0.016 | 0.022 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.039 0.036 | 0.042 |
0.000 0.000 | 0.000 |
0.941 0.938 | 0.943 |
0.000 0.000 | 0.000 |
| 2 spectra, GFYDGVMLVDGFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.994 | 0.006 | ||
| 3 spectra, FASEAEDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.031 | 0.000 | 0.969 | 0.000 | ||
| 2 spectra, WQFLTLR | 0.000 | 0.034 | 0.000 | 0.000 | 0.000 | 0.000 | 0.966 | 0.000 | ||
| 4 spectra, DVWDYVFFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 3 spectra, SFITTDVNPYYDSFVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, NMIDAGDALIYMEPEK | 0.000 | 0.087 | 0.000 | 0.000 | 0.007 | 0.338 | 0.568 | 0.000 | ||
| 2 spectra, YQWNIMK | 0.000 | 0.000 | 0.000 | 0.267 | 0.009 | 0.000 | 0.724 | 0.000 | ||
| 4 spectra, SSQYLMEVAHDLR | 0.000 | 0.148 | 0.000 | 0.000 | 0.000 | 0.000 | 0.852 | 0.000 | ||
| 1 spectrum, ELATEGMHR | 0.000 | 0.000 | 0.167 | 0.157 | 0.000 | 0.000 | 0.676 | 0.000 | ||
| 4 spectra, VDFLK | 0.000 | 0.021 | 0.000 | 0.000 | 0.032 | 0.000 | 0.947 | 0.000 | ||
| 1 spectrum, FSADGMR | 0.000 | 0.184 | 0.000 | 0.000 | 0.000 | 0.057 | 0.759 | 0.000 | ||
| 6 spectra, IQSQNDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, NYPVWQHITLTTLR | 0.208 | 0.100 | 0.000 | 0.000 | 0.000 | 0.000 | 0.692 | 0.000 | ||
| 4 spectra, ADIGDTIVYLVH | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, YTIYSPK | 0.044 | 0.030 | 0.000 | 0.000 | 0.000 | 0.000 | 0.926 | 0.000 | ||
| 1 spectrum, LYTWVEWVK | 0.018 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.982 | 0.000 | ||
| 2 spectra, CEFAVGYQR | 0.000 | 0.000 | 0.000 | 0.039 | 0.000 | 0.000 | 0.925 | 0.036 | ||
| 2 spectra, VMPFVAMIK | 0.000 | 0.076 | 0.000 | 0.000 | 0.000 | 0.000 | 0.924 | 0.000 | ||
| 4 spectra, FDDPLLGPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.024 | 0.000 | 0.976 | 0.000 | ||
| 1 spectrum, EECCPGKPLNVFR | 0.000 | 0.011 | 0.000 | 0.046 | 0.062 | 0.000 | 0.882 | 0.000 | ||
| 3 spectra, NMETFCEESR | 0.000 | 0.073 | 0.000 | 0.026 | 0.000 | 0.000 | 0.901 | 0.000 | ||
| 3 spectra, QGDSCESIIR | 0.000 | 0.045 | 0.000 | 0.000 | 0.050 | 0.000 | 0.904 | 0.000 | ||
| 1 spectrum, LHLGHTFSLSK | 0.058 | 0.077 | 0.010 | 0.000 | 0.040 | 0.000 | 0.816 | 0.000 | ||
| 6 spectra, DGQPCMDHDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.032 | 0.000 | 0.968 | 0.000 | ||
| 7 spectra, SGPANSFNDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.027 | 0.000 | 0.973 | 0.000 | ||
| 1 spectrum, NYMTPAK | 0.000 | 0.028 | 0.000 | 0.000 | 0.000 | 0.000 | 0.972 | 0.000 | ||
| 2 spectra, NMSYQGFTK | 0.000 | 0.124 | 0.000 | 0.000 | 0.000 | 0.000 | 0.876 | 0.000 | ||
| 1 spectrum, QTGEGVGPQEYTLVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, VLDPYPSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.965 | 0.035 | ||
| 3 spectra, EMLANCSSLR | 0.135 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.865 | 0.000 | ||
| 3 spectra, QTFQCLK | 0.000 | 0.000 | 0.012 | 0.080 | 0.113 | 0.000 | 0.794 | 0.000 | ||
| 2 spectra, QEFEFWYPVDLR | 0.000 | 0.000 | 0.115 | 0.000 | 0.000 | 0.000 | 0.885 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
11 spectra |
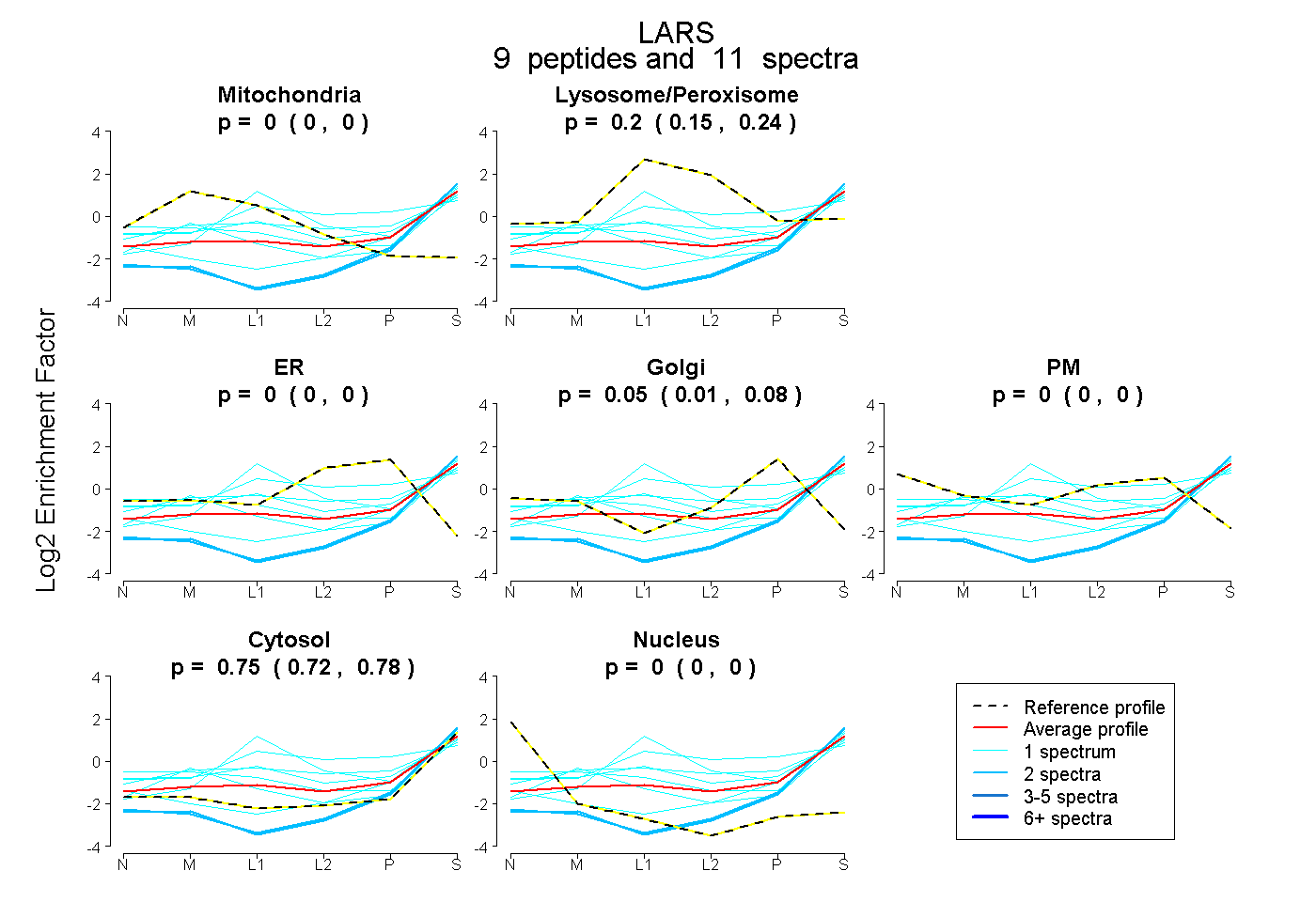 |
0.000 0.000 | 0.000 |
0.196 0.146 | 0.236 |
0.000 0.000 | 0.000 |
0.051 0.014 | 0.084 |
0.000 0.000 | 0.000 |
0.753 0.725 | 0.776 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
43 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
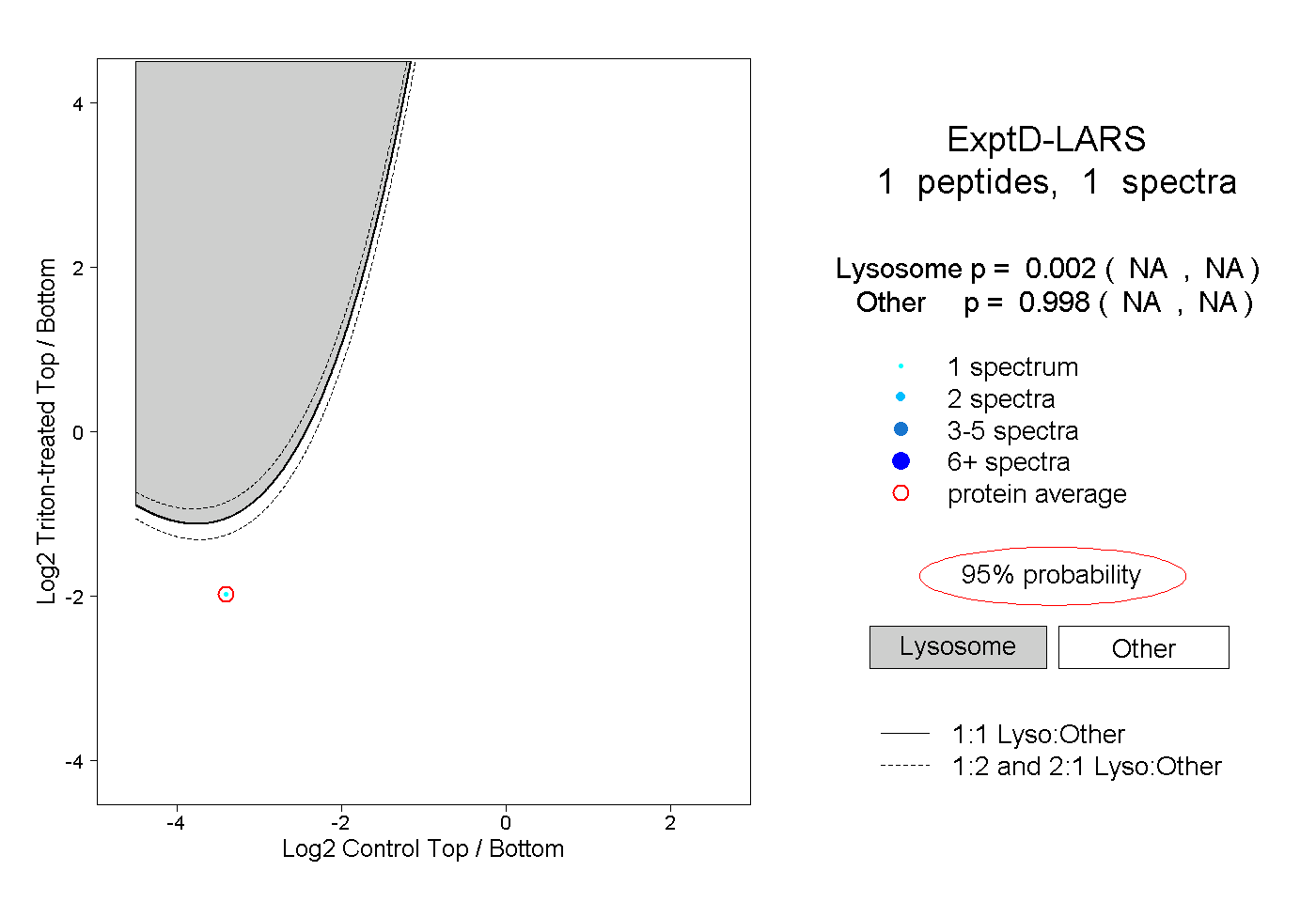 |
0.002 NA | NA |
0.998 NA | NA |