peptides
spectra
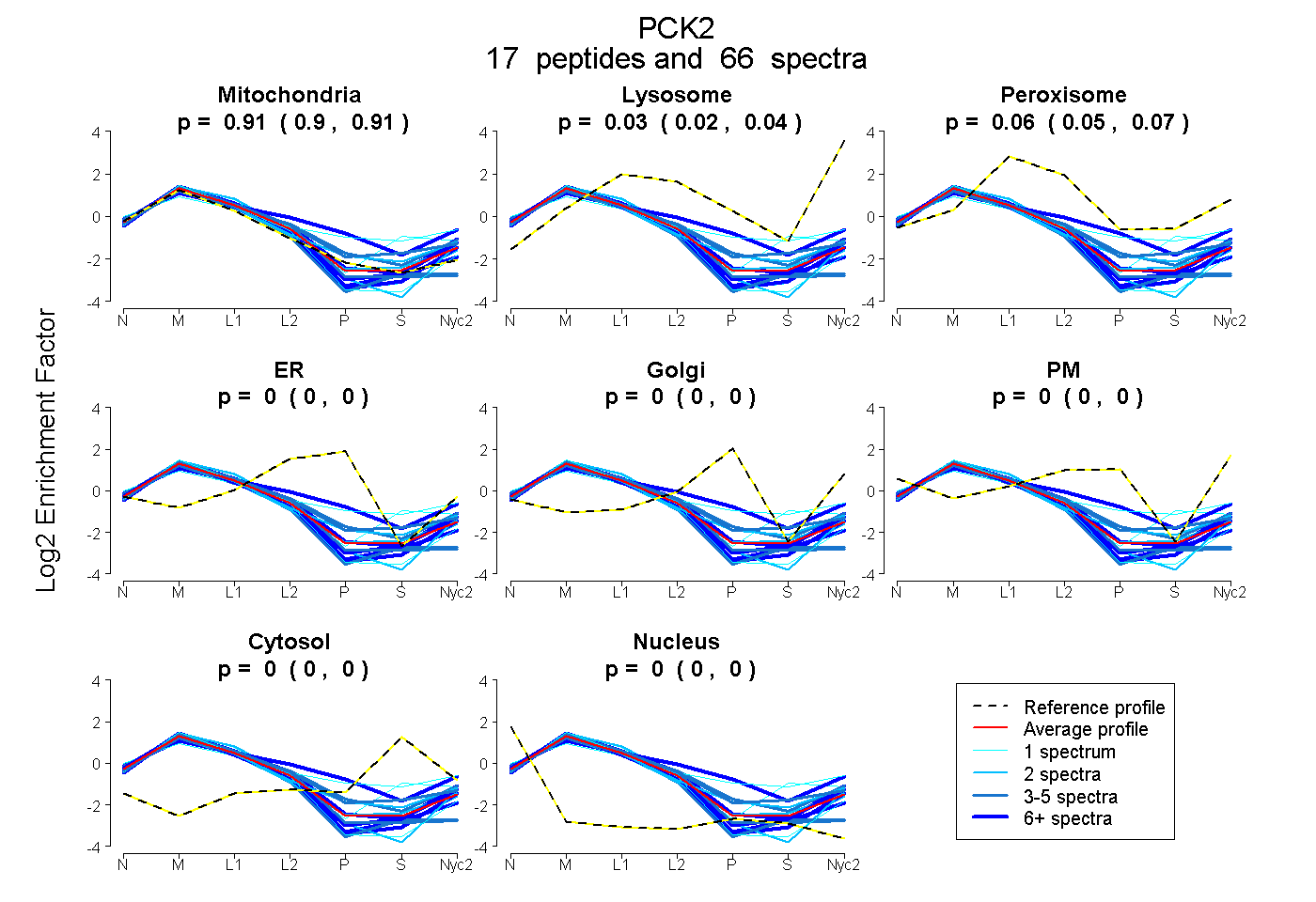
0.901 | 0.909
0.021 | 0.040
0.053 | 0.072
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
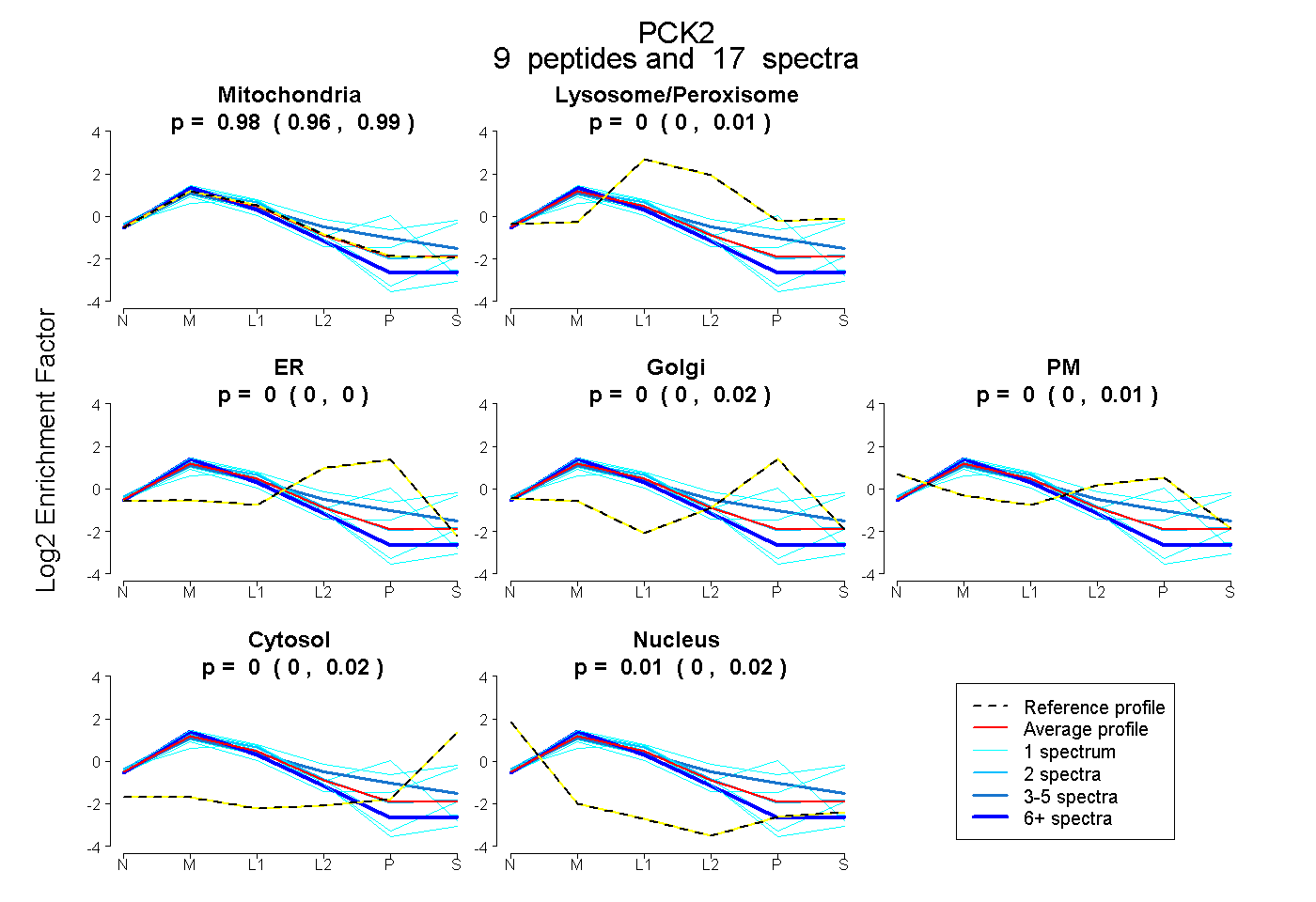
0.960 | 0.989
0.000 | 0.005
0.000 | 0.000
0.000 | 0.015
0.000 | 0.009
0.000 | 0.022
0.000 | 0.020
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
66 spectra |
 |
0.906 0.901 | 0.909 |
0.031 0.021 | 0.040 |
0.063 0.053 | 0.072 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
17 spectra |
 |
0.984 0.960 | 0.989 |
0.000 0.000 | 0.005 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.015 |
0.000 0.000 | 0.009 |
0.004 0.000 | 0.022 |
0.012 0.000 | 0.020 |
| 1 spectrum, FCVPAR | 0.614 | 0.000 | 0.205 | 0.181 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, TVIVTSSQR | 0.946 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.054 | |||
| 3 spectra, LGTHVLQALGDGDFIK | 0.723 | 0.128 | 0.000 | 0.148 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, VLDWICR | 0.974 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.026 | |||
| 1 spectrum, DFWEQEVR | 0.999 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.001 | |||
| 1 spectrum, HGVFVGSAMR | 0.368 | 0.403 | 0.000 | 0.080 | 0.000 | 0.150 | 0.000 | |||
| 1 spectrum, SYLTEQVNQDLPK | 0.666 | 0.053 | 0.000 | 0.000 | 0.000 | 0.282 | 0.000 | |||
| 1 spectrum, EGALDLSGLR | 0.969 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.031 | |||
| 2 spectra, TLIGHVPEQR | 0.988 | 0.012 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
177 spectra |
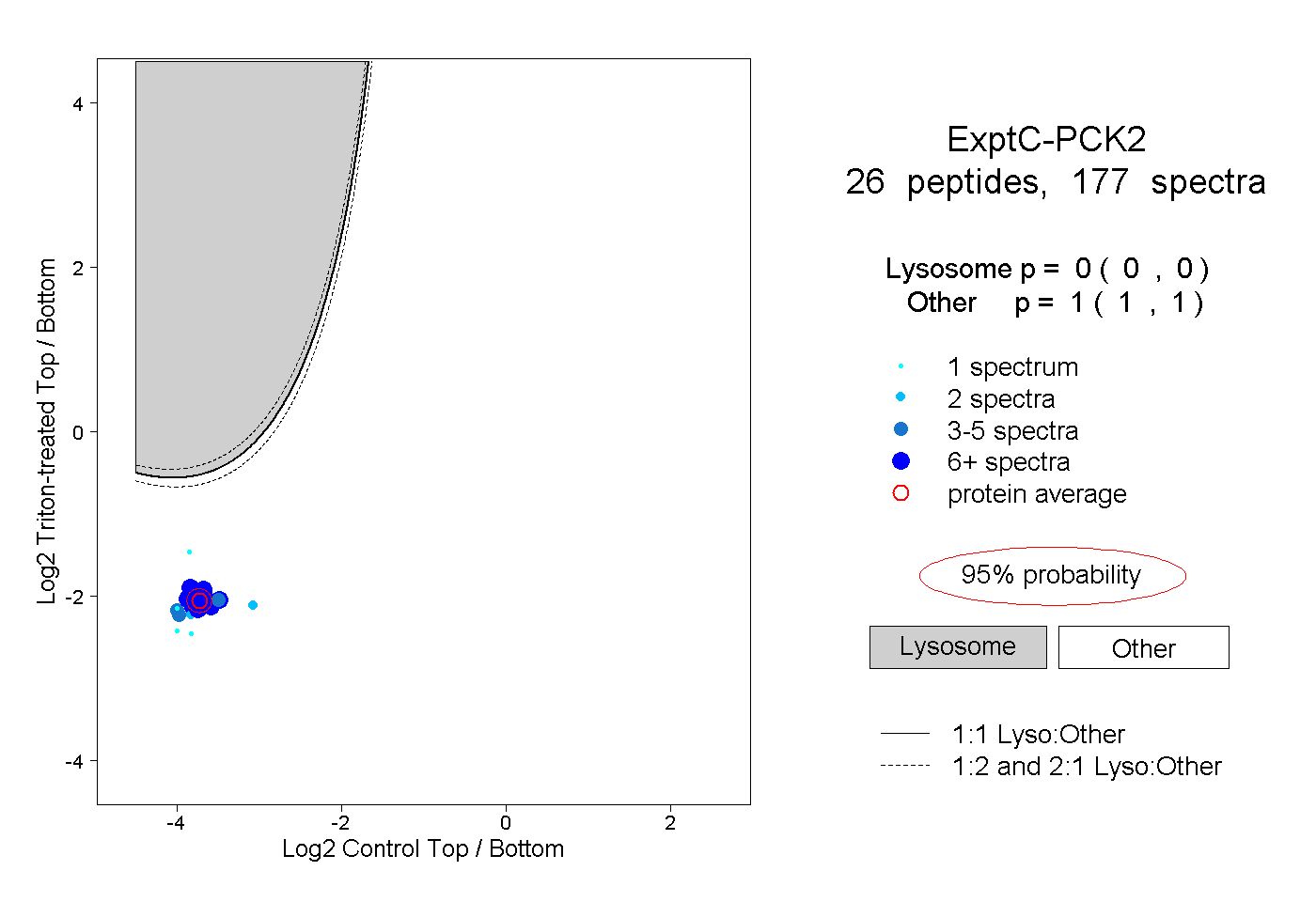 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
14 spectra |
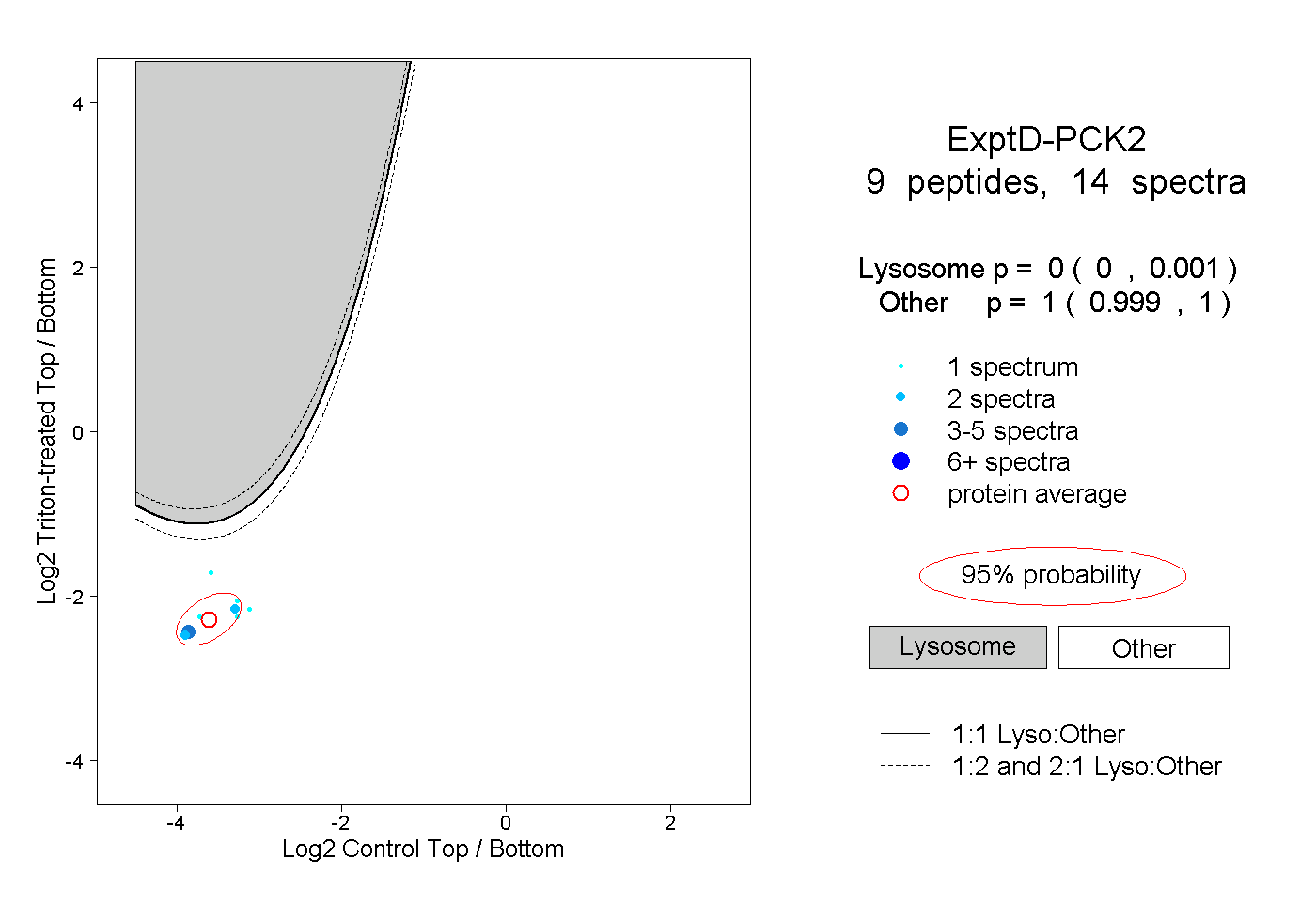 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |