peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.027 | 0.098
0.000 | 0.067
0.000 | 0.000
0.592 | 0.606
0.286 | 0.317
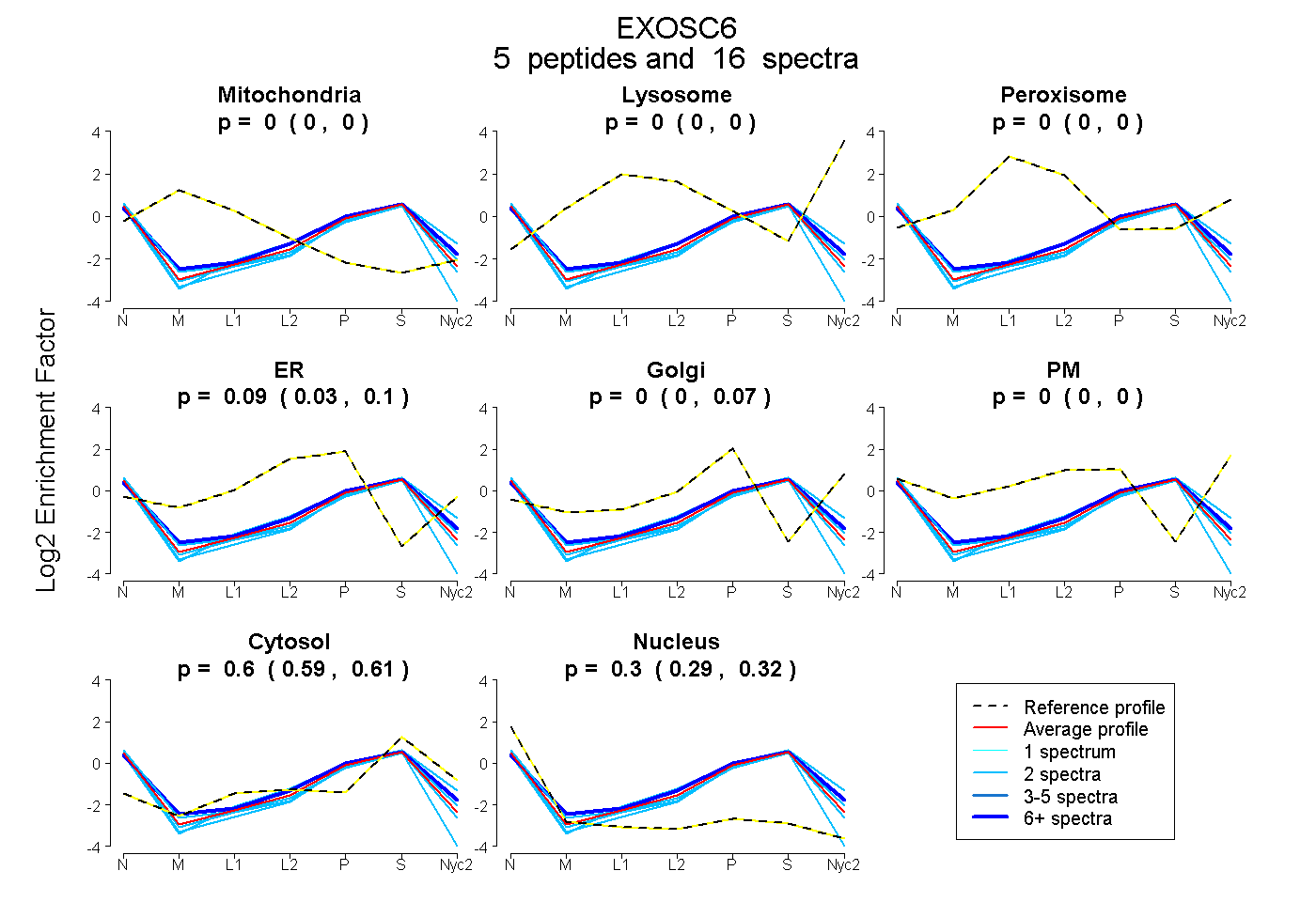
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
16 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.091 0.027 | 0.098 |
0.003 0.000 | 0.067 |
0.000 0.000 | 0.000 |
0.602 0.592 | 0.606 |
0.303 0.286 | 0.317 |
| 2 spectra, GGGPAGAGGEAPAALR | 0.000 | 0.000 | 0.000 | 0.052 | 0.000 | 0.000 | 0.599 | 0.349 | ||
| 8 spectra, LRPVYAR | 0.000 | 0.000 | 0.000 | 0.060 | 0.116 | 0.000 | 0.597 | 0.227 | ||
| 2 spectra, LGLEGCQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.163 | 0.000 | 0.648 | 0.189 | ||
| 2 spectra, VLCAVSGPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.119 | 0.000 | 0.574 | 0.307 | ||
| 2 spectra, LYPVLQQCLVR | 0.000 | 0.000 | 0.000 | 0.002 | 0.000 | 0.000 | 0.538 | 0.460 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
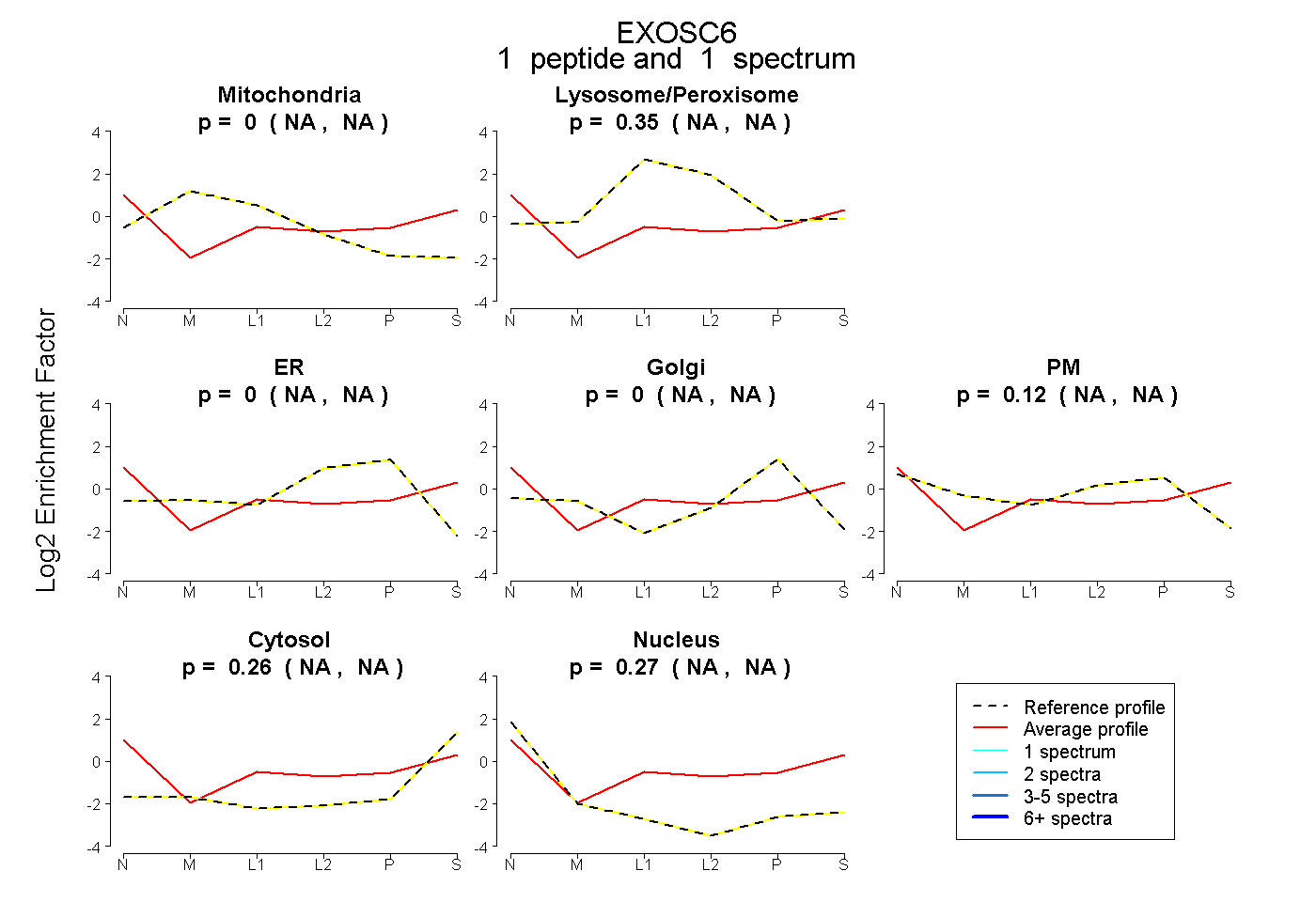 |
0.000 NA | NA |
0.350 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.122 NA | NA |
0.259 NA | NA |
0.269 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
1 spectrum |
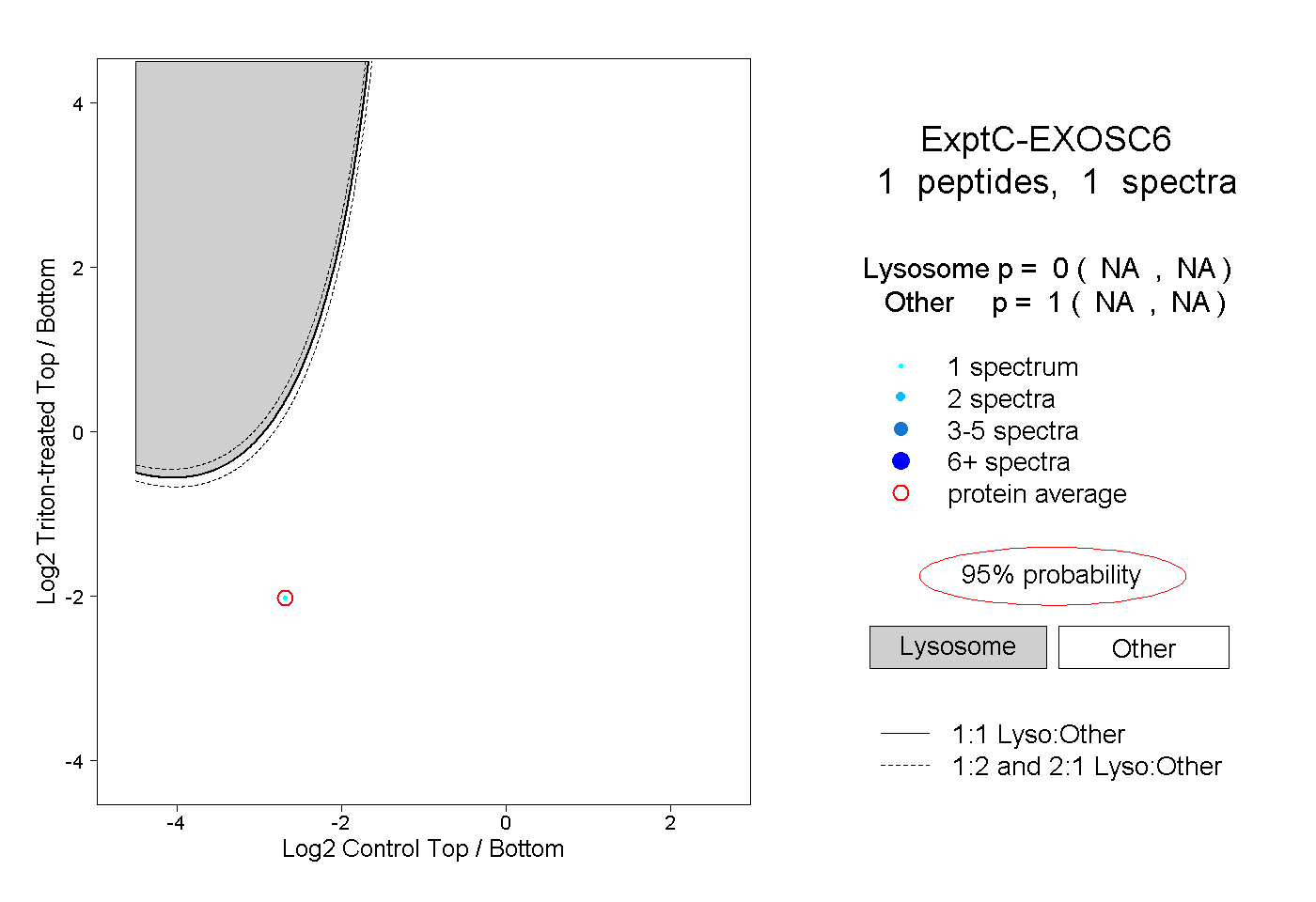 |
0.000 NA | NA |
1.000 NA | NA |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
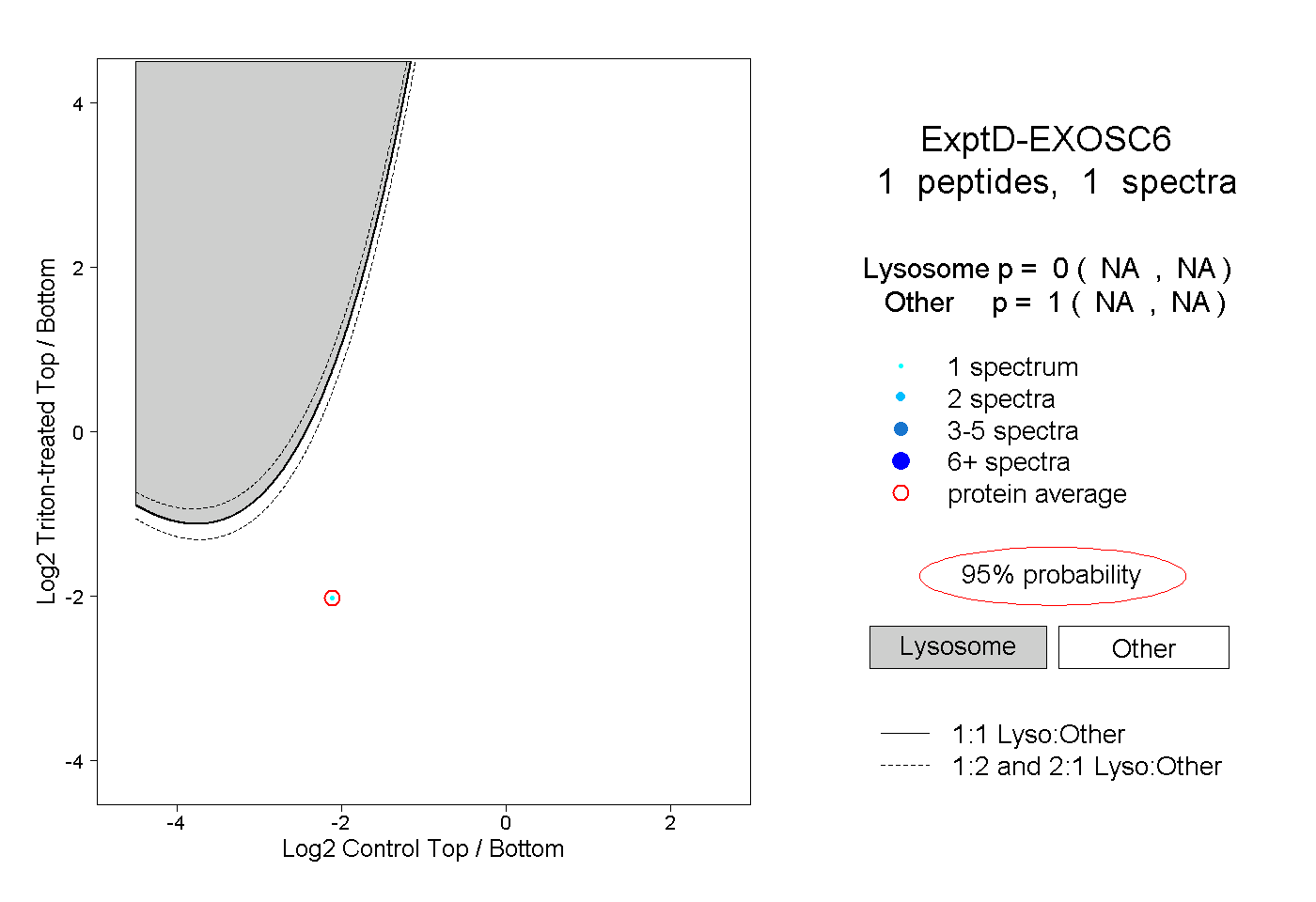 |
0.000 NA | NA |
1.000 NA | NA |