peptides
spectra
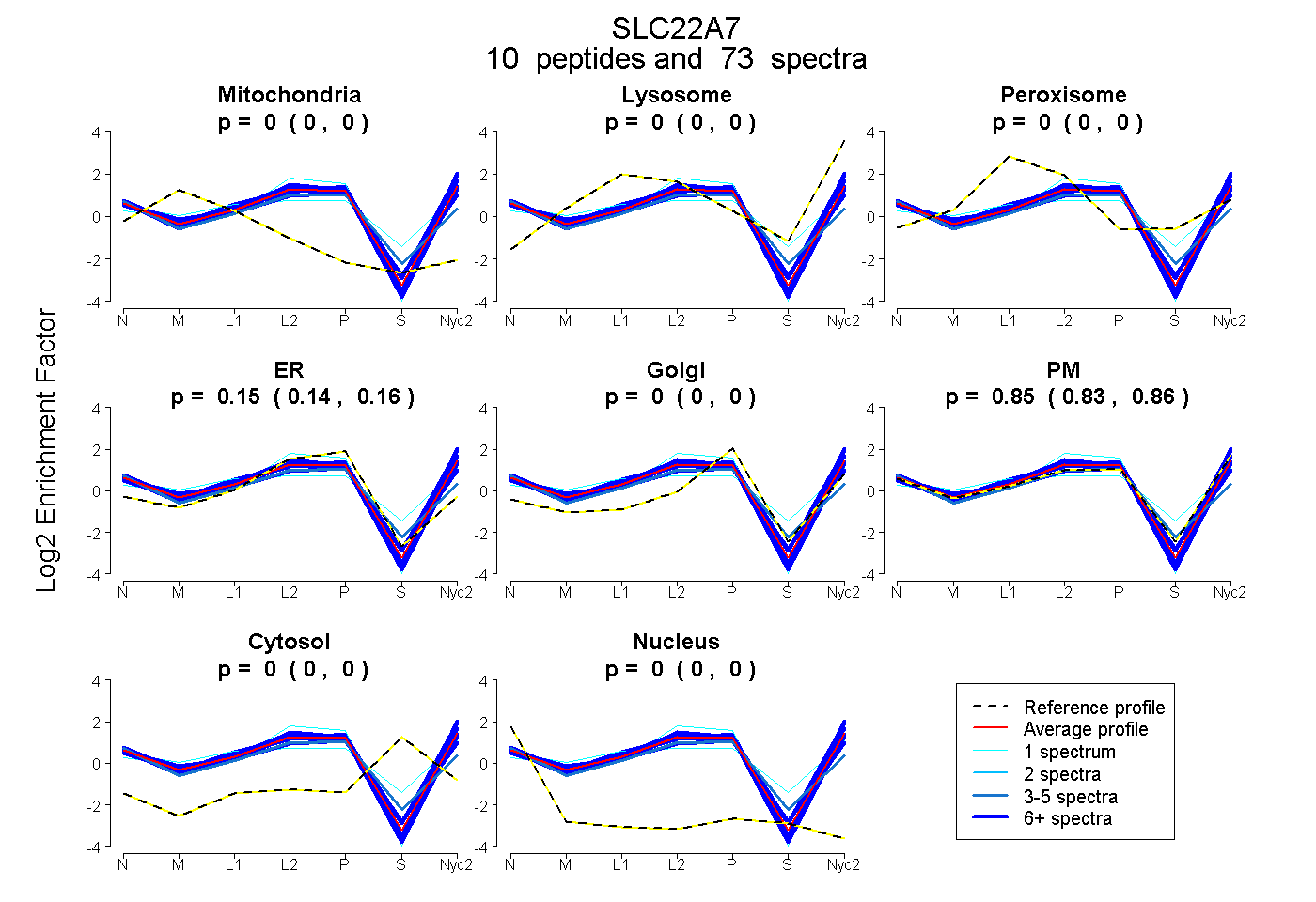
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.142 | 0.165
0.000 | 0.000
0.833 | 0.857
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
73 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.154 0.142 | 0.165 |
0.000 0.000 | 0.000 |
0.846 0.833 | 0.857 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 10 spectra, WLLTQGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | ||
| 1 spectrum, AQLPETIQDVER | 0.040 | 0.000 | 0.208 | 0.000 | 0.036 | 0.650 | 0.066 | 0.000 | ||
| 10 spectra, VGGFGPFQLR | 0.001 | 0.000 | 0.000 | 0.172 | 0.000 | 0.827 | 0.000 | 0.000 | ||
| 6 spectra, ETDGSFSSCLR | 0.013 | 0.000 | 0.000 | 0.198 | 0.000 | 0.753 | 0.000 | 0.036 | ||
| 8 spectra, NLVLMALPR | 0.000 | 0.007 | 0.000 | 0.114 | 0.000 | 0.879 | 0.000 | 0.000 | ||
| 11 spectra, ALQRPSYLDLFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | ||
| 3 spectra, YLLSCAK | 0.000 | 0.000 | 0.085 | 0.347 | 0.000 | 0.483 | 0.000 | 0.086 | ||
| 13 spectra, QTGLGLTALMGR | 0.000 | 0.028 | 0.000 | 0.000 | 0.000 | 0.972 | 0.000 | 0.000 | ||
| 1 spectrum, LNGRPVGEGSLSQEALNNVVTMER | 0.000 | 0.000 | 0.000 | 0.320 | 0.000 | 0.680 | 0.000 | 0.000 | ||
| 10 spectra, GFEDLLDK | 0.000 | 0.000 | 0.000 | 0.240 | 0.000 | 0.760 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
20 spectra |
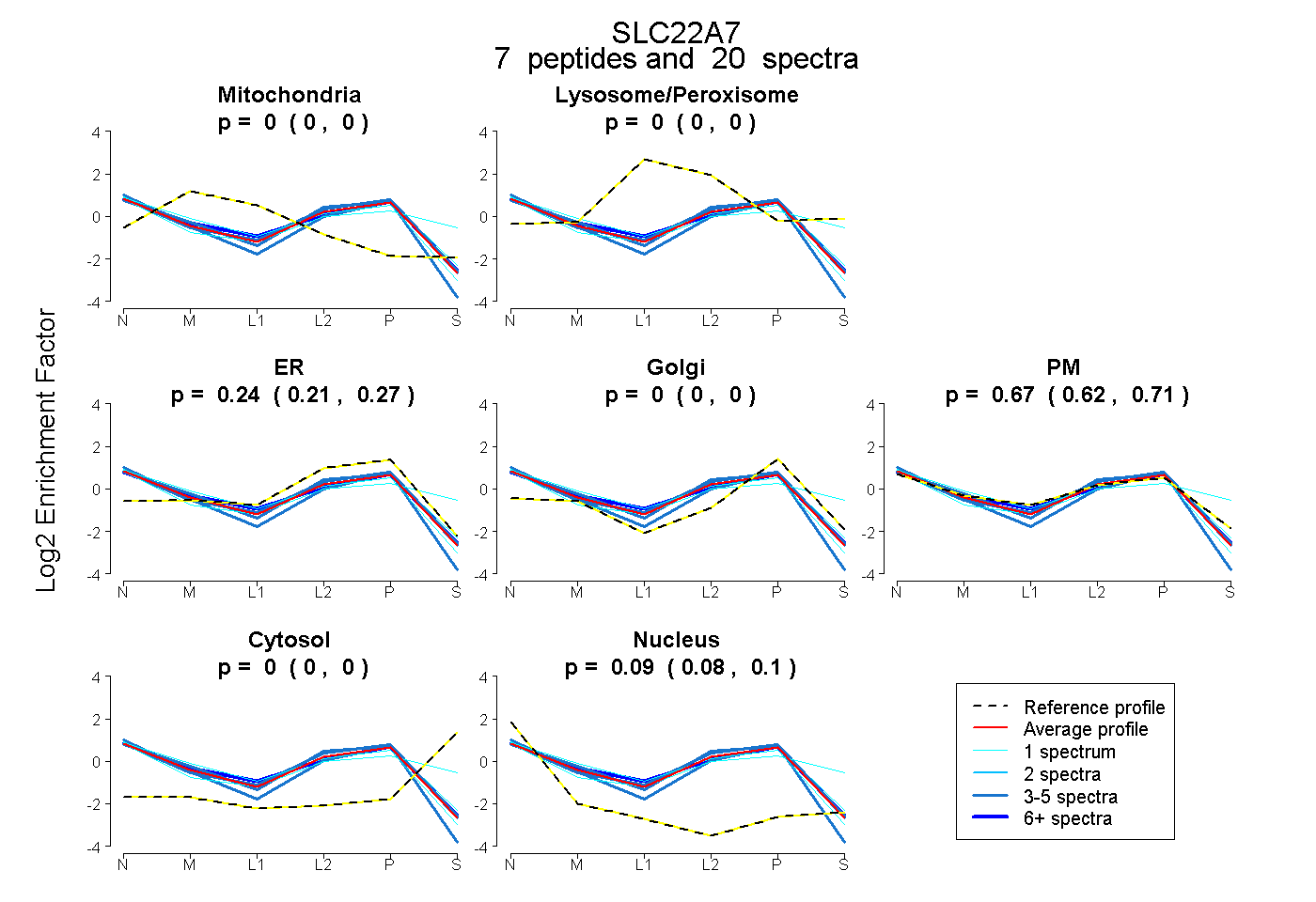 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.244 0.208 | 0.272 |
0.000 0.000 | 0.000 |
0.671 0.624 | 0.707 |
0.000 0.000 | 0.000 |
0.086 0.075 | 0.096 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
79 spectra |
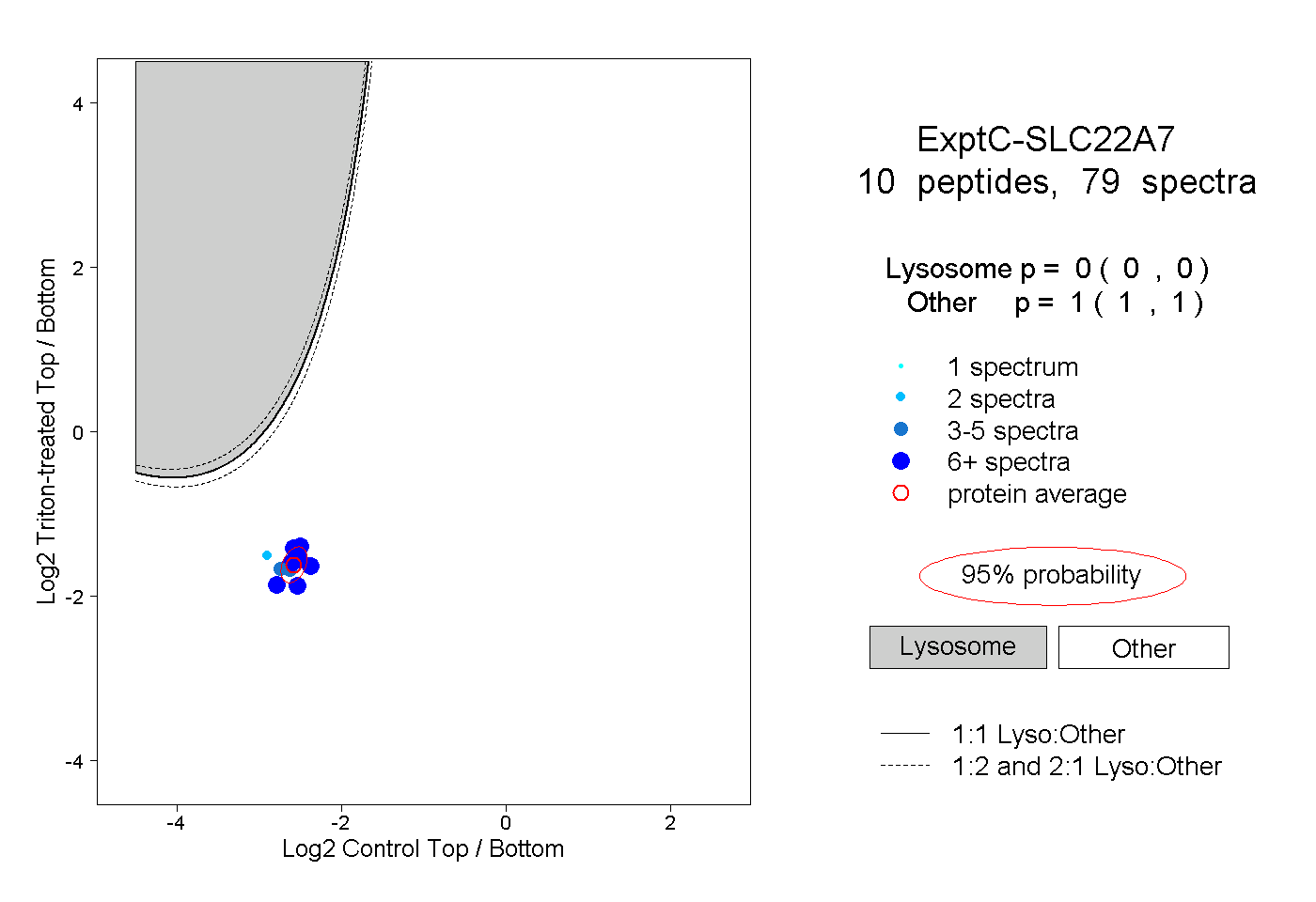 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
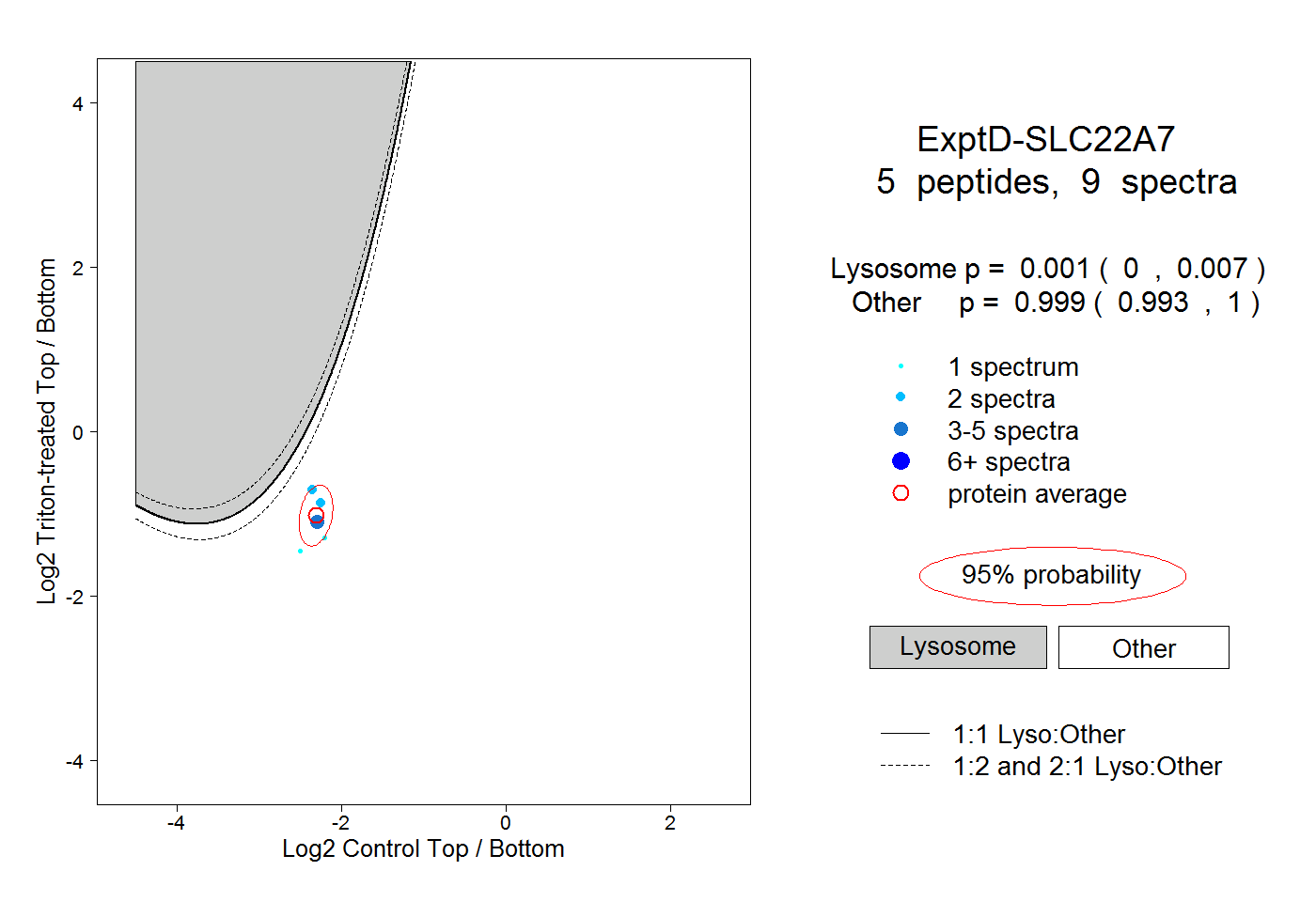 |
0.001 0.000 | 0.007 |
0.999 0.993 | 1.000 |