peptides
spectra
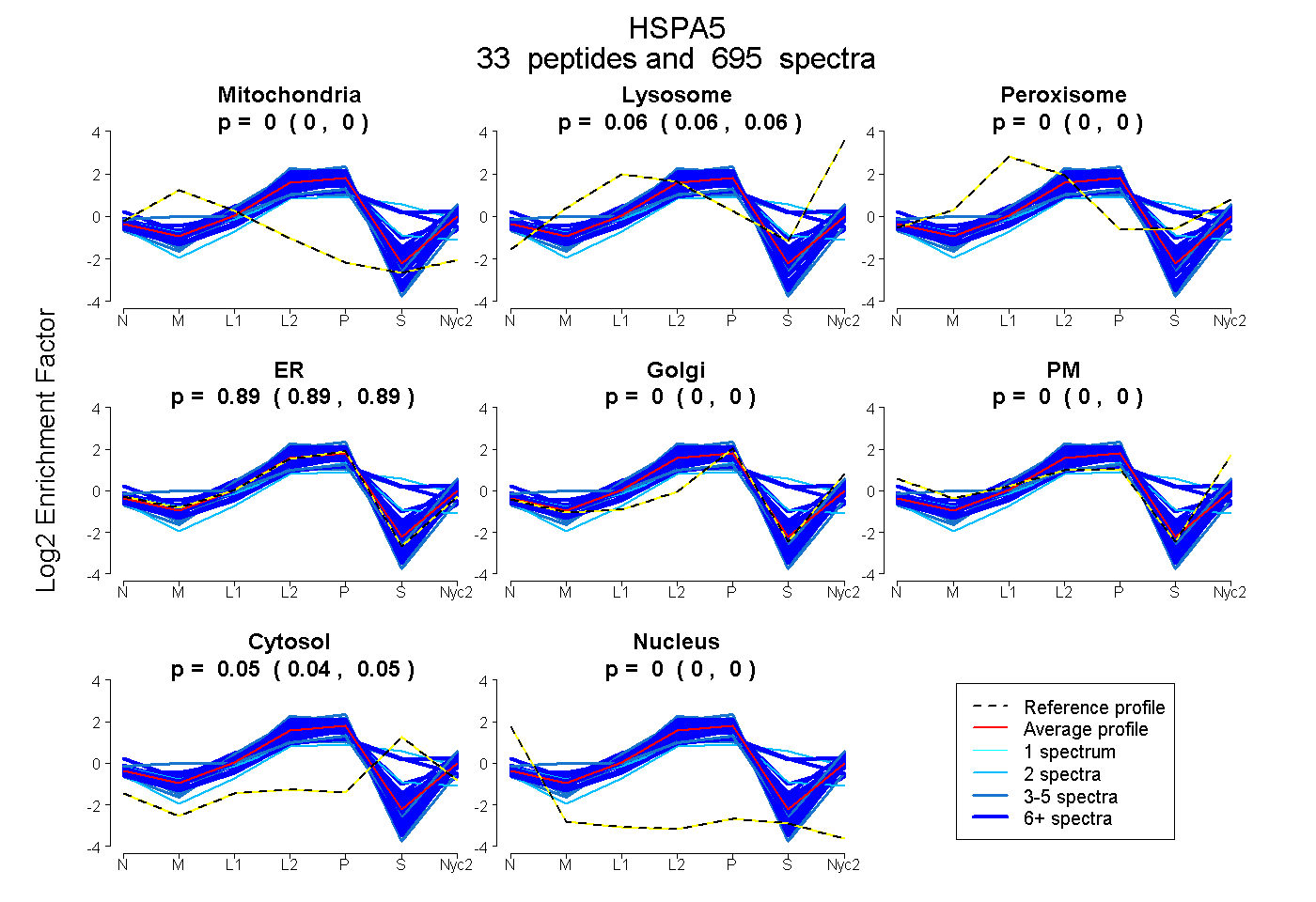
0.000 | 0.000
0.060 | 0.062
0.000 | 0.000
0.891 | 0.895
0.000 | 0.000
0.000 | 0.000
0.044 | 0.047
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
695 spectra |
 |
0.000 0.000 | 0.000 |
0.061 0.060 | 0.062 |
0.000 0.000 | 0.000 |
0.893 0.891 | 0.895 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.046 0.044 | 0.047 |
0.000 0.000 | 0.000 |
| 39 spectra, VYEGERPLTK | 0.000 | 0.023 | 0.000 | 0.966 | 0.000 | 0.011 | 0.000 | 0.000 | ||
| 13 spectra, ELEEIVQPIISK | 0.000 | 0.057 | 0.059 | 0.833 | 0.000 | 0.000 | 0.051 | 0.000 | ||
| 3 spectra, IEIESFFEGEDFSETLTR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 13 spectra, ETAEAYLGK | 0.000 | 0.079 | 0.000 | 0.703 | 0.057 | 0.035 | 0.125 | 0.000 | ||
| 40 spectra, VMEHFIK | 0.000 | 0.034 | 0.035 | 0.813 | 0.000 | 0.000 | 0.117 | 0.000 | ||
| 32 spectra, IQQLVK | 0.000 | 0.054 | 0.000 | 0.946 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 18 spectra, SDIDEIVLVGGSTR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, VTHAVVTVPAYFNDAQR | 0.100 | 0.050 | 0.000 | 0.403 | 0.101 | 0.346 | 0.000 | 0.000 | ||
| 3 spectra, DNHLLGTFDLTGIPPAPR | 0.000 | 0.089 | 0.126 | 0.424 | 0.000 | 0.003 | 0.358 | 0.000 | ||
| 31 spectra, LIGDAAK | 0.000 | 0.163 | 0.011 | 0.450 | 0.000 | 0.000 | 0.376 | 0.000 | ||
| 15 spectra, NELESYAYSLK | 0.000 | 0.036 | 0.000 | 0.905 | 0.000 | 0.059 | 0.000 | 0.000 | ||
| 36 spectra, DAGTIAGLNVMR | 0.000 | 0.095 | 0.010 | 0.856 | 0.000 | 0.023 | 0.016 | 0.000 | ||
| 10 spectra, NTVVPTK | 0.000 | 0.044 | 0.000 | 0.935 | 0.000 | 0.021 | 0.000 | 0.000 | ||
| 2 spectra, IINEPTAAAIAYGLDK | 0.000 | 0.065 | 0.000 | 0.422 | 0.000 | 0.000 | 0.513 | 0.000 | ||
| 7 spectra, NQLTSNPENTVFDAK | 0.000 | 0.053 | 0.072 | 0.583 | 0.000 | 0.176 | 0.115 | 0.000 | ||
| 17 spectra, TFAPEEISAMVLTK | 0.000 | 0.073 | 0.000 | 0.915 | 0.000 | 0.000 | 0.012 | 0.000 | ||
| 109 spectra, LTPEFSHR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, TKPYIQVDIGGGQTK | 0.020 | 0.000 | 0.043 | 0.679 | 0.000 | 0.000 | 0.258 | 0.000 | ||
| 52 spectra, ITITNDQNR | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 14 spectra, STMKPVQK | 0.000 | 0.032 | 0.000 | 0.922 | 0.000 | 0.000 | 0.046 | 0.000 | ||
| 6 spectra, FAEEDK | 0.000 | 0.000 | 0.127 | 0.706 | 0.000 | 0.000 | 0.168 | 0.000 | ||
| 12 spectra, VTAEDK | 0.000 | 0.073 | 0.000 | 0.899 | 0.008 | 0.000 | 0.020 | 0.000 | ||
| 24 spectra, MVNDAEK | 0.000 | 0.086 | 0.000 | 0.818 | 0.089 | 0.000 | 0.007 | 0.000 | ||
| 8 spectra, NQIGDK | 0.000 | 0.013 | 0.000 | 0.878 | 0.000 | 0.109 | 0.000 | 0.000 | ||
| 22 spectra, ALSSQHQAR | 0.000 | 0.000 | 0.127 | 0.805 | 0.000 | 0.000 | 0.000 | 0.068 | ||
| 3 spectra, IEWLESHQDADIEDFK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 52 spectra, VEIIANDQGNR | 0.000 | 0.000 | 0.082 | 0.509 | 0.000 | 0.000 | 0.408 | 0.000 | ||
| 14 spectra, ITPSYVAFTPEGER | 0.000 | 0.052 | 0.000 | 0.923 | 0.000 | 0.000 | 0.025 | 0.000 | ||
| 10 spectra, LTPEEIER | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 11 spectra, TWNDPSVQQDIK | 0.000 | 0.078 | 0.000 | 0.794 | 0.000 | 0.079 | 0.049 | 0.000 | ||
| 5 spectra, EFFNGK | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 44 spectra, VLEDSDLK | 0.000 | 0.055 | 0.000 | 0.919 | 0.000 | 0.026 | 0.000 | 0.000 | ||
| 23 spectra, FEELNMDLFR | 0.000 | 0.093 | 0.000 | 0.907 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
307 spectra |
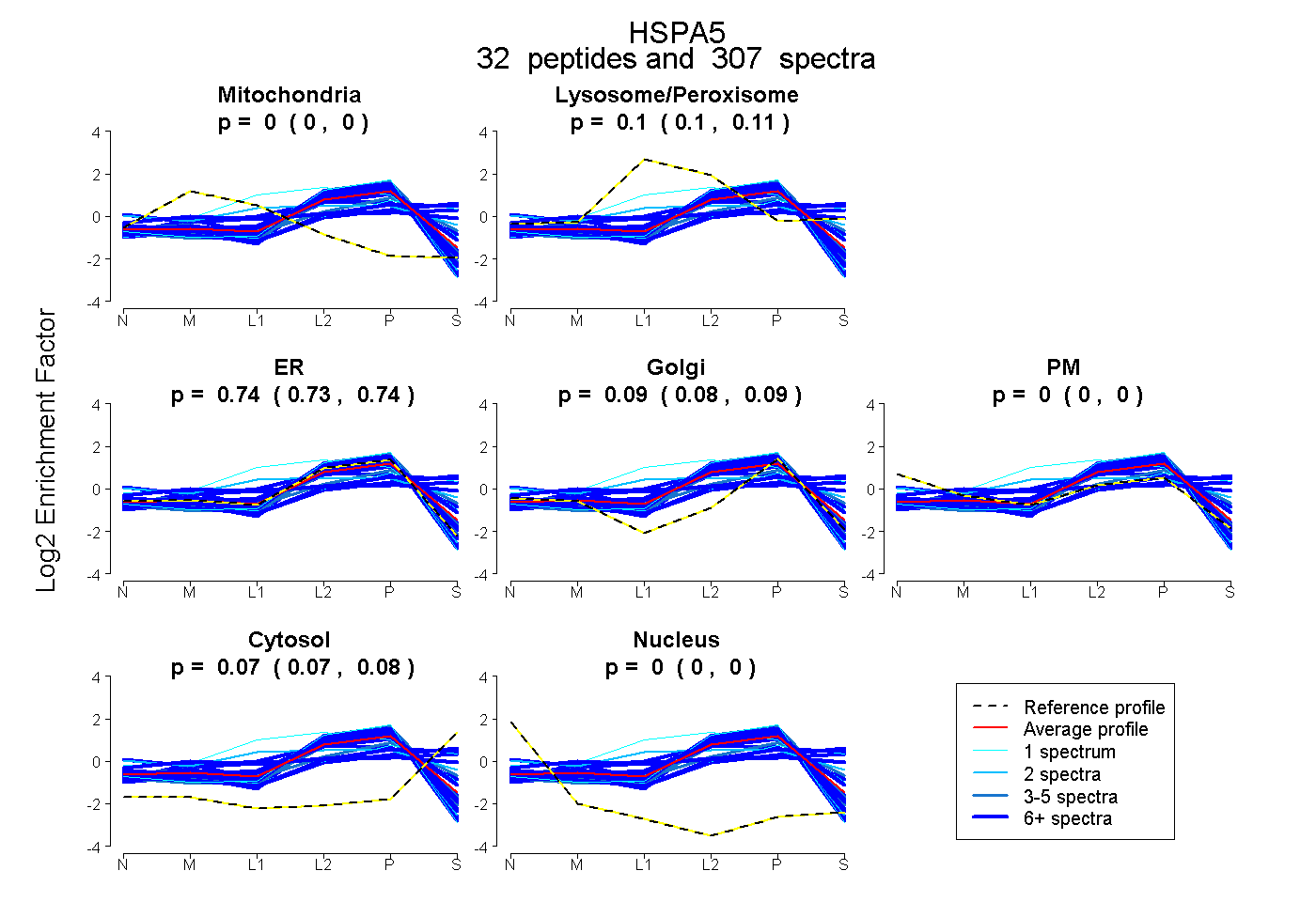 |
0.000 0.000 | 0.000 |
0.104 0.100 | 0.107 |
0.737 0.727 | 0.745 |
0.085 0.078 | 0.091 |
0.000 0.000 | 0.000 |
0.074 0.071 | 0.076 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1237 spectra |
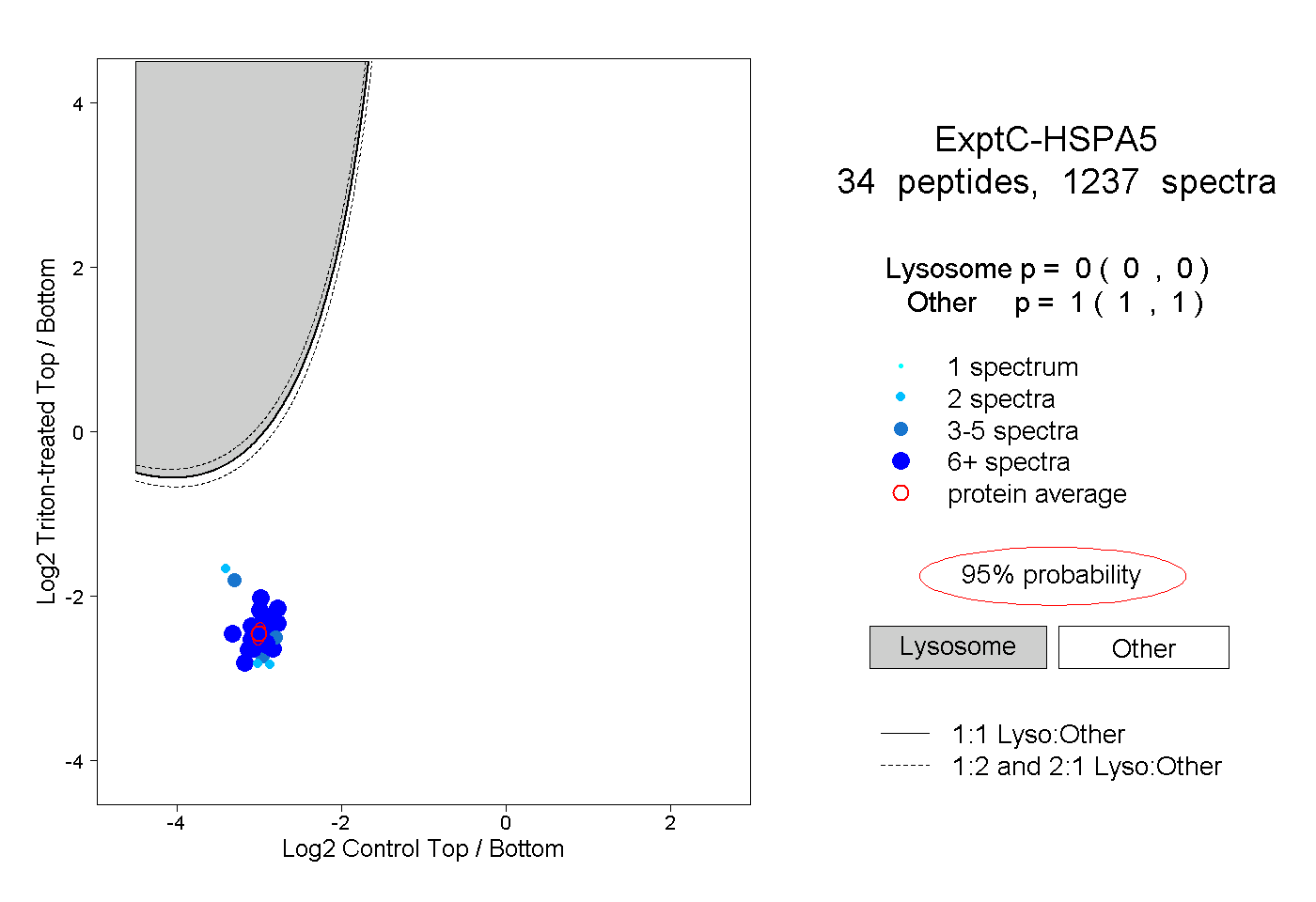 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
127 spectra |
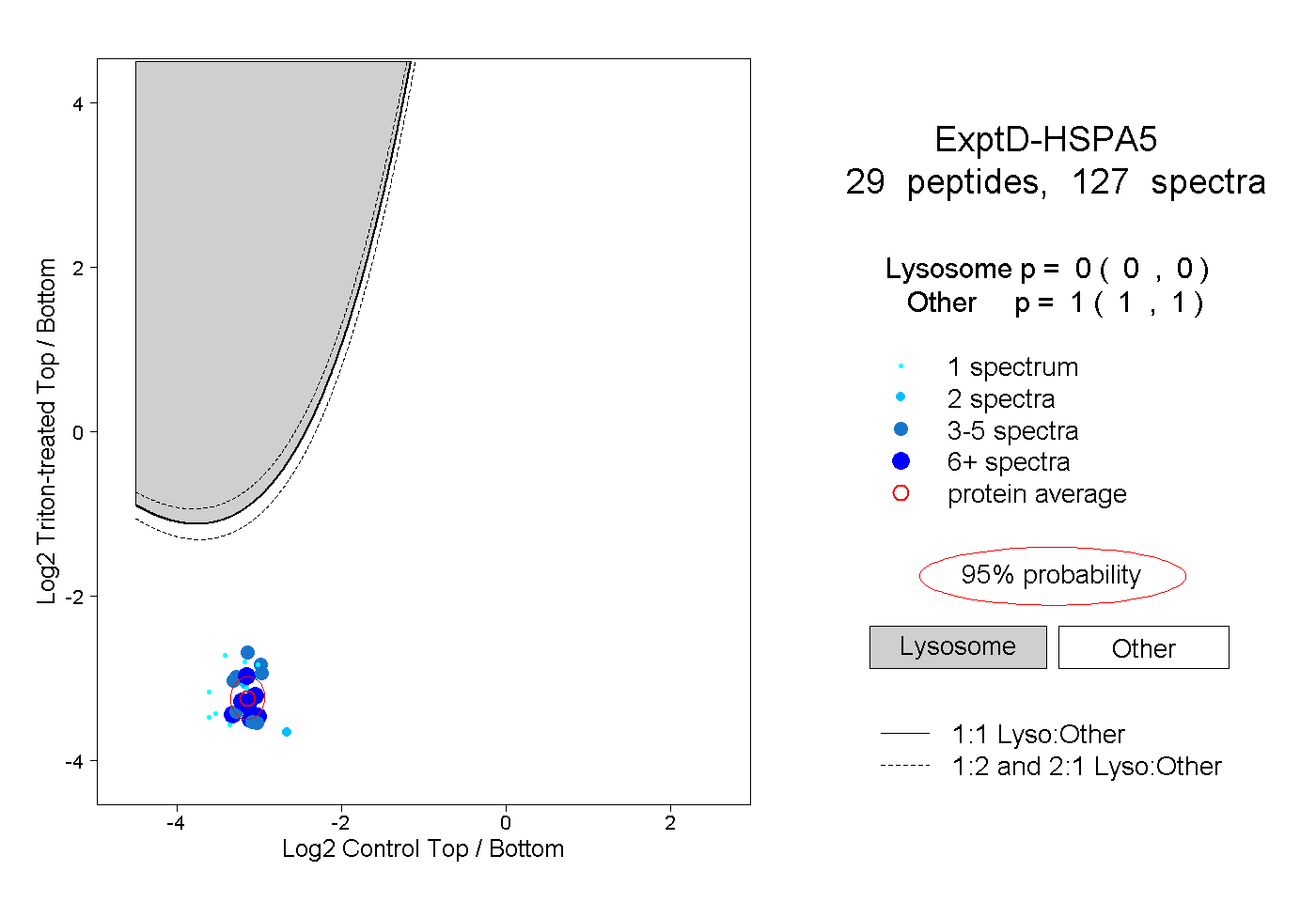 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |