peptides
spectra
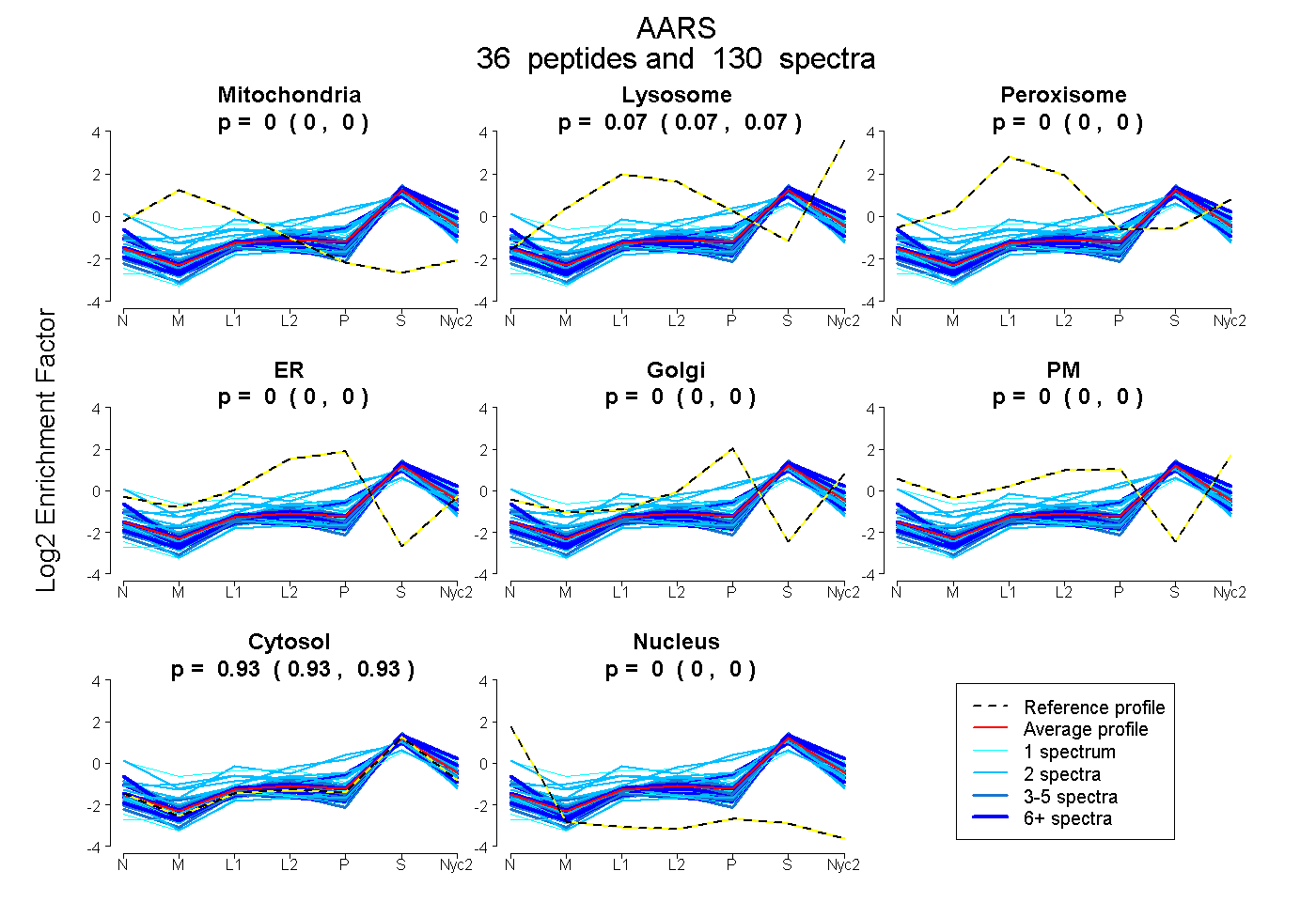
0.000 | 0.000
0.066 | 0.069
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.931 | 0.933
0.000 | 0.000
peptides
spectra
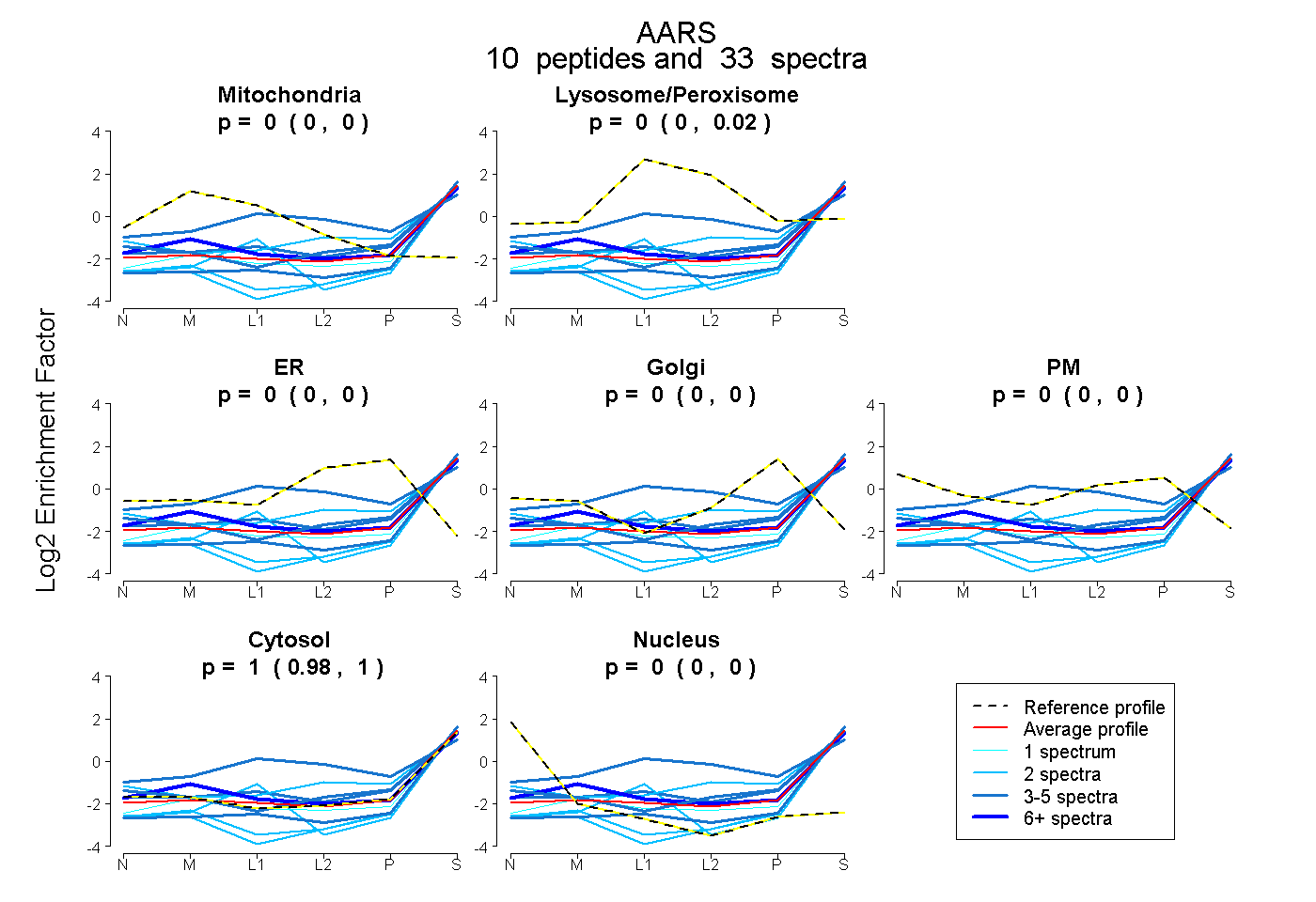
0.000 | 0.000
0.000 | 0.019
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.979 | 1.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
130 spectra |
 |
0.000 0.000 | 0.000 |
0.068 0.066 | 0.069 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.932 0.931 | 0.933 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
33 spectra |
 |
0.000 0.000 | 0.000 |
0.004 0.000 | 0.019 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.996 0.979 | 1.000 |
0.000 0.000 | 0.000 |
| 2 spectra, LFIDEPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 5 spectra, VLADHAR | 0.000 | 0.000 | 0.037 | 0.035 | 0.007 | 0.921 | 0.000 | |||
| 6 spectra, TITVALADGGRPDNTGR | 0.098 | 0.010 | 0.000 | 0.000 | 0.000 | 0.892 | 0.000 | |||
| 2 spectra, ALQGLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, SIDTGMGLER | 0.000 | 0.150 | 0.067 | 0.000 | 0.000 | 0.783 | 0.000 | |||
| 4 spectra, VGAEDTDGIDMAYR | 0.000 | 0.490 | 0.000 | 0.003 | 0.000 | 0.507 | 0.000 | |||
| 5 spectra, GGYVLHIGTIYGNLR | 0.000 | 0.106 | 0.000 | 0.000 | 0.000 | 0.894 | 0.000 | |||
| 4 spectra, VMDDLDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, MFVDEVVTGQECGVVLDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, GSLVAPDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
167 spectra |
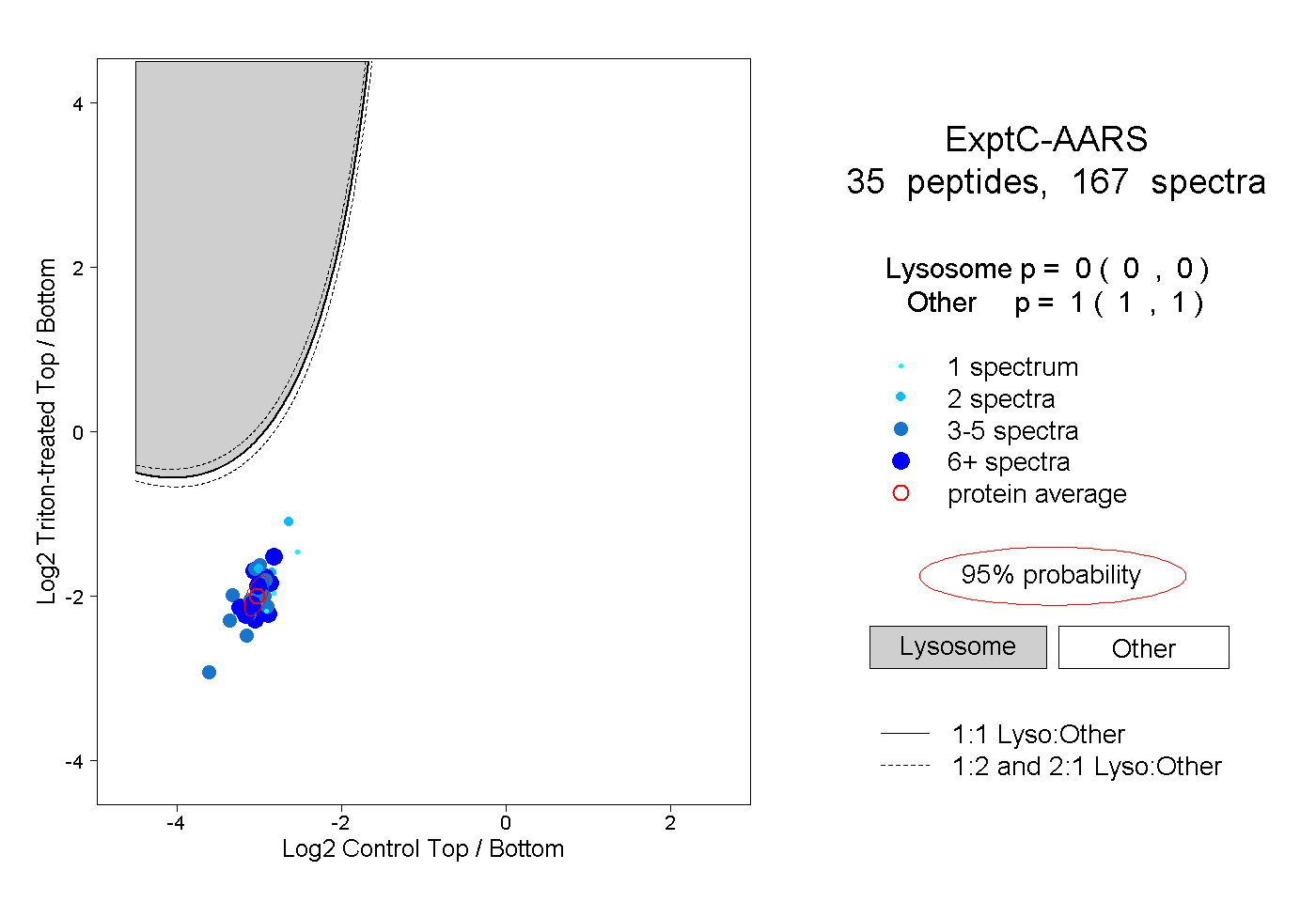 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
21 spectra |
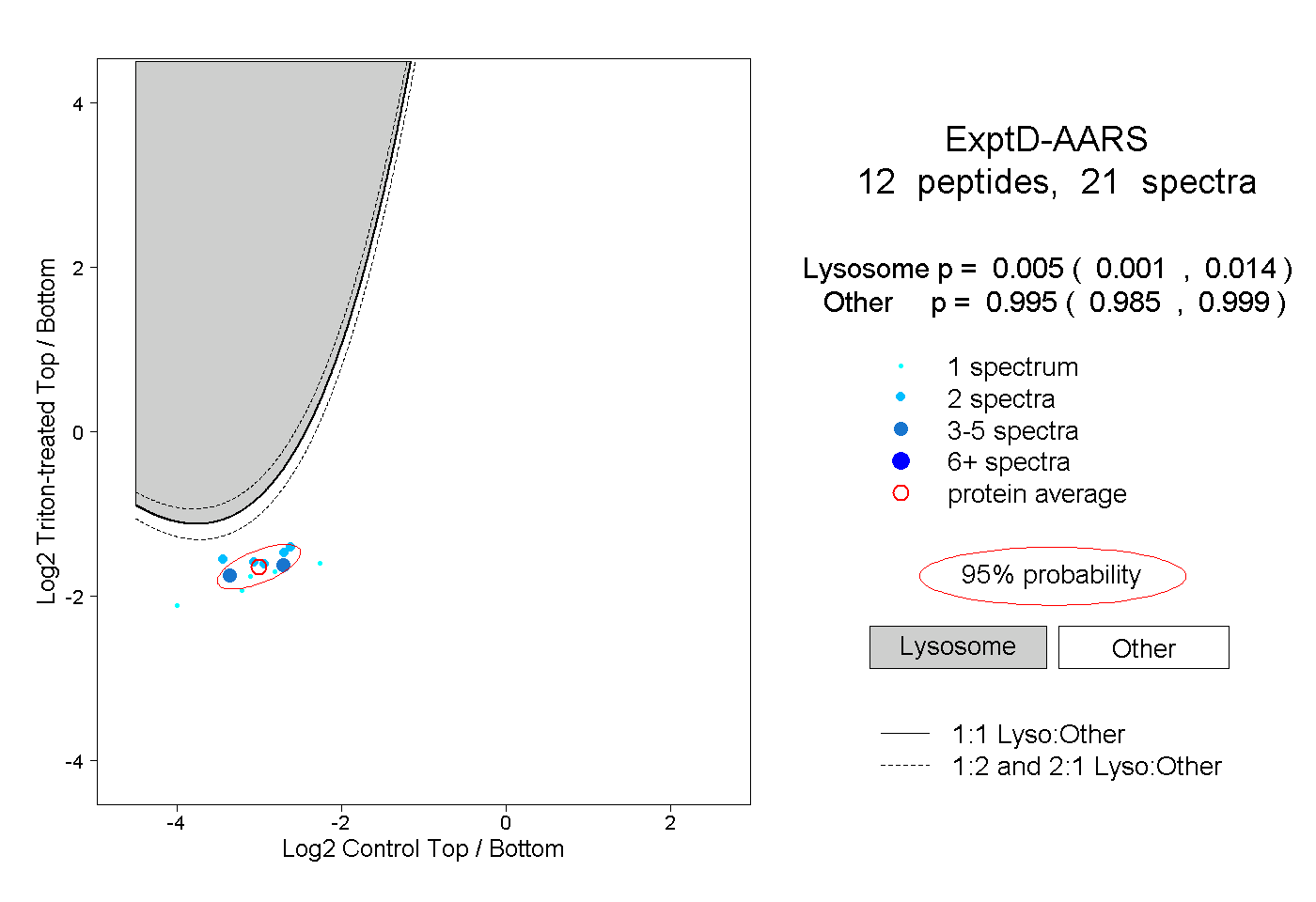 |
0.005 0.001 | 0.014 |
0.995 0.985 | 0.999 |