peptides
spectra
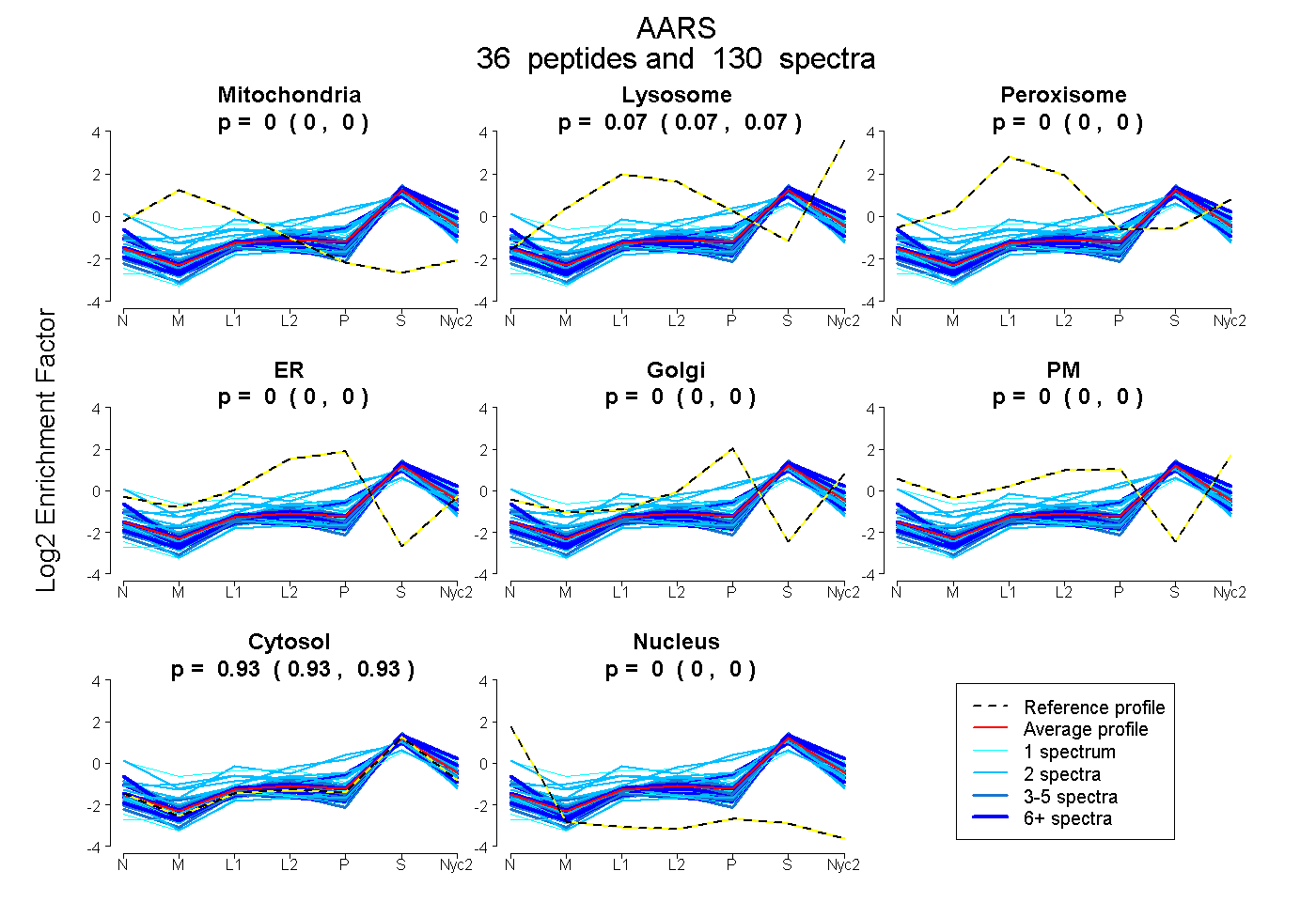
0.000 | 0.000
0.066 | 0.069
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.931 | 0.933
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
130 spectra |
 |
0.000 0.000 | 0.000 |
0.068 0.066 | 0.069 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.932 0.931 | 0.933 |
0.000 0.000 | 0.000 |
| 5 spectra, HNDLDDVGK | 0.000 | 0.066 | 0.000 | 0.000 | 0.000 | 0.000 | 0.934 | 0.000 | ||
| 2 spectra, VGDQVR | 0.000 | 0.060 | 0.000 | 0.000 | 0.063 | 0.000 | 0.878 | 0.000 | ||
| 5 spectra, VGAEDTDGIDMAYR | 0.000 | 0.072 | 0.000 | 0.000 | 0.000 | 0.000 | 0.928 | 0.000 | ||
| 5 spectra, GAMSTEQIK | 0.000 | 0.000 | 0.005 | 0.038 | 0.066 | 0.069 | 0.823 | 0.000 | ||
| 3 spectra, FDFTAK | 0.000 | 0.047 | 0.000 | 0.000 | 0.000 | 0.000 | 0.953 | 0.000 | ||
| 4 spectra, GSLVAPDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, DPDMVK | 0.000 | 0.067 | 0.149 | 0.000 | 0.195 | 0.000 | 0.588 | 0.000 | ||
| 6 spectra, SIDTGMGLER | 0.000 | 0.076 | 0.000 | 0.000 | 0.000 | 0.000 | 0.924 | 0.000 | ||
| 2 spectra, AANTQK | 0.000 | 0.028 | 0.000 | 0.000 | 0.082 | 0.000 | 0.890 | 0.000 | ||
| 7 spectra, GLVVDMDGFEEER | 0.000 | 0.029 | 0.000 | 0.000 | 0.000 | 0.000 | 0.971 | 0.000 | ||
| 3 spectra, DIINEEEVQFLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.984 | 0.016 | ||
| 13 spectra, VMDDLDR | 0.000 | 0.103 | 0.000 | 0.000 | 0.000 | 0.000 | 0.897 | 0.000 | ||
| 2 spectra, MFVDEVVTGQECGVVLDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.980 | 0.020 | ||
| 1 spectrum, LGDVK | 0.000 | 0.051 | 0.000 | 0.000 | 0.000 | 0.000 | 0.949 | 0.000 | ||
| 2 spectra, TCFYAEQGGQIFDEGYLVK | 0.006 | 0.000 | 0.154 | 0.000 | 0.000 | 0.169 | 0.576 | 0.095 | ||
| 6 spectra, GLEATDDSPK | 0.058 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.918 | 0.024 | ||
| 5 spectra, ILPGNMK | 0.000 | 0.084 | 0.000 | 0.000 | 0.000 | 0.000 | 0.916 | 0.000 | ||
| 2 spectra, TITVALADGGRPDNTGR | 0.000 | 0.160 | 0.000 | 0.000 | 0.000 | 0.000 | 0.840 | 0.000 | ||
| 1 spectrum, ALQGLR | 0.000 | 0.133 | 0.000 | 0.000 | 0.000 | 0.000 | 0.867 | 0.000 | ||
| 4 spectra, GYVLR | 0.000 | 0.100 | 0.000 | 0.000 | 0.000 | 0.000 | 0.900 | 0.000 | ||
| 1 spectrum, NSSHAGAFVIVTEEAIAK | 0.105 | 0.000 | 0.219 | 0.000 | 0.000 | 0.143 | 0.515 | 0.018 | ||
| 1 spectrum, GGYVLHIGTIYGNLR | 0.000 | 0.012 | 0.000 | 0.000 | 0.000 | 0.000 | 0.988 | 0.000 | ||
| 1 spectrum, ESDGVLKPLPK | 0.000 | 0.015 | 0.000 | 0.000 | 0.000 | 0.186 | 0.799 | 0.000 | ||
| 6 spectra, AQSAPNK | 0.000 | 0.033 | 0.000 | 0.000 | 0.000 | 0.000 | 0.967 | 0.000 | ||
| 1 spectrum, EIADLGEVLATAVIPQWQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, LFIDEPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, VLADHAR | 0.000 | 0.000 | 0.000 | 0.260 | 0.000 | 0.000 | 0.740 | 0.000 | ||
| 11 spectra, DMSAQATGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 4 spectra, FINYFK | 0.021 | 0.067 | 0.000 | 0.000 | 0.000 | 0.000 | 0.912 | 0.000 | ||
| 2 spectra, ITCLCQVPQNAANR | 0.066 | 0.000 | 0.074 | 0.136 | 0.000 | 0.000 | 0.723 | 0.000 | ||
| 7 spectra, SVLGDADQK | 0.000 | 0.000 | 0.000 | 0.133 | 0.020 | 0.000 | 0.826 | 0.022 | ||
| 4 spectra, AVFDETYPDPVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, ASEWVQQVSGLMDGK | 0.017 | 0.099 | 0.000 | 0.000 | 0.000 | 0.000 | 0.884 | 0.000 | ||
| 3 spectra, LVSVLQNK | 0.000 | 0.000 | 0.055 | 0.000 | 0.000 | 0.064 | 0.877 | 0.004 | ||
| 1 spectrum, QIWQNLGLDEAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, SLSAMEVK | 0.074 | 0.000 | 0.195 | 0.000 | 0.038 | 0.000 | 0.694 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
33 spectra |
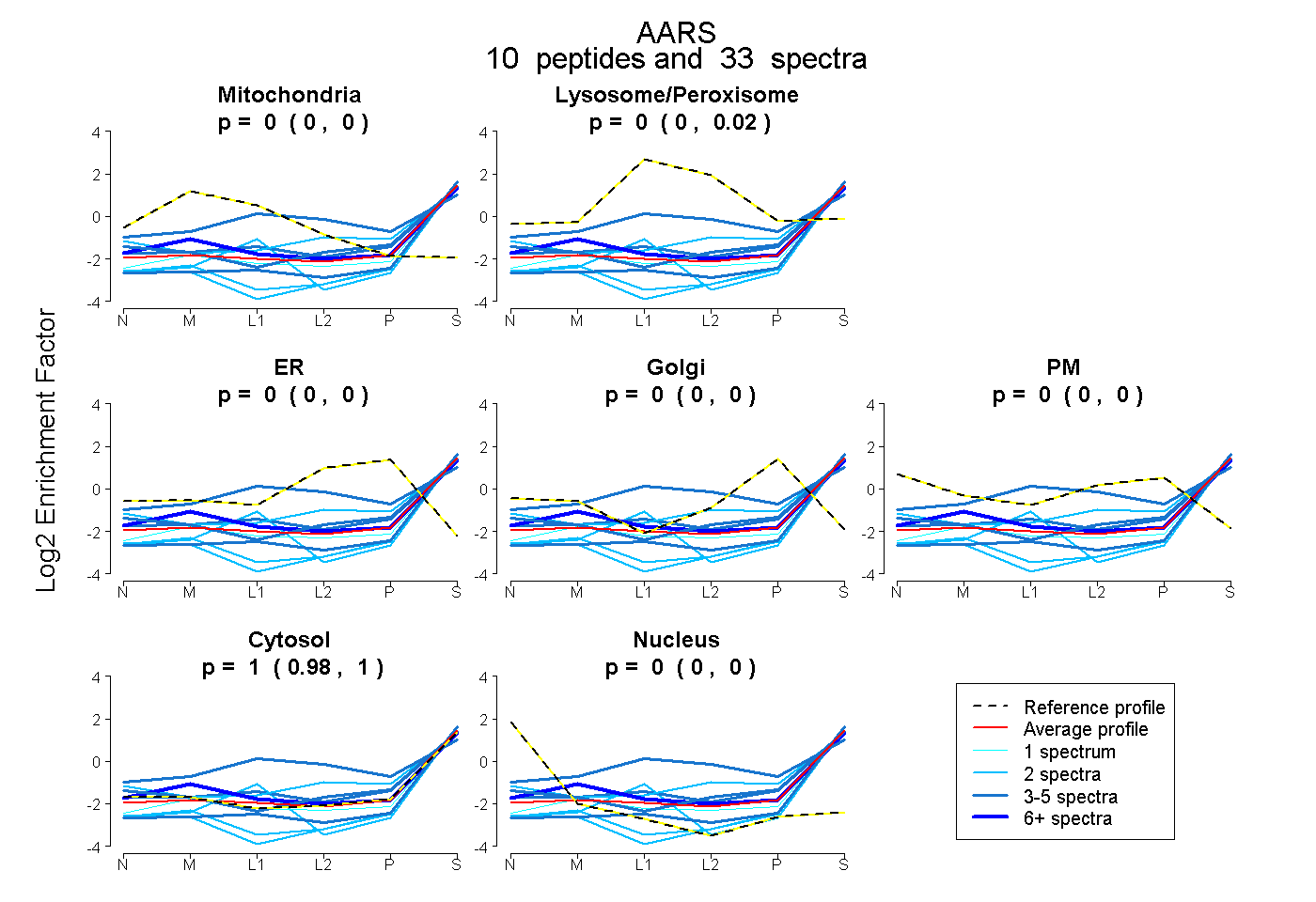 |
0.000 0.000 | 0.000 |
0.004 0.000 | 0.019 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.996 0.979 | 1.000 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
167 spectra |
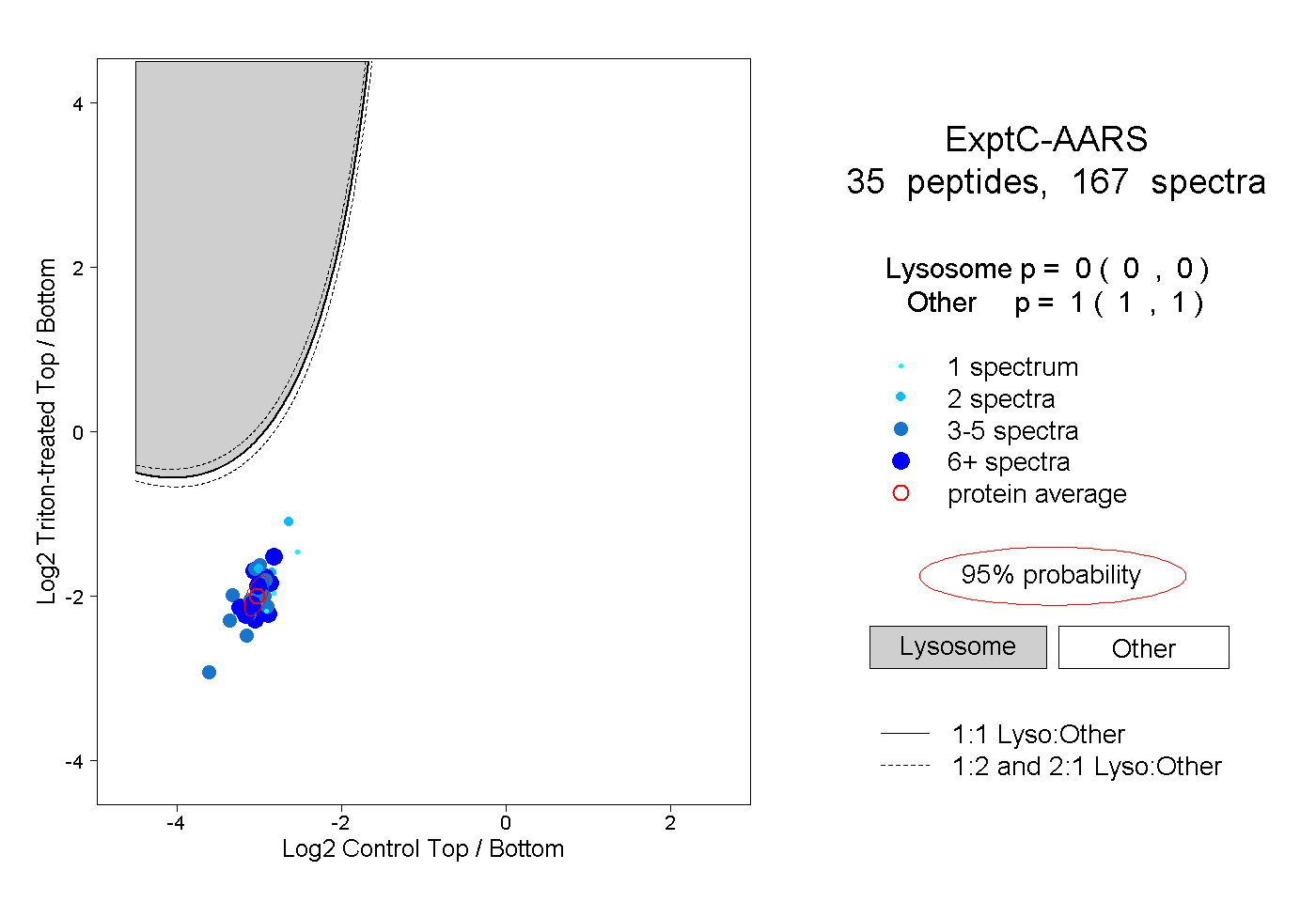 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
21 spectra |
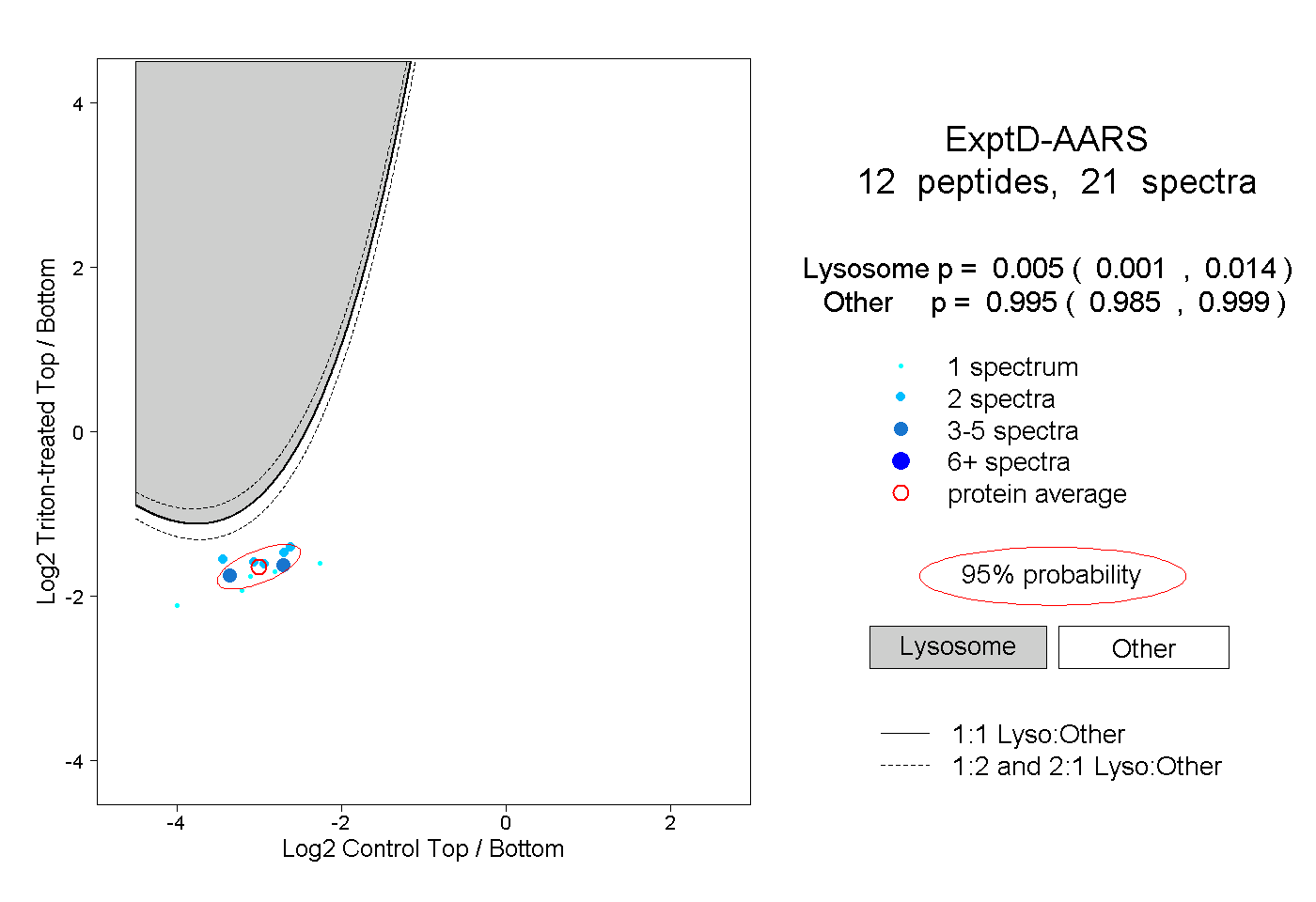 |
0.005 0.001 | 0.014 |
0.995 0.985 | 0.999 |