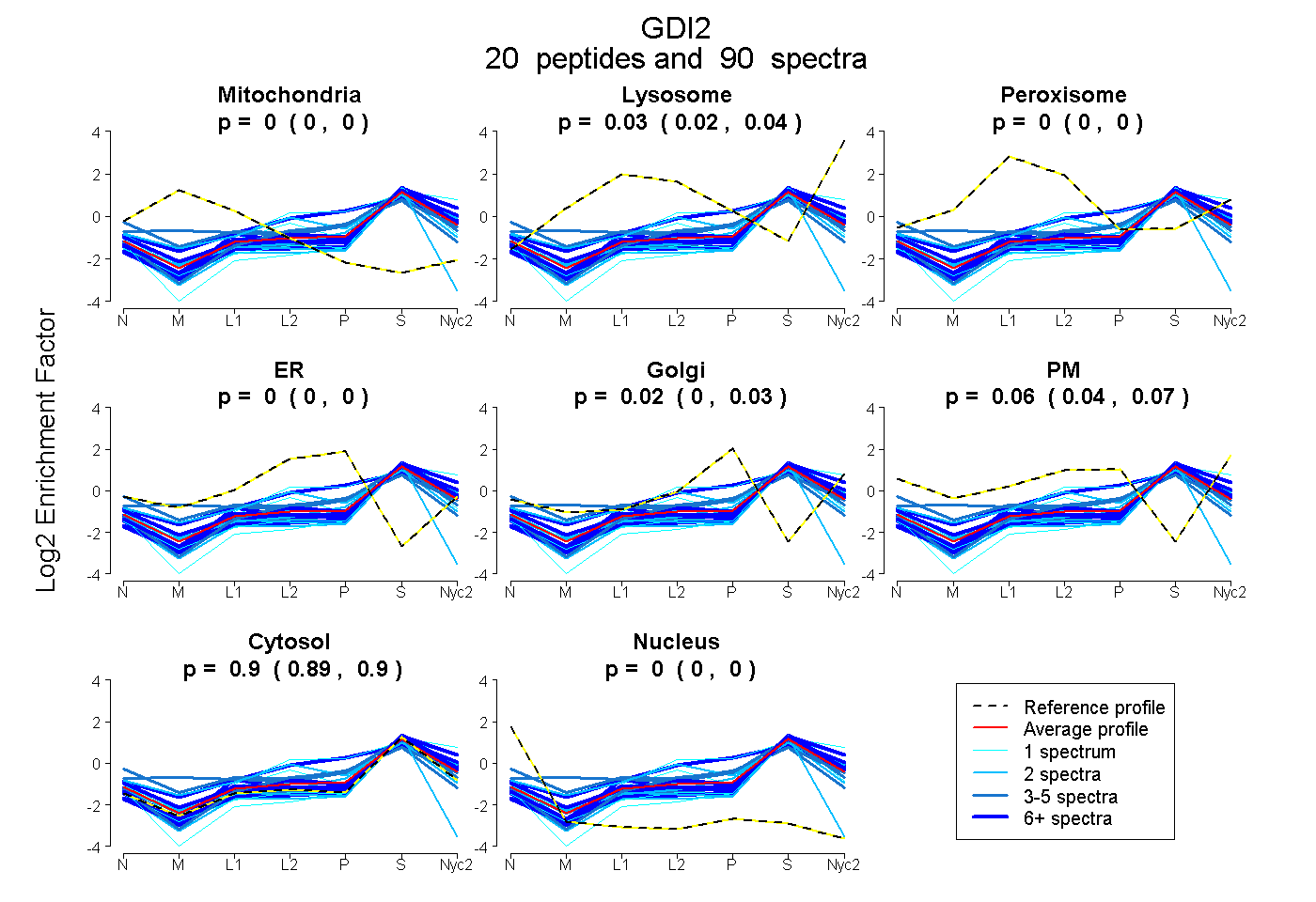
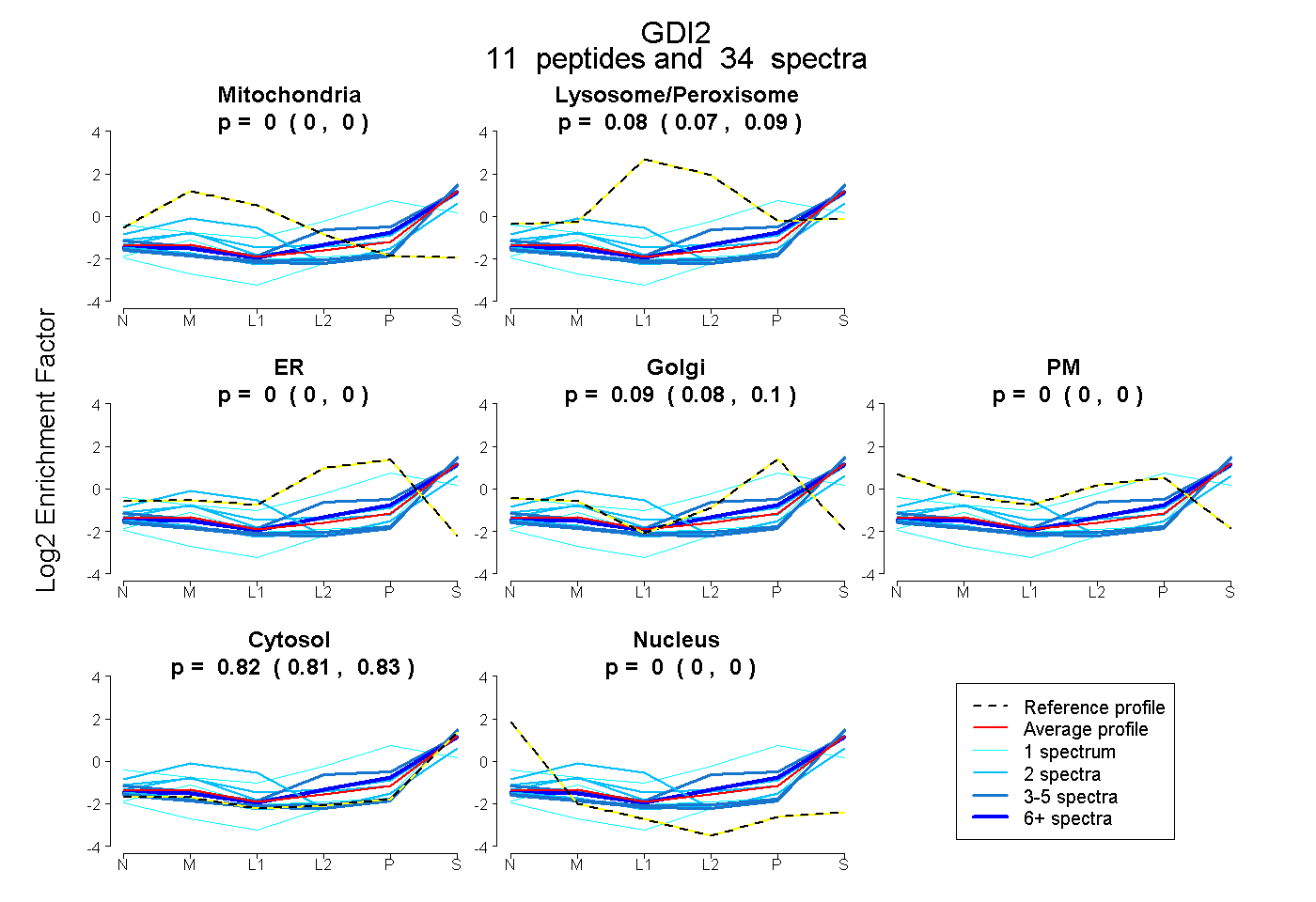
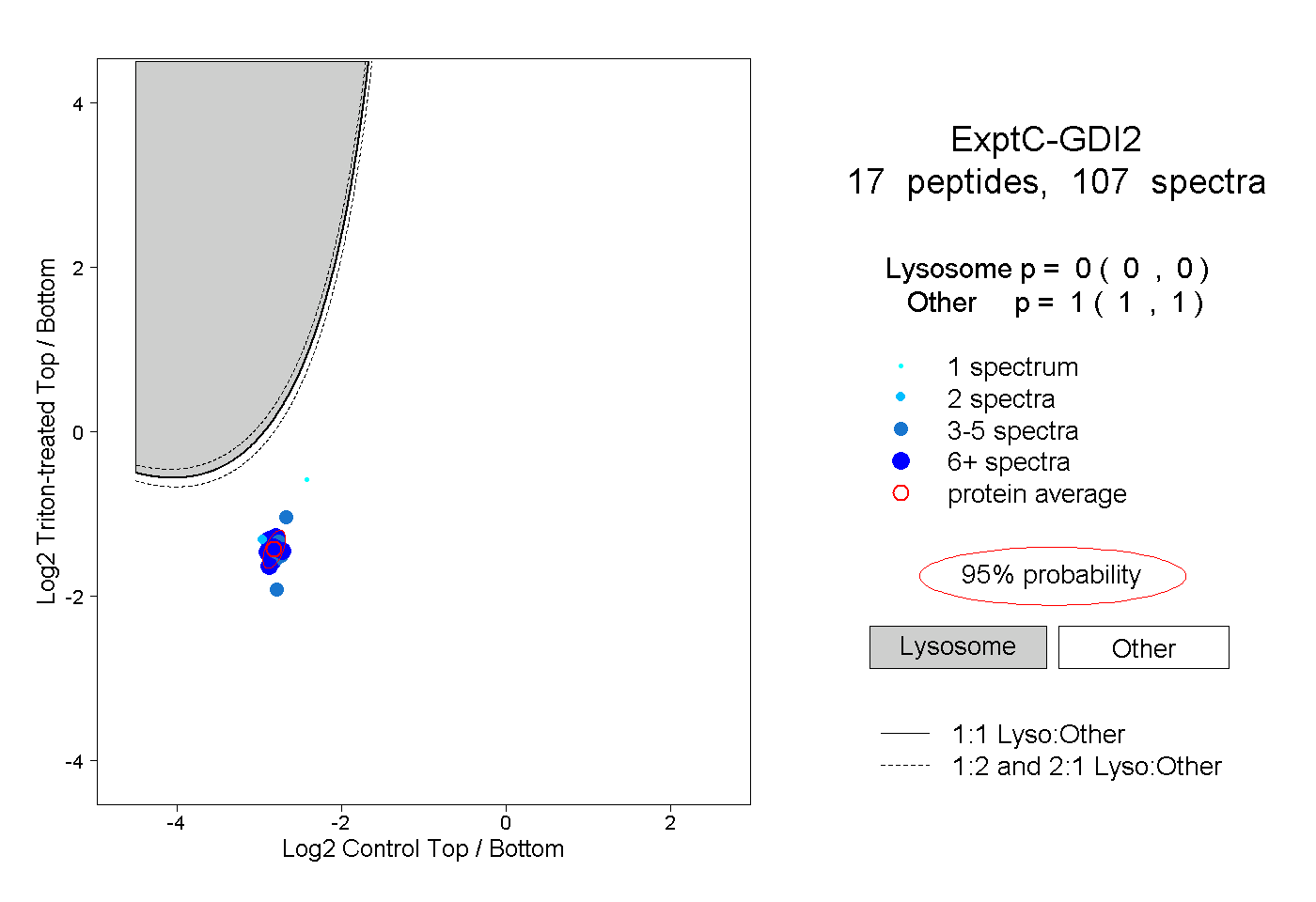
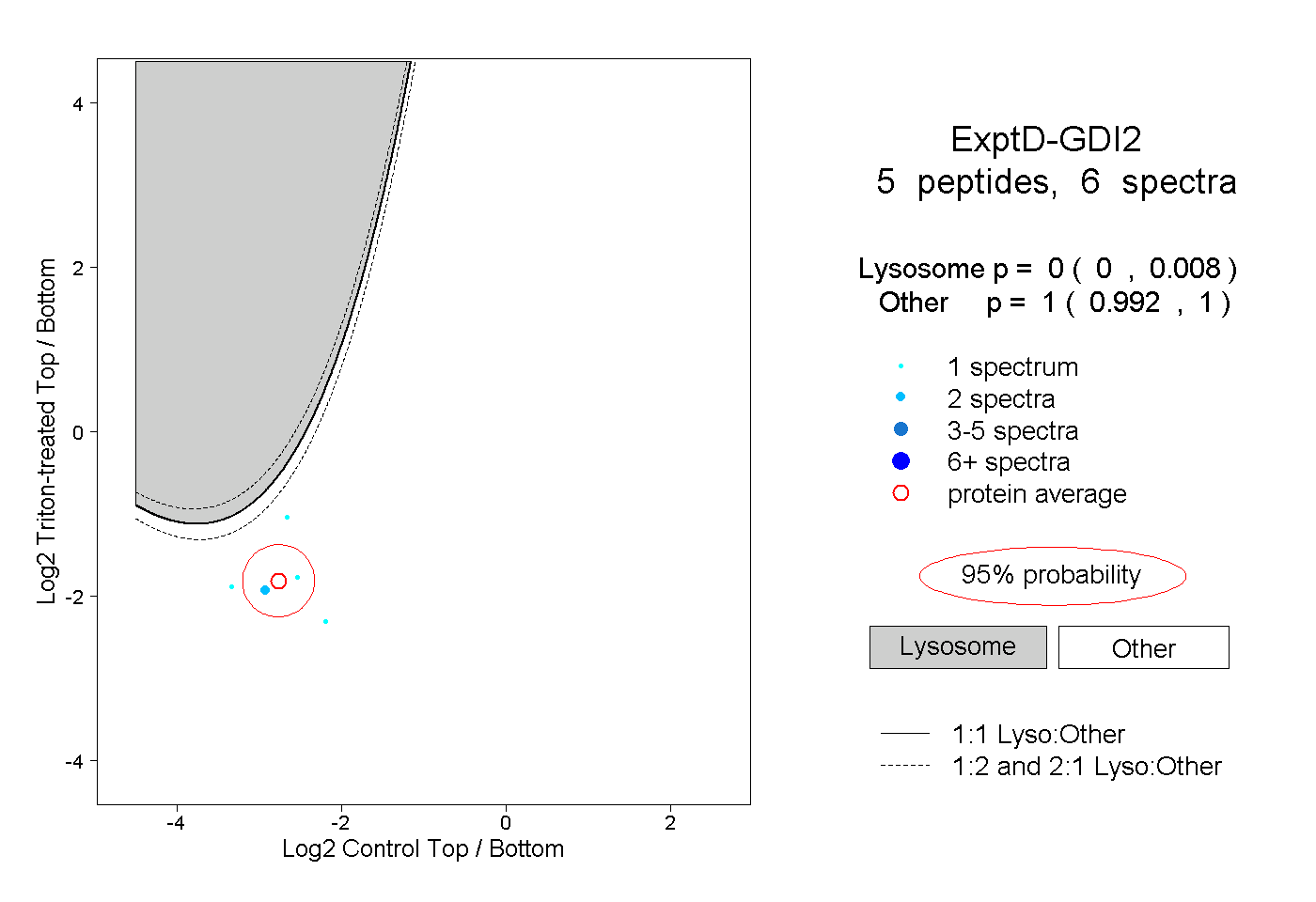
| 1 spectrum, MTGSEFDFEEMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, DLGTDSQIFISR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, QLICDPSYVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 22 spectra, LYSESLAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, SEGEIAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, SPYLYPLYGLGELPQGFAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, TFEGVDPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, EIRPALELLEPIEQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, FDLGQDVIDFTGHSLALYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, FLMANGQLVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, VICILSHPIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LPGQPPASMGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, VIEGSFVYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, DWNVDLIPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, FVSISDLFVPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, MLLFTEVTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VGQVLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |