peptides
spectra
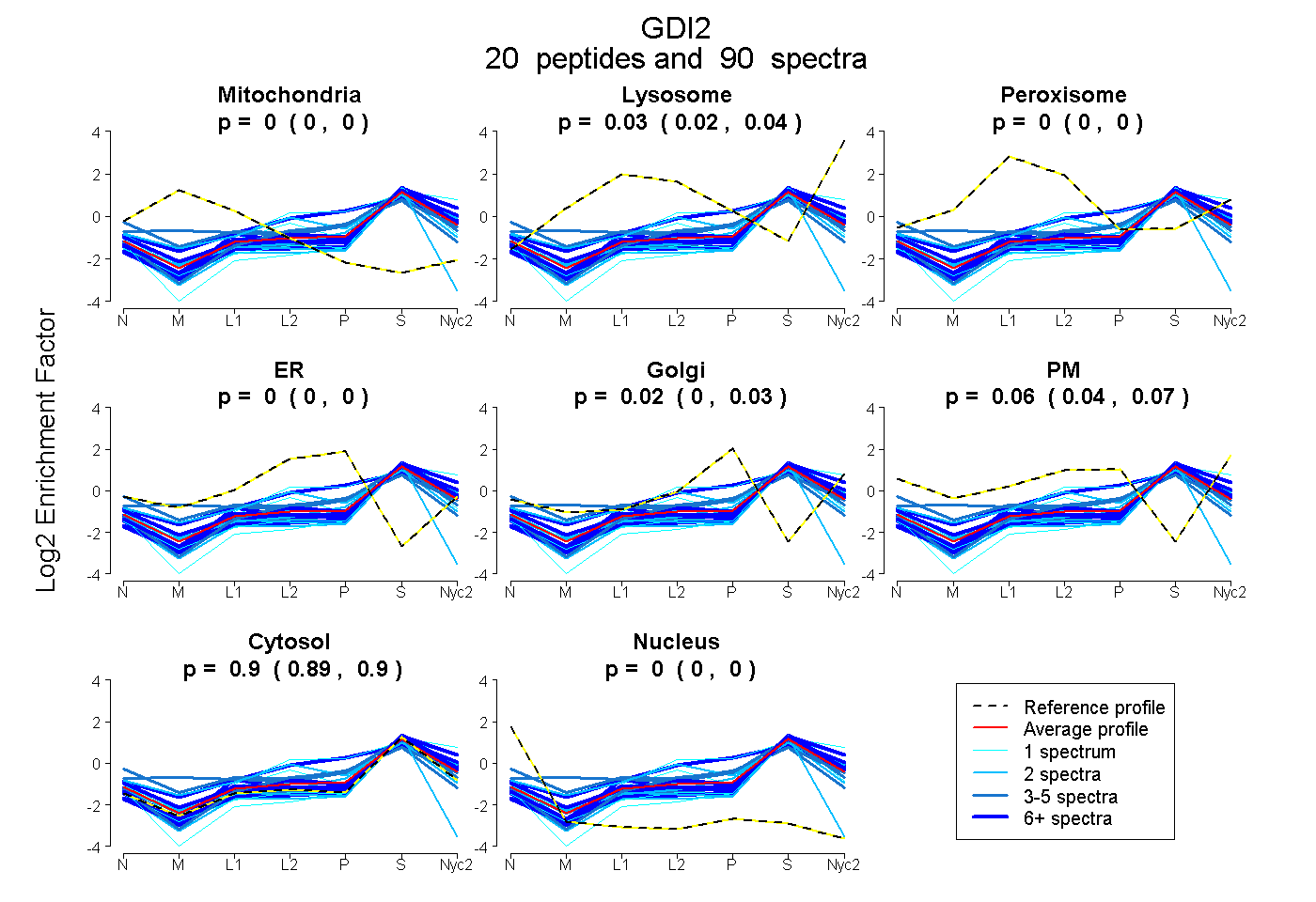
0.000 | 0.000
0.025 | 0.037
0.000 | 0.000
0.000 | 0.000
0.005 | 0.027
0.041 | 0.067
0.892 | 0.900
0.000 | 0.000
peptides
spectra
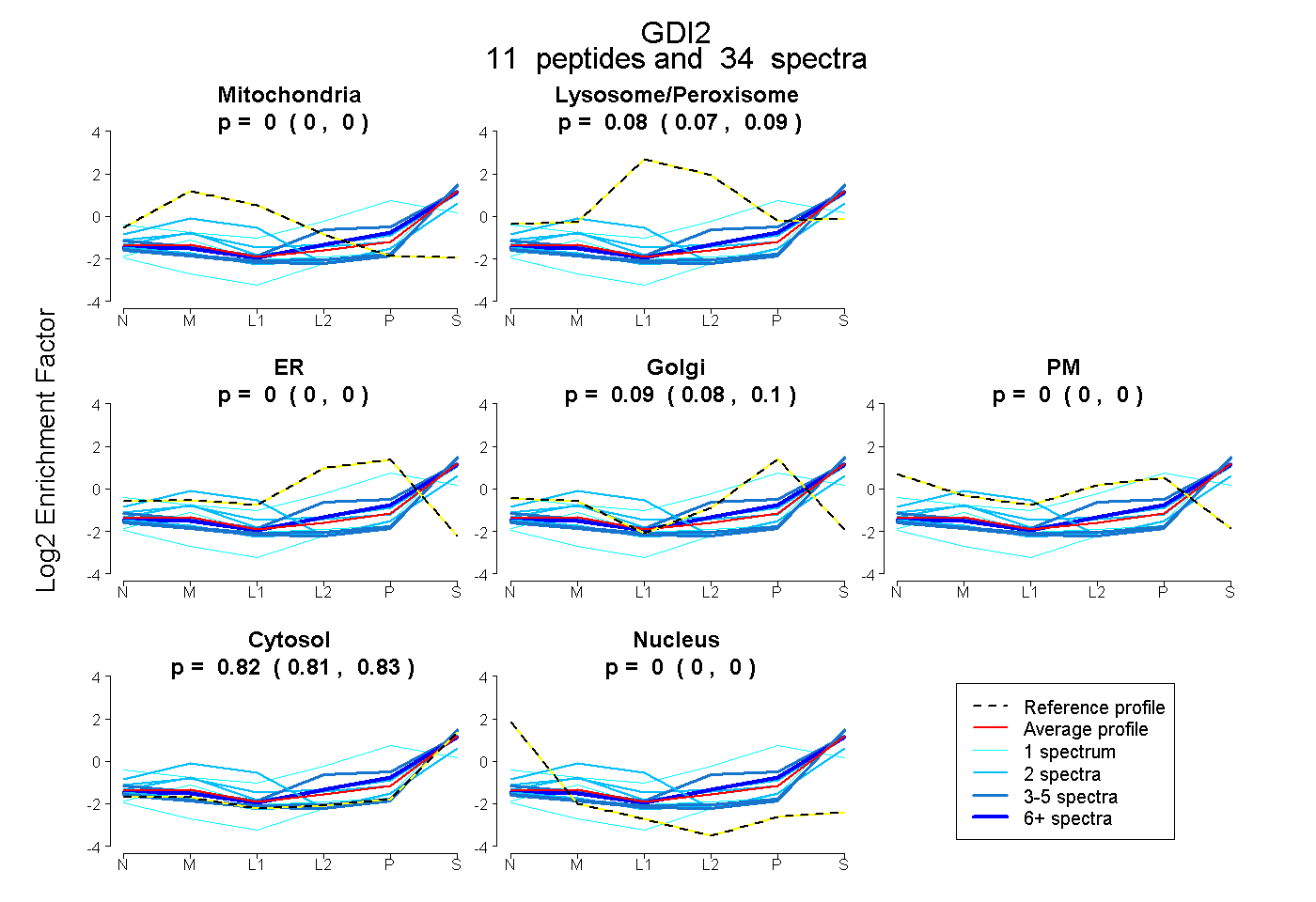
0.000 | 0.000
0.072 | 0.089
0.000 | 0.000
0.081 | 0.104
0.000 | 0.000
0.814 | 0.834
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
90 spectra |
 |
0.000 0.000 | 0.000 |
0.031 0.025 | 0.037 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.017 0.005 | 0.027 |
0.055 0.041 | 0.067 |
0.896 0.892 | 0.900 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
34 spectra |
 |
0.000 0.000 | 0.000 |
0.082 0.072 | 0.089 |
0.000 0.000 | 0.000 |
0.094 0.081 | 0.104 |
0.000 0.000 | 0.000 |
0.824 0.814 | 0.834 |
0.000 0.000 | 0.000 |
| 3 spectra, VICILSHPIK | 0.000 | 0.016 | 0.000 | 0.000 | 0.000 | 0.981 | 0.003 | |||
| 2 spectra, DLGTDSQIFISR | 0.000 | 0.155 | 0.000 | 0.123 | 0.021 | 0.701 | 0.000 | |||
| 1 spectrum, LPGQPPASMGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, AYDATTHFETTCDDIK | 0.000 | 0.274 | 0.000 | 0.474 | 0.000 | 0.252 | 0.000 | |||
| 3 spectra, LYSESLAR | 0.000 | 0.082 | 0.215 | 0.000 | 0.000 | 0.703 | 0.000 | |||
| 2 spectra, TDDYLDQPCCETINR | 0.392 | 0.025 | 0.000 | 0.000 | 0.000 | 0.583 | 0.000 | |||
| 13 spectra, MLLFTEVTR | 0.000 | 0.039 | 0.123 | 0.044 | 0.000 | 0.795 | 0.000 | |||
| 4 spectra, VGQVLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.990 | 0.010 | |||
| 2 spectra, TFEGVDPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.977 | 0.023 | |||
| 2 spectra, EIRPALELLEPIEQK | 0.035 | 0.103 | 0.000 | 0.087 | 0.000 | 0.774 | 0.000 | |||
| 1 spectrum, FDLGQDVIDFTGHSLALYR | 0.066 | 0.002 | 0.000 | 0.000 | 0.000 | 0.932 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
107 spectra |
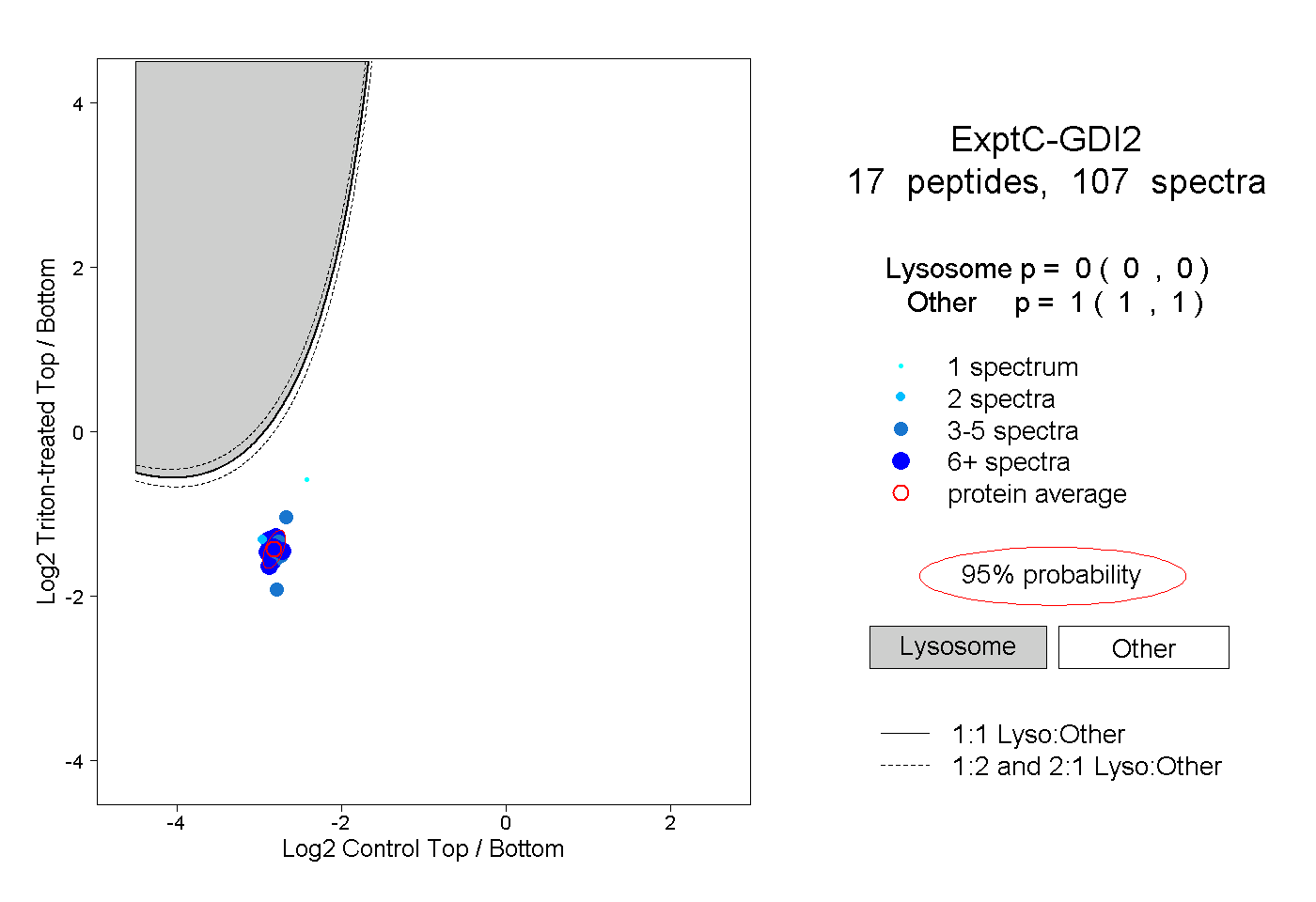 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
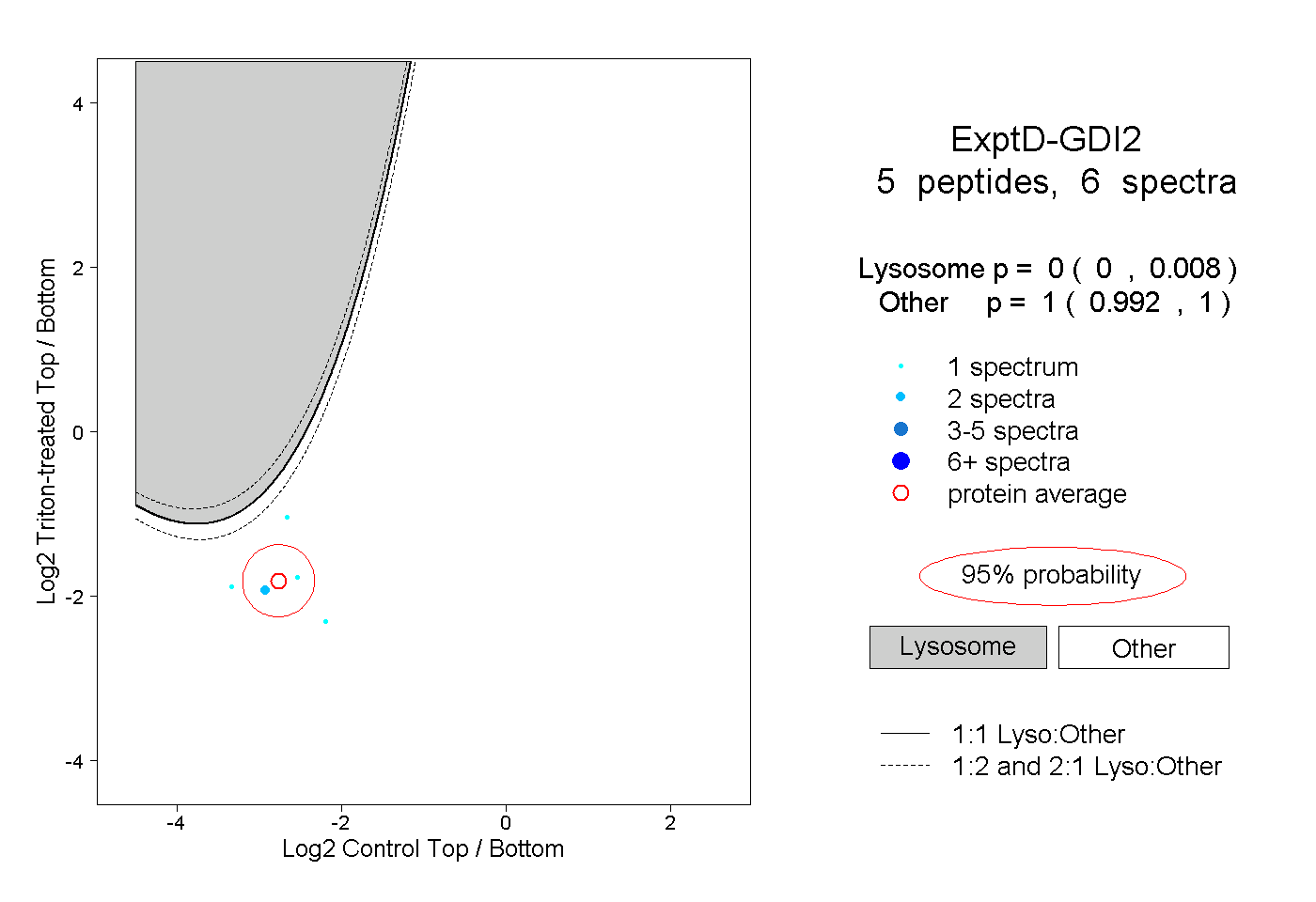 |
0.000 0.000 | 0.008 |
1.000 0.992 | 1.000 |