peptides
spectra
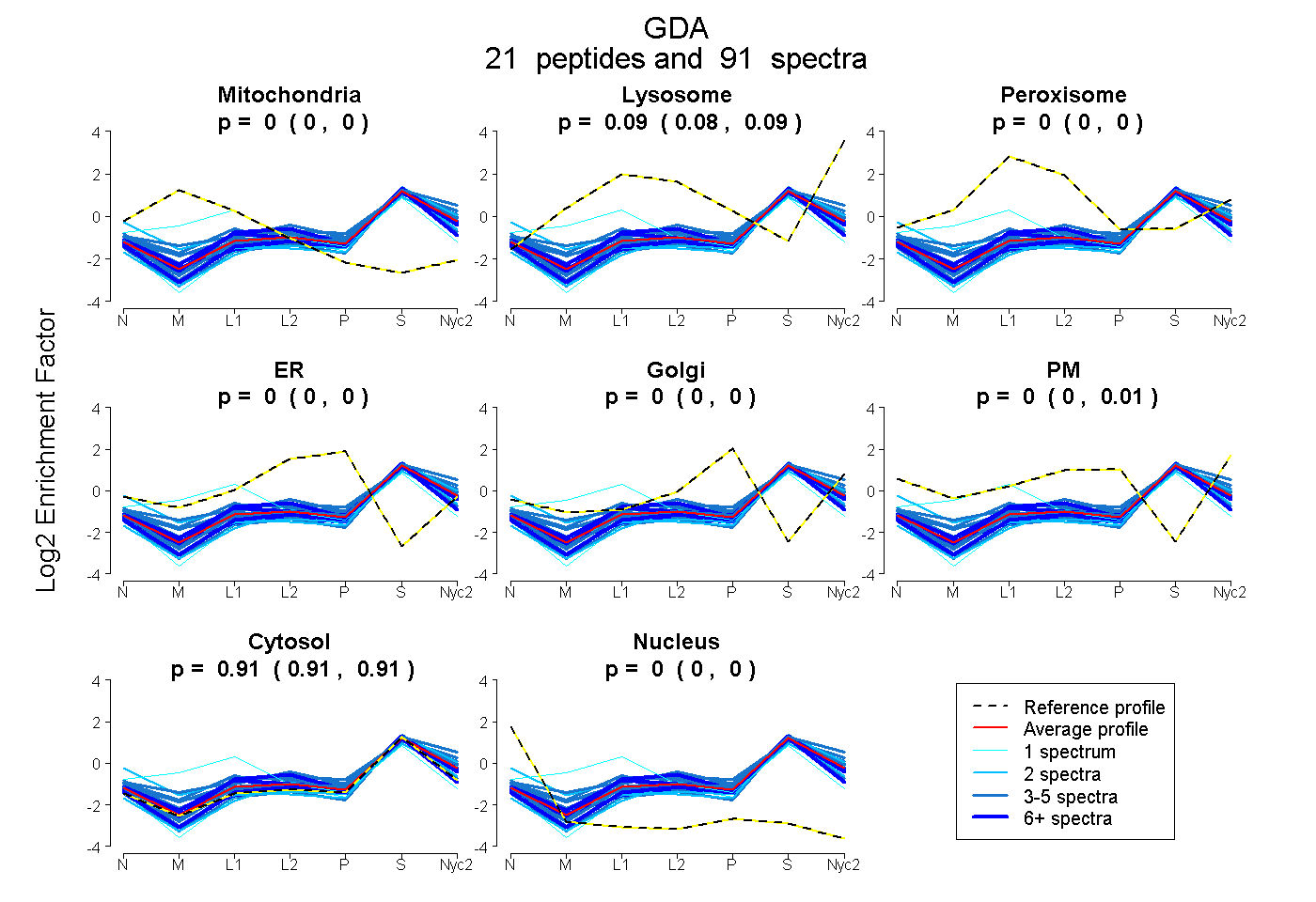
0.000 | 0.000
0.081 | 0.088
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.005
0.910 | 0.914
0.000 | 0.000
peptides
spectra
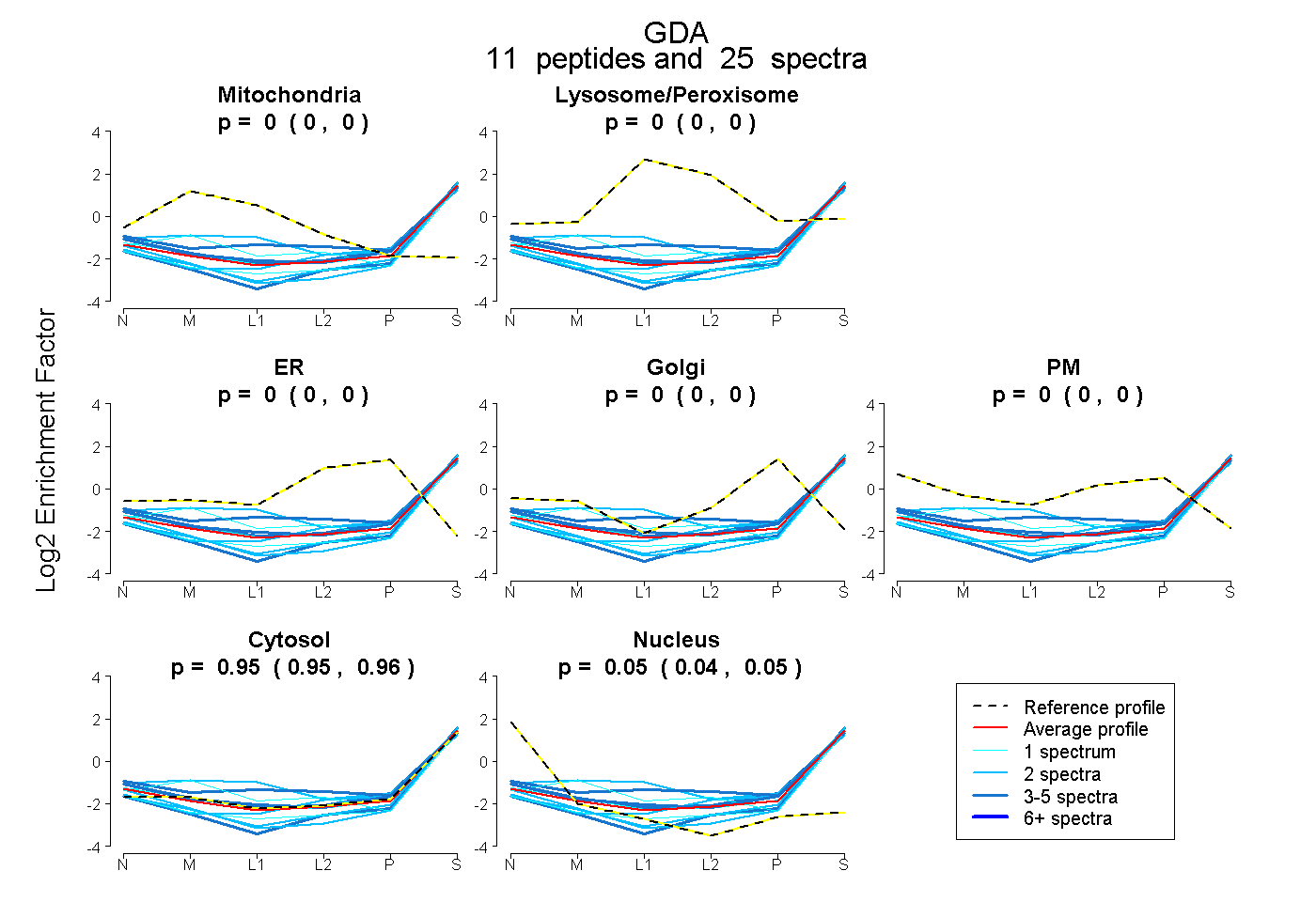
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.947 | 0.956
0.043 | 0.053
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
91 spectra |
 |
0.000 0.000 | 0.000 |
0.085 0.081 | 0.088 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.002 0.000 | 0.005 |
0.912 0.910 | 0.914 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
25 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.952 0.947 | 0.956 |
0.048 0.043 | 0.053 |
| 1 spectrum, FQSTDVAEEVYTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.947 | 0.053 | |||
| 1 spectrum, TVMAHGCYLSEEELNVFSER | 0.140 | 0.000 | 0.000 | 0.000 | 0.000 | 0.860 | 0.000 | |||
| 3 spectra, DFDALLINPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.955 | 0.045 | |||
| 2 spectra, TPQLALIFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.903 | 0.097 | |||
| 2 spectra, EIGNFEVGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 2 spectra, EWCFKPCEIR | 0.113 | 0.136 | 0.000 | 0.000 | 0.000 | 0.751 | 0.000 | |||
| 3 spectra, IVFLEESSQQEK | 0.000 | 0.177 | 0.000 | 0.000 | 0.000 | 0.777 | 0.046 | |||
| 1 spectrum, NIEEVYVGGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.964 | 0.036 | |||
| 3 spectra, AVMVSNVLLINK | 0.000 | 0.000 | 0.000 | 0.000 | 0.045 | 0.909 | 0.046 | |||
| 5 spectra, VKPIVTPR | 0.000 | 0.025 | 0.000 | 0.000 | 0.000 | 0.904 | 0.071 | |||
| 2 spectra, FLYLGDDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.966 | 0.034 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
137 spectra |
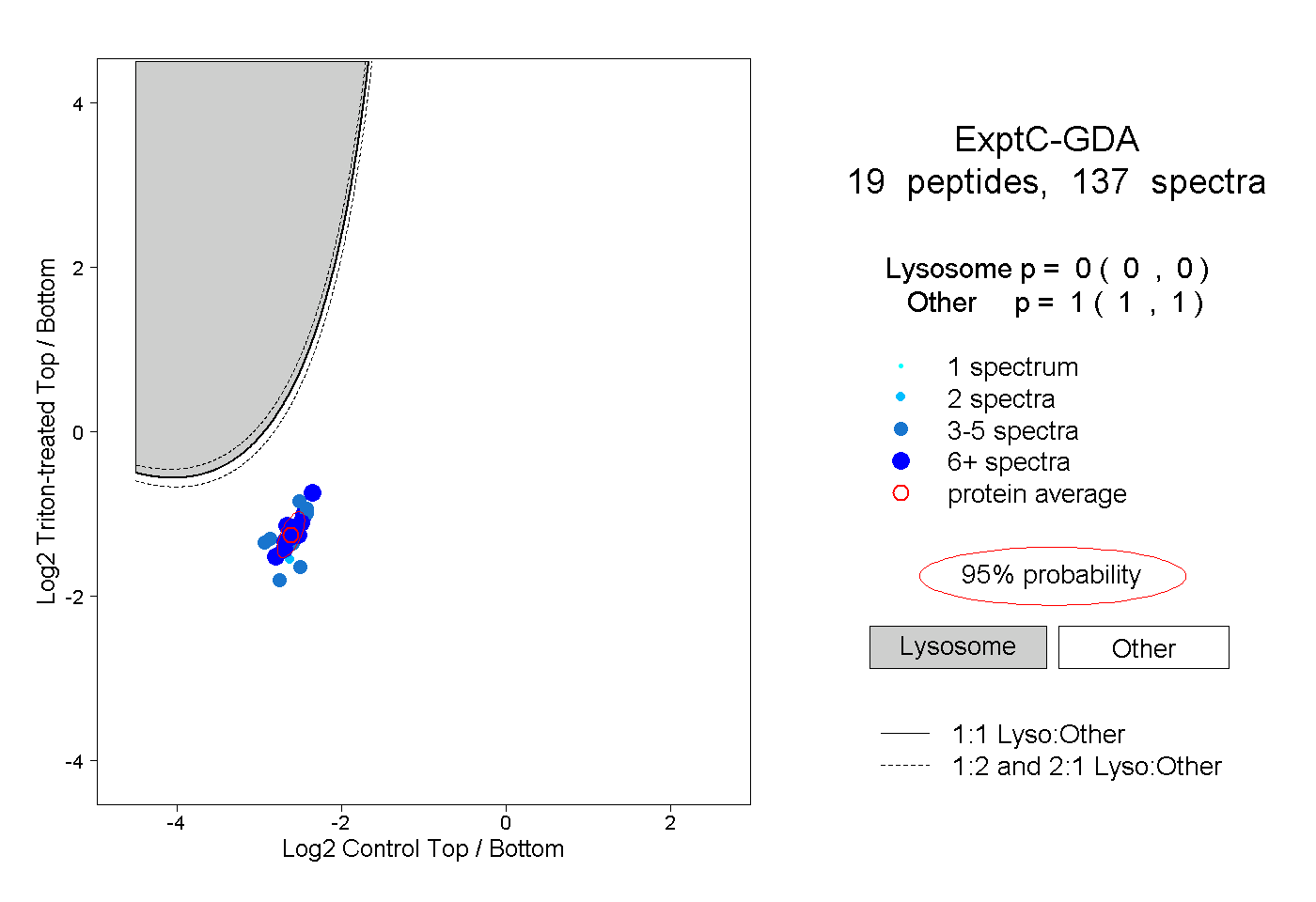 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
6 spectra |
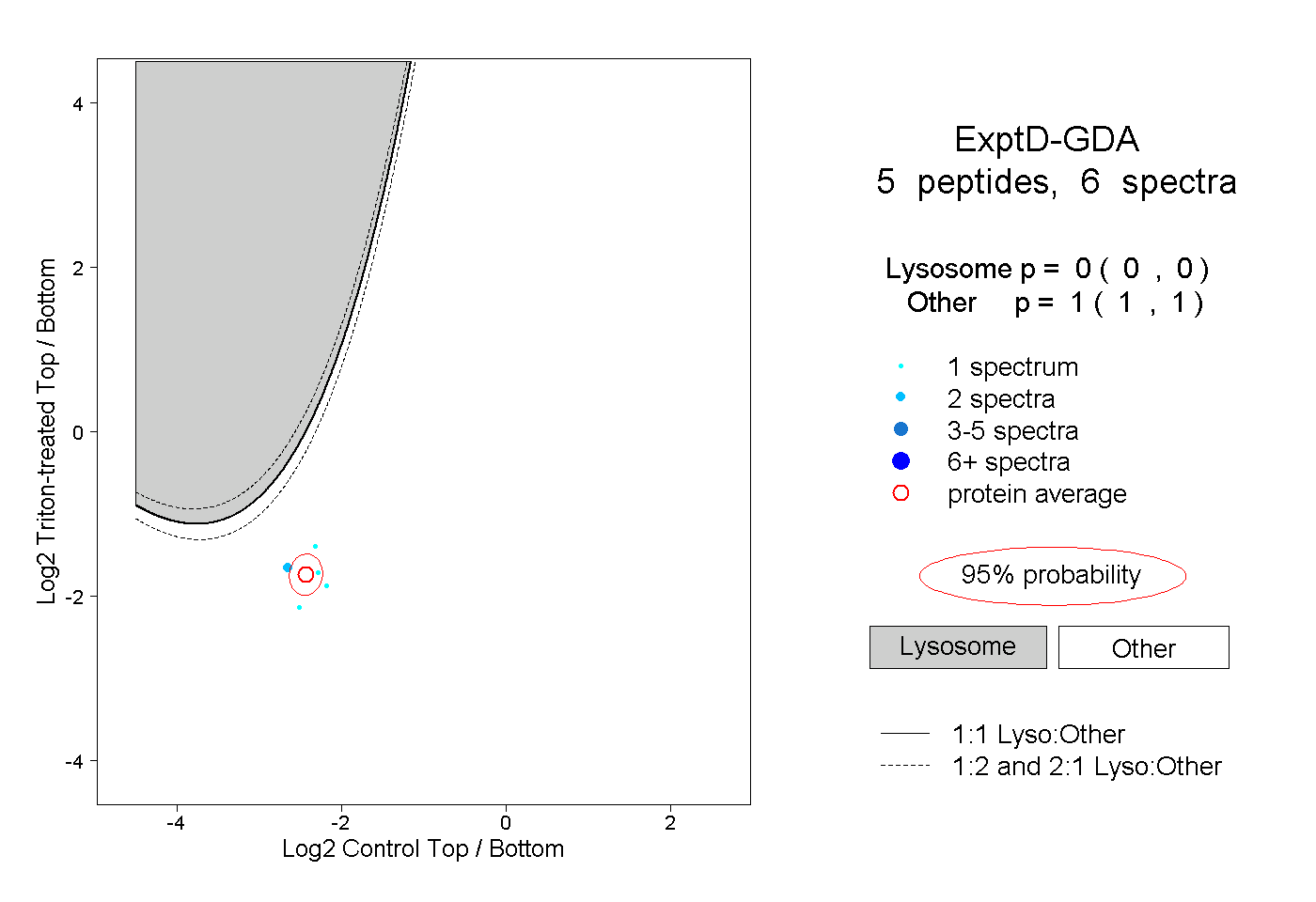 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |