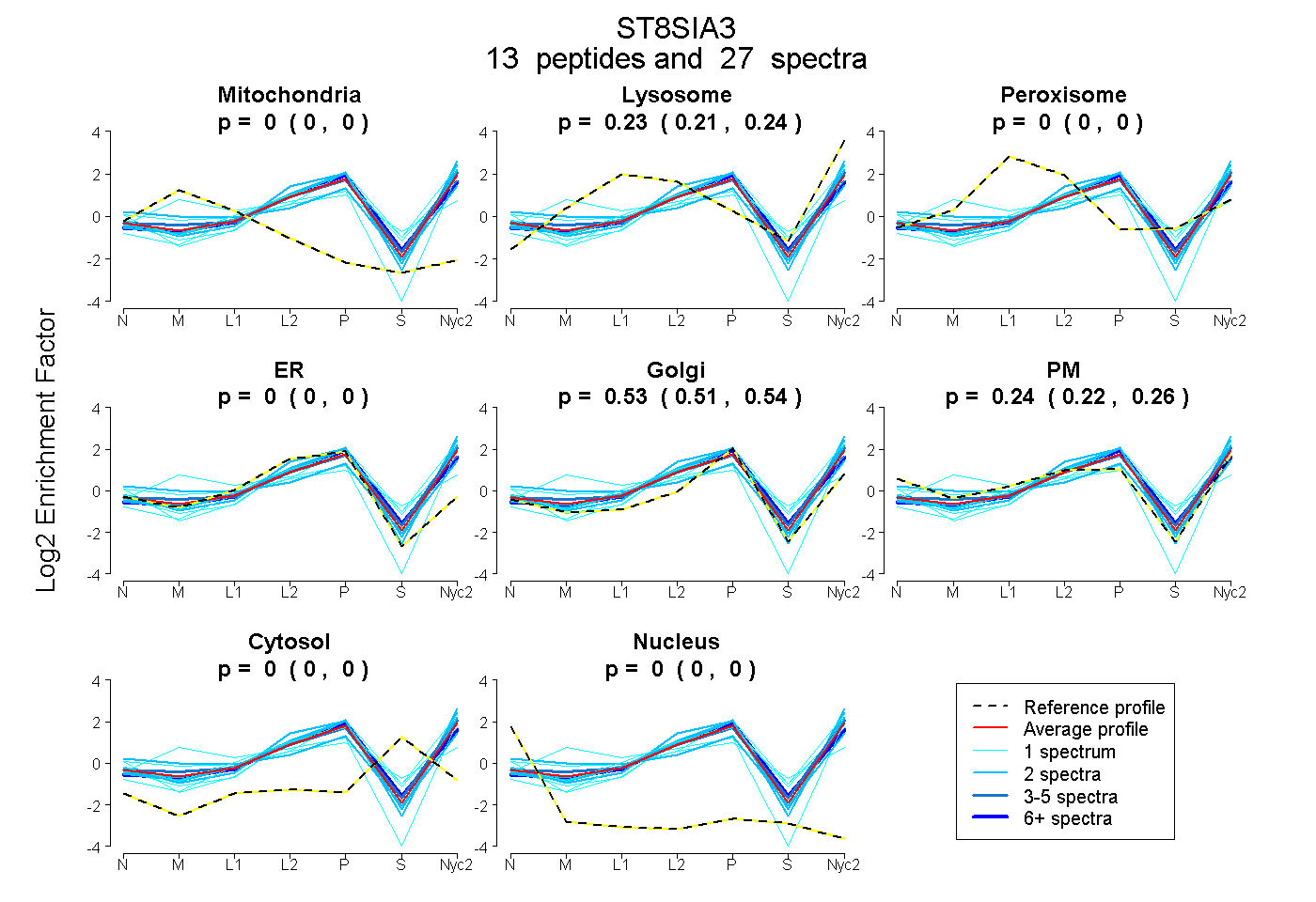
peptides
spectra
0.000 | 0.000
0.214 | 0.237
0.000 | 0.000
0.000 | 0.000
0.514 | 0.543
0.220 | 0.263
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
27 spectra |
 |
0.000 0.000 | 0.000 |
0.227 0.214 | 0.237 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.529 0.514 | 0.543 |
0.244 0.220 | 0.263 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, SDFVFR | 0.068 | 0.125 | 0.000 | 0.000 | 0.112 | 0.695 | 0.000 | 0.000 | ||
| 6 spectra, MYMFHAGFR | 0.000 | 0.276 | 0.000 | 0.107 | 0.618 | 0.000 | 0.000 | 0.000 | ||
| 5 spectra, VQLAWPGNIMQHVNR | 0.000 | 0.273 | 0.000 | 0.000 | 0.505 | 0.222 | 0.000 | 0.000 | ||
| 2 spectra, NNFFLSLK | 0.000 | 0.148 | 0.000 | 0.000 | 0.406 | 0.446 | 0.000 | 0.000 | ||
| 1 spectrum, YYNNLLTIQDR | 0.000 | 0.336 | 0.000 | 0.000 | 0.394 | 0.224 | 0.046 | 0.000 | ||
| 2 spectra, SQFALK | 0.000 | 0.265 | 0.000 | 0.000 | 0.505 | 0.230 | 0.000 | 0.000 | ||
| 1 spectrum, QEILQHVDVIK | 0.000 | 0.201 | 0.000 | 0.000 | 0.645 | 0.155 | 0.000 | 0.000 | ||
| 1 spectrum, TAFLHQR | 0.000 | 0.116 | 0.000 | 0.000 | 0.416 | 0.376 | 0.092 | 0.000 | ||
| 2 spectra, WQESHQLPAEFQLLYR | 0.058 | 0.091 | 0.000 | 0.000 | 0.315 | 0.536 | 0.000 | 0.000 | ||
| 2 spectra, TLVDFFVEHR | 0.000 | 0.257 | 0.000 | 0.006 | 0.581 | 0.155 | 0.000 | 0.000 | ||
| 1 spectrum, SLLPDVSPILNK | 0.000 | 0.270 | 0.000 | 0.000 | 0.641 | 0.000 | 0.089 | 0.000 | ||
| 1 spectrum, CNFAPTEAFHK | 0.000 | 0.000 | 0.221 | 0.000 | 0.275 | 0.341 | 0.164 | 0.000 | ||
| 2 spectra, YASPGAPR | 0.000 | 0.221 | 0.000 | 0.000 | 0.531 | 0.248 | 0.000 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
5 spectra |
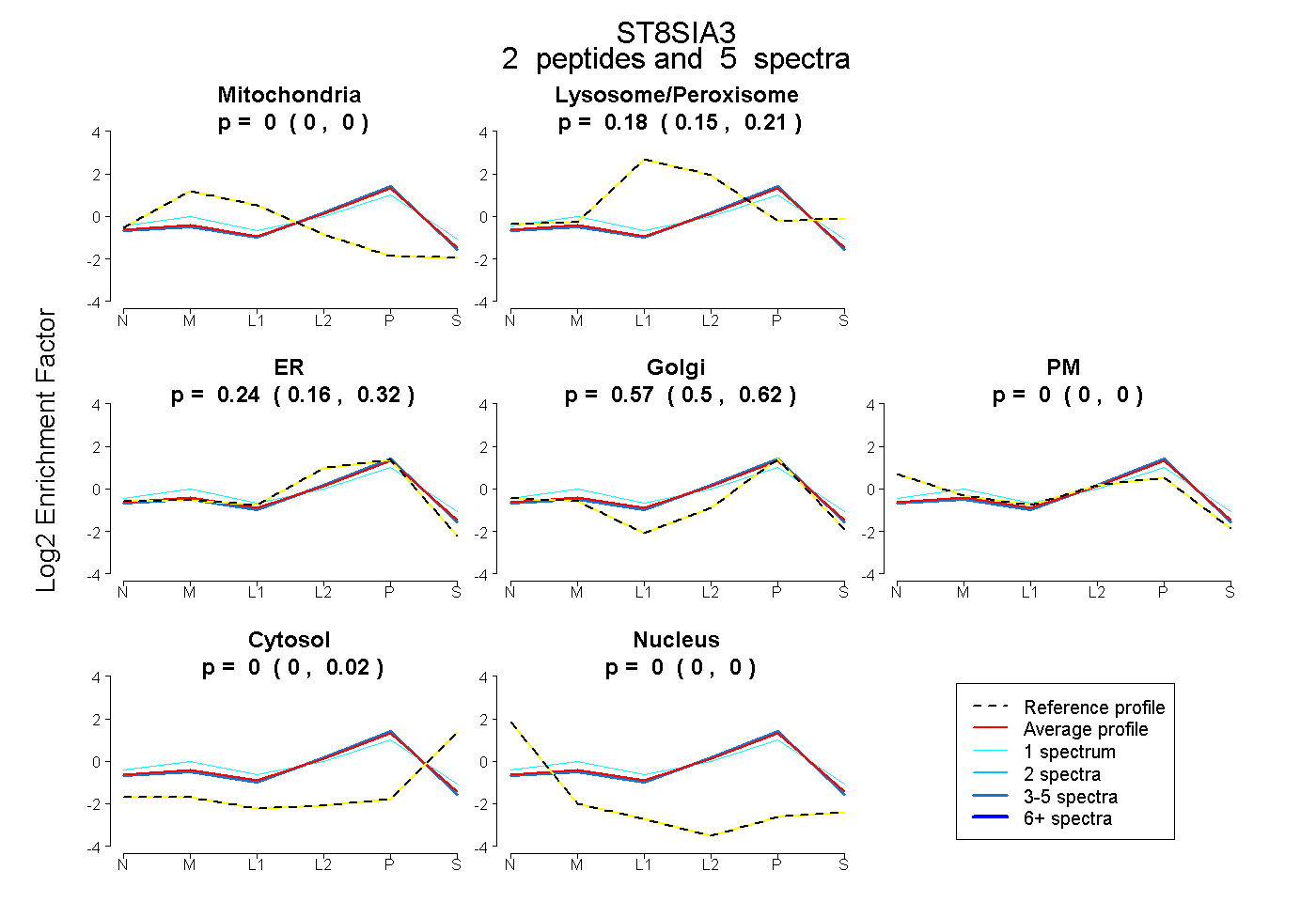 |
0.000 0.000 | 0.000 |
0.184 0.146 | 0.209 |
0.241 0.164 | 0.320 |
0.575 0.501 | 0.616 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.016 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
32 spectra |
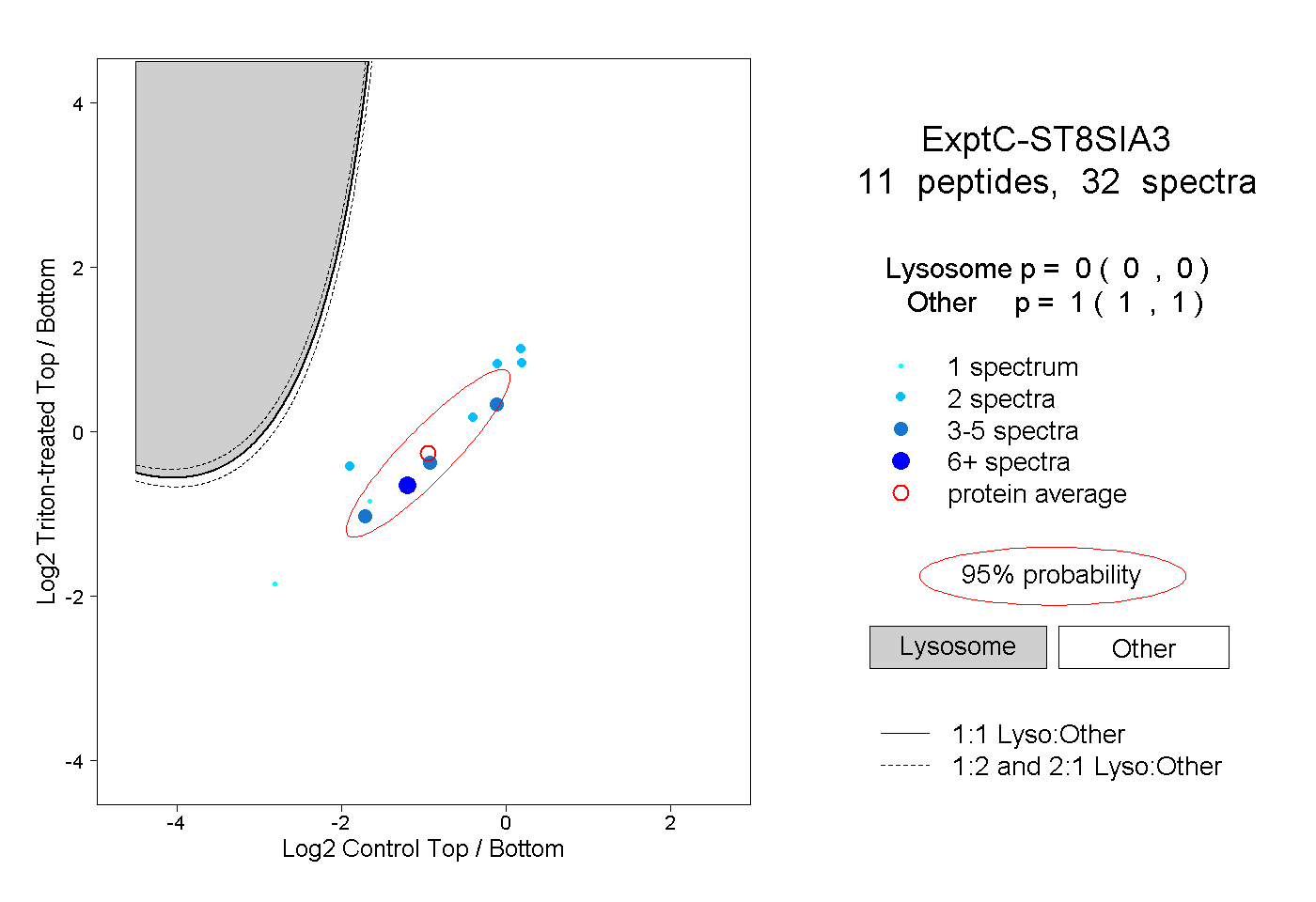 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |