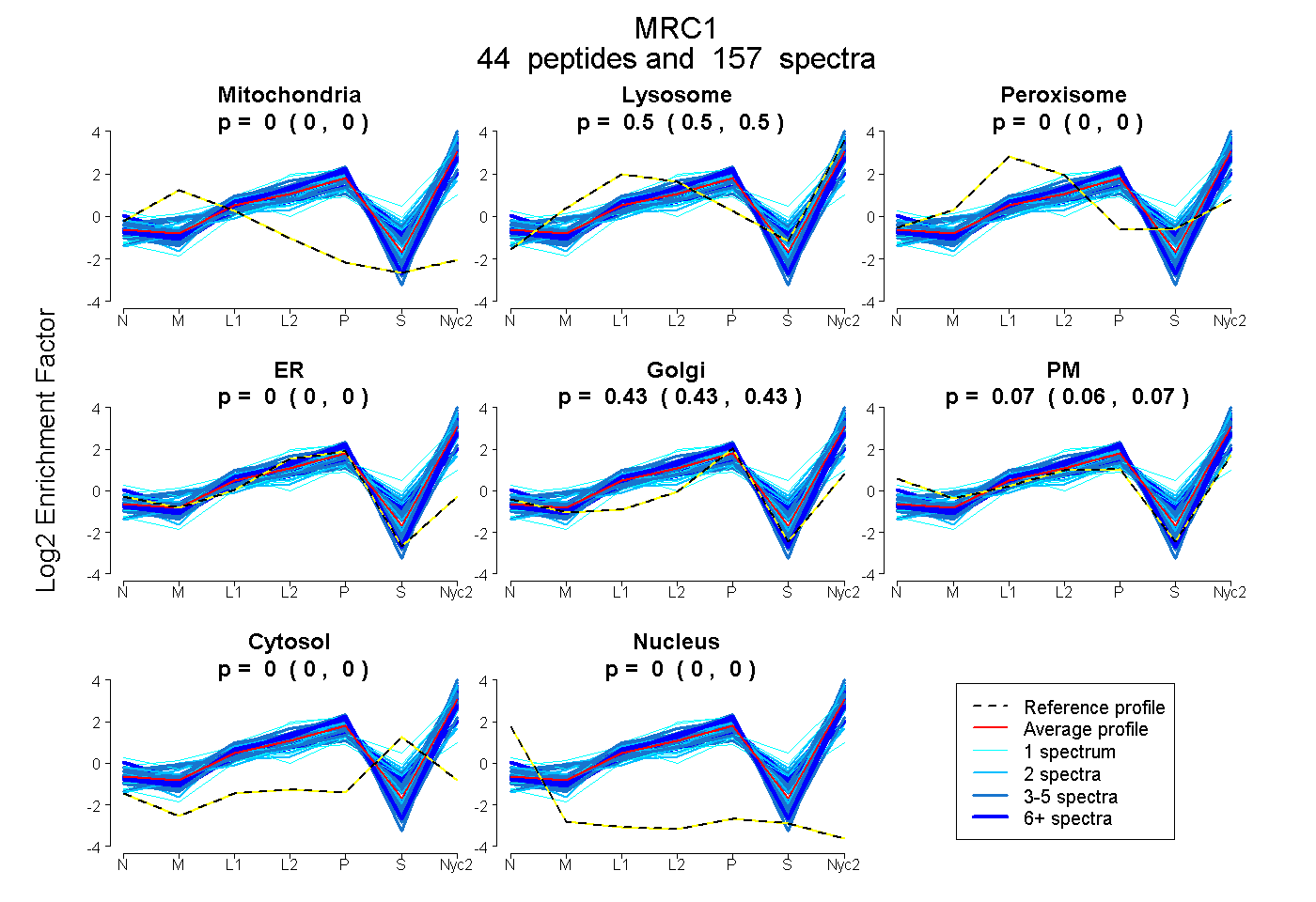
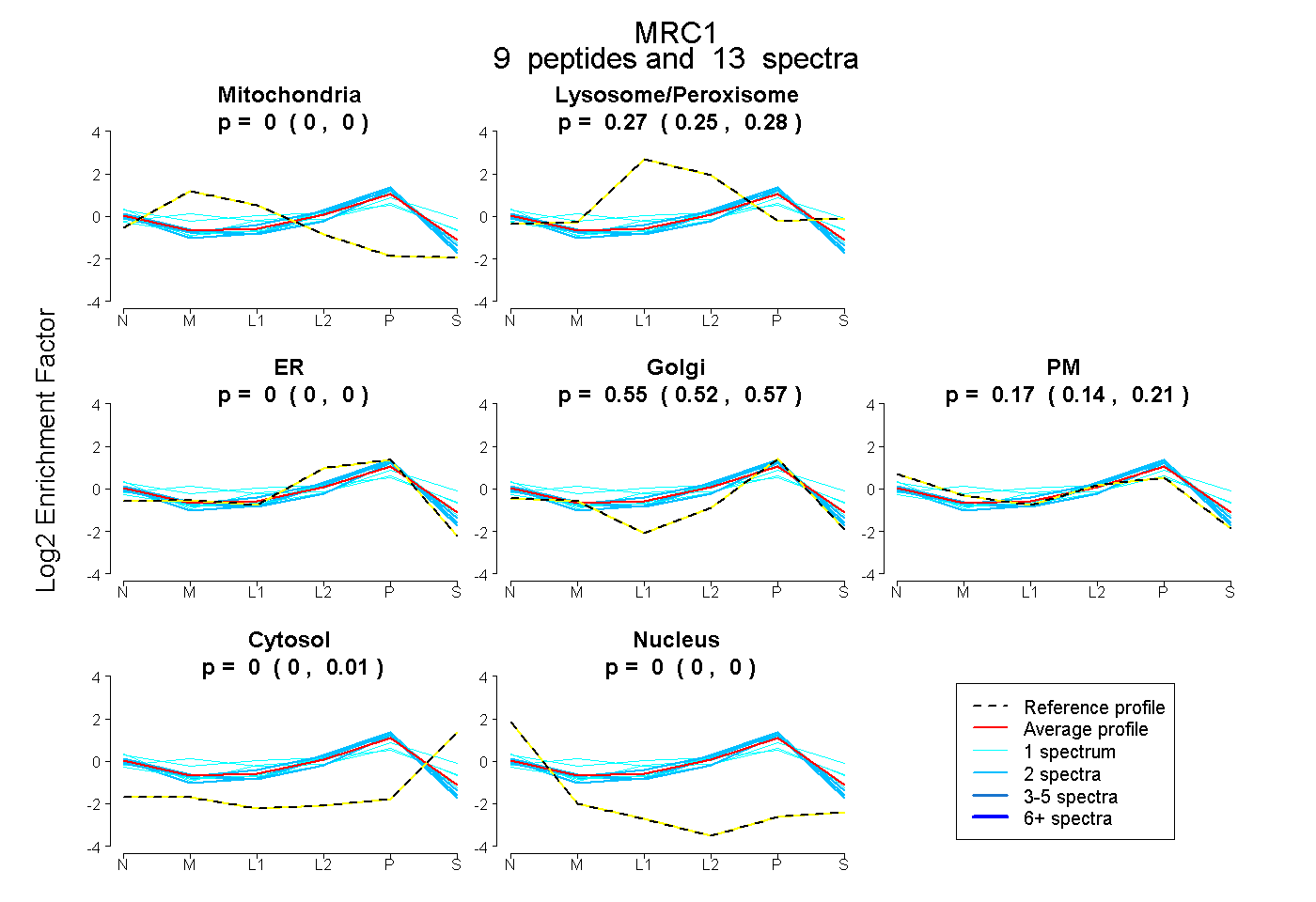
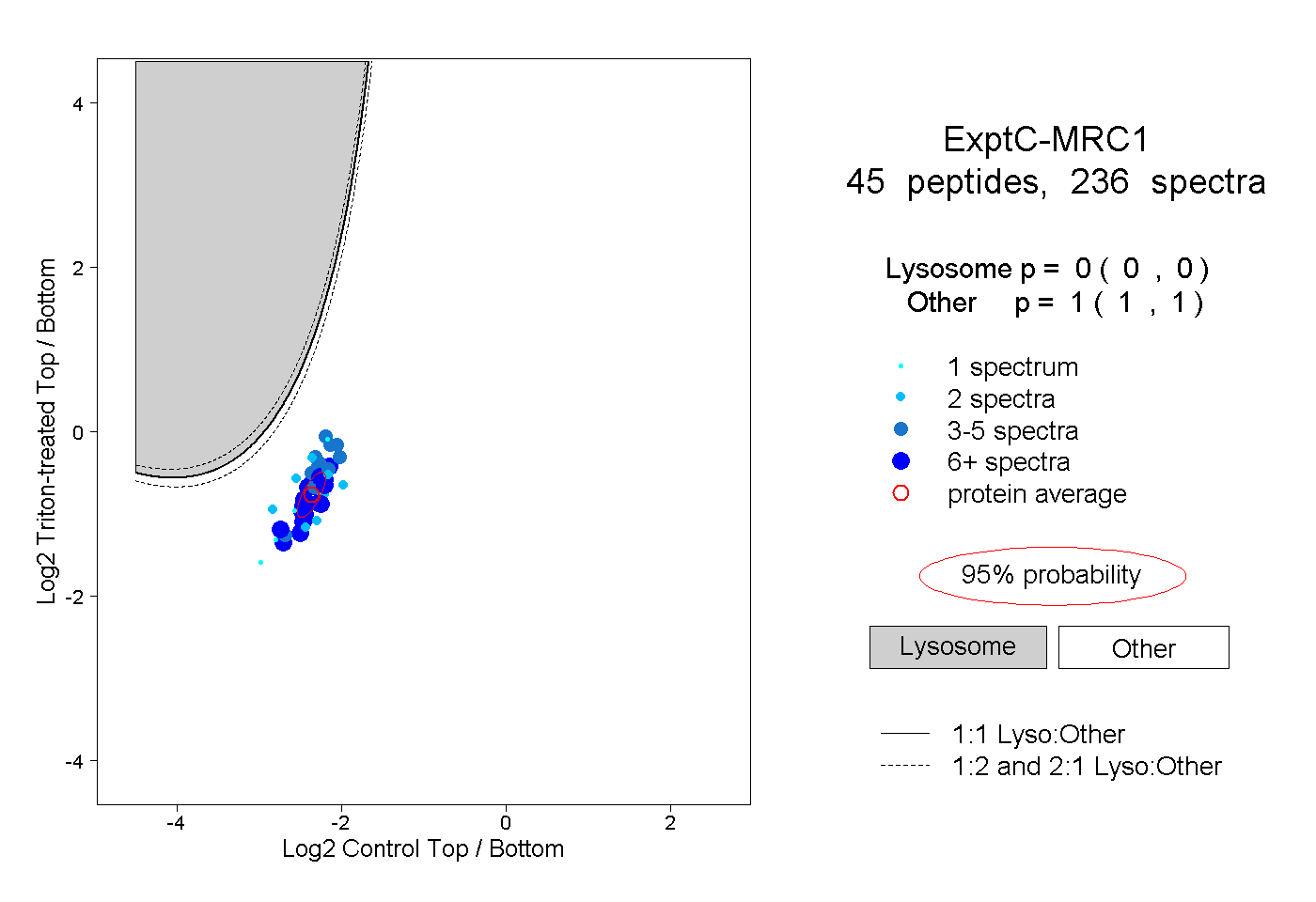
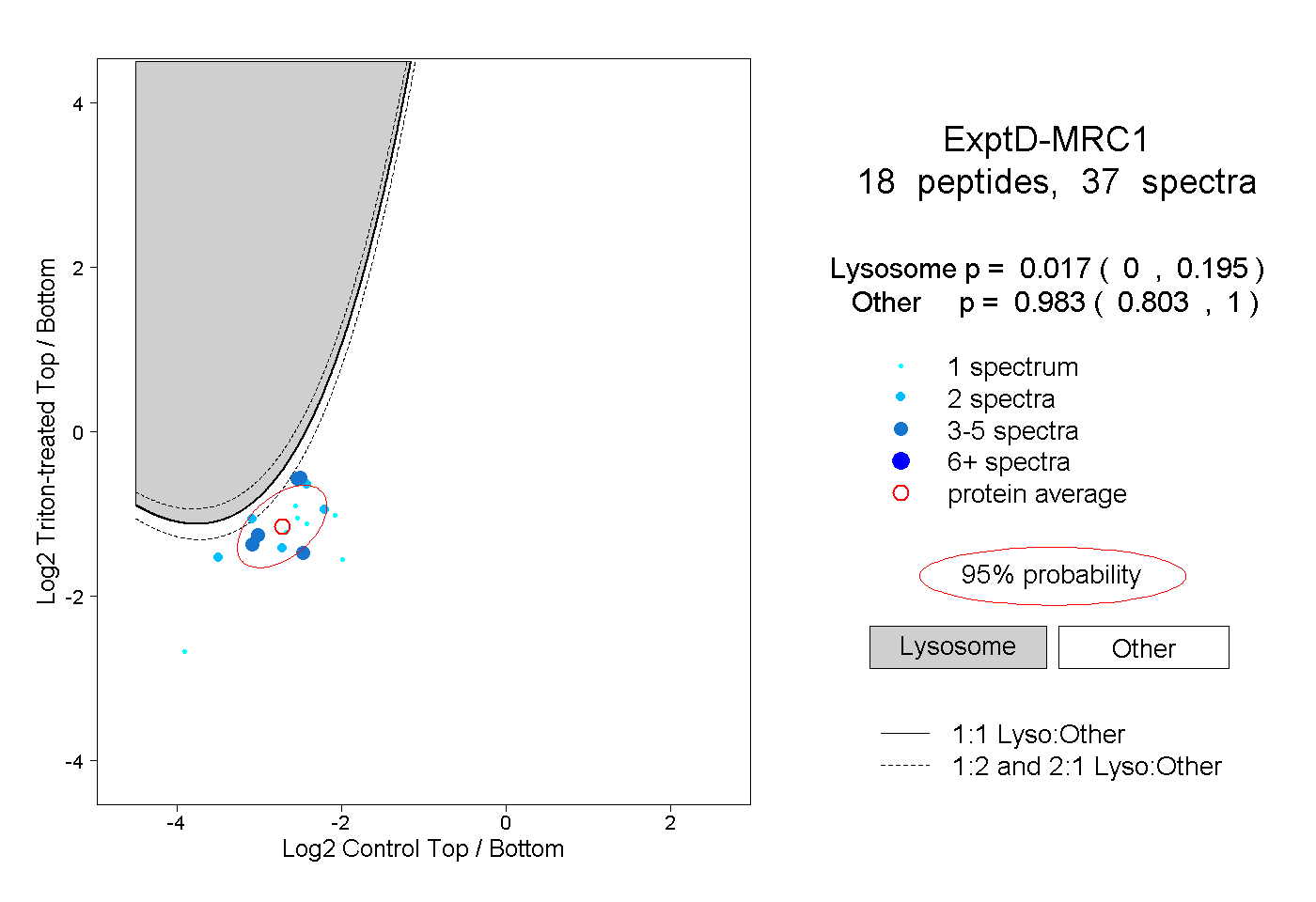
| 4 spectra, NFGDLATIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, AGCVAMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, TWFESR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QEDCVVMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ACEQPLGYICK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DEQQVIWR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, TNFWIGMFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, YFWTGLSDVQNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, DGYWADR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, WLPGEPSHENNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, AIGGELASIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, EQAFVTYHMR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, WVSESQIMSVAFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, SWGQASLECLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, FIWMDGSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, GTELYFNYGNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, EGWHLYNNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, AYLTTVEDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, WYADCTSAGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, WTVDEQVQFTHWNADMPGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YLNWLPGSPSSEPGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, EAGTWMDSTCDSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, GSGLWSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, SCVSLNPGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GYPGGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, VYGTTDDLCSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SPWHEAEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, IQMYFEWSDGTPVTFTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YTNWGTDEPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, SSYALMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SSLSYEDVDCVVVIGGNSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, IFGFAEEEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, CPEDWGTTSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, MDPQPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GNLVSIENAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TSMCFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, MVSQIHTVIPEGAEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, LGYICK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, WENLECVQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, YALQACR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, ACIGLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SACVYMDVDGYWK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, DYQYYFSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, SALTWHQAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, LCLGVPSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |