peptides
spectra
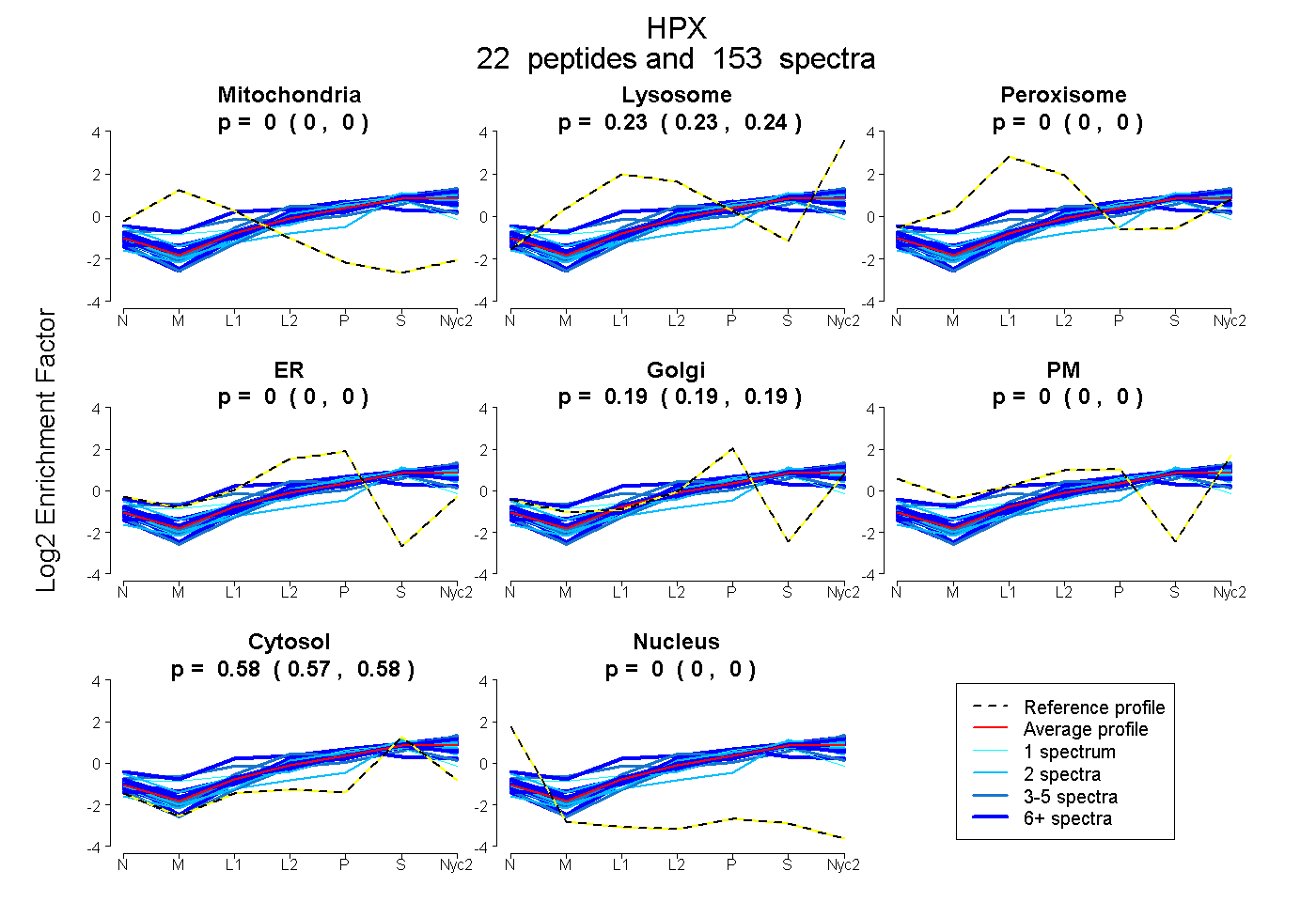
0.000 | 0.000
0.232 | 0.236
0.000 | 0.000
0.000 | 0.000
0.189 | 0.192
0.000 | 0.000
0.574 | 0.577
0.000 | 0.000
peptides
spectra
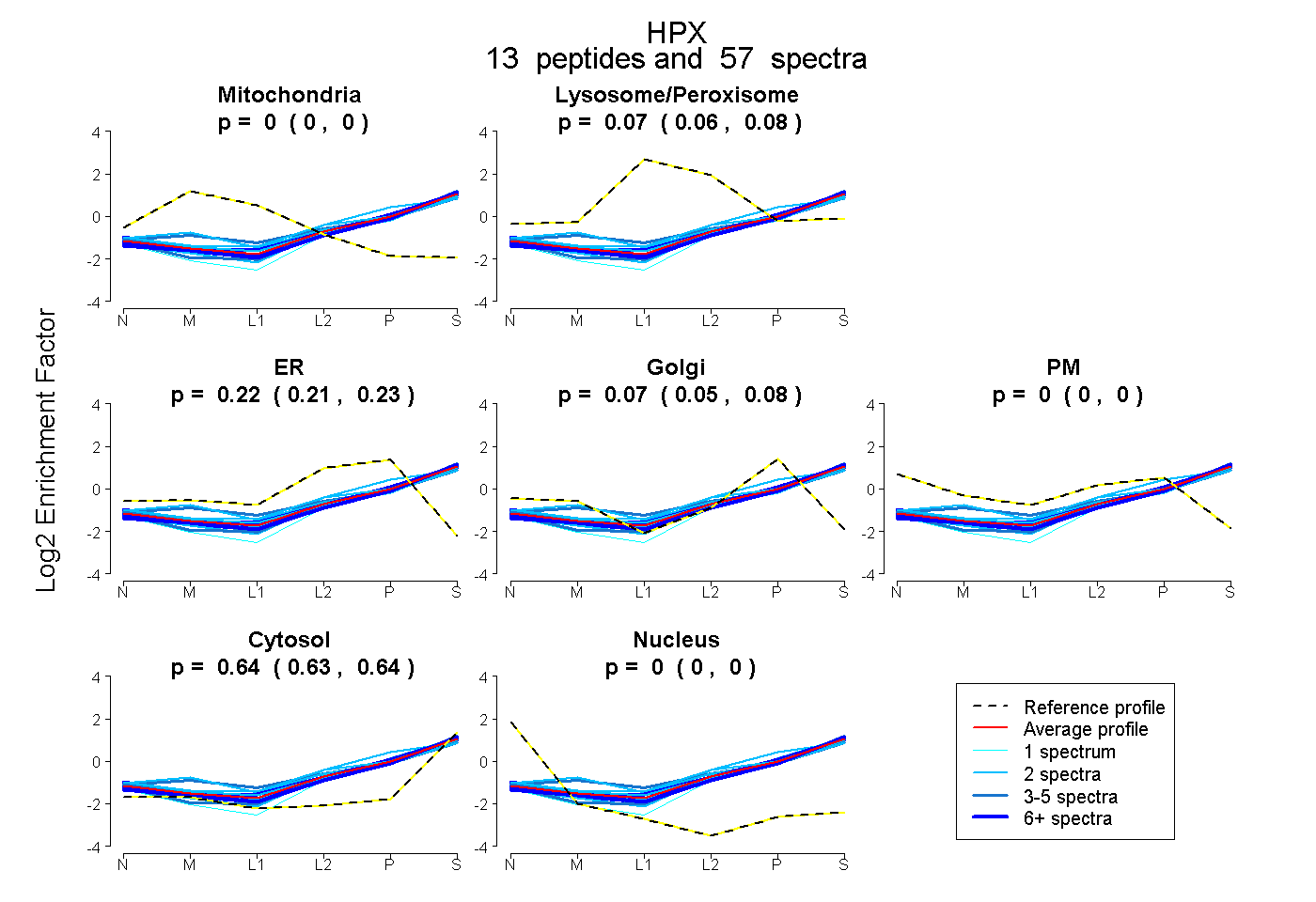
0.000 | 0.000
0.063 | 0.077
0.206 | 0.235
0.055 | 0.079
0.000 | 0.000
0.635 | 0.644
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
153 spectra |
 |
0.000 0.000 | 0.000 |
0.234 0.232 | 0.236 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.191 0.189 | 0.192 |
0.000 0.000 | 0.000 |
0.575 0.574 | 0.577 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
57 spectra |
 |
0.000 0.000 | 0.000 |
0.071 0.063 | 0.077 |
0.222 0.206 | 0.235 |
0.068 0.055 | 0.079 |
0.000 0.000 | 0.000 |
0.639 0.635 | 0.644 |
0.000 0.000 | 0.000 |
| 2 spectra, GPDSVFLIK | 0.000 | 0.000 | 0.296 | 0.000 | 0.000 | 0.704 | 0.000 | |||
| 5 spectra, FNPVTGEVPPR | 0.000 | 0.239 | 0.000 | 0.239 | 0.000 | 0.521 | 0.000 | |||
| 1 spectrum, GGNNLVSGYPK | 0.000 | 0.000 | 0.149 | 0.167 | 0.000 | 0.684 | 0.000 | |||
| 6 spectra, DYFISCPGR | 0.000 | 0.082 | 0.147 | 0.151 | 0.000 | 0.621 | 0.000 | |||
| 14 spectra, LYVTSGR | 0.000 | 0.104 | 0.172 | 0.099 | 0.000 | 0.625 | 0.000 | |||
| 2 spectra, ENGYPK | 0.000 | 0.015 | 0.403 | 0.005 | 0.000 | 0.577 | 0.000 | |||
| 2 spectra, VDGALCLEK | 0.000 | 0.150 | 0.062 | 0.176 | 0.000 | 0.612 | 0.000 | |||
| 2 spectra, SLPQPQK | 0.000 | 0.146 | 0.226 | 0.046 | 0.000 | 0.581 | 0.000 | |||
| 2 spectra, GHSGIR | 0.000 | 0.207 | 0.000 | 0.271 | 0.000 | 0.522 | 0.000 | |||
| 7 spectra, GEFVWR | 0.000 | 0.031 | 0.244 | 0.057 | 0.000 | 0.667 | 0.000 | |||
| 6 spectra, WFWDFATR | 0.000 | 0.014 | 0.276 | 0.000 | 0.000 | 0.710 | 0.000 | |||
| 4 spectra, LWWLDLK | 0.000 | 0.007 | 0.279 | 0.000 | 0.000 | 0.713 | 0.000 | |||
| 4 spectra, NPVTSVDAAFR | 0.000 | 0.017 | 0.267 | 0.064 | 0.000 | 0.651 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
327 spectra |
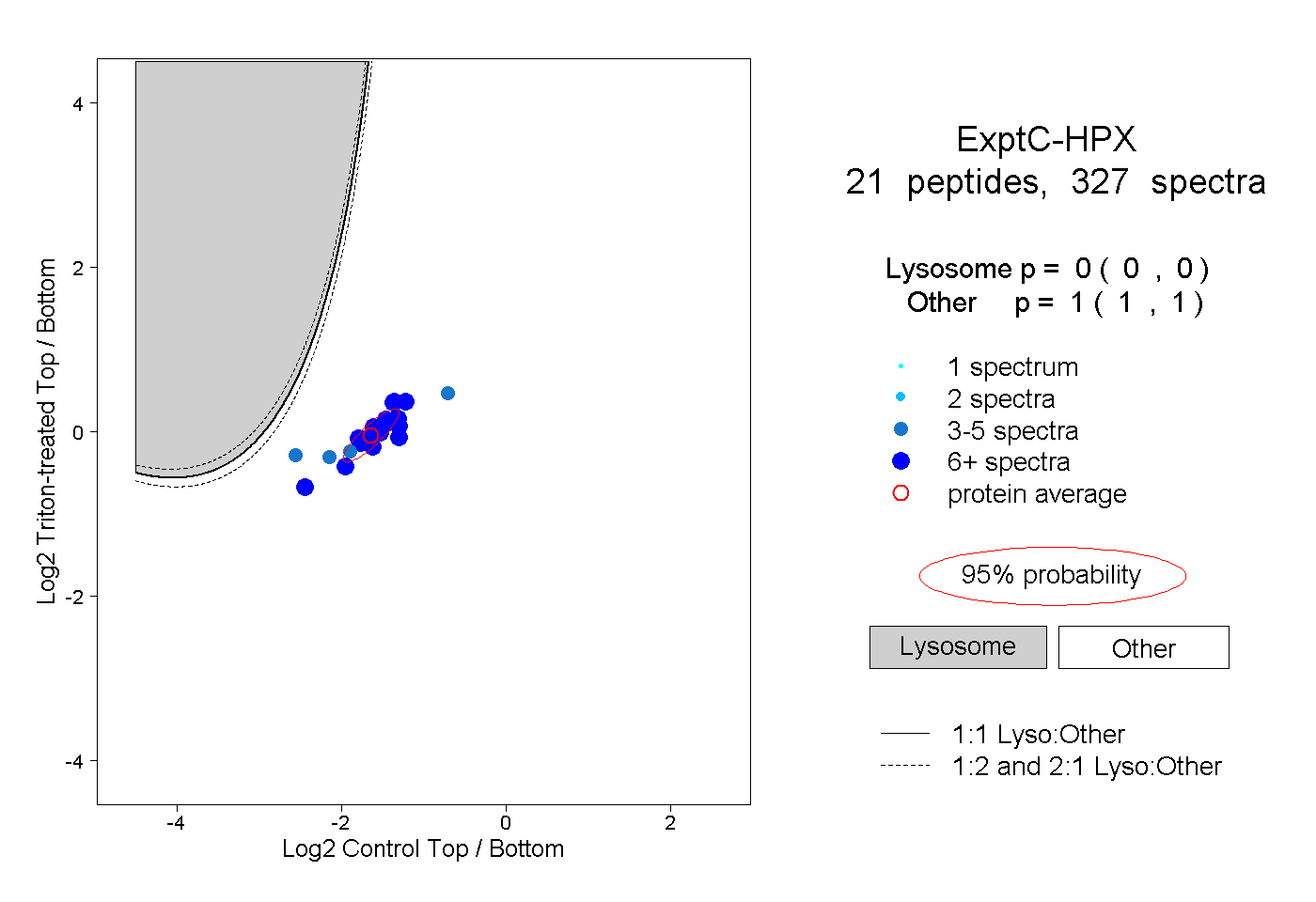 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
43 spectra |
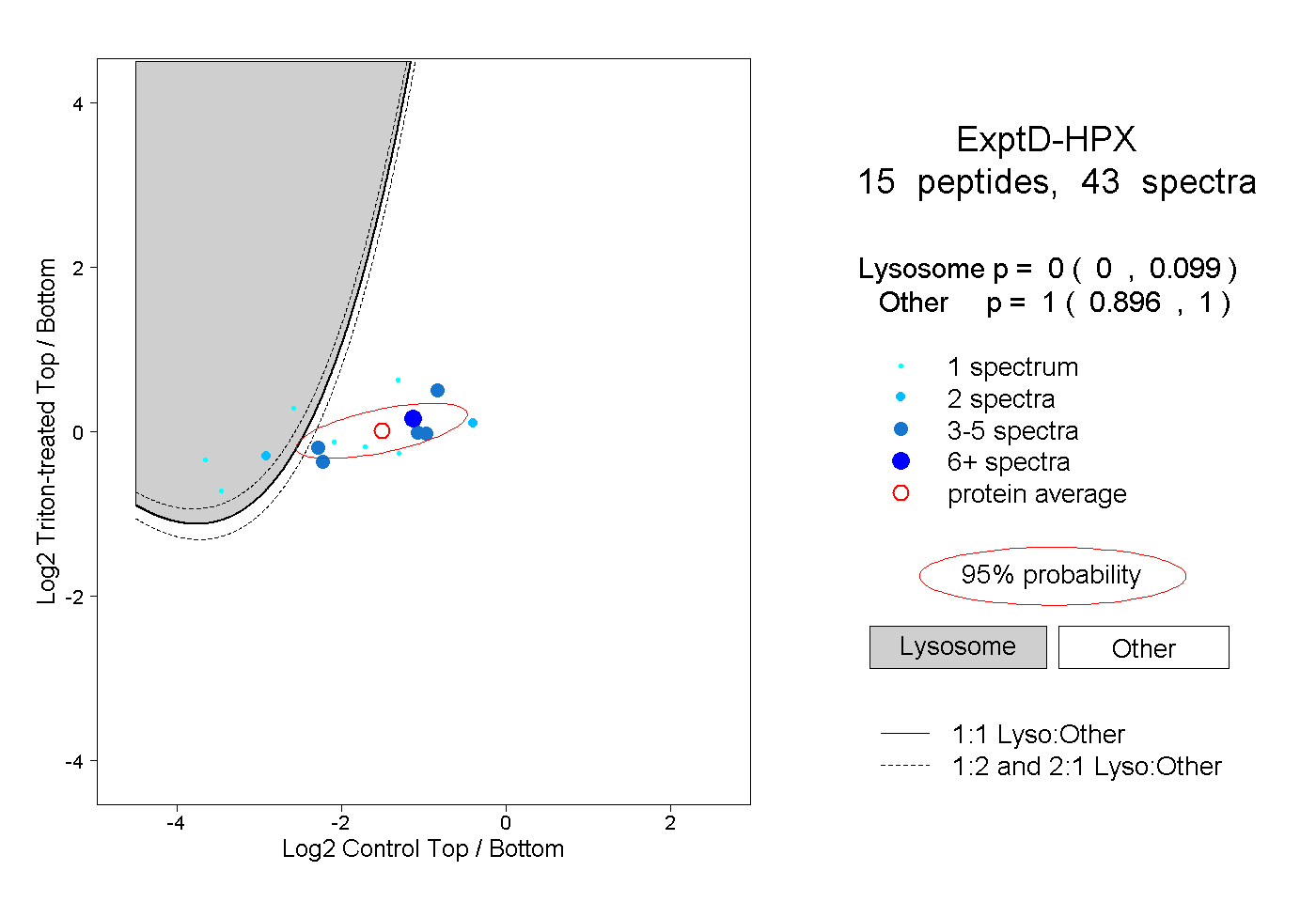 |
0.000 0.000 | 0.099 |
1.000 0.896 | 1.000 |