peptides
spectra
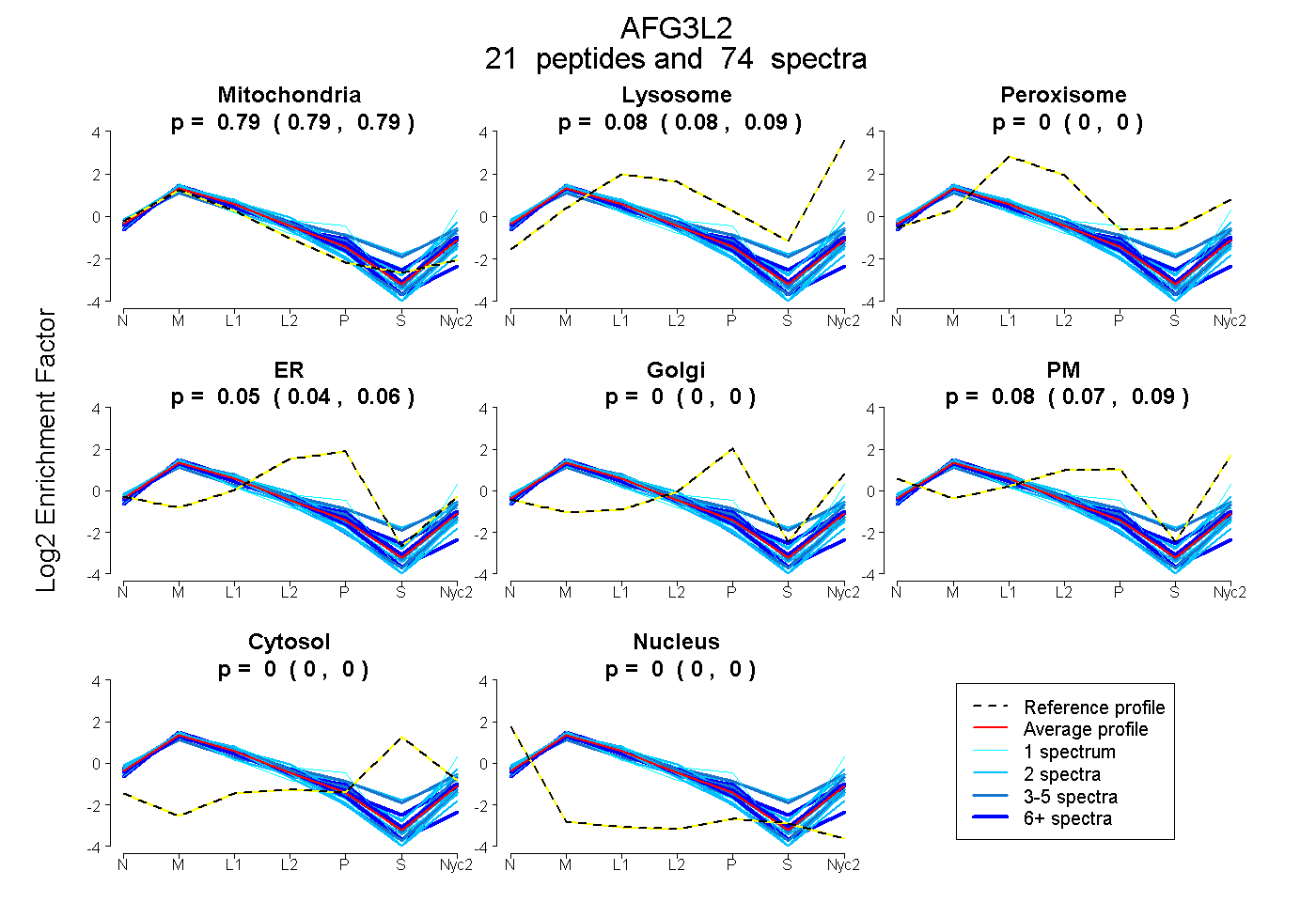
0.785 | 0.792
0.079 | 0.087
0.000 | 0.000
0.041 | 0.056
0.000 | 0.000
0.071 | 0.087
0.000 | 0.000
0.000 | 0.000
peptides
spectra
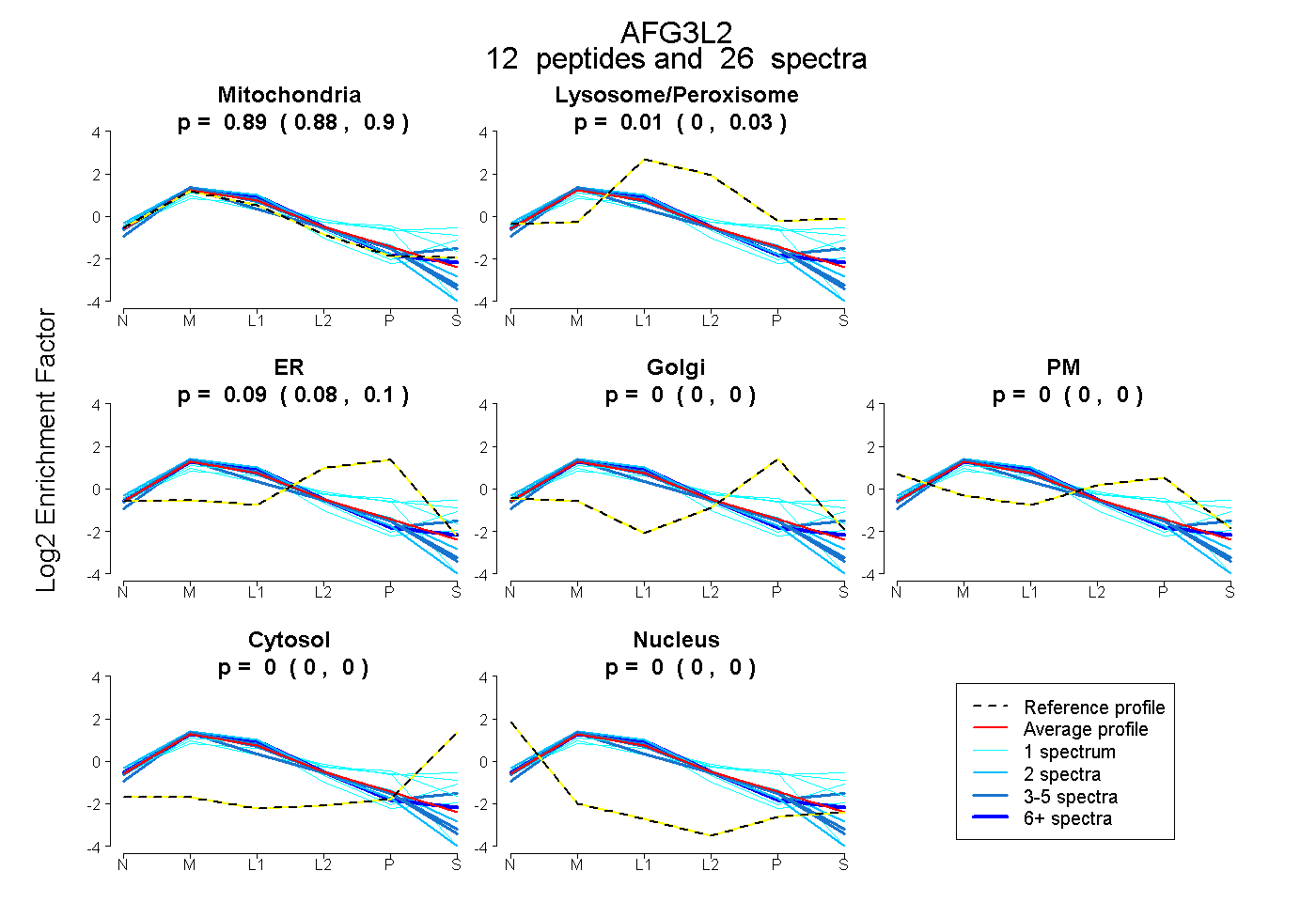
0.881 | 0.904
0.000 | 0.027
0.076 | 0.104
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
74 spectra |
 |
0.789 0.785 | 0.792 |
0.083 0.079 | 0.087 |
0.000 0.000 | 0.000 |
0.049 0.041 | 0.056 |
0.000 0.000 | 0.000 |
0.080 0.071 | 0.087 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
26 spectra |
 |
0.894 0.881 | 0.904 |
0.014 0.000 | 0.027 |
0.092 0.076 | 0.104 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, QIFIGPPDIK | 0.624 | 0.174 | 0.143 | 0.059 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GMGGLFSVGETTAK | 0.518 | 0.236 | 0.000 | 0.191 | 0.000 | 0.054 | 0.000 | |||
| 1 spectrum, EQYLYTK | 0.452 | 0.331 | 0.000 | 0.120 | 0.000 | 0.097 | 0.000 | |||
| 1 spectrum, LEVVDK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, VALLLLEK | 0.934 | 0.066 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, VGQISFDLPR | 0.973 | 0.000 | 0.027 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, VSEEIFFGR | 0.912 | 0.000 | 0.088 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, DLFALAR | 0.712 | 0.000 | 0.288 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, VSIIPR | 0.918 | 0.000 | 0.082 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GAILTGPPGTGK | 0.833 | 0.117 | 0.000 | 0.000 | 0.000 | 0.050 | 0.000 | |||
| 2 spectra, EQLLDR | 0.907 | 0.000 | 0.093 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, MIDDEVR | 0.896 | 0.046 | 0.000 | 0.000 | 0.000 | 0.058 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
319 spectra |
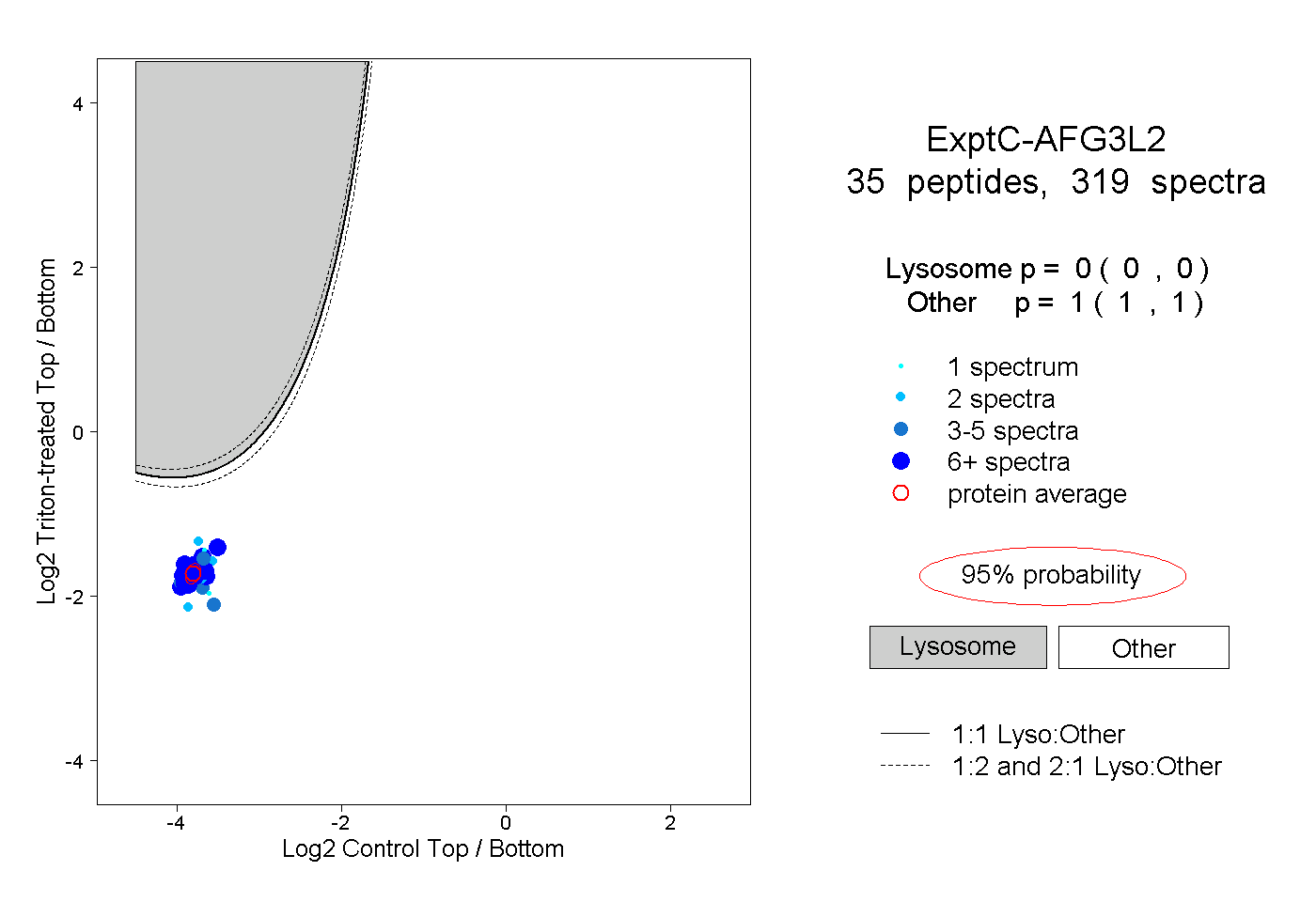 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
35 spectra |
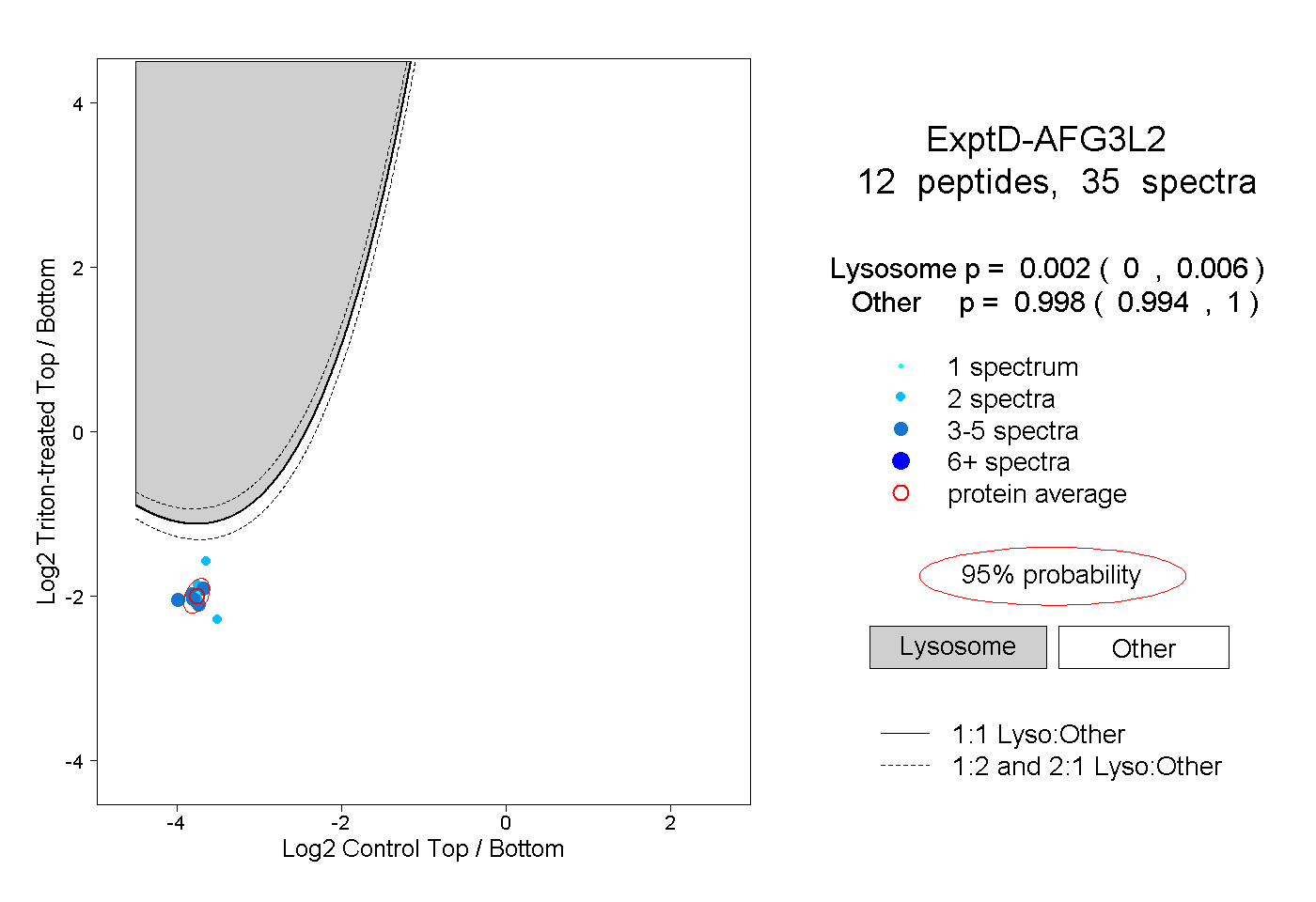 |
0.002 0.000 | 0.006 |
0.998 0.994 | 1.000 |