peptides
spectra
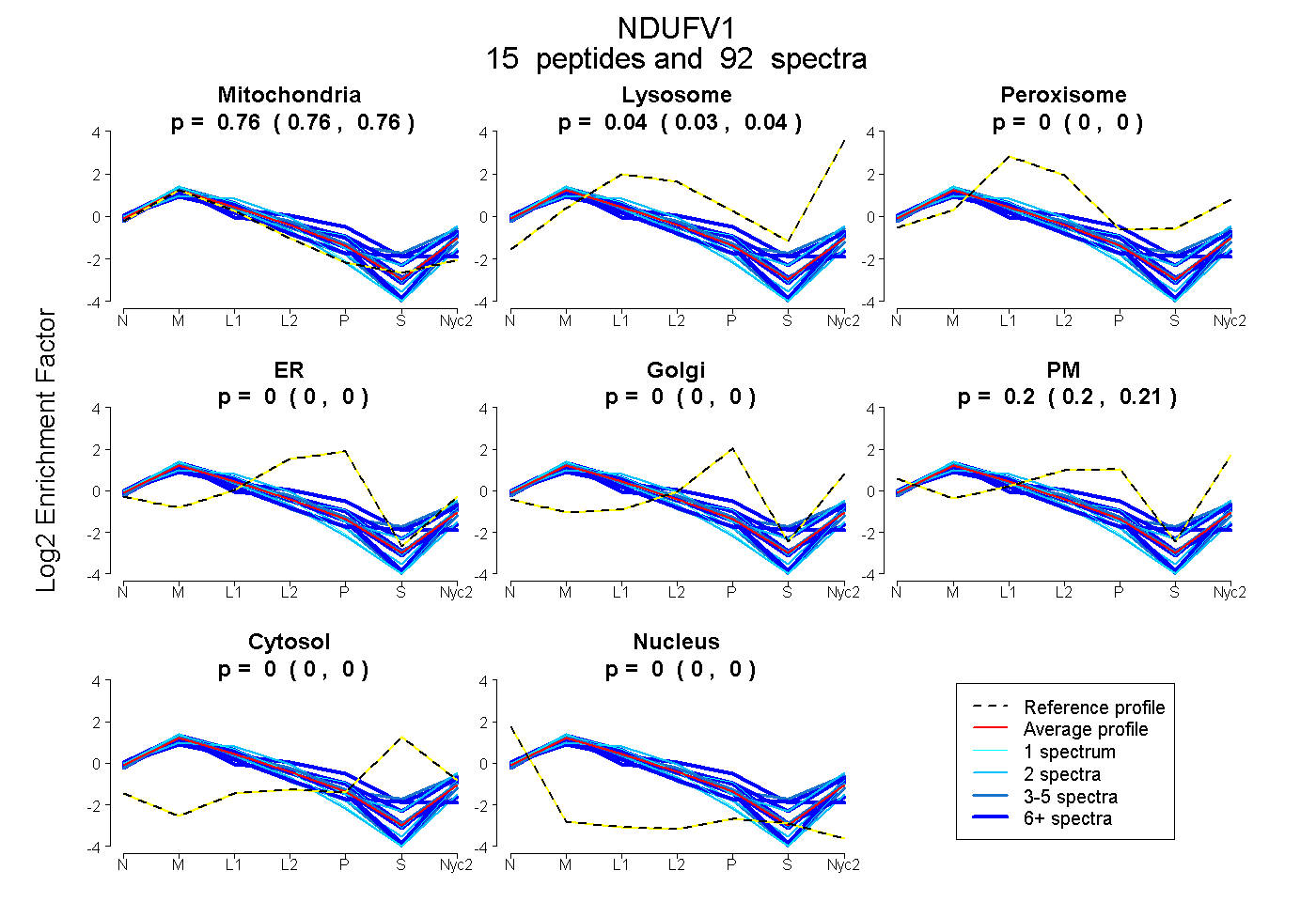
0.757 | 0.763
0.030 | 0.041
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.197 | 0.209
0.000 | 0.000
0.000 | 0.000
peptides
spectra
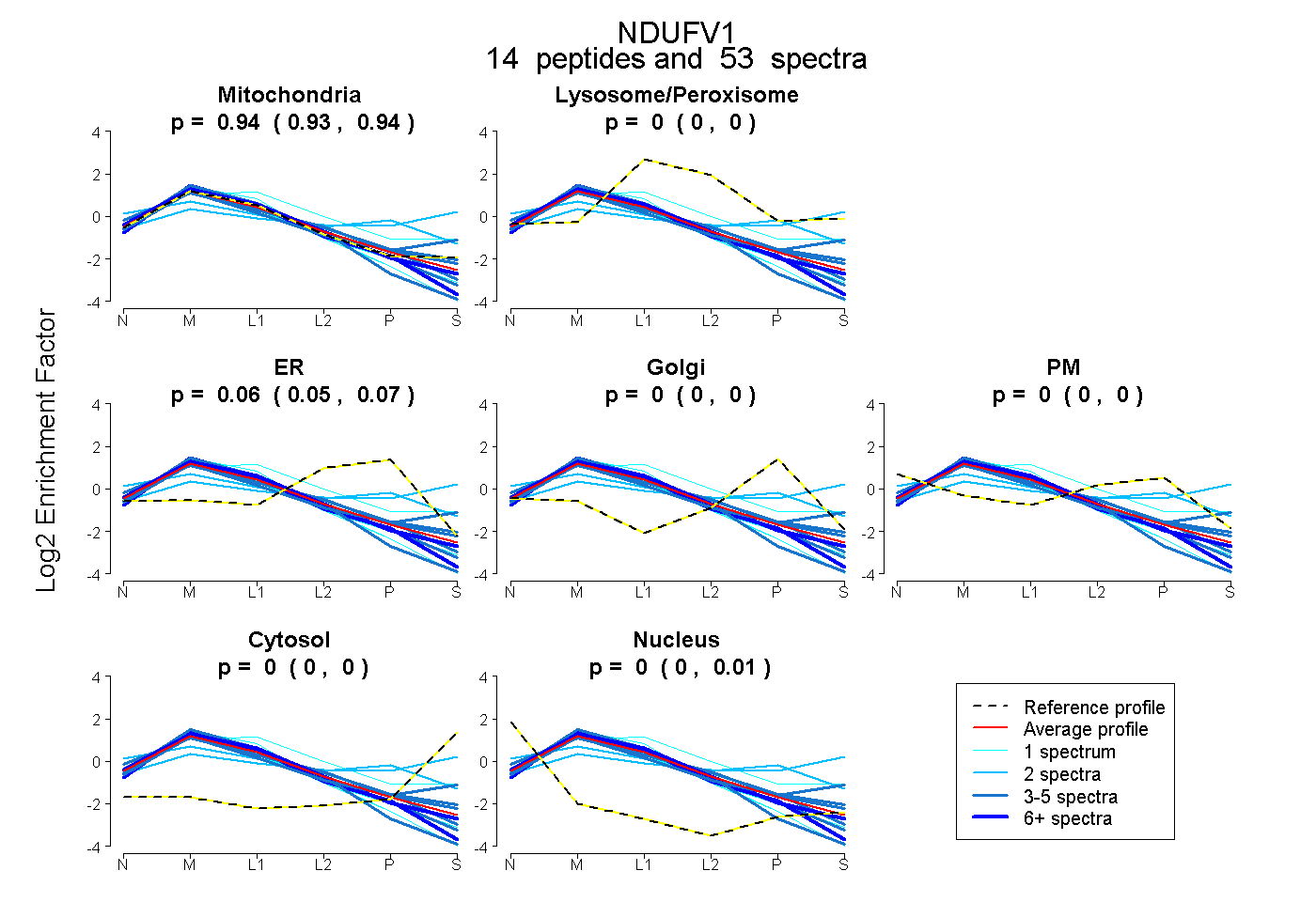
0.929 | 0.944
0.000 | 0.000
0.049 | 0.065
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.001 | 0.007
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
92 spectra |
 |
0.760 0.757 | 0.763 |
0.036 0.030 | 0.041 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.204 0.197 | 0.209 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
53 spectra |
 |
0.938 0.929 | 0.944 |
0.000 0.000 | 0.000 |
0.058 0.049 | 0.065 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.004 0.001 | 0.007 |
| 4 spectra, GPDWILGEMK | 0.905 | 0.000 | 0.095 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GDARPAEIDSLWEISK | 0.969 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.031 | |||
| 2 spectra, FAQQHQAR | 0.424 | 0.127 | 0.000 | 0.149 | 0.299 | 0.001 | 0.000 | |||
| 4 spectra, AAYIYIR | 0.921 | 0.000 | 0.058 | 0.000 | 0.000 | 0.000 | 0.021 | |||
| 4 spectra, QIEGHTICALGDGAAWPVQGLIR | 0.812 | 0.045 | 0.000 | 0.009 | 0.000 | 0.133 | 0.000 | |||
| 8 spectra, HFRPELEDR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, LVEGCLVGGR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, LIEFYK | 0.850 | 0.000 | 0.000 | 0.000 | 0.150 | 0.000 | 0.000 | |||
| 1 spectrum, GEFYNEASNLQVAIR | 0.960 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.040 | |||
| 2 spectra, GAGAYICGEETALIESIEGK | 0.227 | 0.321 | 0.000 | 0.164 | 0.000 | 0.287 | 0.000 | |||
| 5 spectra, IFTNLYGR | 0.998 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.002 | |||
| 1 spectrum, GGAGFPTGLK | 0.989 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.011 | |||
| 1 spectrum, EAYEAGLIGK | 0.652 | 0.326 | 0.000 | 0.021 | 0.000 | 0.001 | 0.000 | |||
| 4 spectra, GGTWFAGFGR | 0.997 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.003 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
271 spectra |
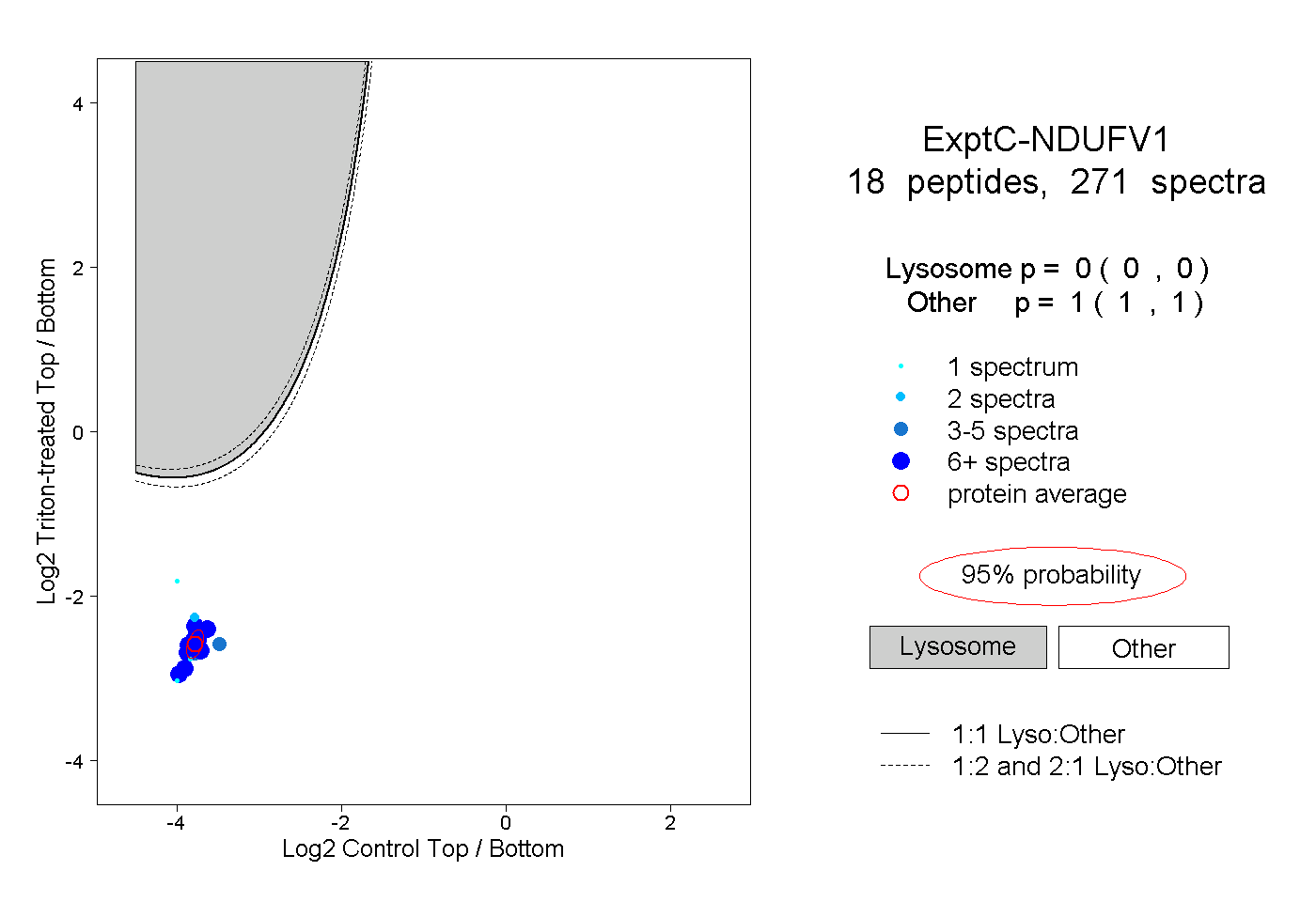 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
25 spectra |
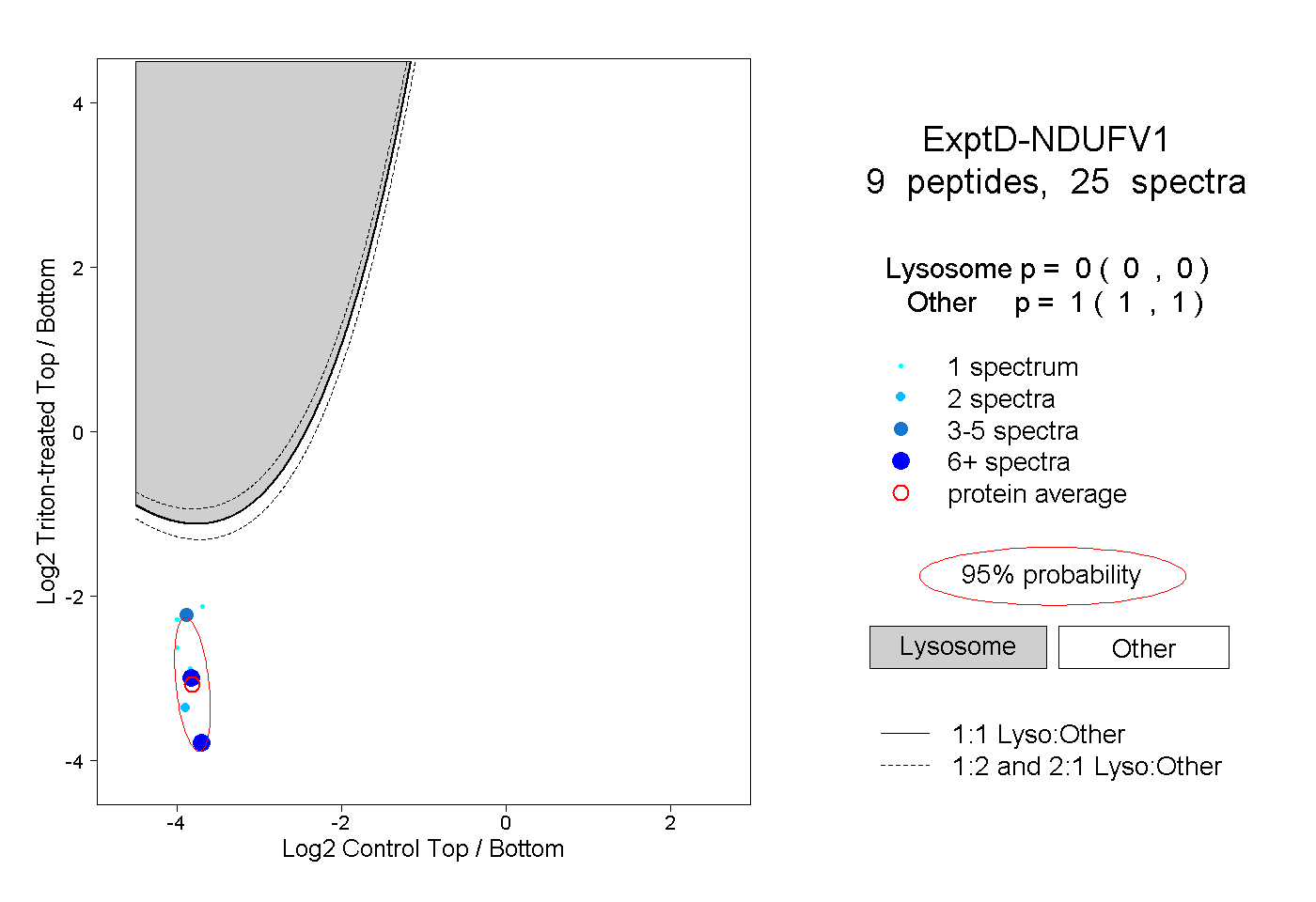 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |