peptides
spectra
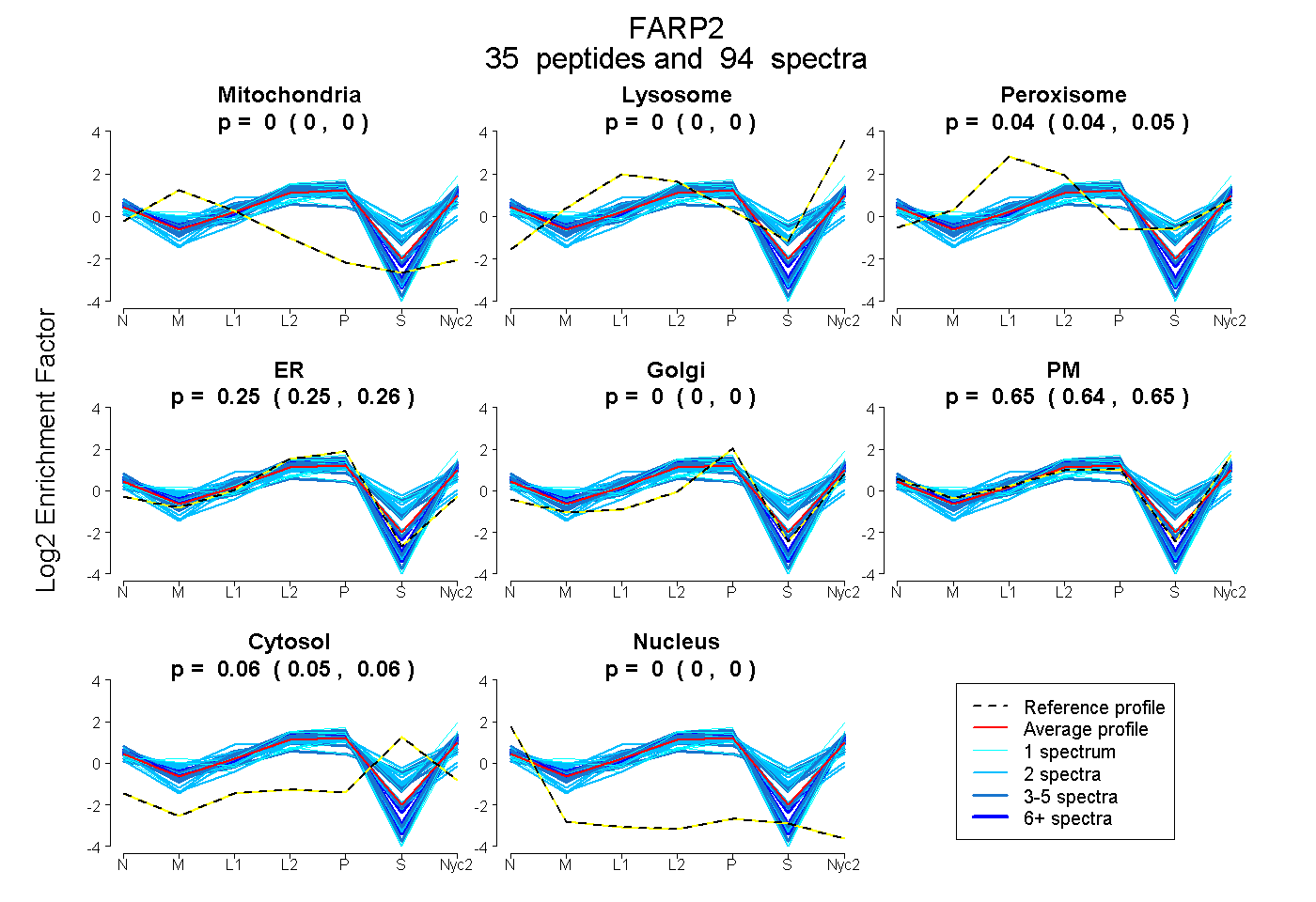
0.000 | 0.000
0.000 | 0.000
0.037 | 0.045
0.248 | 0.259
0.000 | 0.000
0.643 | 0.655
0.051 | 0.058
0.000 | 0.000
peptides
spectra
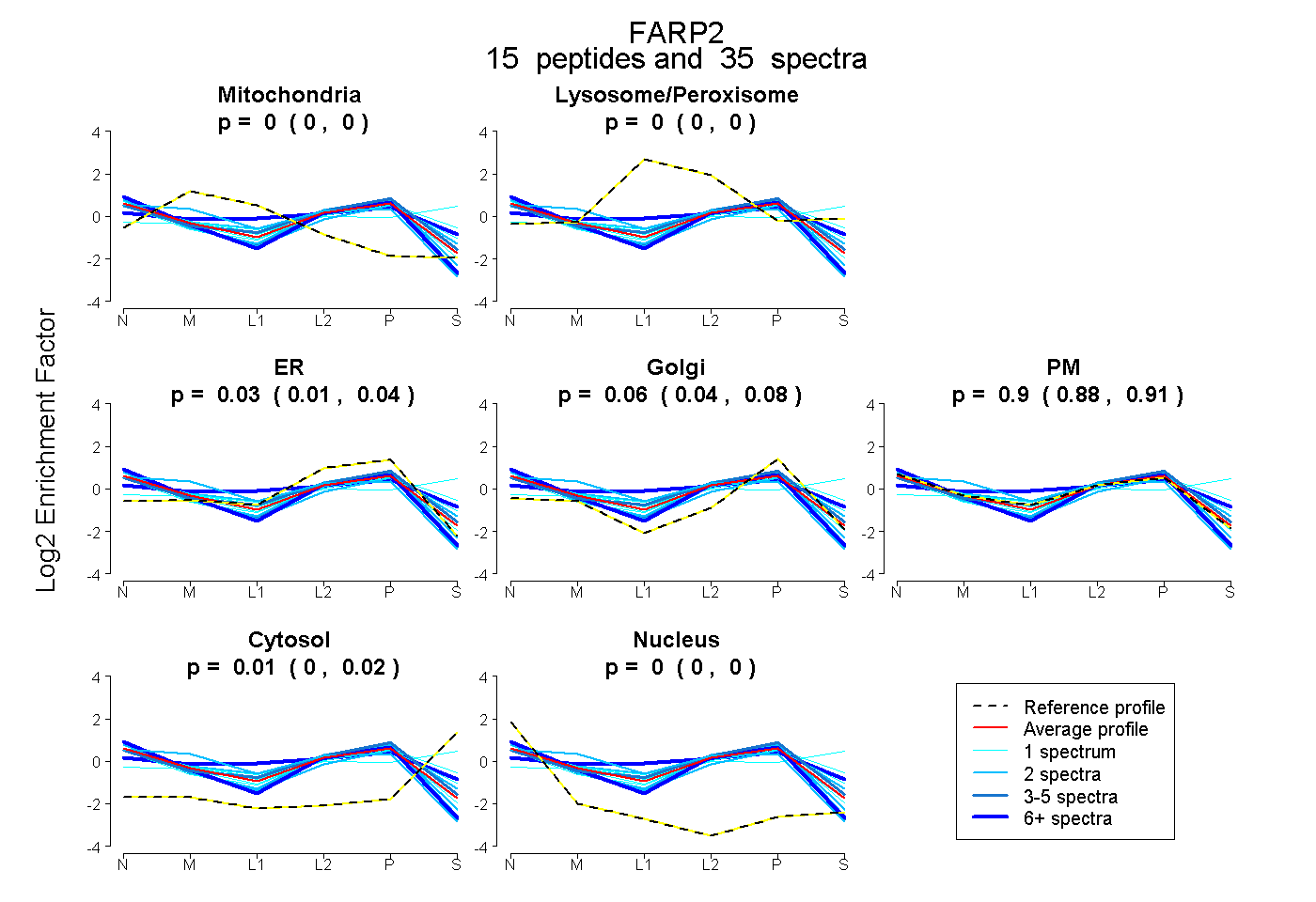
0.000 | 0.000
0.000 | 0.002
0.011 | 0.037
0.044 | 0.075
0.883 | 0.913
0.004 | 0.023
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
94 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.042 0.037 | 0.045 |
0.254 0.248 | 0.259 |
0.000 0.000 | 0.000 |
0.649 0.643 | 0.655 |
0.055 0.051 | 0.058 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
35 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.002 |
0.026 0.011 | 0.037 |
0.060 0.044 | 0.075 |
0.900 0.883 | 0.913 |
0.015 0.004 | 0.023 |
0.000 0.000 | 0.000 |
| 3 spectra, TLPTSGTR | 0.000 | 0.078 | 0.044 | 0.156 | 0.721 | 0.000 | 0.000 | |||
| 1 spectrum, LTEAGLR | 0.000 | 0.077 | 0.000 | 0.064 | 0.688 | 0.171 | 0.000 | |||
| 6 spectra, ILDFHQR | 0.008 | 0.284 | 0.000 | 0.164 | 0.460 | 0.085 | 0.000 | |||
| 6 spectra, TIVVAASTR | 0.000 | 0.000 | 0.178 | 0.064 | 0.672 | 0.000 | 0.086 | |||
| 1 spectrum, GFLPLR | 0.000 | 0.000 | 0.000 | 0.041 | 0.959 | 0.000 | 0.000 | |||
| 2 spectra, YLFALQLR | 0.168 | 0.000 | 0.168 | 0.000 | 0.663 | 0.000 | 0.000 | |||
| 1 spectrum, GFLIPR | 0.000 | 0.000 | 0.116 | 0.051 | 0.816 | 0.000 | 0.018 | |||
| 1 spectrum, QLVDYIR | 0.000 | 0.073 | 0.000 | 0.019 | 0.806 | 0.101 | 0.000 | |||
| 4 spectra, AVFFSR | 0.000 | 0.000 | 0.318 | 0.000 | 0.586 | 0.000 | 0.095 | |||
| 2 spectra, IGDILLR | 0.000 | 0.000 | 0.286 | 0.013 | 0.629 | 0.000 | 0.073 | |||
| 2 spectra, GFLHEVEQR | 0.000 | 0.131 | 0.000 | 0.138 | 0.702 | 0.029 | 0.000 | |||
| 1 spectrum, HTGQTPADSDFQVLEIAR | 0.000 | 0.265 | 0.000 | 0.085 | 0.285 | 0.366 | 0.000 | |||
| 1 spectrum, HDEVLTELEK | 0.000 | 0.093 | 0.000 | 0.125 | 0.778 | 0.004 | 0.000 | |||
| 2 spectra, LLDSTVEIFDIEPK | 0.000 | 0.000 | 0.000 | 0.145 | 0.782 | 0.000 | 0.073 | |||
| 2 spectra, SVTGASQFR | 0.000 | 0.000 | 0.050 | 0.197 | 0.721 | 0.000 | 0.032 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
99 spectra |
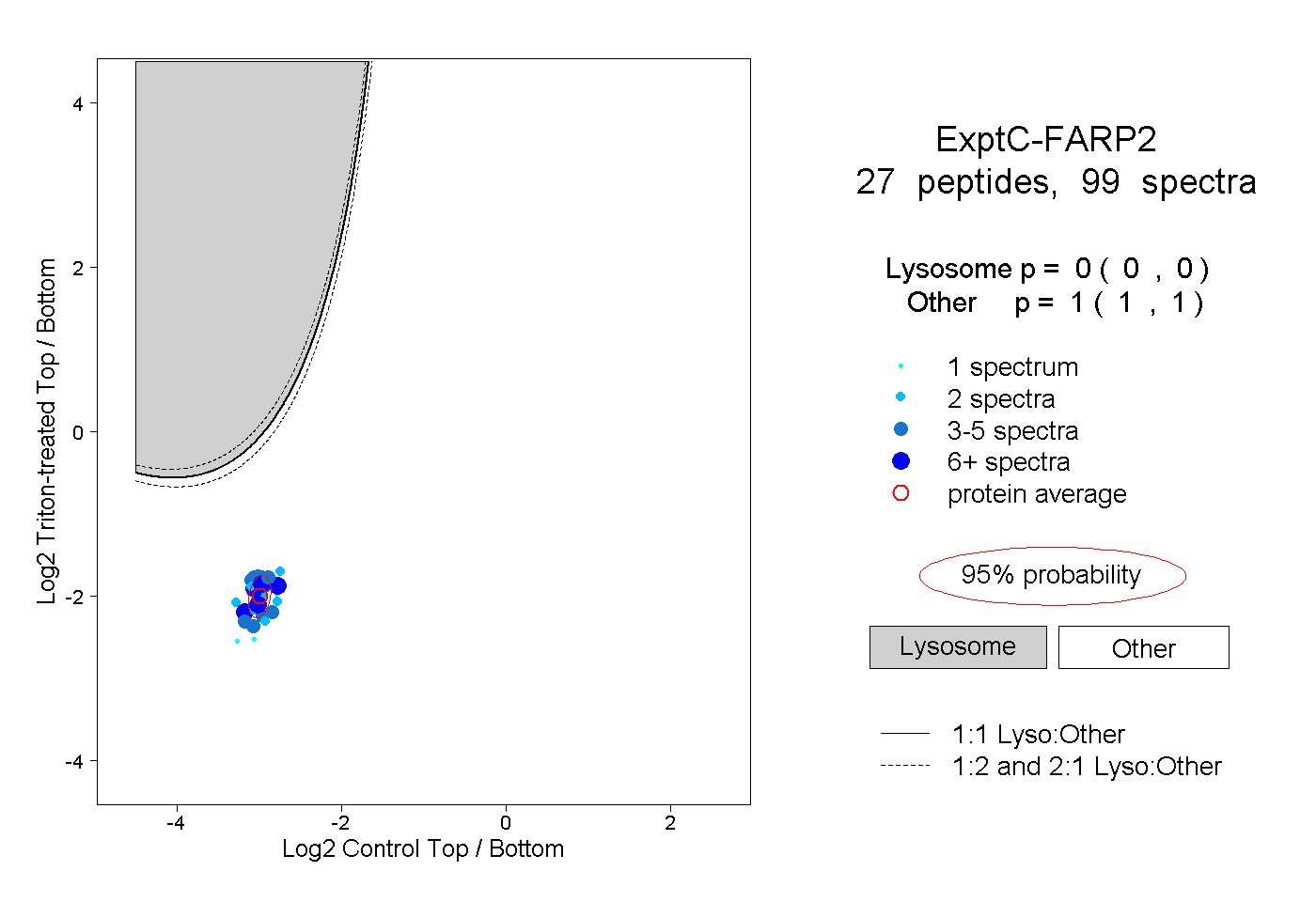 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
12 spectra |
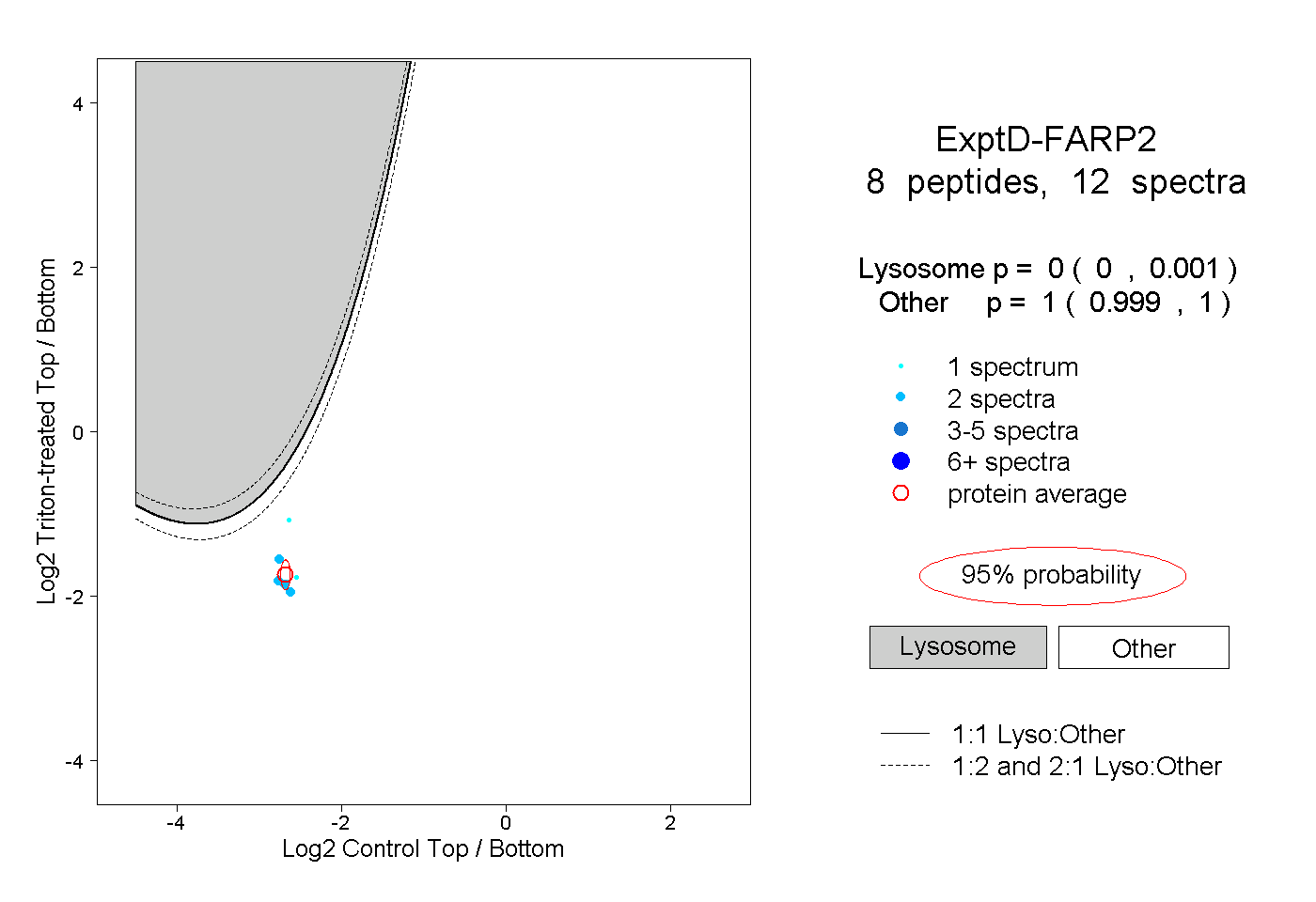 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |