peptides
spectra
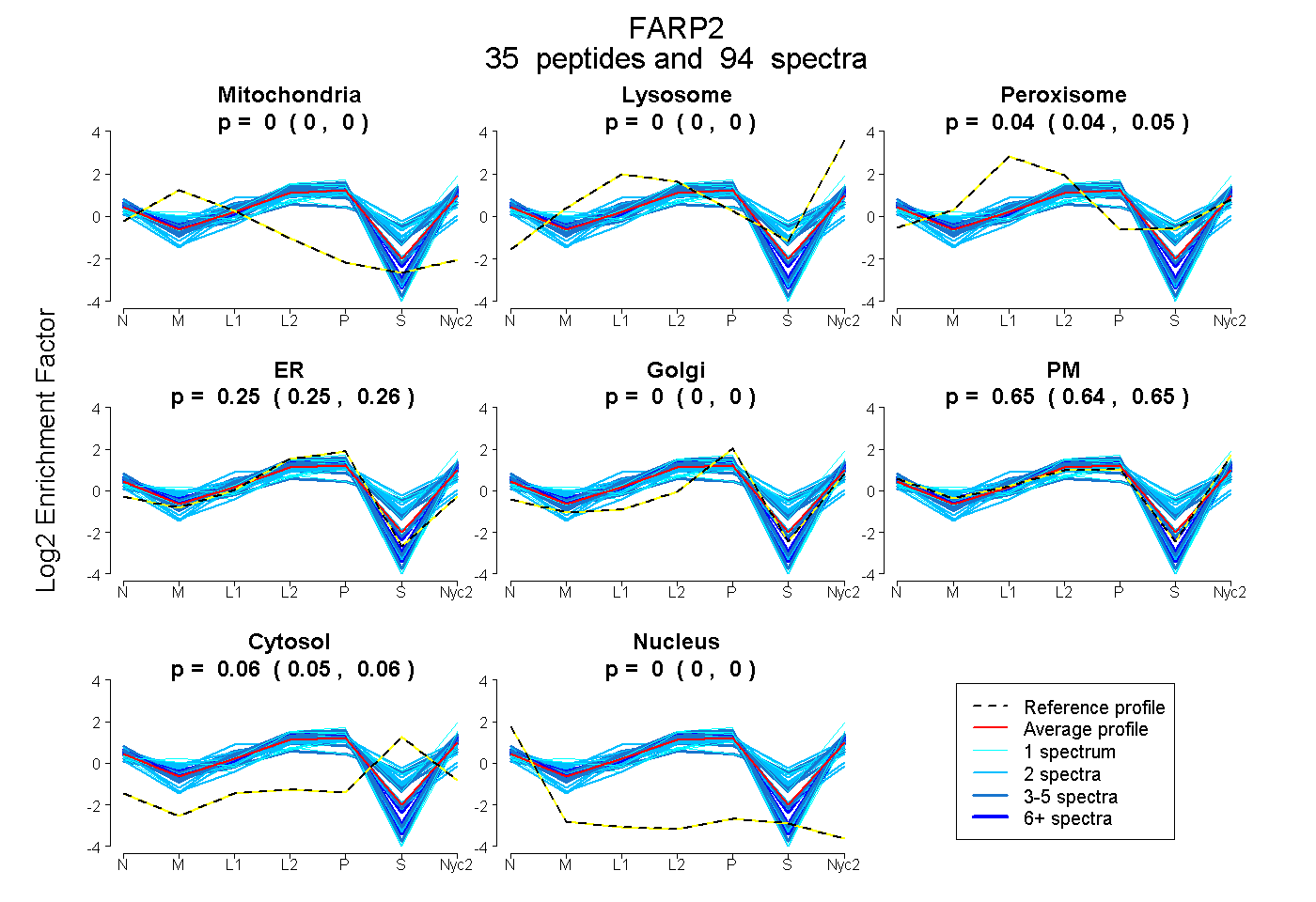
0.000 | 0.000
0.000 | 0.000
0.037 | 0.045
0.248 | 0.259
0.000 | 0.000
0.643 | 0.655
0.051 | 0.058
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
94 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.042 0.037 | 0.045 |
0.254 0.248 | 0.259 |
0.000 0.000 | 0.000 |
0.649 0.643 | 0.655 |
0.055 0.051 | 0.058 |
0.000 0.000 | 0.000 |
| 1 spectrum, WMQDLNAAIQAAK | 0.000 | 0.000 | 0.000 | 0.246 | 0.000 | 0.754 | 0.000 | 0.000 | ||
| 1 spectrum, LSDQPKPK | 0.000 | 0.000 | 0.119 | 0.111 | 0.113 | 0.419 | 0.239 | 0.000 | ||
| 1 spectrum, ANDYLPNQEQSLDK | 0.000 | 0.000 | 0.145 | 0.080 | 0.000 | 0.472 | 0.303 | 0.000 | ||
| 3 spectra, ADHSAAVENQLSGYLLR | 0.000 | 0.000 | 0.155 | 0.000 | 0.000 | 0.569 | 0.276 | 0.000 | ||
| 2 spectra, EFELQK | 0.036 | 0.000 | 0.000 | 0.319 | 0.000 | 0.645 | 0.000 | 0.000 | ||
| 2 spectra, ICVEHHTFFR | 0.070 | 0.000 | 0.196 | 0.474 | 0.000 | 0.222 | 0.000 | 0.038 | ||
| 9 spectra, TIVVAASTR | 0.000 | 0.000 | 0.000 | 0.265 | 0.000 | 0.735 | 0.000 | 0.000 | ||
| 2 spectra, GFLPLR | 0.000 | 0.000 | 0.000 | 0.302 | 0.000 | 0.698 | 0.000 | 0.000 | ||
| 1 spectrum, EACPSLCLDK | 0.000 | 0.000 | 0.082 | 0.185 | 0.038 | 0.418 | 0.278 | 0.000 | ||
| 1 spectrum, YLFALQLR | 0.000 | 0.186 | 0.000 | 0.105 | 0.000 | 0.660 | 0.049 | 0.000 | ||
| 2 spectra, QLVDYIR | 0.000 | 0.000 | 0.106 | 0.134 | 0.000 | 0.589 | 0.171 | 0.000 | ||
| 1 spectrum, MDNQEEQK | 0.000 | 0.035 | 0.032 | 0.268 | 0.000 | 0.665 | 0.000 | 0.000 | ||
| 1 spectrum, FFPPDPGQLQEEYTR | 0.124 | 0.000 | 0.105 | 0.168 | 0.242 | 0.361 | 0.000 | 0.000 | ||
| 4 spectra, EFTSYFQR | 0.000 | 0.026 | 0.120 | 0.000 | 0.092 | 0.675 | 0.087 | 0.000 | ||
| 13 spectra, AVFFSR | 0.000 | 0.000 | 0.037 | 0.247 | 0.006 | 0.708 | 0.000 | 0.001 | ||
| 1 spectrum, GFLHEVEQR | 0.000 | 0.000 | 0.000 | 0.253 | 0.000 | 0.742 | 0.000 | 0.005 | ||
| 3 spectra, ANTTMHVCWYR | 0.000 | 0.000 | 0.202 | 0.135 | 0.034 | 0.407 | 0.222 | 0.000 | ||
| 2 spectra, HTGQTPADSDFQVLEIAR | 0.000 | 0.035 | 0.125 | 0.103 | 0.000 | 0.546 | 0.191 | 0.000 | ||
| 3 spectra, SVTGASQFR | 0.000 | 0.000 | 0.019 | 0.326 | 0.000 | 0.637 | 0.018 | 0.000 | ||
| 4 spectra, TLPTSGTR | 0.000 | 0.000 | 0.000 | 0.296 | 0.000 | 0.704 | 0.000 | 0.000 | ||
| 2 spectra, INTFNWSK | 0.000 | 0.000 | 0.006 | 0.252 | 0.000 | 0.447 | 0.295 | 0.000 | ||
| 2 spectra, CDGQVLLTQVWK | 0.073 | 0.000 | 0.084 | 0.552 | 0.000 | 0.268 | 0.023 | 0.000 | ||
| 2 spectra, DSSSSPVDPQAPHIK | 0.000 | 0.000 | 0.163 | 0.093 | 0.206 | 0.391 | 0.148 | 0.000 | ||
| 2 spectra, ILDFHQR | 0.000 | 0.000 | 0.054 | 0.102 | 0.000 | 0.664 | 0.180 | 0.000 | ||
| 6 spectra, DLLEER | 0.000 | 0.000 | 0.000 | 0.353 | 0.000 | 0.647 | 0.000 | 0.000 | ||
| 2 spectra, LSLSPER | 0.000 | 0.000 | 0.114 | 0.186 | 0.000 | 0.540 | 0.159 | 0.000 | ||
| 2 spectra, DLVGVENLIAPGR | 0.000 | 0.000 | 0.000 | 0.220 | 0.000 | 0.780 | 0.000 | 0.000 | ||
| 2 spectra, INLAVSHMGVLVFQGTTK | 0.017 | 0.000 | 0.111 | 0.116 | 0.000 | 0.757 | 0.000 | 0.000 | ||
| 3 spectra, WMEVIK | 0.000 | 0.000 | 0.000 | 0.260 | 0.000 | 0.740 | 0.000 | 0.000 | ||
| 3 spectra, EADSIHK | 0.000 | 0.000 | 0.213 | 0.256 | 0.032 | 0.390 | 0.109 | 0.000 | ||
| 3 spectra, SHVYFFR | 0.000 | 0.000 | 0.120 | 0.109 | 0.000 | 0.674 | 0.097 | 0.000 | ||
| 4 spectra, IGDILLR | 0.000 | 0.000 | 0.000 | 0.189 | 0.000 | 0.776 | 0.000 | 0.035 | ||
| 1 spectrum, DLEVITVWFR | 0.000 | 0.000 | 0.000 | 0.334 | 0.000 | 0.666 | 0.000 | 0.000 | ||
| 1 spectrum, HDEVLTELEK | 0.000 | 0.000 | 0.000 | 0.472 | 0.000 | 0.528 | 0.000 | 0.000 | ||
| 2 spectra, QSISFTDGLR | 0.000 | 0.109 | 0.042 | 0.170 | 0.000 | 0.401 | 0.279 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
35 spectra |
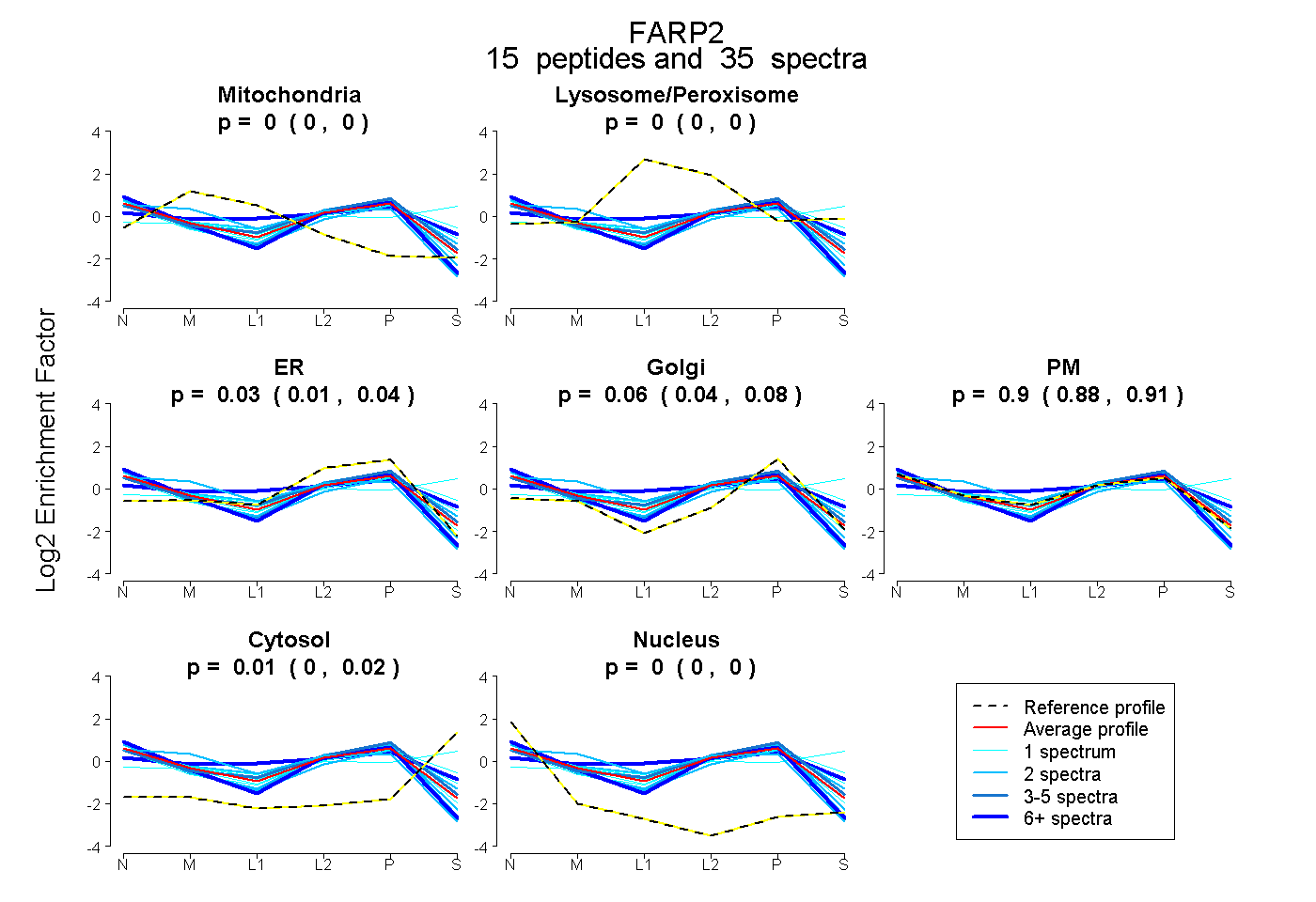 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.002 |
0.026 0.011 | 0.037 |
0.060 0.044 | 0.075 |
0.900 0.883 | 0.913 |
0.015 0.004 | 0.023 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
99 spectra |
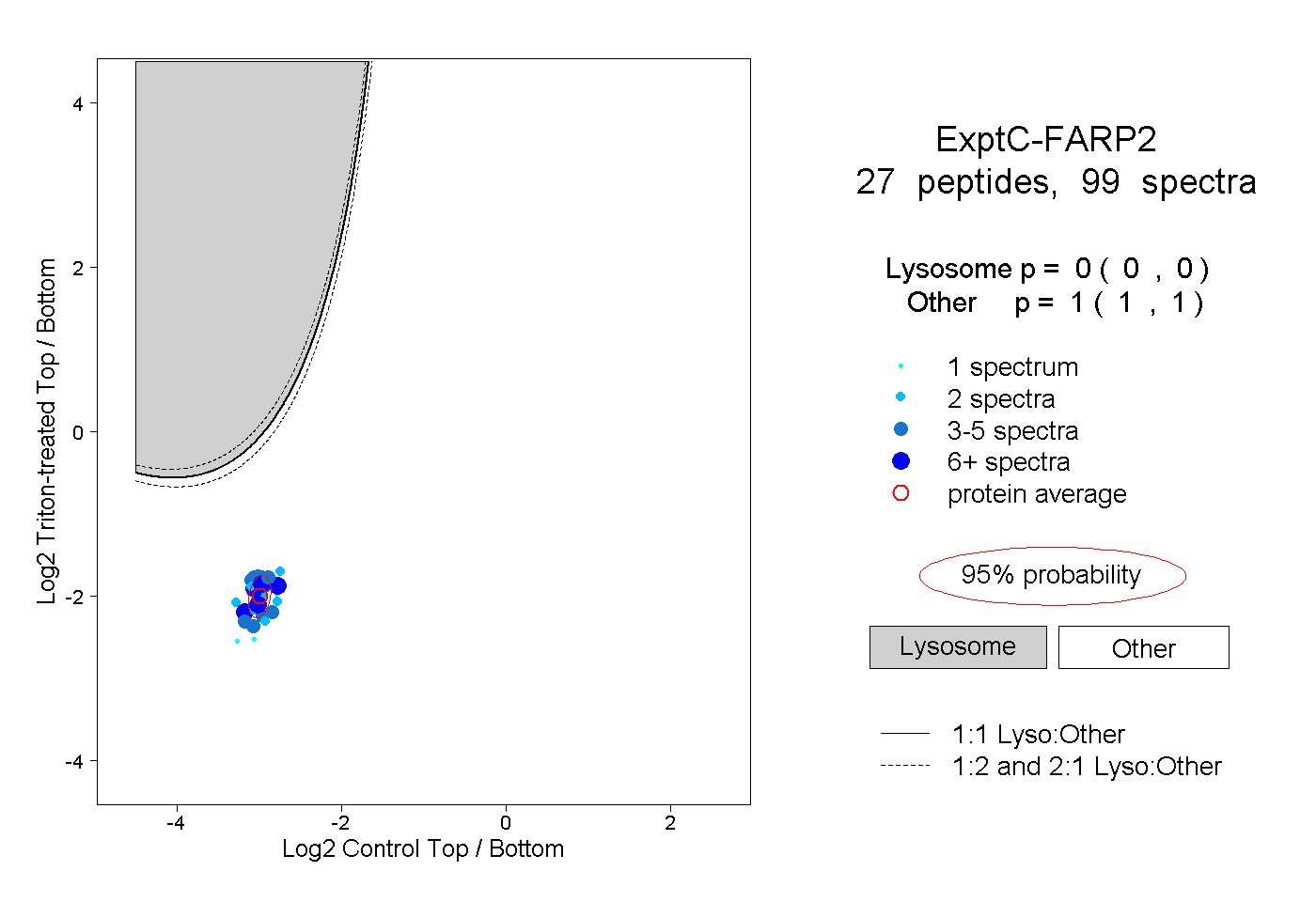 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
12 spectra |
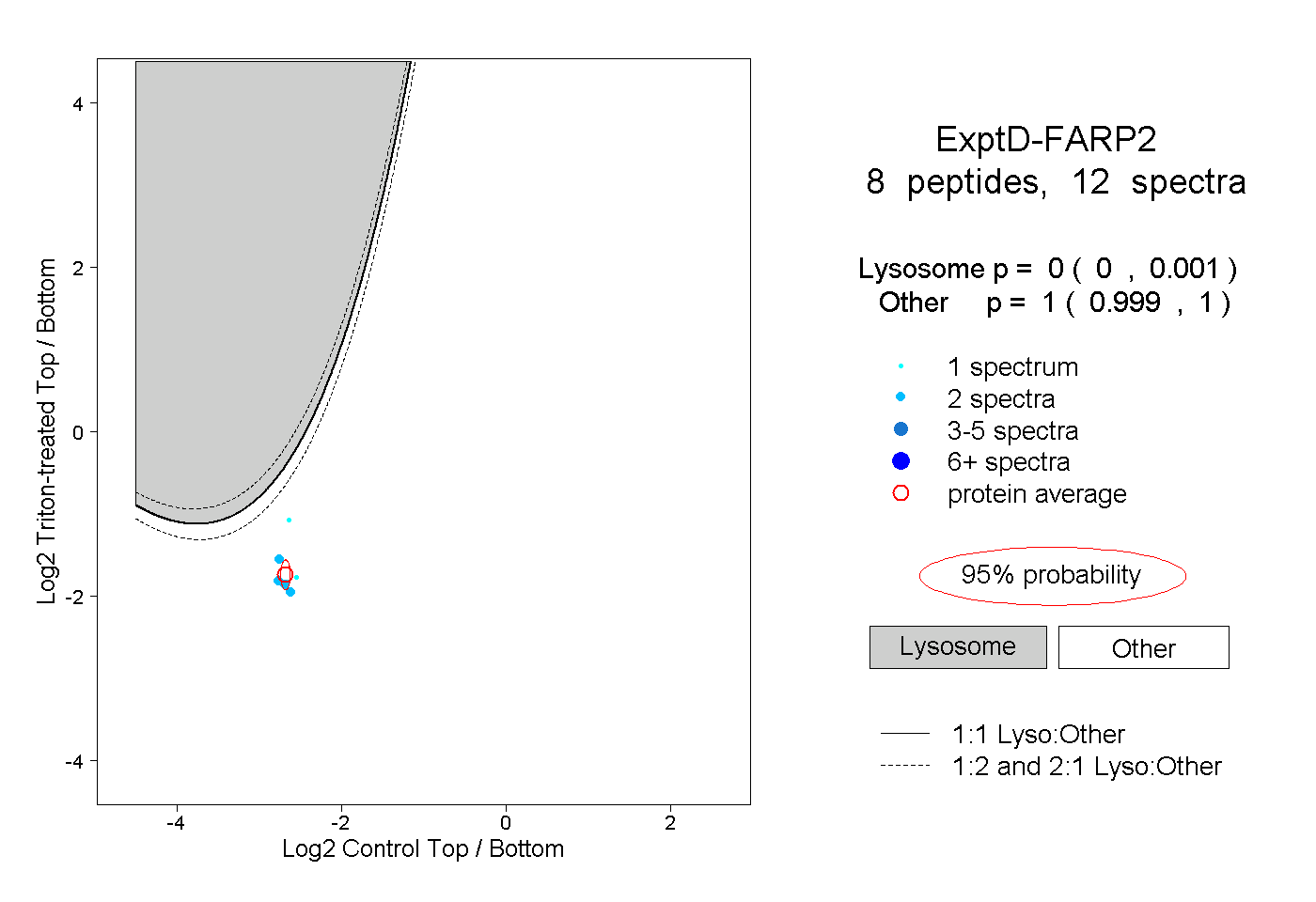 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |