peptides
spectra
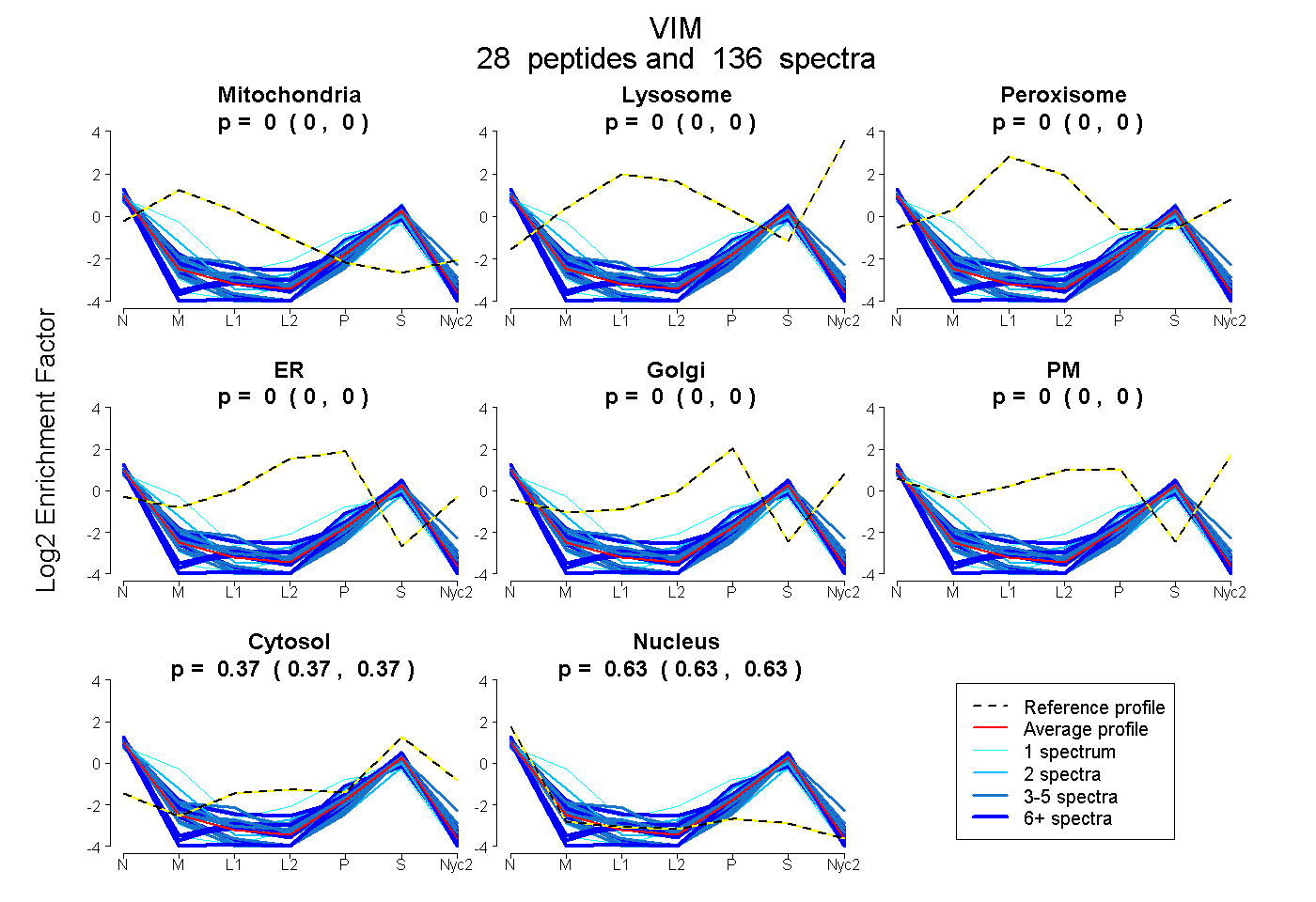
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.372 | 0.375
0.625 | 0.628
peptides
spectra
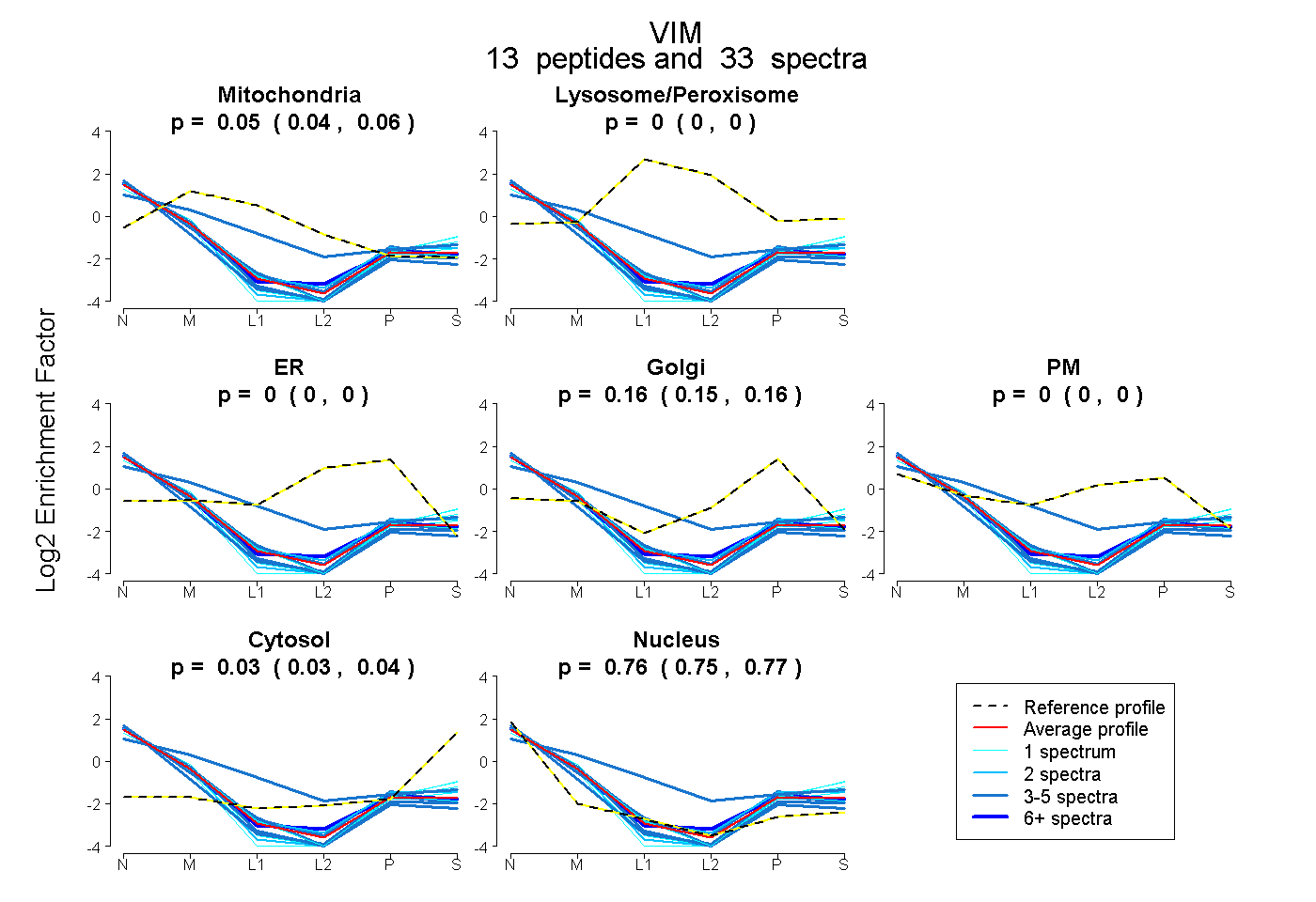
0.037 | 0.064
0.000 | 0.000
0.000 | 0.000
0.145 | 0.163
0.000 | 0.000
0.026 | 0.040
0.750 | 0.766
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
136 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.373 0.372 | 0.375 |
0.627 0.625 | 0.628 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
33 spectra |
 |
0.052 0.037 | 0.064 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.155 0.145 | 0.163 |
0.000 0.000 | 0.000 |
0.034 0.026 | 0.040 |
0.759 0.750 | 0.766 |
| 1 spectrum, MFGGSGTSSRPSSNR | 0.000 | 0.000 | 0.000 | 0.082 | 0.000 | 0.135 | 0.783 | |||
| 1 spectrum, VELQELNDR | 0.063 | 0.000 | 0.000 | 0.141 | 0.000 | 0.000 | 0.796 | |||
| 5 spectra, TYSLGSALRPSTSR | 0.097 | 0.000 | 0.000 | 0.044 | 0.000 | 0.000 | 0.859 | |||
| 1 spectrum, GTNESLER | 0.000 | 0.000 | 0.000 | 0.080 | 0.000 | 0.182 | 0.739 | |||
| 1 spectrum, EYQDLLNVK | 0.026 | 0.000 | 0.000 | 0.092 | 0.000 | 0.086 | 0.797 | |||
| 2 spectra, NLQEAEEWYK | 0.038 | 0.000 | 0.000 | 0.197 | 0.000 | 0.065 | 0.700 | |||
| 3 spectra, QDVDNASLAR | 0.023 | 0.000 | 0.000 | 0.118 | 0.000 | 0.010 | 0.848 | |||
| 2 spectra, EEAESTLQSFR | 0.000 | 0.000 | 0.000 | 0.139 | 0.000 | 0.028 | 0.832 | |||
| 3 spectra, SYVTTSTR | 0.000 | 0.000 | 0.000 | 0.149 | 0.000 | 0.000 | 0.851 | |||
| 4 spectra, FADLSEAANR | 0.063 | 0.000 | 0.000 | 0.207 | 0.000 | 0.000 | 0.730 | |||
| 6 spectra, ILLAELEQLK | 0.044 | 0.000 | 0.000 | 0.202 | 0.000 | 0.022 | 0.732 | |||
| 3 spectra, QVQSLTCEVDALK | 0.460 | 0.008 | 0.000 | 0.000 | 0.160 | 0.036 | 0.336 | |||
| 1 spectrum, DNLAEDIMR | 0.000 | 0.000 | 0.000 | 0.084 | 0.000 | 0.207 | 0.709 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
31 spectra |
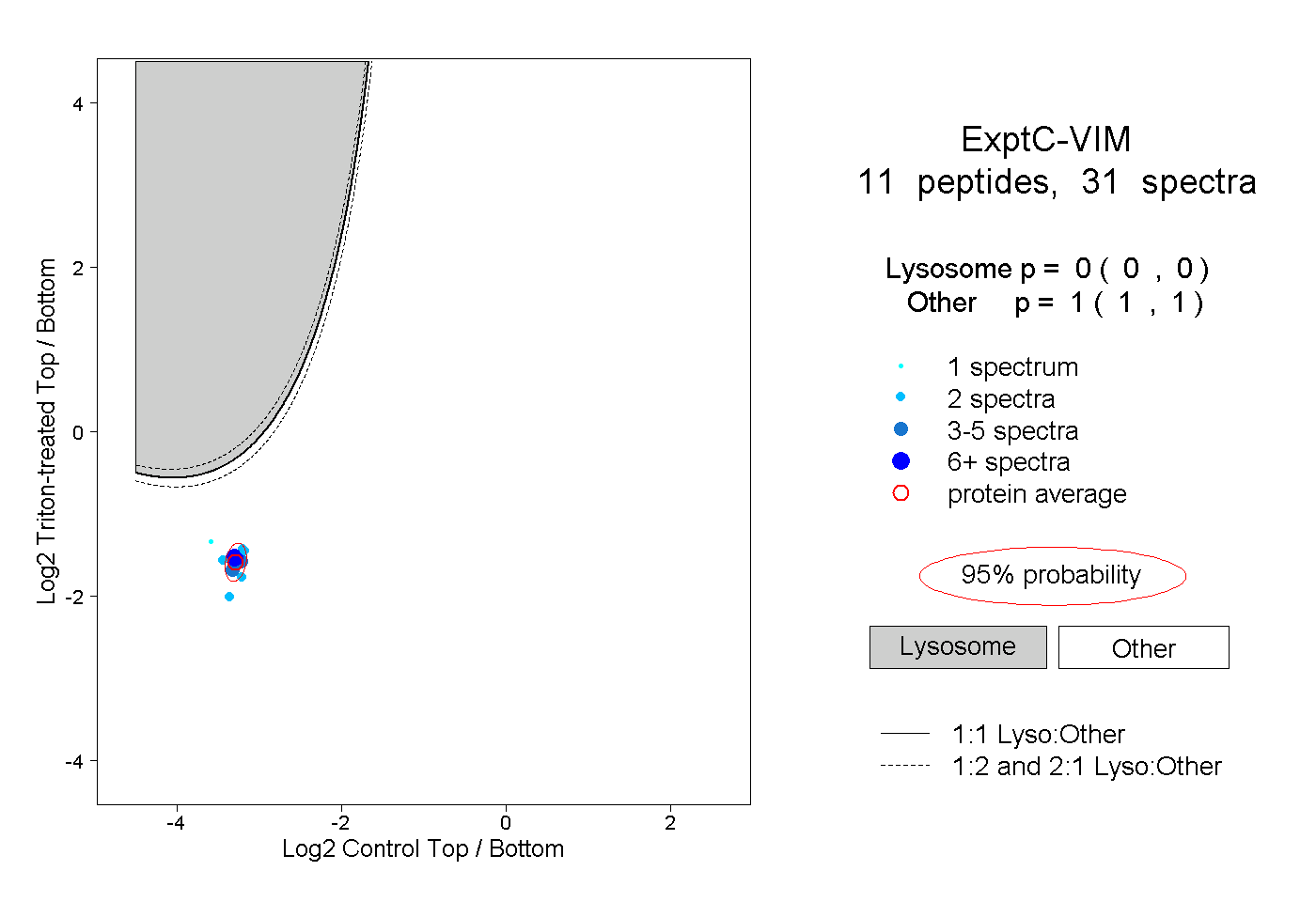 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
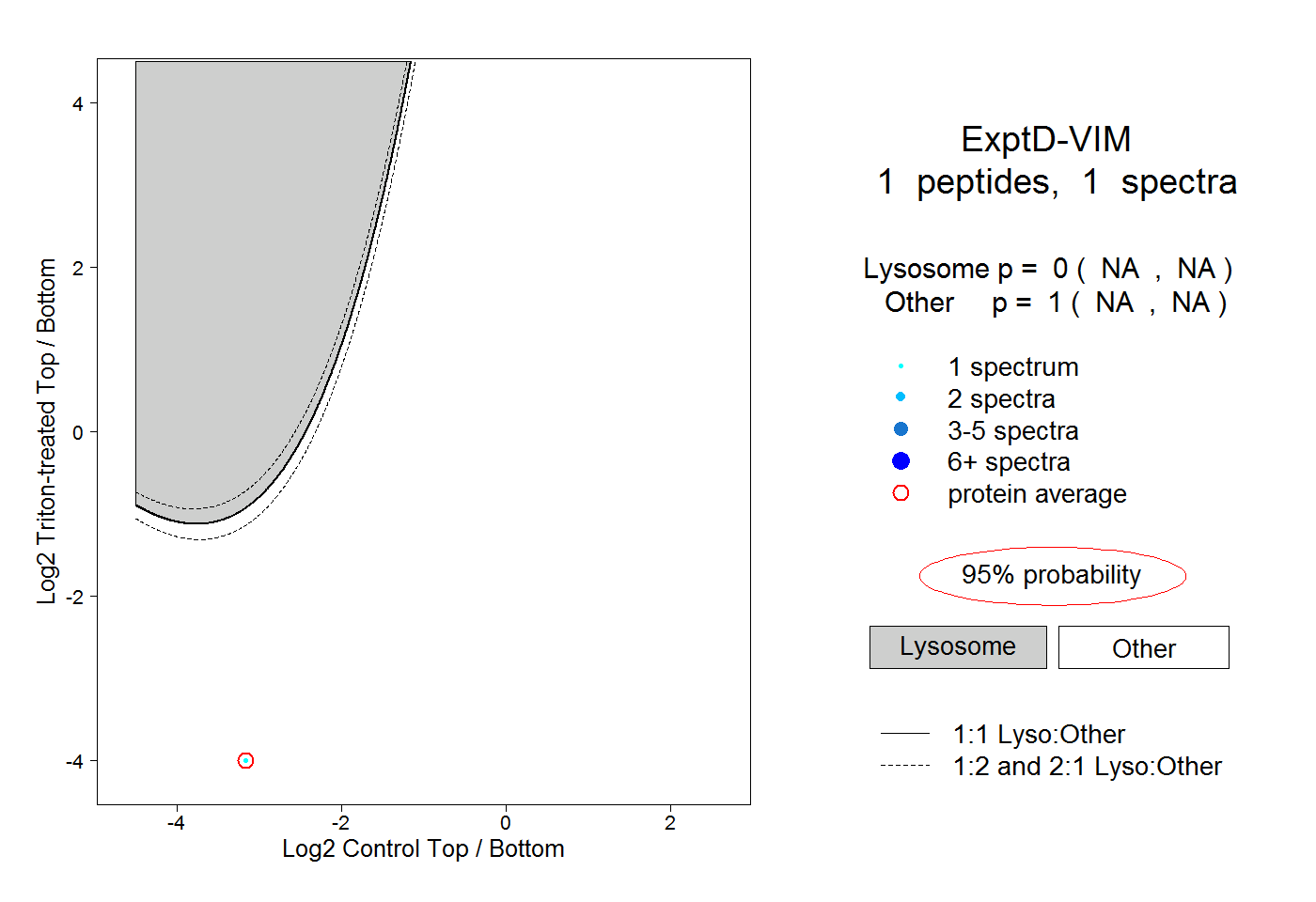 |
0.000 NA | NA |
1.000 NA | NA |