peptides
spectra
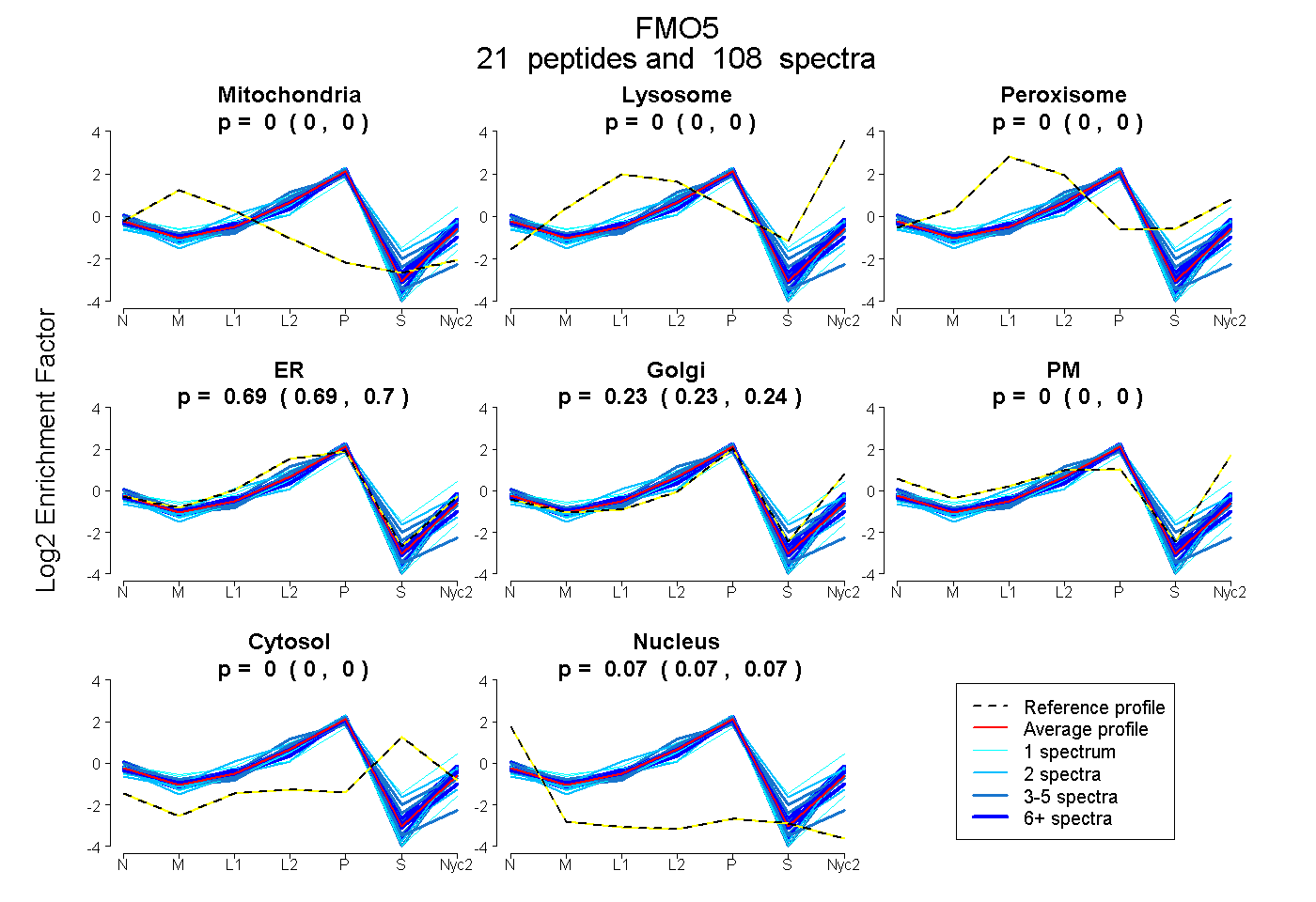
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.686 | 0.699
0.226 | 0.241
0.000 | 0.000
0.000 | 0.000
0.071 | 0.075
peptides
spectra
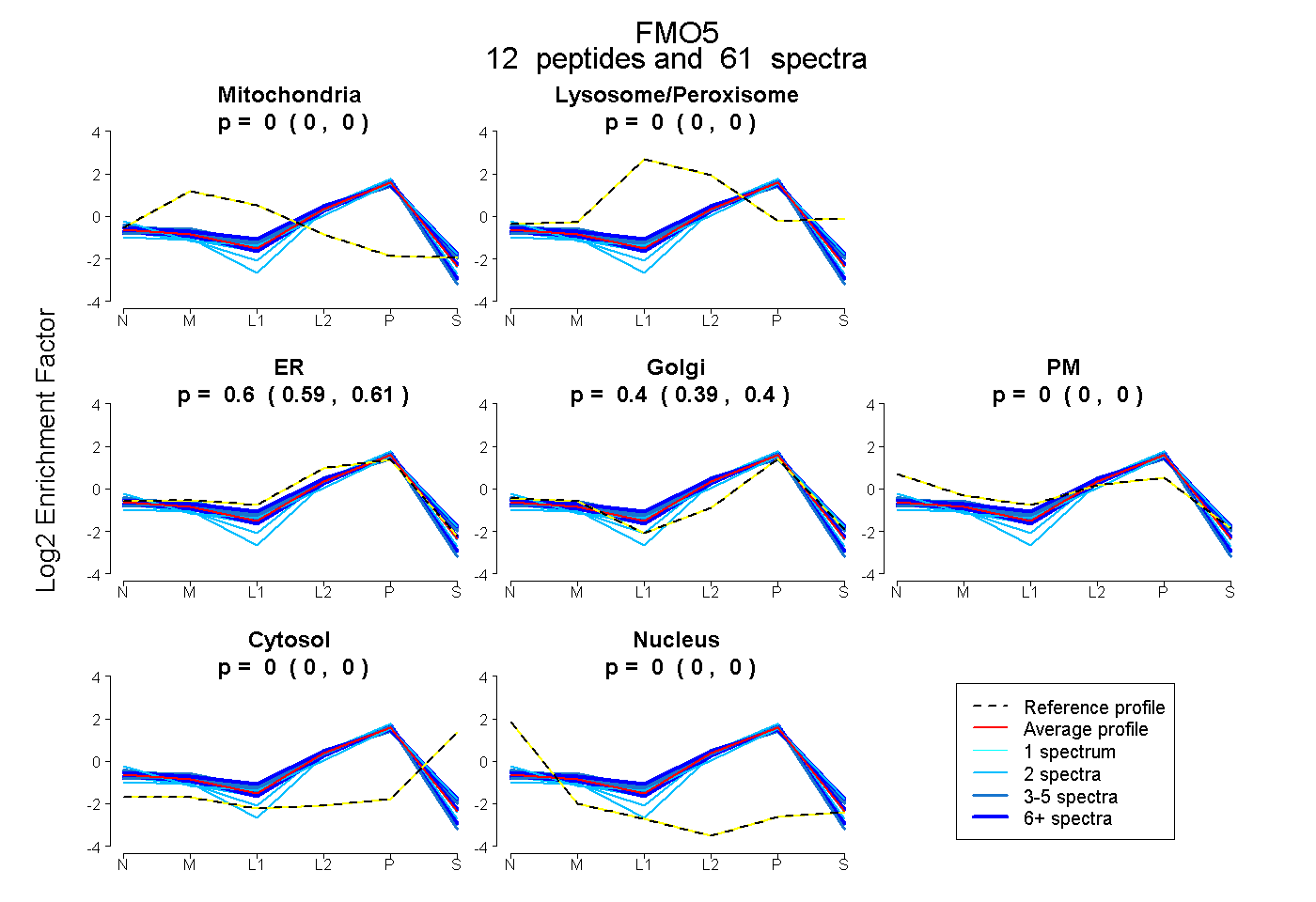
0.000 | 0.000
0.000 | 0.000
0.594 | 0.609
0.390 | 0.405
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
108 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.693 0.686 | 0.699 |
0.235 0.226 | 0.241 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.073 0.071 | 0.075 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
61 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.602 0.594 | 0.609 |
0.398 0.390 | 0.405 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 2 spectra, YVDSQR | 0.000 | 0.024 | 0.451 | 0.503 | 0.000 | 0.011 | 0.011 | |||
| 3 spectra, TILTTEDR | 0.000 | 0.000 | 0.694 | 0.306 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, IISGLVK | 0.000 | 0.000 | 0.599 | 0.401 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, IAVIGSGASGLTCIK | 0.000 | 0.000 | 0.681 | 0.307 | 0.000 | 0.012 | 0.000 | |||
| 10 spectra, GAWILNR | 0.000 | 0.000 | 0.614 | 0.386 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, WATQVFK | 0.000 | 0.036 | 0.651 | 0.297 | 0.000 | 0.017 | 0.000 | |||
| 5 spectra, EFGLLK | 0.000 | 0.000 | 0.787 | 0.193 | 0.000 | 0.000 | 0.020 | |||
| 12 spectra, QVFLSTR | 0.000 | 0.000 | 0.531 | 0.469 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, HGYPIDILLSSR | 0.000 | 0.000 | 0.597 | 0.363 | 0.000 | 0.040 | 0.000 | |||
| 2 spectra, DSSGTSLVTVR | 0.000 | 0.000 | 0.316 | 0.684 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, KPLMTR | 0.000 | 0.000 | 0.505 | 0.495 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, ITNYLSK | 0.000 | 0.000 | 0.674 | 0.301 | 0.000 | 0.025 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
213 spectra |
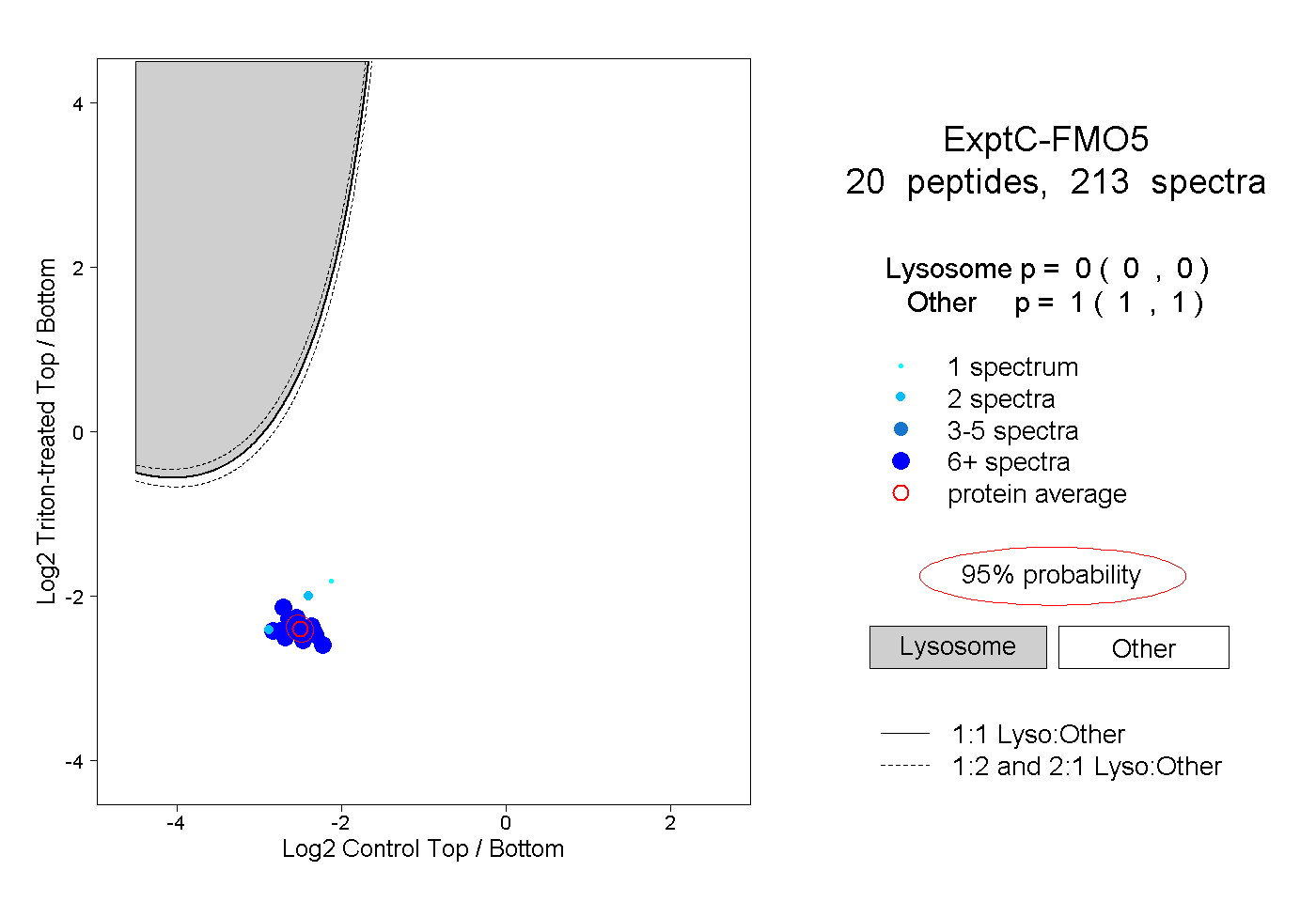 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
31 spectra |
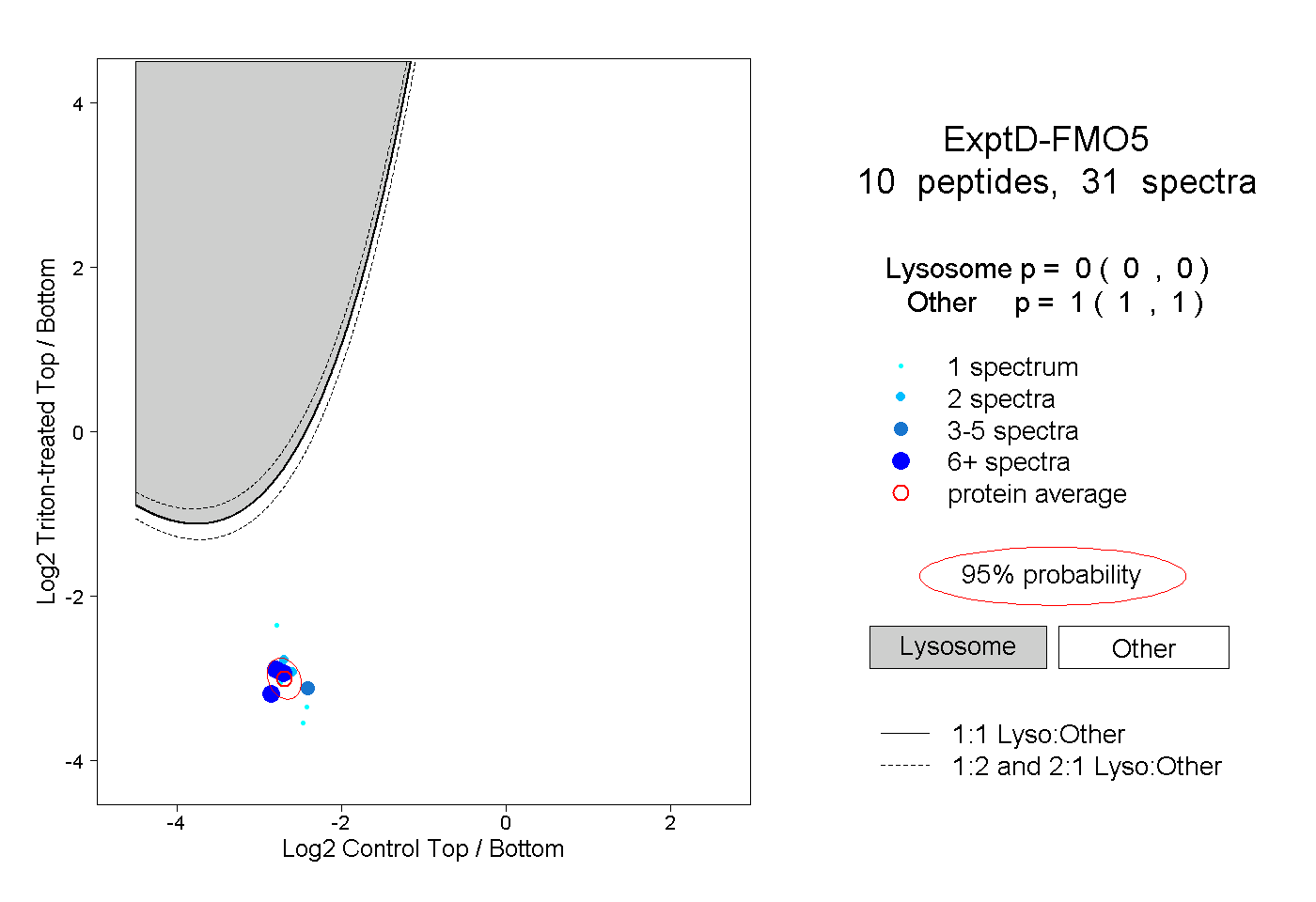 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |